MARKAH MOLEKULER DALAM IDENTIFIKASI DAN ANALISIS
KEKERABATAN TUMBUHAN SERTA IMPLIKASINYA
BAGI MATA KULIAH GENETIKA
(Telaah keilmuan genetika molekuler tumbuhan)
SUPARMAN 1
1
Dosen Pada Program Studi Pendidikan Biologi FKIP Universitas Khairun
Email : [email protected]
ABSTRAK
Sifat morfologi tanaman meliputi batang, variasi bunga dan bagian-bagian bunga serta variasi bentuk daun telah lama menjadi acuan identifikasi, pemetaan kekerabatan dan taksonomi tanaman, namun sifat morfologi dinilai terbatas karena langsung dipengaruhi lingkungan. Penanda lain yang lebih stabil berupa penanda biokimia seperti isozyma. Penanda ini lebih baik, kurang dipengaruhi kondisi pertumbuhan karakter kuantitatif dan lebih cocok untuk identifikasi varietas, namun terkadang penanda ini juga tidak menunjukan perbedaan yang nyata antar genotip yang diuji. Keterbatasan tersebut, memunculkan markah molekuler, yakni penanda yang ditentukan langsung oleh materi genetik berupa DNA. Sekuen DNA memberikan banyak character state karena perbedaan laju perubahan basa-basa nukleotida di dalam lokus yang berbeda dan lebih akurat serta menghasilkan kekerabatan yang lebih alami. Karakter markah molekuler berupa sekuen DNA pada tumbuhan dapat diambil dari genom nDNA, cpDNA, dan mtDNA. Sekuen DNA yang banyak digunakan pada tumbuhan ialah : mikrosatelit, ITS, gen rbcL, gapC, ndhF, matK, dan psaA. Gen rbcL secara khusus telah direkomendasikan sebagai DNA pada tumbuhan. Perkembangan markah molekuler memberikan implikasi berupa penambahan materi pada kuliah genetika yakni materi dasar bioinformatika dan filogenetik molekuler sebagai tool dalam analisis data molekuler. Lebih jauh lagi, bioinformatika dan filogenetika molekuler ini dapat direkomendasikan menjadi matakuliah pilihan.
Kata kunci : markah molekuler, sekuen DNA, kekerabatan tumbuhan, DNA barkode
Karakter morfologi yang berupa bentuk
bunga, daun, batang, biji dan karakter fisiologi
yang berupa kandungan fitokimia merupakan
landasan utama identifikasi dan klasifikasi
tumbuhan. Sistem taksonomi yang ada
sekarang ini berdasarkan kemiripan morfologi
dan fisiologi tersebut. Salah satu panduan
pengelompokan tumbuhan adalah Cronquist
(1981) dalam Suparman (2011) yang
mengklasifikasikan ribuan tumbuhan dalam
sistem terintegrasi berdasarkan karakter
morfologi. Backer dan Van Den Brink (1965)
juga membukukan ratusan tamanan yang ada di
Pengelompokan berdasarkan morfologi
pada tumbuhan masih memiliki banyak
keterbatasan, contoh nyata pada klasifikasi
Genus Mangifera terbaru yang dipublikasi oleh
Kostermans Bompard mengindikasikan
keraguan pengelompokan (Yonemori, dkk.
2002). Hal ini dapat dianalisis pada kelompok
uncertain position untuk 11 spesies dari
Mangifera yang telah diidentifikasi.
Keterbatasan markah morfologi juga dapat
terlihat pada pengelompokan tanaman
Philantus niruri (Hidayat, dkk. 2008) yang
karakter warna tumbuhannya sangat
dipengaruhi oleh lingkungan sekitar.
Perkembangan biologi molekuler mulai
berperan penting dalam perkembangan
berbagai cabang Biologi, begitu juga peranan
biologi molekuler dalam identifikasi dan
pengelompokan kekerabatan tumbuhan. Semua
proses kehidupan seperti perkembangan,
fisiologi, dan reproduksi semua organisme
dapat dilihat dengan pendekatan molekuler.
Studi evolusi saat ini dipengaruhi oleh
perkembangan Biologi molekuler, dan
sebaliknya pendekatan evolusi juga digunakan
untuk memahami dan mengembangkan Biologi
molekuler (Nei dan Kumar, 2000).
Perkembangan kedua ilmu tersebut
berpengaruh pada pendekatan filogenetik,
sehingga kekerabatan antar organisme yang
awalnya hanya berdasarkan data morfologi,
anatomi, fisiologi dan paleontologi tetapi
sekarang berkembang teknik molekuler dalam
rekonstruksi filogenetik. Hal ini juga untuk
menjembatani adanya organisme kompleks
yang sulit dibedakan hanya dengan data
morfologi. Data molekuler tersebut seperti peta
restriksi, hibridisasi DNA, sekuen protein dan
sekuen DNA. Peneliti cenderung menggunakan
sekuen DNA karena dianggap lebih mudah
dibanding dengan informasi molekuler yang
lain (Li dan Graur, 1991).
Latar belakang tersebut memicu penulis
untuk memaparkan penggunaan markah
molekuler berupa sekuen DNA yang spesifik
dalam menganalisis kekerabatan dan
identifikasi tumbuhan sebagai karakter
alternatif yang menyediakan data lebih akurat
serta implikasi dari perkembangan ilmu
genetika molekuler ini terhadap matakuliah
genetika.
MARKAH MOLEKULER SEBAGAI SUATU PENANDA
Markah molekuler merupakan penanda
yang berbasiskan asam amino, protein atau
sekuen DNA sebagai bahan utama. Penggunaan
sekuen DNA sebagai penanda baik dalam
identifikasi maupun taksonomi telah lama
digunakan karena lebih menunjukan sifat yang
alami. Pada dasarnya prinsip penggunaan
morfologi, yakni untuk mengenali suatu
individu atau spesies. Pada suatu individu yang
lengkap, penggunaan ciri dan tanda morfologi
dapat langsung membantu ahli taksonomi.
Keterbatasan sifat morfologi mulai terlihat pada
saat keterbatasan sampel morfologi, misalnya
tidak ditemukan secara lengkap
karakter-karakter morfologi yang merupakan kunci
identifikasi bagi suatu jenis. Karakter
morfologi yang ditemukan secara lengkap
namun beda usia juga akan mengalami masalah
dalam identifikasi, hal ini disebabkan ada
beberapa tanaman yang menghasilkan senyawa
tertentu misalnya minyak atsiri pada saat
dewasa sehingga pada saat masih muda tidak
ditemukan.
Karakter morfologi berupa warna cendrung
berbeda pada perlakuan lingkungan yang
berbeda seperti pada kasus tanaman
Phyllanthus niruri/meniran (Hidayat dkk,
2008). Pada sistem klasifikasi sebelumnya,
meniran digolongkan menjadi tiga kelompok
berdasarkan karakter morfologi warna batang
dan cabang, yaitu meniran merah, meniran
kuning, dan meniran hijau, tetapi karakter
warna batang ini cenderung mengecoh karena
sangat dipengaruhi oleh lingkungan.
Penggunaan sifat morfologi dalam
filogenetik dan taksonomi sering mengecoh
karena bersifat tentatif. Objek-objek yang
sedang dianalisis harus berada dalam kondisi
sama, berasal dari tempat yang berkondisi sama
dan usia yang relatif sama. Objek penelitian
dari spesies yang sama menghasilkan
kesimpulan berbeda jika berasal dari usia yang
berbeda, atau berasal dari tempat dengan
kondisi lingkungan yang berbeda, atau
pengambilan sampel beda usia. Analisis dari
awetan kering juga sangat sulit untuk
identifikasi, karena tidak cukup hanya
membandingkan satu bagian saja, misalnya
daun atau batang saja, tetapi dibutuhkan semua
bagian tumbuhan. Penggunaan markah
molekuler ternyata memudahkan dalam
pengambilan sampel, karena dapat
menggunakan sampel dari semua bagian tubuh
tumbuhan dengan jumlah kuantitaif yang tidak
banyak, hal ini karena DNA pada tubuh
tumbuhan terdapat pada semua bagian
manapun dengan pola yang sama.
Pengaruh lingkungan terhadap perubahan
morfologi dan fisiologi yang tidak permanen
memperlihatkan bahwa karakter luar yang
dihasilkan oleh tumbuhan karena respon
lingkungan tidak stabil. Hal ini mengecohkan
identifkasi dan analisis kekerabatan tumbuhan
bahkan pada makhkuk hidup secara umum.
Markah molekuler dinilai lebih stabil sebagai
penanda dan identifikasi serta dalam analisis
taksonomi, Li dan Graur (1991),
mengungkapkan bahwa DNA menyediakan
morfologi dan fisiologi, serta lebih cepat,
praktis, dan efisien dalam pengerjaan.
Sekuen DNA memberikan banyak
character state karena perbedaan laju
perubahan basa-basa nukleotida di dalam lokus
yang berbeda dan lebih akurat serta
menghasilkan kekerabatan yang lebih alami.
Sistematika molekuler dengan menggunakan
markah molekuler pada tanaman telah
digunakan secara luas sebagaimana pada
organisme lain dalam determinasi hubungan
filogenetik (Asahina, dkk. 2010). Pada
sistematika Angiospermae pendekatan
filogenetik dengan karakter molekuler telah
digunakan dan efektif dalam mengelompokan
takson yang belum terselesaikan dengan
pendekatan fenetik (Reddy, 2009).
Penggunaan sekuen DNA juga dapat
mengatasi kelemahan dari data morfologi yang
diketahui memiliki keterbatasan karakter dan
cenderung dipengaruhi lingkungan. Kelebihan
penggunaan markah molekuler, pertama sekuen
DNA memberikan data yang lebih akurat
terhadap karakter-karakter yang ada (Hidayat
2008), kedua sekuen DNA menyediakan
banyak character state karena perbedaan laju
perubahan basa-basa nukleotida di dalam lokus
yang berbeda adalah besar, ketiga sekuen DNA
telah terbukti menghasilkan sebuah hubungan
kekerabatan yang lebih alami. Karakter dari
markah molekuler berupa sekuen DNA pada
tumbuhan dapat diambil dari Inti, kloroplas,
dan mitokondria.
JENIS-JENIS MARKAH MOLEKULR
Banyaknya gen pada genom makhluk
hidup menyebabkan kesulitan jika harus
dianalisis secara keseluruhan untuk identifikasi
dan analisis kekerabatan dari satu atau lebih
tingkat takson makhkuk hidup. Langkah yang
sedang dilakukan oleh para ahli molekuler ialah
mencari suatu gen yang dapat mencirikan suatu
jenis sekaligus membedakan antara satu jenis
dengan jenis lainnya. Gen tersebut akan
berfungsi sebagai suatu barkode sehingga lebih
praktis dan efisien dalam identifikasi jenis
tumbuhan dan analisis kekerabatan dari suatu
genus.
Gen yang dijadikan markah molekuler
pada makhkuk hidup harus gen yang lestari
moderat “moderate conserved” dan memiliki
variasi yang cukup pada tiap spesies, hal ini
akan sangat bermanfaat dalam rekonstruksi
filogenetik dan analisis pada level populasi.
Perbedaan laju mutasi pada kingdom hewan,
tumbuhan, protista dan jamur menyebabkan
seleksi pengambilan gen penanda yang
berbeda. Masing-masing gen penanda yang
dapat diajadikan rujukan dalam identifikasi dan
taksonomi pada tiap kingdom ditunjukan pada
Tabel 1. Markah molekuler pada level spesies pada masing-masing kingdom (Hajibabaei, 2007)
Secara umum untuk kelompok hewan telah
direkomendasikan COI, 16s-RNA, dan Cytb
dalam identifikasi dan penggunaan dalam
markah molekuler. Semua gen tersebut
merupakan bagian dari genom mitokondria.
COI, merupakan gen cytochrome c oxidase
yang terdapat pada genom mitokondria, gen ini
merupakan bagian dari subunit kompleks
sitokrom oksidase yang merupakan bagian dari
rantai transpor elektron. Beberapa penelitian
menunjukan bahwa sekuen dari COI telah
efektif dalam identifikasi, secara khusus dalam
kelompok hewan lebih dari 95% berhasil
dipisahkan dalam level sepesies pada hewan
dengan menggunakan sekuen COI
(Ratnasingham dan Hebert, 2007).
Sekuen nonkoding yang banyak digunakan
sebagai markah molekuler ialah ITS, “Internal Transcribed Spacer” merupakan suatu daerah non fungsional RNA yang ada antara struktur
rRNA pada prekursor transcript umum. ITS
berukuran kecil kurang lebih 700 pasang basa
dan memiliki salinan yang banyak pada genom
inti. Pada kelompok jamur, ITS
memperlihatkan hasil yang lebih efektif
dibandingkan dengan sekuen lain dan
dierekomendasikan sebagai DNA barkode
universal dalam semua kingdom fungi pada
consortium barcode of life (CBOL). Sementara
kelompok protista dapat juga menggunakan
sekuen ITS.
Pada kelompok tumbuhan, beberapa gen
telah banyak digunakan untuk analisis
filogenetik dan identifikasi tumbuhan
diantaranya mikrosatelit, ITS, gen rbcL, gapC,
ndhF, matK, dan psaA (Suparman, 2011).
Mikrosatelit adalah sekuen DNA sederhana
terdiri dari dua sampai enam pasang basa
berulang yang disebut pula dengan Simple
Sequence Repeat (SSRs). Penggunaan
mikrosatelit banyak pada penelitian eukariotik
karena terdistribusi merata pada genom
eukariotik. Markah ini bersifat kodominan dan
dapat mendeteksi keragaman alel pada level
tinggi.
Gen/sekuen Lokasi genomik Jumlah sekuen genomik
Hewan Tumbuhan Protista Jamur
CO1-barkod Mitokondria 19577 520 1931 410
16s-RNA Mitokondria 41381 221 2059 285
Cytb Mitokondria 88324 165 1920 1084
ITS1-rDNA Inti sel 12175 57693 68839 56675
ITS2-rDNA Inti sel 13923 58065 67332 56349
18S-Rdna Inti sel 21063 17121 32290 33327
Gambar 1. Ilustrasi posisi, arah dan panjang basa gen rbcL pada genom kloroplas, berdasarkan Judd, dkk. (2002) ; Yoshinaga, dkk. (1996).
Salah satu markah molekuler yang banyak
digunakan dalam filogenetik tumbuhan yakni
rbcL. Gen rbcL tanaman merupakan pengkode
sub unit besar enzim riboluse-1,5-bisphosphate
carboxylse (RubisCo) yang berada di genom
kloroplas (Judd dkk, 2001) dan merupakan gen
yang universal pada hampir semua tanaman,
sehingga penggunaanya akan efektif mengenali
keragaman dalam semua tanaman. Penggunaan
markah gen rbcL pada analisis filogenetik
diantara spesies dalam satu genus telah
dilakukan, seperti pada genus Zygophyllum dari
famili Zygophyllaceae (Bellstedt dkk, 2008)
dan genus Caragana dari famili Leguminoseae.
Gen rbcL merupakan gen pengkode salah
satu enzim fotosintesis yakni large subunit
Ribulosa-1,5-bisphosphate carboxylase
(RuBisCo) atau RUBP karboksilase (Judd, dkk.
2002; Lane, 1984) yang berperan pada tahap
awal siklus Calvin dari fotosintesis, selain
fungsi utamanya dalam menghasilkan
RuBisCo, rbcL telah umum digunakan untuk
menyediakan sekuen data dalam analisis
filogenetik tumbuhan (Chase, dkk. 1993; Judd,
dkk. 2002). Penggunaan gen rbcL dalam
filogenetik tumbuhan karena gen ini dimiliki
oleh semua spesies tumbuhan kecuali
tumbuhan parasit, bahkan ditemukan pula pada
sejenis flagelata (La Du, dkk,.2002), jika dilihat
dari protein yang dihasilkan maka gen rbcL
mudah dideteksi. Hal ini karena RuBisCo yang
dihasilkan oleh gen rbcL sangat melimpah
dalam sel tumbuhan yakni sampai 15% dari
total protein tumbuhan (Lane, 1984), dan
melebihi 50% dari total protein dalam kloroplas
(Alberts, dkk. 2002). Gen yang terdapat pada
genom kloroplas tumbuhan ini memiliki
panjang basa nukleotida sekitar 1428 base pair
(2006; Judd, dkk. 2002).
Efektivitas penggunaan gen rcbL dalam
filogenetik pada tumbuhan bunga telah
memperlihatkan hubungan kekerabatan evolusi
diantara kelompok organisme (taxon) yang
diteliti, selain itu gen rbcL juga merupakan gen
yang sangat lestari pada hampir semua
2005). Consortium Barcode Of Life (CBOL)
pada kelompok kerja bidang tanaman juga
merekomendasikan penggunaan rbcL sebagai
barcode salah satu penanda pada identifikasi
tumbuhan secara umum yang dikombinasikan
bersama dengan gen matK (CBOL, 2009), hal
ini berdasarkan eksistensi, efektifitas dan
kelestarian laju mutasi kedua gen tersebut pada
hampir semua spesies tumbuhan. DNA barcode
ini, pada bidang sistematika dapat digunakan
dalam mengidentifikasi spesies tumbuhan, juga
berguna dalam analisis filogentik dan analisis
populasi (Hajibabaei dkk, 2007), rekomendasi
ini memperkuat alasan penggunaan rbcL dalam
analisis filogenetik dan kekerabatan tanaman
dalam satu genus.
Penggunaan gen rbcL pada penelitian
filogenetik menunjukan pola filogenetik yang
tidak bertentangan dengan sistematika
tumbuhan berdasarkan karakter morfologi
dalam sistem Cronquist, misalnya analisis pada
Caryophyllidae menghasilkan pohon yang yang
bersifat monofiletik, begitu juga Apocynaceae,
Apiaceae, dan Brassicaseae (Judd, 2002).
Kelajuan mutasi rbcL yang lebih lambat dari
gen-gen kloroplas lainnya, memungkinkan
rbcL masih membawa informasi gen nenek
moyang lebih. Barraclough (1996)
mengemukakan terdapat korelasi positif antara
kelajuan evolusi sequen gen rbcL dengan
diversifikasi spesies pada Angiospermae.
Lambatnya laju mutasi pada gen rbcL ini
kemungkinan berkaitan dengan fungsinya yang
sangat esensial bagi tumbuhan sebagai
pengkode enzim rubisko. Pada beberapa
spesies tumbuhan, perkiraan lokasi gen rbcl
dalam genom dapat diketahui degnan melihat
peta genom kloroplas yang telah ada, misalnya
pada tanaman Jagung, Kentang dan Tomat,
serta 87 spesies lainnya yang telah
diidentifikasi (Ravi, dkk. 2008), berdasarkan
peta kloroplas tersebut dapat digambarkan
posisi gen rbcL dari gen-gen lainnya pada
kloroplas.
BIOINFORMATIKA DAN FILOGENETIK MOLEKULER
Penggunaan markah molekuler dalam
identifikasi, analisis kekerabatan dan taksonom
tumbuhan tidak lepas dari ilmu bioinformatika
yang merupakan perangkat pembantu dari
tahap awal sampai akhir dari pengolahan
pengolahan data molekuler. Bioinformatika
merupakan ilmu interdisiplin yang
menghubungkan ilmu komputer dan biologi,
atau gabungan dari biologi dan informatik yang
mengembangkan teknologi menggunakan
komputer untuk menyimpan, mengambil,
memanipulasi dan mendistribusikan data yang
berhubungan dengan makromolekuler biologi
seperti DNA, RNA, dan protein.
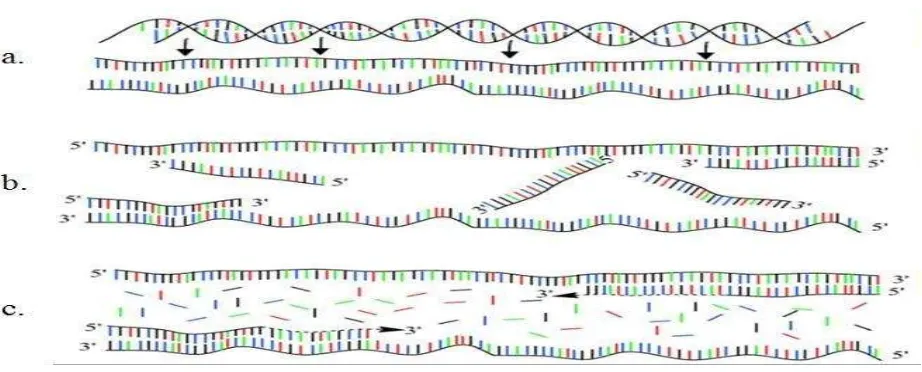
Gambar 2. Proses amplifikasi DNA/gen target (a) DNA awal yang mengalami denaturasi, yakni pemisahan DNA dengan pasangannya. (b) Anealling proses menempelnya primer dengan gen target. (c) ekstensi, proses pemanjangan gen target yang telah ditempeli primer dan tahap akhir dari siklus pertama PCR. (Newton & graham, 1995).
dan analisis fungsi gen dan genom, serta
produknya (Xiong, 2006).
Penggunaan markah molekuler setelah
diketahui gen target yang akan digunakan
untuk identifikasi maka hal yang pertama
dilakukan ialah desain primer dengan perangkat
bioinformatika. Desain primer biasanya
dilakukan setelah mengetahui sekuen DNA
yang lestari dengan cara mensejajarkan
beberapa sekuen gen yang sama dari jenis yang
berbeda. Primer ini berfungsi sebagai
penginisiasi dalam mengisolasi gen target
dalam proses PCR. DNA genom yang telah
diisiolasi selanjtunya di PCR untuk
mengamplifikasi gen target. Proses PCR ini
menggunakan prinsip denaturasi, anealling dan
elongasi DNA target.
Hasil PCR gen dilakukan elektroforesis
dan dilihat dibawah sinar ultraviolet, untuk
lebih akurat dapat dilakukan proses sekuensing
yakni pembacaan sekuen DNA dengan
menggunakan dDNTp sehingga didapatkan
huruf-huruf yang mencerminkan basa-basa
nitrogen yang ada pada sekuen DNA tersebut.
Hasil sekuensing dapat dianalisis dengan fungsi
BLAST pada genebank, yakni membandingkan
sekuen gen dengan gen yang telah ada di
genebank. Langkah selanjutnya dapat
dilakukan analisis bioinformatika tingkat lanjut
baik filogenentik molekuler maupun
identifikasi open reading frame (orf).
Proses isolasi DNA, yang diawali dengan
desain primer gen untuk isolasi serta analisis
filogenetik molekuler dan beberapa analisis
molekuler yang belum diaajarkan di prodi
Pendidikan Biologi Universitas Khairun, materi
ini sudah mulai dikenalkan pada matakuliah
genetika lanjut. Lebih khusus akan di
rekomendasikan pada matakuliah tersendiri
pada pilihan bioinformatika, filogenetik
molekuler, dan rekayasa genetik.
Kesimpulan
Penggunaan markah molekuler telah
memberikan paradigma baru yang berguna
dalam identifikasi tumbuhan, analisis
filogenetik, dan analisis taksonomi tumbuhan
karena tidak dipengaruhi langsung oleh
lingkungan. Sekuen gen rbcL telah
direkomendasikan oleh barcode of life sebagai
DNA barkode pada tumbuhan. Secara khusus
perkembangan markah molekuler berimplikasi
pada penambahan materi perkuliahan genetika
lanjut di prodi Pendidikan Biologi Unkhair
serta rekomendasi penambahan matakuliah
pilihan bioinformatika, filogenetik molekuler,
dan rekayasa genetik.
REFERENSI
Asahina, H., Shinozaki, J., Masuda, K., Morimitsu, Y., dan Satake, M. (2010) : Identification of medicinal Dendrobium species by phylogenetic analyses using matK and rbcL sequences. The Japanese Society of Pharmacognosy and Springer. J Nat Med 64:133–138.
Backer, C.A. dan Van Den Brink, R.C.B. (1965) : Flora of Java (Spermatophytes
only) Vol. II, Angiospermae, Families 111-160. N.V.P Nordhoff, Groningen, Netherland.
Bellstedt, D.U., van Zyl, L., Marais, E.M., Bytebier, B., de Villiers, C.A., Makwarela, A.M., dan Dreyer, L.L. (2008) : Phylogenetic relationships, character evolution and biogeography of Southern African members of Zygophyllum (Zygophyllaceae) based on three plastid regions. Molecular Phylogenetics and Evolution 47 : 932– 949. Elsevier Inc
Ga Hun Boo, Kyung Min Lee, et al., 2009, Classification of the Genus Ishige (Ishigeales, Phaeophyceae) in the North Pacific Ocean with Recognition of Ishige Foliacea Based on Plastid rbcL and Mitochondrial Cox3 Gene Sequences1, J. Phycol 45: 906–913, Phycological Society of America
Hajibabaei, M, Singer, G.A.C, Hebert, P.D.N, and Hickey, D.A. (2007). DNA barcoding: how it complements taxonomy, molecular phylogenetics and population genetics. TRENDS in Genetics Vol.xxx No.x: 1-6
Hidayat, et al., 2008, Analisis Filogenetik Molekuler pada Phylantus niruri L (Euphorbiaceae), Jurnal Matematika dan Sains Vol. 13 No 1.
Judd, W.S., Campbel, C.S., Kellog, E. A., Stevens, P. F., dan Donoghue, M. J. (2002) : Plant Systematics : Phylogenetic Approach, 2nd edition. Sinauer Associates, Inc. Publisher, Sunderland, Massachusets-USA.
Li, W., dan Graur, D. (1991) : Fundamental of Molecular Evolution. Sinauer Associates, Inc.
Li, Xiaoxian and Zhou, Zhekun, 2008, Phylogenetic studies of the core Alismatales inferred from morphology and rbcL sequences, Progress in natural Science 19: 931-945, Elsevier limited and Science in China Press.
Maistro, Silvia, et al., 2007, Moleclular Phylogeny and Evolution Of The Order Tribonematales (Heterokonta, Xanthophyceae) Based On Analysis Of Plastidial Genes rbcL and psaA, Molecular Phylogeny and Evolultion 43: 407-417, Elsevier Inc.
Nei, M., dan Kumar, S. (2000) : Molecular Evolution and Phylogenetics. Oxford University Press.
Newton, C.R, Graham, A., (1995) : PCR, Intoduction to Biotechniques. Bios Scientific Publisher ltd.
Ratnasingham, S., Hebert, P.D., 2007. The Barcode of Life Data System. Molecular ecology Notes.
Reddy, B.U. (2009) : Molecular phylogeny of Angiospermic plant families using rbcL gene Sequences. International Journal of Bioinformatics Research, 1(2) : pp-27-36.
Roche, 2009. PCR Applications Manual 3rd .
Barcode Loci May Not Work in Complex Groups: A Case Study with Indian Berberis Species. PLoS ONE 5(10): e13674.
doi:10.1371/journal.pone.0013674
Suparman. 2011. Analisis filogenetik Genus Mangifera Menggunakan Gen rbcL DNA Kloroplas. (Tesis S2 tidak diterbitkan). SITH-ITB. Bandung
Xiong, J. 2006. Essential Bioinformatics. Cambridge University Press: New York.
Yonemori, K., Honso, C., Kanzaki, S., Wiadthong, W., dan Sugiura, A. (2002) : Phylogentic relathionship of mangifera species revealed by ITS sequences of nuclear ribosomal DNA and a possibility of their hybrid origin. Plant Syst. Evol. (Fabaceae) based on DNA sequence data from rbcL, trnS–trnG, and ITS. Journal Molecular Phylogenetics and Evolution