SIMULASI PENAMBATAN MOLEKULER GENISTEIN PADA
RESEPTOR ESTROGEN ALFA
Oleh:
Ricardo Kenny Chandra
NIM: 108114186
INTISARI
Kanker payudara merupakan jenis kanker yang paling sering ditemui di
seluruh dunia dan mencakup 16% dari seluruh kejadian kanker pada wanita. Dua
dari tiga prevalensi kanker payudara yang terjadi disebabkan adanya
over
-ekspresi
reseptor estrogen alfa (RE
α
). Genistein, salah satu senyawa fito-esterogen
diketahui dapat berinteraksi dengan beberapa protein dalam tubuh, salah satunya
adalah
REα
.
Pada penelitian ini, dilakukan penapisan genistein sebagai ligan untuk
REα
dengan menggunakan perangkat lunak PLANTS1.2 dan
Python-based
protein-ligand interaction fingerprinting
(PyPLIF). Hasil yang didapatkan,
divisualisasikan untuk mengetahui bagaimana genistein berinteraksi di dalam
kantung ikatan
REα
menggunakan
perangkat lunak PyMOL1.2.
Hasil penelitian menunjukkan bahwa secara statistik protokol yang
dikembangkan oleh Radifar
et al.
(2013) tidak dapat mengenali genistein sebagai
ligan
REα
dan tidak dapat digunakan untuk elusidasi mode ikatan genistein
karena tidak mampu mereproduksikan mode ikatan ligan
co-crystal
yang
digunakan. Elusidasi mode ikatan dilakukan dengan menggunakan parameter
ChemPLP dan terindentifikasi setidaknya tiga mode ikatan genistein pada
REα
.
Kata kunci: Kanker payudara, genistein,
REα
,
in silico screening
,
ABSTRACT
Breast cancer is the most frequent cancer worldwide and cover 16% of
total cancer incidence on woman. Two out of three breast cancer prevalence are
caused by estrogen receptor alpha (ERα) overexpression. Genistein, one of pyhto
-estrogen is known for its ability to interact with some proteins, one of which is
ERα.
Screening genistein as ligand for ERα was
mainly completed using
PLANTS1.2 and
Python-based protein-ligand interaction fingerprinting
(PyPLIF)
software. The results were visualized to examine how genistein interact with
binding pocket of ERα using
PyMOL1.2 software.
Statistically, the result shown that the protocol developed by Radifar
et al.
(2013) could
not recognize genistein as ligand for ERα and could not reproduce
co-crystal binding mode. Therefore, the protocol could not be used to elucidate
genistein binding mode. To elucidate genistein binding mode, ChemPLP
parameter was used and at least three genistein binding mode were found.
SIMULASI PENAMBATAN MOLEKULER
GENISTEIN PADA RESEPTOR ESTROGEN ALFA
SKRIPSI
Diajukan untuk Memenuhi Salah Satu Syarat
Memperoleh Gelar Sarjana Farmasi (S.Farm.)
Program Studi Ilmu Farmasi
Oleh:
Ricardo Kenny Chandra
NIM: 108114186
FAKULTAS FARMASI
UNIVERSITAS SANATA DHARMA
YOGYAKARTA
Persetujuan Pembimbing
SIMULASI PENAMBATAN MOLEKULER GENISTEIN
PADA ESTROGEN RESEPTOR
ALFA
Skripsi
yang diajukan
oleh
:Ricardo
Kenny
Chandra
NIM
:
108114186Telah
disetujui oleh
:Istyastono, Ph.D., Apt tanggal2l Februai2014
Pembimbing
Pendamping
Agustina
Setiawati,
M.Sc., Apt.
tanggal21
Februari2014
Pengesahan
Skripsi Berjudul
SIMULASI PENAMBATAN MOLEKULER
GENISTEIN
PADA RESEPTOR ESTROGEN
ALFA
Oleh:
Ricardo
Kenny
Chandra
NIM:
108114186Dipertahankan
di
Hadapan Panitia
Penguji Skripsi
Fakultas Farmasi
Universitas
SanataDharma
Pada
tanggaL
2AFebruari 2014
Mengetahui,
Fakultas Farmasi
Universitas
SanataDharma
Panitia
Penguji
Skripsi
1.
Enade PerdanaIstyastono, Ph.D.,
Apt.
2.
Agustina
Setiawati,
M.Sc., Apt.
3.
Jeffry
Julianus,
M.Si.
4.
Nunung Yuniarti, M.Si.,
Ph.D.,
Apt.
111
,-(
Ipang
Djunarko, M.Sc., Apt.
A
$
iv
Halaman Persembahan
“
No one saves us but ourselves. No one can and no one may.
We ourselves must walk the path.
”
- Gautama Buddha.
“It is better to conquer yourself
than to win a thousand
battles. Then the victory is yours.
It cannot be taken from you, not by angels or by demons,
heaven or hell.” –
Gautama Buddha.
“I think that the power is the principle.
The principle of moving forward, as though you have the
confidence to move forward,
eventually gives you confidence when you look back and see what
you've done.” –
Robert Downey Jr.
Karya kecilku ini kupersembahkan untuk:
Buddha, Dhamma, dan Sangha yang telah mengajarkanku jalan
kehidupan
Papa dan Mama yang senantiasa memberikanku semangat, kasih
sayang, dan dukungan
Bapak/Ibu dosen dan staff pengajar Fakultas Farmasi USD
Sahabat-sahabatku tersayang
Serta
PERNYATAAN
KEASLIAN KARYA
Sl,r,a ,,',",'tratakrn denuan
scsr-rnggulrnyabahu,a
skripsi
yang
berjuclLrl"Sinrr-rlasi
Pcnanrbatan N,lolel<ulcrCenistein
PadaReseptor Estroqcn
i\lfa".
tidak
rrcnlllili
ltltrva
atauttagian
kan,a orang
lair-i.kccuali
vaug telah
ciisebutkarr clalan-rkr-rtipan clan
clalirr
pirstaka. scbagaintana la1,rkn1,akarya ilmiah.
Apabila
tli
kcnrLrclianhari
clitemr-rkanindikasi
plagiarisnre dalanr
naskahini.
nraka
str-vaberscclia
rlcnanggung
segala
sanksi
sesuaipcraturan
perunclang-r-rnclangan yan g
bcrlirku.
Yogyakarta,
21Februari 2014
Penulisd-\
LEMBAR PERNYATAAN
PERSETUJUAN
PUBLIKASI
ILMIAH
UNTUK KEPENTINGAN AKADENIIS
Yang
bcrtanda tansan
cli balr,ahini.
saya nrahasisu,a L-lniversitas SanalaDhanra:
Nanra :
Ricariio
Kenn1, CiranclraNomol
t\{ahasisrva
: I
081 l,+ I 86Dcrr-ri
pengembangan
ihru
perigetahuan,
sayamernberikan
kepacla PerpustiikaanUnir,.crsitas
Sanata
Dharma
karya
ilrriah
saya
yang
berjuclul:"Sinrulasi
Penamb:rtan
hlolekuler
Genistein
pada
Rcseptor Estrogen
Alla"
bcsertirpelangkat
1,.angcliperlukan
(bila
acia).Dcngan
dernikian
sitl'a
n-iernberikan kcpaclaperpr-rstakaan
Unil,ersitas
Sanata
Dhama
hak
untuk
r-r-rcnyirnpan.rrengalihkan
clalanr
bentuk
meclia lain.
rrcngclolanl,a
claianr
benturk
pan-91<alanclatu-n-renclistribr"rsikan secara
tcrtratas,
clan mer-r-ipr-rblikasikarrnl'adi irrternet atau
nrcclialain
untuk
kepentingan
akaden-ristiurpit perlu
mcn-tinta
t.1indari
sa1,alrauplur
irernberikan
rq,alty
kepada
sayaselana
tetap mencantumkan nama
saya seba-{ai peu iri is.Demikian
pcmyataan
ini
yang
sayabuat
densan sebcnalnya.Dibuat
di
Yogyakarta
Pada
tanggal: 21 Februari
201,1Yang
menyatakan
vii
PRAKATA
Puji syukur penulis panjatkan kepada Tuhan Yang Maha Esa atas rahmat
dan karunia-Nya yang diberikan sehingga penyusunan skripsi yang berjudul
“
SIMULASI
PENAMBATAN
MOLEKULER
GENISTEIN
PADA
RESEPTOR ESTROGEN ALFA
” dapat dilaksanakan dengan baik. Skripsi ini
disusun sebagai salah satu syarat untuk meraih gelar Sarjana Farmasi (S.Farm.) di
Fakultas Farmasi, Universitas Sanata Dharma, Yogyakarta.
Selama proses penelitian dan penyusunan skripsi ini, penulis mendapatkan
banyak bantuan dan dukungan dari berbagai pihak. Oleh karena itu, penulis
mengucapkan terima kasih kepada:
1.
Ipang Djunarko, M.Sc., Apt., selaku Dekan Fakultas Farmasi Universitas
Sanata Dharma.
2.
C.M. Ratna Rini Nastiti, M.Pharm., Apt., selaku Ketua Program Studi
Fakultas Farmasi Universitas Sanata Dharma Yogyakarta.
3.
Enade Perdana Istyastono, Ph.D., Apt., selaku dosen pembimbing yang
telah memberikan bimbingan, masukan serta pengarahan dalam penelitian
dan penyusunan skripsi ini.
4.
Agustina Setiawati, M.Sc., Apt., selaku dosen pembimbing yang telah
memberikan bimbingan serta pengarahan dalam penelitian dan
penyusunan skripsi ini.
viii
6.
Nunung Yuniarti, M.Si., Ph.D., Apt., sebagai dosen penguji yang telah
memberikan kritik dan saran yang membangun selama proses pembuatan
skripsi.
7.
Muhammad Radifar, S.Farm., yang telah memberikan pengarahan dan
bimbingan kepada peneliti selama penyusunan skripsi.
8.
Mas Ottok selaku laboran Laboratorium Teknologi Farmasetik Fakultas
Farmasi Universitas Sanata Dharma yang senantiasa menemani dan
memberikan fasilitas selama proses pelaksanaan penelitian di
laboratorium.
9.
Papa dan mama tersayang yang telah memberikan dukungan, semangat
dan dorongan kepada penulis selama proses penyusunan skripsi.
10.
Astuti Malyawati Soesanto dan Chandra Dewa Nata, teman seperjuangan
yang telah bersama-sama berjuang untuk menyelesaikan penelitian.
11.
Rosiana Cahyono, atas kesabaran, pengertian, doa, dukungan, dan
semangat yang selalu diberikan kepada penulis selama proses penelitian
dan penyusunan skripsi ini.
12.
Sahabatku Hendy, Tora, Suryo, Tian, Christian, Aji, Djanuar, Archie,
Hans, Thomas, Angga, Lili dan Reza terima kasih atas kebersamaan serta
canda tawa selama pengerjaan skripsi ini
14.
Semua
pihak yang
tidak
dapatpenulis
sebutkan satu
per
satu
yang
telah
membantu dalam
prosespenyusunan
skripsi ini.
Akhir
kata,
penulis
menyadari bahwa masih
banyak kekurangan
dalam
penyusunan
skripsi
ini
mengingat keterbatasan kemampuan
dan pengetahuan
penulis.
Oleh karena
itu,
penulis mengharapkan kritik
dan saranyang membangun
dari
semuapihak.
Semogaskripsi
ini
dapatmemberikan manfaat bagi
pembaca.Penulis
l)
Li
Ricardo
Kenny
Chandra
x
DAFTAR ISI
HALAMAN JUDUL...
HALAMAN PERSETUJUAN PEMBIMBING...
HALAMAN PENGESAHAN...
HALAMAN PERSEMBAHAN...
PERNYATAAN KEASLIAN KARYA...
LEMBAR PERNYATAAN PERSETUJUAN PUBLIKASI KARYA
ILMIAH UNTUK KEPENTINGAN AKADEMIS...
PRAKATA...
DAFTAR ISI...
DAFTAR TABEL...
DAFTAR GAMBAR...
DAFTAR LAMPIRAN...
DAFTAR SINGKATAN KATA...
INTISARI...
ABSTRACT...
BAB I. PENGANTAR...
A.
Latar Belakang...
1.
Permasalahan...
2.
Keaslian Penelitian...
3.
Manfaat Penelitian...
B.
Tujuan Penelitian...
i
ii
iii
iv
v
vi
vii
xi
1.
Tujuan Umum...
2.
Tujuan Khusus...
BAB II. PENELAAHAN PUSTAKA...
A.
Kanker Payudara ...
B.
Reseptor Estrogen...
C.
Genistein...
D.
Penapisan Virtual...
E.
Interaction Fingerprint
……….
...
F.
PyPLIF………
...
G.
Landasan Teori……
...
H.
Hipotesis
……….
BAB III. METODE PENELITIAN...
A.
Jenis dan Rancangan Penelitian...
B.
Variabel Penelitian………...
...
C.
Definisi Operasional...
D.
Bahan dan Alat Penelitian...
E.
Tata Cara Penelitian...
1.
Pengunduhan
co-crystal
RE
α...
..
2.
Pengunduhan struktur genistein...
3.
Simulasi penambatan...
a.
Uji efektivitas genistein...
b.
Elusidasi pose ikatan………..
...
xii
BAB IV. HASIL DAN PEMBAHASAN...
A.
Uji efektivitas genistein.…
...
B.
Elusidasi pose ikatan...
BAB V. KESIMPULAN DAN SARAN...
A.
Kesimpulan...
B.
Saran...
DAFTAR PUSTAKA...
LAMPIRAN...
BIOGRAFI PENULIS...
xiii
DAFTAR TABEL
Tabel I.
Tabel II.
Tabel III.
Tabel IV.
Tabel V.
Nilai RMSD penambatan kembali OHT Tc-PLIF
filter
…..
...
Nilai RMSD penambatan kembali OHT Tc-PLIF tanpa
filtrasi...
Nilai RMSD penambatan kembali OHT ChemPLP
filter
…….
Nilai RMSD penambatan kembali OHT ChemPLP tanpa
filtrasi………...
Konfigurasi pose representatif dari tiap kelompok………
25
34
43
xiv
DAFTAR GAMBAR
Gambar 1.
Gambar 2.
Gambar 3.
Gambar 4.
Gambar 5.
Gambar 6.
Gambar 7.
Gambar 8.
Gambar 9.
Proses perkembangan kanker...
Perbandingan struktur 17β
-estradiol (A) dengan genistein (B...
Flowchart
pengambilan keputusan penelitian...
Histogram sebaran nilai Tc-PLIF genistein...
Histogram sebaran nilai RMSD genistein...
Plot
kelompok RMSD genistein...
Visualisasi mode ikatan representatif genistein (B, C, D) dan
senyawa standar OHT (A) pada RE
α
...
Perbandingan mode ikatan representatif kelompok 1 (ungu)
dengan
representatif kelompok 2 (hijau)………
..
Struktur senyawa modifikasi genistein (A), Ruang berikatan
untuk senyawa modifikasi genistein (B)
………...
..
5
9
19
23
61
62
63
xv
DAFTAR LAMPIRAN
Lampiran 1.
Lampiran 2.
Lampiran 3.
Lampiran 4.
Lampiran 5.
Lampiran 6.
Lampiran 7.
Lampiran 8.
Lampiran 9.
Hasil Analisa Statistik dengan R 3.0.1...
Script
yang digunakan untuk menambatkan genistein pada
RE
α
...
Script
yang digunakan untuk filtrasi nilai Tc-PLIF
filter
terbaik
……….
Script
yang digunakan untuk menambatkan kembali OHT
pada RE
α………
Script
yang digunakan untuk menghitung nilai RMSD OHT
Tc-PLIF
filter
……….
Script
yang digunakan untuk menghitung nilai RMSD OHT
Tc-PLIF tanpa filtrasi
……….
Script
yang digunakan untuk menghitung nilai RMSD OHT
ChemPLP
filter
………..
Script
yang digunakan untuk menghitung nilai RMSD OHT
ChemPLP tanpa filtrasi
………..
Script
yang digunakan untuk menghitung nilai RMSD
genistein ChemPLP
filter
………...
71
72
73
74
75
76
77
78
xvi
DAFTAR SINGKATAN KATA
ABC
AF
AP-1
ChemPLP
DBD
EF
RE
α
RE
β
ERE
IFP
LBD
PDB
PLANTS
PVBS
PyPLIF
RMSD
Tc
Tc-PLIF
WHO
ATP-Binding Cassette
Activation Function
Transcription Factor Activator Protein-1
Chemical Piecewise Linear Potential
DNA Binding Domain
Enrichment Factor
Reseptor Estrogen Alfa
Reseptor Estrogen Beta
Estrogen Response Element
Interaction Fingerprint
Ligand Binding Domain
Protein Data Bank
Protein-Ligand Ants System
Penapisan Virtual Berbasis Struktur
Python-Based Protein-Ligand Interaction Fingerprinting
Root Mean Square Distance
Tanimoto Coefficient
xvii
INTISARI
Kanker payudara merupakan jenis kanker yang paling sering ditemui di
seluruh dunia dan mencakup 16% dari seluruh kejadian kanker pada wanita. Dua
dari tiga prevalensi kanker payudara yang terjadi disebabkan adanya
over
-ekspresi
reseptor estrogen alfa (RE
α
). Genistein, salah satu senyawa fito-esterogen
diketahui dapat berinteraksi dengan beberapa protein dalam tubuh, salah satunya
adalah
REα
.
Pada penelitian ini, dilakukan penapisan genistein sebagai ligan untuk
REα
dengan menggunakan perangkat lunak PLANTS1.2 dan
Python-based
protein-ligand interaction fingerprinting
(PyPLIF). Hasil yang didapatkan,
divisualisasikan untuk mengetahui bagaimana genistein berinteraksi di dalam
kantung ikatan
REα
menggunakan
perangkat lunak PyMOL1.2.
Hasil penelitian menunjukkan bahwa secara statistik protokol yang
dikembangkan oleh Radifar
et al.
(2013) tidak dapat mengenali genistein sebagai
ligan
REα
dan tidak dapat digunakan untuk elusidasi mode ikatan genistein
karena tidak mampu mereproduksikan mode ikatan ligan
co-crystal
yang
digunakan. Elusidasi mode ikatan dilakukan dengan menggunakan parameter
ChemPLP dan terindentifikasi setidaknya tiga mode ikatan genistein pada
REα
.
Kata kunci: Kanker payudara, genistein,
REα
,
in silico screening
,
xviii
ABSTRACT
Breast cancer is the most frequent cancer worldwide and cover 16% of
total cancer incidence on woman. Two out of three breast cancer prevalence are
caused by estrogen receptor alpha (ERα) overexpression. Genistein, one of pyhto
-estrogen is known for its ability to interact with some proteins, one of which is
ERα.
Screening genistein as ligand for ERα was
mainly completed using
PLANTS1.2 and
Python-based protein-ligand interaction fingerprinting
(PyPLIF)
software. The results were visualized to examine how genistein interact with
binding pocket of ERα using
PyMOL1.2 software.
Statistically, the result shown that the protocol developed by Radifar
et al.
(2013) could
not recognize genistein as ligand for ERα and could not reproduce
co-crystal binding mode. Therefore, the protocol could not be used to elucidate
genistein binding mode. To elucidate genistein binding mode, ChemPLP
parameter was used and at least three genistein binding mode were found.
1
BAB I
PENGANTAR
A.
Latar Belakang
Kanker merupakan suatu penyakit yang disebabkan oleh pertumbuhan sel
abnormal yang membelah secara terus-menerus (Ramirez, 2007).
World Health
Organization
(WHO) melaporkan bahwa lebih dari 508.000 orang wanita di dunia
meninggal akibat kanker payudara pada tahun 2011 serta angka kejadian kanker
payudara di sebagian besar negara berkembang mencapai 40 orang penderita
untuk tiap 100.000 orang wanita tiap tahunnya (Anonim, 2013).
Menurut Herynk, Selever, Thirugnanasampanthan, Cui, dan Fuqua
(2009),
REα
diketahui berperan penting dalam terjadinya kanker payudara, karena
dua dari tiga prevalensi kanker payudara disebabkan oleh adanya
over-
ekspresi
REα
yang memicu tumbuhnya kanker. Terapi yang banyak digunakan untuk
mengobati kanker adalah kemoterapi, namun kemoterapi mempunyai kekurangan
berupa efek samping yang dapat menurunkan kualitas hidup seseorang secara
signifikan (Hwang, Chang, dan Park, 2013). Oleh karena itu, perlu dikembangkan
suatu senyawa alam yang berpotensi dalam menghambat aktivitas
REα
dan
memiliki efek samping yang lebih ringan.
Genistein merupakan isoflavon (4’,5,7
-trihidroksiisoflavon) yang banyak
ditemukan pada daun tanaman subteranian (
Trifolium subterraneum
L. var.
berinteraksi dengan beberapa target biokimia dalam sel tubuh, yaitu protein tirosin
kinase, topoisomerase II, reseptor estrogen, transport ATP-
binding
cassette
(ABC), dan protein-protein lainnya (Polkowski dan Mazurek, 2000). Secara
in
vitro,
genistein telah diketahui aktivitasnya dalam menghambat
REα
pada sel
kanker payudara (Gilani dan Anderson, 2002), namun belum banyak dilakukan
penelitian mengenai aktivitas genistein pada
REα
secara
in silico
.
Uji
in silico
mengenai aktivitas
REα
didasarkan pada metode
penambatan Penapisan Virtual Berbasis Struktur (PVBS). Dalam penelitian ini,
dilakukan
interaction
fingerprint
(IFP) untuk memilih jenis ikatan antara ligan
dan asam amino yang tepat dan dapat digunakan sebagai
anchor
dalam
menentukan ligan yang dapat berikatan dengan molekul target. Pada penelitian ini
program IFP yang digunakan adalah PyPLIF yang dikembangkan oleh Radifar,
Yuniarti, dan Istyastono pada tahun 2013.
1.
Permasalahan
1.
Apakah genistein merupakan ligan bagi
REα
secara
in silico
menurut
protokol penapisan yang dikembangkan oleh Radifar
et al
. (2013) ?
2.
Bagaimanakah pose genistein di dalam kantung ikatan
REα
?
2.
Keaslian Penelitian
Radifar, Leonardus BS Kardono, Muhammad Hanafi, Enade P. Istyastono
pada tahun 2012 dan
“
In silico
Screening and Binding Mode Analysis of
Celecoxib as a Ligand for Estrogen Receptor Alpha
” oleh Florenti
nus Dika
Octa Riswanto, Agustina Setiawati, Sri Hartati Yuliani, Enade Perdana
Istyastono pada tahun 2013.
3.
Manfaat Penelitian
a.
Manfaat teoretis
Hasil penelitian diharapkan memberikan tambahan informasi mengenai
ikatan genistein terhadap
REα
sehingga dapat menjadi acuan dalam
pengembangan antagonis
REα
.
b.
Manfaat praktis
Penelitian ini diharapkan dapat menjadi salah satu pilihan obat untuk
mengatasi kanker payudara yang berasal dari bahan alam.
c.
Manfaat metodologis
B.
Tujuan Penelitian
1.
Tujuan umum
Penelitian ini bertujuan untuk mengidentifikasi senyawa alami yang
dapat menjadi ligan bagi
REα
.
2.
Tujuan khusus
Tujuan khusus dari penelitian ini antara lain:
a.
Mengetahui dan menguji apakah protokol penapisan
in silico
yang
dikembangkan oleh Radifar
et al.
(2013) mampu mengenali genistein
sebagai ligan pada
REα
.
b.
Mengetahui pada tingkat atomik pose genistein di dalam kantung ikatan
5
BAB II
PENELAAHAN PUSTAKA
A.
Kanker Payudara
Kanker merupakan suatu penyakit yang disebabkan oleh pertumbuhan sel
abnormal yang membelah secara terus-menerus (Ramirez, 2007). Kanker
payudara merupakan jenis kanker yang paling umum pada wanita di negara maju
dan berkembang.
World Health Organization
(WHO) melaporkan bahwa lebih
dari 508.000 orang wanita di dunia meninggal akibat kanker payudara pada tahun
2011 serta angka kejadian kanker payudara di sebagian besar negara berkembang
mencapai 40 orang penderita untuk tiap 100.000 orang wanita per tahunnya
(Anonim, 2013).
Sama seperti kanker pada umumnya, proses pertumbuhan kanker payudara
dapat dibagi menjadi tiga tahapan, yaitu inisiasi, promosi, dan progresi (Gambar
1). Tahap inisiasi merupakan tahap mutasi pada satu atau lebih gen pada sel yang
berperan penting dalam mengatur proliferasi sel dan bersifat tidak terbalikkan
(Ramirez, 2007). Ketika sel telah termutasi oleh agen inisiasi, sel tersebut rentan
terhadap agen promosi (tahap promosi). Agen promosi dapat meningkatkan
kecepatan proliferasi sel sehingga jumlah sel yang termutasi meningkat dalam
jaringan. Tahap progresi merupakan kelanjutan dari promosi, namun pertumbuhan
sel kanker tidak lagi bergantung pada paparan agen promosi. Pada tahap tersebut,
sel kanker dapat tumbuh secara mandiri dan bersifat invasif melalui metastasis ke
seluruh tubuh (Braun dan Anderson, 2007).
Umumnya, pada tahap awal terjadinya kanker payudara ditemukan adanya
overekspresi
REα
.
REα
yang berikatan dengan estrogen menyebabkan adanya
stimulasi pembelahan sel dan pertumbuhan tumor (Allred, Brown, dan Medina,
2004). Mekanisme estrogen dalam menstimulasi proliferasi sel kanker payudara
dapat disebabkan karena genotoksisitas dari estrogen. Induksi dari gen faktor
pemicu pertumbuhan yang berada di stroma dan sel epitel juga dapat
menyebabkan proliferasi (Ramirez, 2007).
B.
Reseptor Estrogen
Aksi estrogen dalam menstimulasi pertumbuhan kanker payudara
dimediasi oleh 2 reseptor, yaitu RE
α
dan reseptor estrogen beta (RE
β)
.
REα
dan
transkripsi. Aktivasi transkripsi oleh
REα
diperantarai setidaknya dengan 2
activation function
(AF) yang berbeda, yaitu: AF-1 pada ujung rantai N dan AF-2
yang terletak pada
Ligand Binding Domain
(LBD) (Kushner
et al
., 2000).
Aktivitas AF-1 diatur oleh faktor pertumbuhan melalui jalur MAP kinase,
sedangkan AF-2 diaktivasi oleh ikatan dengan ligan agonis. DNA
Binding
Domain
(DBD) pada
REα
berfungsi untuk berikatan dengan
Estrogen Response
Element
(ERE) pada DNA untuk menginduksi terjadinya transkripsi (Hewitt dan
Korach, 2002).
Mekanisme stimulasi transkripsi oleh
REα
diawali dengan terjadinya
ikatan antara ligan agonis dengan LBD.
REα
yang telah teraktivasi akan
membentuk
homodimer
dan masuk ke dalam nukleus untuk berikatan dengan
ERE dan merekrut
co-activator
transkripsi (Hewitt dan Korach, 2002). Ikatan
antara
REα
dengan
co-activator
dipengaruhi oleh jenis ligan (agonis atau
antagonis) yang berikatan pada LBD. Ikatan dengan ligan agonis akan
mengakibatkan perubahan konformasi pada heliks 12 dan membentuk motif
LXXLL (L sebagai Leusin, X sebagai asam amino apapun) atau biasa disebut NR
box
,
yang dapat dikenali oleh
co-activator
sebagai tempat berikatannya dengan
REα
. Ikatan dengan ligan antagonis akan mengakibatkan heliks 12 untuk menutup
NR
box
, sehingga
co-activator
tidak dapat membentuk kompleks dengan
REα
(Shiau
et al
., 1998). Setelah
dimer
REα
membentuk kompleks dengan
co-activator
, kompleks tersebut
akan berikatan dengan ERE pada gen target dan
Peningkatan jumlah
REα
pada epitel payudara meningkatkan resiko
terkena kanker payudara (Ali dan Coombes, 2000). Dua dari tiga prevalensi
kanker payudara disebabkan oleh adanya ekspresi
REα
yang memicu tumbuhnya
tumor (Herynk
et al.
, 2009). Estrogen yang mengikat pada
REα
mengaktivasi
jalur
signaling
yang mengakibatkan proliferasi seluler dan diferensiasi pada
jaringan normal mamalia. Namun demikian, penyimpangan aktivasi
REα
menyebabkan proliferasi sel yang tidak terkontrol dan menyebabkan terjadinya
kanker payudara (Li, Meeran, Patel, Chen, Hardy, dan Tollefsbol, 2013).
Di sisi lain, estradiol juga dapat berikatan dengan
REβ
walaupun dengan
afinitas 50% lebih kecil dibandingkan dengan afinitasnya terhadap
REα
(Omoto,
Eguchi, Yamaguchi, dan Hayashi, 2003). Secara
in vitro
,
REβ
diketahui memiliki
aktivitas dalam menghambat transkripsi yang diinduksi oleh
REα
pada sel kanker
payudara (Hayashi
et al.
, 2003).
REβ
diketahui mempunyai beberapa varian
isoform
, dua di antaranya adalah
REβ
1 dan
REβcx/β2 (Omoto
et al
., 2003).
Kedua
isoform
tersebut, menghambat transkripsi yang diinduksi oleh
REα
dengan
mekanisme yang berbeda, yaitu:
REβ
1 berkompetisi dengan
REα
untuk berikatan
dengan ERE pada target gen dan dapat membentuk
homodimer
atau
heterodimer
dengan
REα
, sedangkan
REβ
cx menginhibisi ikatan antara
REα
dengan ERE
melalui mekanisme yang belum diketahui (Hayashi
et al
., 2003). Ikatan antara
homodimer
REα
pada ERE menghasilkan stimulasi transkripsi yang lebih besar
dibandingkan ikatan ERE dengan
homodimer
atau
heterodimer
REβ
1 (Omoto
et
al.
, 2003). Penghambatan
REβ
1 dan
REβ
cx terhadap fungsi proliferasi
REα
C.
Genistein
Genistein merupakan isoflavon (4’,5,7
-trihidroksiisoflavon) yang banyak
ditemukan pada daun tanaman subteranian (
Trifolium subterraneum
L. var.
Dwalganup) dan kacang kedelai (
Glycine max
) (Mariane, 2011). Kacang kedelai
mengandung kurang lebih 0,1% genistin (konjugat glikosidik dari genistein) yang
akan dimetabolisme oleh bakteri dan enzim di dalam saluran pencernaan menjadi
genistein (Pomfrey, 2005).
Genistein memiliki struktur
yang mirip dengan 17β
-estradiol (varian
estrogen endogen yang memiliki afinitas terbesar dengan
REα
) terutama pada
gugus hidroksi yang terletak pada kedua sisinya (Gambar 2). Genistein
mempunyai sifat antioksidan dan antikanker dengan mengurangi kadar
reactive
oxygen species
, dan juga menginduksi ekspresi enzim antioksidan seperti
superoxide dismutase
dan
catalase
(Park
et al
., 2010) serta memodulasi gen yang
meregulasi siklus sel dan apoptosis (Sarkar dan Li, 2002). Genistein diketahui
dapat berinteraksi dengan beberapa target biokimia dalam sel tubuh, yaitu protein
tirosin kinase, topoisomerase II, reseptor estrogen, transport ABC, dan
protein-protein lainnya (Polkowski dan Mazurek, 2000).
Efek protektif terhadap kanker dari senyawa isoflavonoid diperkirakan
terjadi melalui beberapa mekanisme, yaitu penghancuran radikal bebas,
modifikasi enzim yang dapat mendetoksifikasi karsinogen, dan inhibisi terjadinya
induksi
transcription factor activator protein
-1 (AP-1) oleh tumor (Shih,
Pickwell, dan Quattrochi, 2002). Menurut Pomfrey (2005), mekanisme
antikarsinogenik genistein yang berhubungan dengan
REα
antara lain: kompetisi
dengan estrogen endogen karena ikatan antara genistein dengan
REα
menghasilkan aktifitas estrogenik yang lemah (1.000-100.000 kali lebih lemah
dari
17β
-estradiol), inhibisi fosforilasi protein tirosin kinase dari reseptor, dan
mengurangi regulasi ekspresi
REα
.
D.
Penapisan Virtual
Penapisan Virtual Berbasis Struktur
(PVBS) merupakan analog komputasi
dari
High Throughput Screening
dan mengacu pada evaluasi sifat-sifat senyawa
secara
in silico
seperti aktivitas dari beberapa penyusun molekul yang berbeda
(Melagraki dan Afantitis, 2011). Penapisan virtual banyak digunakan sebagai
metode untuk penemuan obat baru dengan tujuan utama yaitu mengidentifikasi
suatu senyawa kimia baru yang mempunyai probabilitas tinggi untuk berikatan
pada protein target dan menghasilkan respon biologis yang diinginkan (Ghosh,
Nie, An, dan Huang, 2006).
algoritma matematis yang disebut dengan
scoring function
kemudian digunakan
untuk mengevaluasi kecocokan antara senyawa yang ditambatkan dan molekul
target.
Scoring function
merupakan pendekatan secara matematika yang
digunakan untuk memprediksi kekuatan interaksi non-kovalen pada proses
penambatan. Tahap selanjutnya adalah menyeleksi dan mengurutkan senyawa
berdasarkan
binding score
dan/atau kriteria lainnya (Cheng, Li, Zhou, Wang, dan
Bryant, 2012). ChemPLP merupakan
scoring function
yang menilai interaksi yang
ada berdasarkan gaya tarik-menarik dan tolak-menolak antara protein dan ligan
(Korb, Stützle, dan Exner, 2006). Kelemahan dari
scoring function
konvensional
(termasuk ChemPLP) adalah tidak mampu membedakan antara pose yang relevan
dengan pose yang tidak relevan, terutama untuk senyawa dengan berat molekul
yang kecil seperti fragmen (Marcou dan Rognan, 2006).
Validasi internal digunakan untuk memeriksa apakah simulasi penambatan
yang digunakan protokol PVBS dapat menghasilkan ulang pose dari ligan
co-crystal
dengan cara menambatkan kembali ligan pada molekul target
berulang-ulang. Parameter yang digunakan pada validasi internal adalah nilai RMSD (
Root
Mean Square Distance
) antara atom besar dari pose penambatan dan pose struktur
kristal. Nilai RMSD yang dianggap
acceptable
adalah kurang dari 2,0 Å (Marcou
dan Rognan, 2006). Validasi retrospektif bertujuan untuk mengetahui apakah
protokol PVBS yang digunakan dapat membedakan antara ligan positif dengan
decoy
. Parameter yang digunakan pada validasi retrospektif adalah
Enrichment
Factor
(EF). Semakin besar nilai EF menunjukkan protokol PVBS yang
Menurut penelitian yang dilakukan oleh Anita
et al
. (2012), protokol
PVBS yang digunakan dapat menjadi alat yang valid untuk menapiskan ligan aktif
pada
REα
secara virtual dan diketahui bahwa molekul air yang terdapat pada
REα
(PDB code: 3ERT) mempunyai peran penting dalam meningkatkan
kualitas dari protokol PVBS.
E.
Interaction Fingerprint
Aspek utama dari
interaction
fingerprint
(IFP) adalah pemilihan jenis
ikatan antara ligan dan asam amino yang tepat dan dapat digunakan sebagai
anchor
dalam menentukan ligan yang dapat berikatan dengan molekul target.
Informasi yang didapat, ditampilkan dalam bentuk data yang dapat dengan mudah
dimengerti dan diproses dengan metode komputasi. Kelebihan utama dari metode
ini adalah kemampuannya untuk membandingkan data
fingerprint
dan
menghitung kesamaannya (antara senyawa yang diuji dengan senyawa reference)
dengan Tanimoto
coefficient
(Tc) yang dapat memfasilitasi pencarian kesamaan
secara cepat. Dalam penapisan virtual,
fingerprint
dapat digunakan untuk
menapiskan
database
untuk mengidentifikasi senyawa yang cocok dengan sifat
dari ligan bioaktif (Bielska, Lucas, Czerwoniec, Kasprzak, Kaminska, dan
Bujnicki, 2011).
Fingerprint
dapat diklasifikasikan sesuai dengan dimensinya, yaitu 1D,
2D, dan 3D.
Fingerprint
yang paling popular dan efisien adalah
fingerprint
2D.
Pada
fingerprint
2D, dihasilkan data dalam bentuk 2D, yaitu interaksi molekul
ada atau tidak adanya jenis interaksi tersebut antara ligan dengan molekul target
(Bielska
et al.
, 2011).
Salah satu kelemahan dari
software
IFP adalah menggunakan
software
berbayar atau pustaka berbayar. Oleh karena itu, pada tahun 2013 Radifar
et al.
mengembangkan suatu perangkat lunak
IFP yaitu PyPLIF yang menggunakan
OpenBabel
(sebuah pustaka
open source
) untuk menghasilkan perangkat lunak
IFP yang tak berbayar (Radifar
et al.
, 2013).
F.
PyPLIF
Python-based
protein-ligand
interaction
fingerprinting
(PyPLIF)
merupakan program/
script
yang digunakan untuk menganalisa interaksi protein
dengan ligan dari hasil penambatan molekuler. Menurut Marcou dan Rognan
(2006),
interaction fingerprinting
merupakan parameter yang lebih baik
dibandingkan dengan fungsi scoring berbasis energi dalam menentukan
kesuksesan penambatan. Salah satu kelebihan dari PyPLIF adalah program ini
berdasar pada
Open Babel Library
, sebuah pustaka
open source
yang menyajikan
peralatan IFP lengkap dan dapat diakses gratis oleh semua orang (Radifar
et al.
,
2013).
PyPLIF dapat menghasilkan IFP dengan mengubah interaksi molekuler
dari ligand-protein menjadi
bit array
berdasarkan pilihan residu dan tipe interaksi.
Setiap residu terdapat 7
bits
yang menggambarkan 7 tipe interaksi yaitu apolar
(
van der Waals), aromatic face to face
,
aromatic edge to face,
ikatan hidrogen
interaksi elektrostatik (protein bermuatan negatif). Menurut Radifat
et al.
(2013),
dengan melakukan filtrasi pada pose yang berikatan hidrogen dengan Asp351,
kualitas protokol penapisan pada reseptor
REα
dapat ditingkatkan.
Bit arrays
dari pose penambatan dibandingkan dengan standar dan
diperiksa kesamaannya menggunakan Tanimoto
coefficient protein-ligand
interaction fingerprinting
(Tc-PLIF). Nilai Tc-PLIF berkisar antara 0,000 sampai
1,000, dengan nilai 0,000 menandakan bahwa tidak ada kemiripan, dan nilai 1,000
menandakan bahwa IFP pose penambatan antara ligan dengan standar identik.
Nilai Tc-PLIF untuk ligan aktif lebih besar sama dengan 0,600 (Marcou dan
Rognan,
2006).
G.
Landasan Teori
Kanker payudara merupakan suatu penyakit yang disebabkan oleh
pertumbuhan sel abnormal yang membelah secara terus menerus. Umumnya
penyebab terjadinya kanker payudara adalah adanya overekspresi
REα
pada epitel
payudara.
Salah satu senyawa alam yang telah terbukti baik secara
in vitro
maupun
in vivo
dapat bersifat sebagai antikanker yaitu genistein yang termasuk dalam
golongan isoflavon. Genistein diketahui dapat berinteraksi dengan beberapa target
biokimia dalam sel tubuh, seperti
REα
. Dengan menggunakan perangkat lunak
PyPLIF dan protokol yang telah divalidasi oleh Radifar
et al
. (2013) dilakukan
simulasi penambatan genistein pada
REα
dan mengidentifikasi pose ikatan antara
H.
Hipotesis
1.
Genistein merupakan ligan bagi
REα
secara
in silico
menurut protokol
penapisan yang dikembangkan Radifar
et al.
(2013).
16
BAB III
METODE PENELITIAN
A.
Jenis dan Rancangan Penelitian
Penelitian yang berjudul
“Simulasi Penambatan Moleku
ler Genistein
pada Reseptor Estrogen Alf
a”
termasuk penelitian komputasi eksperimental yang
terdapat intervensi terhadap variabel yang dilakukan dengan bantuan komputer.
B.
Variabel Penelitian
1.
Variabel Penelitian
a.
Variabel Utama
1)
Variabel bebas
: Protokol penambatan.
2)
Variabel tergantung : Nilai Tc-PLIF, ChemPLP dan pose genistein di
dalam kantung ikatan
REα
.
b.
Variabel Pengacau
1)
Variabel pengacau terkendali
a)
Spesifikasi perangkat keras komputasi dan versi perangkat lunak.
2)
Variabel pengacau tak terkendali
a)
Sifat algoritma penambatan molekuler yang stokastik.
C.
Definisi Operasional
1.
Protokol penelitian: Algoritma yang digunakan oleh Anita
et al.
(2012) dan
telah direvalidasi oleh Radifar
et al.
(2013).
3.
Filter
: Penyaringan pose ligan yang mempunyai interaksi
hidrogen dengan Asp351.
D.
Bahan dan Alat Penelitian
1.
Bahan yang digunakan dalam penelitian
a.
Protokol yang telah dikembangkan oleh Anita
et al
. (2012) dan
divalidasi kembali oleh Radifar
et al.
(2013).
b.
Struktur
co-crystal
dari
REα
(didapatkan dari PDB code: 3ERT)
c.
Struktur tiga dimensi genistein (didapatkan dari zinc.docking.org,
dengan kode: ZINC188253300)
d.
Docking Software
PLANTS 1.2 (Korb
et al
., 2006) PyPLIF (Radifar
et
al
., 2013) untuk menilai kembali pose penambatan,
Open Babel
sebagai
pustaka
fingerprinting
open access
, PyMOL1.2 (Lill dan Danielson,
2011) untuk menampilkan data, dan R 3.0.1. (R Development Core
Team, 2013) untuk analisa statistik.
2.
Alat atau Instrumen Penelitian
E.
Tata Cara Penelitian
1.
Pengunduhan
co-crystal
REα
Pengunduhan dilakukan dari website PDB (www.rcsb.org) dengan
PDB code: 3ERT.
2.
Pengunduhan struktur genistein
Struktur genistein diunduh dari ZINC (zinc.docking.org) dengan
kode: ZINC188253300
3.
Simulasi penambatan
a.
Uji efektivitas genistein
Uji efektivitas genistein dilakukan menggunakan protokol yang
dikembangkan oleh Anita
et al.
(2012) dan validasi kembali oleh Radifar
et al.
(2013) dengan 1.000 kali pengulangan. Protokol menggunakan
PLANTS1.2 sebagai perangkat lunak simulasi penambatan dan PyPLIF
sebagai perangkat lunak IFP. Diambil nilai Tc-PLIF terbesar dari tiap
penambatan pada pose yang memiliki interaksi hidrogen dengan Asp351.
Jika nilai Tc-PLIF terbesar muncul lebih dari satu, maka diambil pose
dengan nilai ChemPLP yang lebih baik. Seluruh nilai Tc-PLIF dihitung
secara statistik dengan taraf kepercayaan 95% bahwa nilai Tc-PLIF tidak
kurang dari 0,600 dengan menggunakan perangkat lunak R 3.0.1.
b.
Elusidasi pose ikatan
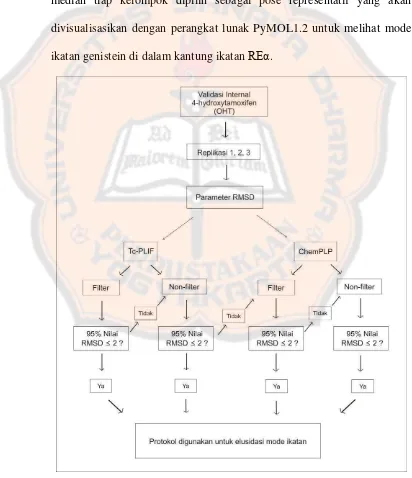
(Gambar 3). Protokol yang terpilih, kemudian digunakan untuk
mendapatkan pose dengan nilai ChemPLP terbaik sebagai pembanding
untuk menghitung nilai RMSD dari setiap pose genistein dengan
REα
.
Nilai RMSD setiap pose, dikelompokkan dengan menggunakan metode
k-means clustering
pada perangkat lunak R 3.0.1. Pose pada nilai RMSD
[image:39.595.99.511.258.736.2]median tiap kelompok dipilih sebagai pose representatif yang akan
divisualisasikan dengan perangkat lunak PyMOL1.2 untuk melihat mode
ikatan genistein di dalam kantung ikatan
REα
.
F.
Tata Cara Analisis Hasil
Data Tc-PLIF dianalisis dengan perangkat lunak R 3.0.1 menggunakan uji
Shapiro-wilk
untuk melihat distribusi data tiap kelompok. Jika didapatkan
distribusi data yang tidak normal maka dilanjutkan dengan
wilcoxon rank sum
test
. Apabila didapatkan distribusi data yang normal maka dilakukan uji variansi
21
BAB IV
HASIL DAN PEMBAHASAN
Salah satu tujuan pengembangan metode
in silico
adalah sebagai
pendekatan untuk menemukan obat baru, namun untuk melakukan pendekatan
secara
in silico
dibutuhkan protokol yang telah tervalidasi. Dengan tujuan untuk
mengelusidasi pose ikatan genistein dengan
REα
, penelitian ini menggunakan
pendekatan kimia medisinal komputasi berupa penapisan virtual dengan protokol
penapisan virtual yang dikembangkan oleh Anita
et al
. (2012) dan divalidasi
kembali oleh Radifar
et al
. (2013). Ligan yang akan ditambatkan pada
REα
adalah
genistein yang merupakan senyawa fitoestrogen yang telah diketahui aktif sebagai
antagonis
REα
secara
in vitro
maupun
in vivo
(Gilani dan Anderson, 2002),
sehingga penelitian ini juga dapat digunakan sebagai validasi prospektif dari
protokol penapisan virtual yang digunakan.
Senyawa genistein yang merupakan ligan pada penelitian ini ditambatkan
pada
REα
dengan menggunakan perangkat lunak PLANTS1.2 dengan luaran
berupa pose ikatan antara genistein dengan
REα
dan skor ChemPLP. Hasil
penambatan molekul dilakukan identifikasi IFP
dengan menggunakan perangkat
lunak PyPLIF serta dilakukan filtrasi pada pose ligan yang mempunyai ikatan
hidrogen dengan Asp351 (Radifar
et al.
, 2013), sehingga hanya diterima pose
A.
Uji efektivitas genistein
Efektivitas genistein pada
REα
ditentukan berdasarkan nilai Tc-PLIF
yang merupakan kemiripan IFP antara ligan dengan standar. Standar yang
digunakan adalah 4-hidroksitamoksifen (OHT), metabolit aktif dari
tamoksifen yang memiliki afinitas 100 kali lipat lebih besar dari estradiol
untuk berikatan dengan
REα
(Berry, 2008). Jika genistein mempunyai IFP
yang mirip dengan OHT, maka genistein dapat dikatakan sebagai ligan yang
aktif pada
REα
. Nilai Tc-PLIF yang diterima adalah lebih besar atau sama
dengan 0,600 dari senyawa standar (Marcou dan Rognan, 2006).
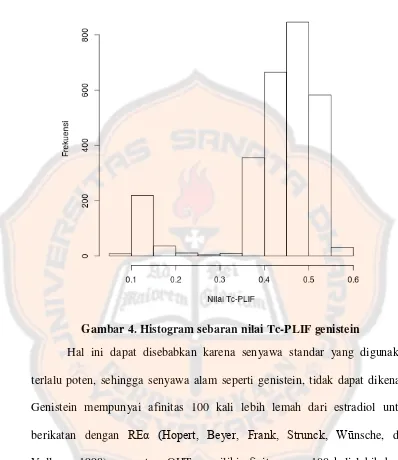
Dari hasil penambatan yang dilakukan, didapatkan nilai Tc-PLIF
rata-rata yang sebesar 0,425±0,112 dan nilai median sebesar 0,458 dengan sebaran
nilai ditampilkan dalam bentuk histogram (Gambar 4). Uji
Shapiro-wilk
menunjukkan bahwa nilai Tc-PLIF yang didapatkan tidak terdistribusi normal
dengan variansi yang tidak homogen, sehingga dilakukan uji
Wilcoxon
untuk
mengetahui apakah nilai Tc-PLIF tidak lebih kecil dari 0,600 (Lampiran 1).
Secara statistik, dengan taraf kepercayaan 95%, nilai Tc-PLIF
genistein lebih kecil dari 0,600, menandakan bahwa genistein tidak aktif pada
REα
secara
in silico
. Hasil ini berlawanan dengan hasil uji secara
in vitro
dan
in vivo
yang mengatakan bahwa genistein aktif dalam menghambat
REα
(Gilani dan Anderson, 2002). Oleh karena itu, dapat disimpulkan menurut
protokol yang dikembangkan oleh Radifar
et al
. (2013) genistein bukan
Gambar 4. Histogram sebaran nilai Tc-PLIF genistein
B.
Elusidasi pose ikatan
Sebelum senyawa genistein ditambatkan pada
REα
, dilakukan validasi
internal untuk mengetahui apakah protokol yang digunakan dapat
menghasilkan kembali pose dari ligan
co-crystal
dengan parameter nilai
RMSD antara atom-atom besar pada pose penambatan dan pose struktur
crystal
. Protokol akan diterima apabila nilai RMSD yang dihasilkan kurang
dari 2,0 Å (Anita
et al
., 2012). Protokol yang dapat menghasilkan kembali
pose dari ligan
co-crystal
(95% dari nilai RMSD yang dihasilkan kurang dari
2,0 Å) akan digunakan untuk elusidasi pose ikatan genistein di dalam kantung
ikatan
REα
. Prosedur validasi internal dilakukan sesuai dengan
flowchart
prosedur pengambilan keputusan penelitian (Gambar 3).
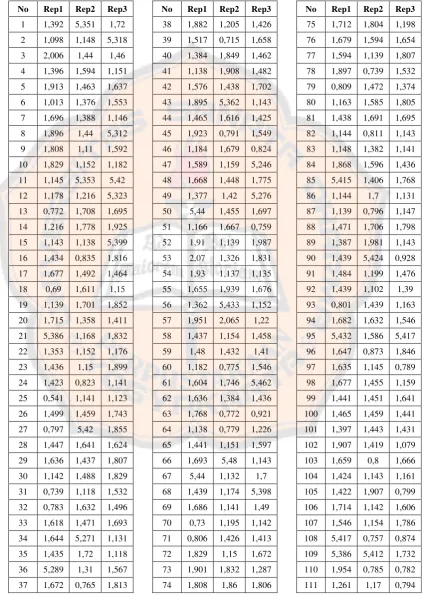
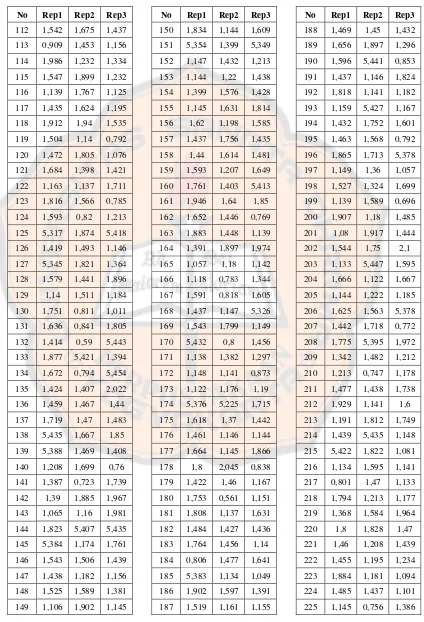
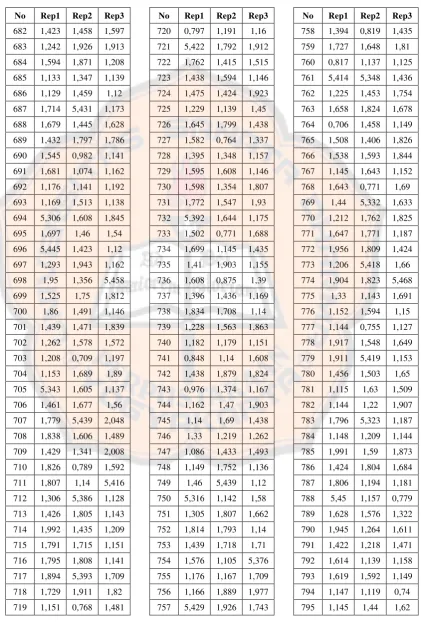
Berdasarkan Tabel I dan II diketahui bahwa protokol dengan parameter
Tc-PLIF tidak dapat menghasilkan kembali pose
co-crystal
, karena nilai
RMSD yang lebih kecil dari 2,0 Å tidak mencapai 95%. Dengan
menggunakan parameter ChemPLP, 100% nilai RMSD yang dihasilkan lebih
kecil dari 2,0 Å untuk ketiga replikasi (Tabel III dan IV). Oleh karena itu,
parameter ChemPLP
filter
digunakan untuk menentukan pose ikatan genistein
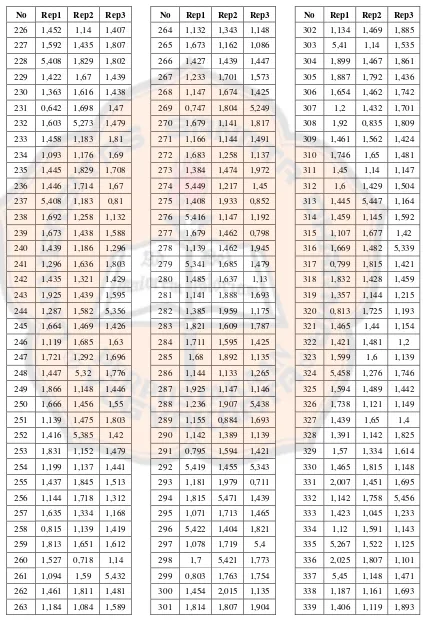
Tabel I. Nilai RMSD penambatan kembali OHT Tc-PLIF
filter
No Rep1 Rep2 Rep3
1 1,392 5,351 1,72 2 1,098 1,148 5,318 3 2,006 1,44 1,46 4 1,396 1,594 1,151 5 1,913 1,463 1,637 6 1,013 1,376 1,553 7 1,696 1,388 1,146 8 1,896 1,44 5,312 9 1,808 1,11 1,592 10 1,829 1,152 1,182 11 1,145 5,353 5,42 12 1,178 1,216 5,323 13 0,772 1,708 1,695 14 1,216 1,778 1,925 15 1,143 1,138 5,399 16 1,434 0,835 1,816 17 1,677 1,492 1,464 18 0,69 1,611 1,15 19 1,139 1,701 1,852 20 1,715 1,358 1,411 21 5,386 1,168 1,832 22 1,353 1,152 1,176 23 1,436 1,15 1,899 24 1,423 0,823 1,141 25 0,541 1,141 1,123 26 1,499 1,459 1,743 27 0,797 5,42 1,855 28 1,447 1,641 1,624 29 1,636 1,437 1,807 30 1,142 1,488 1,829 31 0,739 1,118 1,532 32 0,783 1,632 1,496 33 1,618 1,471 1,693 34 1,644 5,271 1,131 35 1,435 1,72 1,118 36 5,289 1,31 1,567 37 1,672 0,765 1,813
No Rep1 Rep2 Rep3
38 1,882 1,205 1,426 39 1,517 0,715 1,658 40 1,384 1,849 1,462 41 1,138 1,908 1,482 42 1,576 1,438 1,702 43 1,895 5,362 1,143 44 1,465 1,616 1,425 45 1,923 0,791 1,549 46 1,184 1,679 0,824 47 1,589 1,159 5,246 48 1,668 1,448 1,775 49 1,377 1,42 5,276 50 5,44 1,455 1,697 51 1,166 1,667 0,759 52 1,91 1,139 1,987 53 2,07 1,326 1,831 54 1,93 1,137 1,135 55 1,655 1,939 1,676 56 1,362 5,433 1,152 57 1,951 2,065 1,22 58 1,437 1,154 1,458 59 1,48 1,432 1,41 60 1,182 0,775 1,546 61 1,604 1,746 5,462 62 1,636 1,384 1,436 63 1,768 0,772 0,921 64 1,138 0,779 1,226 65 1,441 1,151 1,597 66 1,693 5,48 1,143 67 5,44 1,132 1,7 68 1,439 1,174 5,398 69 1,686 1,141 1,49 70 0,73 1,195 1,142 71 0,806 1,426 1,413 72 1,829 1,15 1,672 73 1,901 1,832 1,287 74 1,808 1,86 1,806
No Rep1 Rep2 Rep3
Tabel I. lanjutan
No Rep1 Rep2 Rep3
112 1,542 1,675 1,437 113 0,909 1,453 1,156 114 1,986 1,232 1,334 115 1,547 1,899 1,232 116 1,139 1,767 1,125 117 1,435 1,624 1,195 118 1,912 1,94 1,535 119 1,504 1,14 0,792 120 1,472 1,805 1,076 121 1,684 1,398 1,421 122 1,163 1,137 1,711 123 1,816 1,566 0,785 124 1,593 0,82 1,213 125 5,317 1,874 5,418 126 1,419 1,493 1,146 127 5,345 1,821 1,364 128 1,579 1,441 1,896 129 1,14 1,511 1,184 130 1,751 0,811 1,011 131 1,636 0,841 1,805 132 1,414 0,59 5,443 133 1,877 5,421 1,394 134 1,672 0,794 5,454 135 1,424 1,407 2,022 136 1,459 1,467 1,44 137 1,719 1,47 1,483 138 5,435 1,667 1,85 139 5,388 1,469 1,408 140 1,208 1,699 0,76 141 1,387 0,723 1,739 142 1,39 1,885 1,967 143 1,065 1,16 1,981 144 1,823 5,407 5,435 145 5,384 1,174 1,761 146 1,543 1,506 1,439 147 1,438 1,182 1,156 148 1,525 1,589 1,381 149 1,106 1,902 1,145
No Rep1 Rep2 Rep3
150 1,834 1,144 1,609 151 5,354 1,399 5,349 152 1,147 1,432 1,213 153 1,144 1,22 1,438 154 1,399 1,576 1,428 155 1,145 1,631 1,814 156 1,62 1,198 1,585 157 1,437 1,756 1,435 158 1,44 1,614 1,481 159 1,593 1,207 1,649 160 1,761 1,403 5,413 161 1,946 1,64 1,85 162 1,652 1,446 0,769 163 1,883 1,448 1,139 164 1,391 1,897 1,974 165 1,057 1,18 1,142 166 1,118 0,783 1,344 167 1,591 0,818 1,605 168 1,437 1,147 5,326 169 1,543 1,799 1,149 170 5,432 0,8 1,456 171 1,138 1,382 1,297 172 1,148 1,141 0,873 173 1,122 1,176 1,19 174 5,376 5,225 1,715 175 1,618 1,37 1,442 176 1,461 1,146 1,144 177 1,664 1,145 1,866 178 1,8 2,045 0,838 179 1,422 1,46 1,167 180 1,753 0,561 1,151 181 1,808 1,137 1,631 182 1,484 1,427 1,436 183 1,764 1,456 1,14 184 0,806 1,477 1,641 185 5,383 1,134 1,049 186 1,902 1,597 1,391 187 1,519 1,161 1,155
No Rep1 Rep2 Rep3
Tabel I. lanjutan
No Rep1 Rep2 Rep3
226 1,452 1,14 1,407 227 1,592 1,435 1,807 228 5,408 1,829 1,802 229 1,422 1,67 1,439 230 1,363 1,616 1,438 231 0,642 1,698 1,47 232 1,603 5,273 1,479 233 1,458 1,183 1,81 234 1,093 1,176 1,69 235 1,445 1,829 1,708 236 1,446 1,714 1,67 237 5,408 1,183 0,81 238 1,692 1,258 1,132 239 1,673 1,438 1,588 240 1,439 1,186 1,296 241 1,296 1,636 1,803 242 1,435 1,321 1,429 243 1,925 1,439 1,595 244 1,287 1,582 5,356 245 1,664 1,469 1,426 246 1,119 1,685 1,63 247 1,721 1,292 1,696 248 1,447 5,32 1,776 249 1,866 1,148 1,446 250 1,666 1,456 1,55 251 1,139 1,475 1,803 252 1,416 5,385 1,42 253 1,831 1,152 1,479 254 1,199 1,137 1,441 255 1,437 1,845 1,513 256 1,144 1,718 1,312 257 1,635 1,334 1,168 258 0,815 1,139 1,419 259 1,813 1,651 1,612 260 1,527 0,718 1,14 261 1,094 1,59 5,432 262 1,461 1,811 1,481 263 1,184 1,084 1,589
No Rep1 Rep2 Rep3
264 1,132 1,343 1,148 265 1,673 1,162 1,086 266 1,427 1,439 1,447 267 1,233 1,701 1,573 268 1,147 1,674 1,425 269 0,747 1,804 5,249 270 1,679 1,141 1,817 271 1,166 1,144 1,491 272 1,683 1,258 1,137 273 1,384 1,474 1,972 274 5,449 1,217 1,45 275 1,408 1,933 0,852 276 5,416 1,147 1,192 277 1,679 1,462 0,798 278 1,139 1,462 1,945 279 5,341 1,685 1,479 280 1,485 1,637 1,13 281 1,141 1,888 1,693 282 1,385 1,959 1,175 283 1,821 1,609 1,787 284 1,711 1,595 1,425 285 1,68 1,892 1,135 286 1,144 1,133 1,265 287 1,925 1,147 1,146 288 1,236 1,907 5,438 289 1,155 0,884 1,693 290 1,142 1,389 1,139 291 0,795 1,594 1,421 292 5,419 1,455 5,343 293 1,181 1,979 0,711 294 1,815 5,471 1,439 295 1,071 1,713 1,465 296 5,422 1,404 1,821 297 1,078 1,719 5,4 298 1,7 5,421 1,773 299 0,803 1,763 1,754 300 1,454 2,015 1,135 301 1,814 1,807 1,904
No Rep1 Rep2 Rep3
Tabel I. lanjutan
No Rep1 Rep2 Rep3
340 1,685 1,466 0,772 341 0,813 1,436 0,804 342 5,445 5,418 1,349 343 1,668 1,506 5,425 344 1,807 1,505 1,146 345 1,533 1,644 1,67 346 1,557 1,143 1,407 347 1,808 1,268 1,71 348 1,924 5,397 1,582 349 1,686 1,144 1,441 350 1,455 1,144 1,725 351 1,13 1,46 1,07 352 1,885 1,137 1,444 353 1,722 1,901 1,627 354 1,643 5,434 1,914 355 1,156 1,469 1,149 356 1,465 1,418 0,871 357 5,459 1,633 0,766 358 1,835 0,802 1,824 359 1,247 1,498 1,666 360 1,145 1,458 1,693 361 1,12 1,511 1,909 362 1,144 1,434 1,39 363 1,455 1,646 1,174 364 1,248 1,435 1,828 365 1,773 1,378 1,321 366 1,281 5,417 1,81 367 1,169 1,146 1,837 368 1,415 1,139 1,6 369 0,83 1,461 1,234 370 1,694 1,142 1,439 371 1,934 1,593 1,682 372 5,412 1,14 1,128 373 1,139 1,812 1,437 374 1,769 0,753 1,184 375 1,159 1,381 1,614 376 1,69 1,433 1,935 377 5,482 1,894 1,636
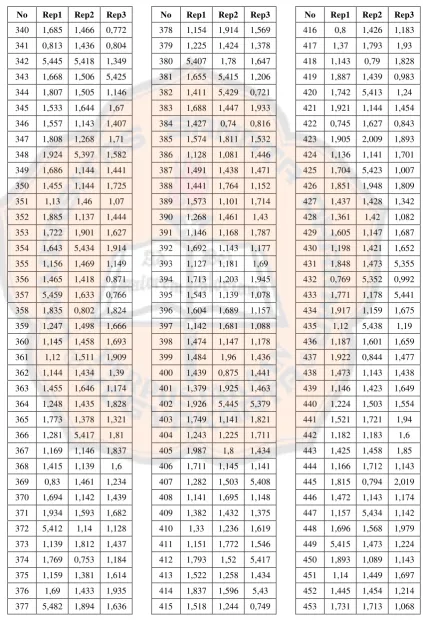
No Rep1 Rep2 Rep3
378 1,154 1,914 1,569 379 1,225 1,424 1,378 380 5,407 1,78 1,647 381 1,655 5,415 1,206 382 1,411 5,429 0,721 383 1,688 1,447 1,933 384 1,427 0,74 0,816 385 1,574 1,811 1,532 386 1,128 1,081 1,446 387 1,491 1,438 1,471 388 1,441 1,764 1,152 389 1,573 1,101 1,714 390 1,268 1,461 1,43 391 1,146 1,168 1,787 392 1,692 1,143 1,177 393 1,127 1,181 1,69 394 1,713 1,203 1,945 395 1,543 1,139 1,078 396 1,604 1,689 1,157 397 1,142 1,681 1,088 398 1,474 1,147 1,178 399 1,484 1,96 1,436 400 1,439 0,875 1,441 401 1,379 1,925 1,463 402 1,926 5,445 5,379 403 1,749 1,141 1,821 404 1,243 1,225 1,711 405 1,987 1,8 1,434 406 1,711 1,145 1,141 407 1,282 1,503 5,408 408 1,141 1,695 1,148 409 1,382 1,432 1,375 410 1,33 1,236 1,619 411 1,151 1,772 1,546 412 1,793 1,52 5,417 413 1,522 1,258 1,434 414 1,837 1,596 5,43 415 1,518 1,244 0,749
No Rep1 Rep2 Rep3
Tabel I. lanjutan
No Rep1 Rep2 Rep3
454 1,779 1,745 1,758 455 1,511 1,147 1,138 456 1,474 5,408 1,461 457 1,946 1,326 1,355 458 1,172 1,455 1,737 459 5,354 0,802 1,542 460 1,903 1,931 1,156 461 1,922 1,592 1,159 462 1,806 1,62 1,67 463 1,435 0,769 1,138 464 1,654 1,154 1,591 465 1,525 1,507 1,144 466 1,921 1,42 0,906 467 1,61 5,233 1,606 468 1,819 1,44 1,398 469 1,167 1,165 1,428 470 5,319 1,439 1,87 471 5,407 1,301 1,134 472 1,453 1,394 1,131 473 1,18 1,447 1,815 474 1,566 1,043 1,806 475 5,448 1,808 0,747 476 1,819 1,135 1,591 477 1,451 0,803 1,806 478 1,735 1,575 1,144 479 1,719 1,942 1,154 480 1,132 1,42 1,139 481 1,047 1,952 2,048 482 1,447 1,479 1,446 483 1,437 1,951 0,786 484 1,898 1,419 5,347 485 1,704 1,875 1,59 486 1,126 1,133 1,49 487 1,145 1,139 1,145 488 2,049 1,176 1,167 489 1,91 1,705 1,152 490 0,772 1,738 1,472 491 1,567 1,081 1,976
No Rep1 Rep2 Rep3
492 1,658 1,697 1,689 493 1,477 1,44 0,977 494 1,744 1,712 1,811 495 5,398 1,445 1,59 496 0,798 1,139 0,788 497 1,129 1,147 1,142 498 1,321 1,402 1,413 499 1,806 5,446 1,706 500 1,702 1,589 0,907 501 1,547 1,72 1,594 502 1,154 1,705 1,416 503 1,606 1,45 0,753 504 1,146 1,763 0,874 505 1,085 1,703 1,104 506 1,813 1,137 1,723 507 0,676 1,64 1,681 508 1,63 1,588 1,587 509 1,203 1,614 1,127 510 1,809 1,462 1,7 511 1,079 1,438 1,139 512 1,471 5,407 0,806 513 1,806 1,807 1,427 514 1,225 1,122 1,436 515 1,433 1,857 1,712 516 1,436 1,109 1,771 517 1,694 1,341 1,439 518 1,799 1,438 1,664 519 1,147 1,869 1,441 520 1,425 1,711 1,666 521 1,581 1,834 1,552 522 1,519 1,663 5,336 523 1,452 1,138 1,526 524 0,789 1,525 1,068 525 1,481 1,91 1,141 526 5,38 0,746 1,908 527 1,496 1,439 1,595 528 1,901 1,138 1,565 529 1,845 1,217 1,457
No Rep1 Rep2 Rep3
Tabel I. lanjutan
No Rep1 Rep2 Rep3
568 1,723 1,555 1,661 569 1,521 1,191 1,184 570 1,658 1,881 1,441 571 1,433 0,748 1,45 572 1,453 1,144 1,141 573 1,418 1,499 0,936 574 1,509 1,558 1,901 575 1,134 1,93 1,434 576 1,15 0,755 1,176 577 1,684 1,151 1,812 578 0,964 1,804 1,44 579 1,173 1,17 5,438 580 1,841 1,141 1,156 581 1,958 1,177 2,15 582 1,642 1,595 1,648 583 1,959 1,789 1,515 584 1,17 1,431 1,171 585 1,448 1,561 1,157 586 1,458 1,139 1,961 587 5,45 1,145 1,172 588 1,521 1,506 1,204 589 1,49 1,181 1,197 590 1,217 1,199 1,018 591 1,833 0,72 1,66 592 1,178 1,136 1,189 593 1,81 1,726 1,423 594 1,162 1,4 1,43 595 0,842 1,676 1,457 596 1,151 1,439 1,413 597 5,384 5,445 1,474 598 1,461 1,34 1,695 599 1,482 1,773 1,671 600 1,837 1,141 1,566 601 1,835 1,395 1,902 602 1,435 1,731 1,422 603 1,184 1,183 1,146 604 1,597 1,925 1,125 605 1,369 1,686 1,308
No Rep1 Rep2 Rep3
606 1,313 1,854 1,187 607 1,206 1,605 1,125 608 1,584 1,303 1,563 609 1,514 1,861 1,817 610 1,595 1,139 5,412 611 1,643 1,139 1,439 612 1,14 1,611 1,422 613 1,692 1,696 1,425 614 5,411 1,437 1,143 615 1,441 1,241 1,809 616 5,417 0,789 1,843 617 5,429 1,485 1,148 618 1,456 1,962 1,393 619 1,666 1,412 1,299 620 1,504 0,823 1,673 621 1,509 1,561 1,173 622 0,796 2,086 1,692 623 1,441 0,76 1,825 624 1,439 0,747 1,512 625 1,716 1,933 1,144 626 1,855 1,134 1,905 627 1,14 1,887 1,173 628 1,25 1,439 0,769 629 1,64 5,303 1,822 630 1,668 1,592 1,42 631 1,811 1,246 1,147 632 5,349 1,135 1,138 633 1,732 5,409 5,428 634 1,471 1,493 0,774 635 1,155 1,807 1,443 636 1,917 1,525 1,815 637 0,772 1,092 1,418 638 5,423 1,918 1,331 639 1,159 1,595 1,596 640 5,416 1,838 1,663 641 1,484 1,721 1,183 642 1,366 1,287 0,911 643 1,142 1,942 5,438
No Rep1 Rep2 Rep3
Tabel I. lanjutan
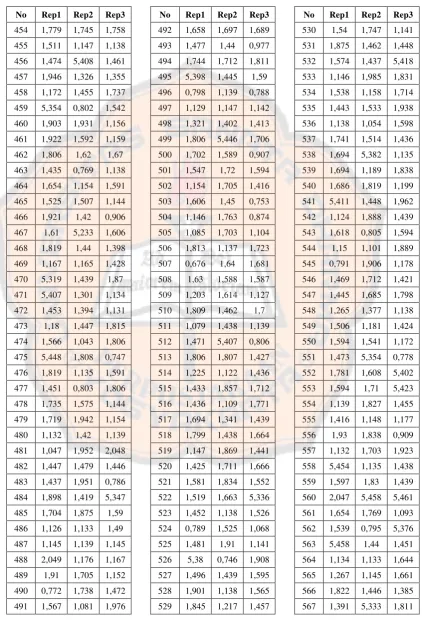
No Rep1 Rep2 Rep3
682 1,423 1,458 1,597 683 1,242 1,926 1,913 684 1,594 1,871 1,208 685 1,133 1,347 1,139 686 1,129 1,459 1,12 687 1,714 5,431 1,173 688 1,679 1,445 1,628 689 1,432 1,797 1,786 690 1,545 0,982 1,141 691 1,681 1,074 1,162 692 1,176 1,141 1,192 693 1,169 1,513 1,138 694 5,306 1,608 1,845 695 1,697 1,46 1,54 696 5,445 1,423 1,12 697 1,293 1,943 1,162 698 1,95 1,356 5,458 699 1,525 1,75 1,812 700 1,86 1,491 1,146 701 1,439 1,471 1,839 702 1,262 1,578 1,572 703 1,208 0,709 1,197 704 1,153 1,689 1,89 705 5,343 1,605 1,137 706 1,461 1,677 1,56 707 1,779 5,439 2,048 708 1,838 1,606 1,489 709 1,429 1,341 2,008 710 1,826 0,789 1,592 711 1,807 1,14 5,416 712 1,306 5,386 1,128 713 1,426 1,805 1,143 714 1,992 1,435 1,209 715 1,791 1,715 1,151 716 1,795 1,808 1,141 717 1,894 5,393 1,709 718 1,729 1,911 1,82 719 1,151 0,768 1,481
No Rep1 Rep2 Rep3
720 0,797 1,191 1,16 721 5,422 1,792 1,912 722 1,762 1,415 1,515 723 1,438 1,594 1,146 724 1,475 1,424 1,923 725 1,229 1,139 1,45 726 1,645 1,799 1,438 727 1,582 0,764 1,337 728 1,395 1,348 1,157 729 1,595 1,608 1,146 730 1,598 1,354 1,807 731 1,772 1,547 1,93 732 5,392 1,644 1,175 733 1,502 0,771 1,688 734 1,699 1,145 1,435 735 1,41 1,903 1,155 736 1,608 0,875 1,39 737 1,396 1,436 1,169 738 1,834 1,708 1,14 739 1,228 1,563 1,863 740 1,182 1,179 1,151 741 0,848 1,14 1,608 742 1,438 1,879 1,824 743 0,976 1,374 1,167 744 1,162 1,47 1,903 745 1,14 1,69 1,438 746 1,33 1,219 1,262 747 1,086 1,433 1,493 748 1,149 1,752 1,136 749 1,46 5,439 1,12 750 5,316 1,142 1,58 751 1,305 1,807 1,662 752 1,814 1,793 1,14 753 1,439 1,718 1,71 754 1,576 1,105 5,376 755 1,176 1,167 1,709 756 1,166 1,889 1,977 757 5,429 1,926 1,743
No Rep1 Rep2 Rep3
Tabel I. lanjutan
No Rep1 Rep2 Rep3
796 5,436 1,825 1,699 797 1,815 1,899 1,648 798 1,163 1,538 1,181 799 1,6 1,204 1,838 800 1,891 1,815 1,464 801 1,726 0,76 1,696 802 1,416 0,613 1,467 803 1,183 1,694 1,478 804 1,175 1,145 1,143 805 0,863 0,766 5,348 806 1,889 1,532 1,703 807 1,132 1,144 1,897 808 1,639 1,606 1,174 809 5,237 1,454 1,136 810 0,797 1,823 1,141 811 1,93 1,821 1,4 812 1,584 1,141 1,466 813 1,451 1,435 1,139 814 1,635 1,439 1,601 815 1,437 5,27 1,899 816 1,685 1,084 1,417 817 1,591 1,436 1,639 818 0,875 1,7 1,163 819 1,369 1,169 1,721 820 1,852 1,181 1,695 821 1,692 1,418 1,144 822 1,168 1,15 1,409 823 5,41 1,429 1,687 824 1,457 1,473 1,101 825 1,847 1,415 1,146 826 1,143 1,113 1,178 827 2,001 1,926 1,474 828 1,128 1,143 5,455 829 1,127 1,806 1,555 830 1,158 1,707 1,368 831 1,907 1,453 1,144 832 1,314 1,868 1,142 833 1,239 1,438 1,439
No Rep1 Rep2 Rep3
834 1,15 1,228 1,795 835 1,584 1,142 1,438 836 0,822 1,523 1,139 837 1,423 5,247 1,14 838 5,437 1,705 1,596 839 5,406 1,428 1,432 840 1,53 1,138 5,347 841 1,156 1,065 1,878 842 1,812 1,146 1,456 843 1,21 1,137 1,144 844 1,488 1,394 1,646 845 1,824 5,438 1,155 846 1,809 5,398 1,438 847 1,986 5,327 1,438 848 0,793 1,446 1,193 849 1,895 2,03 1,612 850 5,426 1,687 1,802 851 1,137 1,887 1,497 852 1,937 1,125 1,908 853 1,483 1,181 1,186 854 0,806 1,436 1,537 855 1,732 0,869 1,903 856 5,412 1,864 1,139 857 1,491 1,918 1,145 858 1,673 1,432 1,909 859 1,375 1,916 1,887 860 1,14 0,903 5,252 861 1,829 1,461 1,508 862 1,634 1,265 1,463 863 5,3 1,897 1,139 864 0,768 0,913 1,378 865 1,898 5,416 1,655 866 5,406 1,164 1,257 867 0,788 1,181 1,976 868 1,681 1,131 1,902 869 1,503 1,794 1,143 870 1,454 1,592 5,295 871 1,44 1,437 1,139
No Rep1 Rep2 Rep3
Tabel I. lanjutan
No Rep1 Rep2 Rep3
910 1,922 1,374 1,784 911 1,663 1,796 1,148 912 1,146 5,439 1,139 913 1,095 1,465 1,63 914 1,822 1,456 1,594 915 1,903 1,185 1,055 916 2,012 1,78 1,138 917 1,826 0,703 1,817 918 1,778 1,279 1,813 919 5,256 1,136 1,652 920 1,448 0,816 1,922 921 1,646 1,805 1,873 922 1,471 1,957 1,113 923 1,145 1,633 1,163 924 1,214 0,81 1,182 925 2,05 1,13 1,095 926 1,696 1,238 0,797 927 1,629 1,157 1,103 928 5,363 1,41 1,771 929 1,341 1,786 1,146 930 1,169 1,143 1,053 931 1,195 1,142 1,37 932 1,902 1,908 1,442 933 1,71 5,471 1,584 934 1,443 1,51 1,431 935 5,382 1,485 1,471 936 1,57 1,188 1,391 937 1,812 1,763 1,562 938 1,516 0,968 1,188 939 1,485 1,218 1,139 940 5,37 1,449 1,135 941 1,242 1,871 5,392 942 1,141 1,542 1,591
No Rep1 Rep2 Rep3
943 1,496 1,145 1,689 944 1,915 1,163 1,137 945 1,814 1,676 1,442 946 1,157 1,547 1,81 947 1,136 1,175 1,239 948 1,56 1,452 1,637 949 1,952 5,42 1,419 950 1,208 1,69 1,897 951 1,147 1,683 1,686 952 1,613 5,43 1,818 953 1,592 1,186 1,605 954 1,465 1,431 1,438 955 1,483 1,949 1,614 956 0,848 1,439 1,807 957 1,513 1,191 0,842 958 1,564 1,592 5,465 959 5,311 1,169 1,714 960 1,606 1,907 1,66 961 1,69 1,144 1,809 962 1,882 5,427 1,195 963 1,896 1,546 1,701 964 1,083 1,438 1,529 965 1,781 0,728 5,389 966 1,235 1,182 1,182 967 1,298 5,446 1,145 968 1,141 1,147 1,44 969 1,137 1,453 1,592 970 1,93 1,142 5,402 971 1,907 1,393 1,693 972 1,266 1,559 1,44 973 1,553 1,14 1,84 974 1,218 1,755 1,768 975 1,152 1,189 1,372
No Rep1 Rep2 Rep3
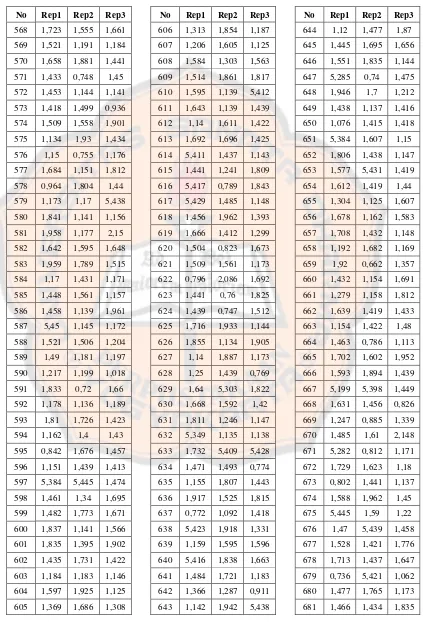
976 1,162 1,345 1,873 977 1,695 5,396 5,421 978 1,148 5,278 1,141 979 1,429 1,36 1,824 980 1,379 1,396 1,74 981 1,812 1,908 1,849 982 1,696 1,805 1,702 983 1,815 1,438 1,235 984 1,423 1,895 1,445 985 2,015 1,665 1,432 986 5,421 1,438 1,542 987 1,463 1,141 5,427 988 1,739 1,72 1,194 989 1,198 1,141 1,542 990 1,778 1,59