BAB V
HUBUNGAN FILOGENETIK Pyricularia PADA RUMPUT DAN PADI Abstrak
Pyricularia grisea Sacc. [anamorf Magnaporthe grisea (Hebert) Barr]
sebagai penyebab penyakit blas pada rumput Digitaria spp. dipisahkan dari Pyricularia oryzae Cav. (anamorf dari Magnaporthe oryzae B. Couch) penyebab
blas pada padi dan anggota serealia lainnya melalui pendekatan molekuler. Penelitian ini bertujuan menganalisis hubungan filogenetik Pyricularia dari
rumput (d4 dari Digitaria ciliaris dan pr10.a.S4 dari Panicum repens) dengan Pyricularia dari padi (ok6 dan ou6.S4) berdasarkan sekuen ITS beserta 5.8S
rDNA. Hasil amplifikasi daerah ITS beserta 5.8S rDNA berukuran 543 pb pada d4, pr10.a.S4, ok6, dan ou6.S4. Pyricularia d4, ok6, dan ou6.S4 memiliki
kesamaan sekuen 100%. Sebaliknya, pr10.a.S4 terhadap ketiga isolat tersebut di atas berbeda satu nukleotida pada 5.8S rDNA dan lima nukleotida pada bagian hulu 26S rDNA. Isolat d4 dan pr10.a.S4 berasal dari rumput memiliki hubungan filogenetik sangat dekat dengan P. oryzae dari padi, baik dengan ok6 maupun
ou6.S4. Sekuen ITS beserta 5.8S rDNA tidak dapat digunakan untuk memisahkan semua Pyricularia yang dianalisis dalam penelitian ini. Berdasarkan prioritas
maka d4 dan pr10.a.S4 sebagai P. grisea. Sedangkan ok6 dan ou6.S4 berdasarkan
kesamaan sekuen ITS beserta 5.8S rDNAnya sementara juga dinamakan P. grisea.
Kata kunci: Pyricularia grisea, Digitaria ciliaris, Panicum repens, padi, ITS, 5.8S
rDNA.
Pendahuluan
Pyricularia merupakan cendawan penyebab penyakit blas pada padi dan
anggota Graminae lainnya dengan kisaran inangnya sekitar 50 spesies (Ou 1985).
Pyricularia grisea memiliki morfologi yang serupa, tidak dapat dibedakan dengan Pyricularia oryzae yang telah dikenal sebagai penyebab penyakit blas pada padi
(Yaegashi & Udagawa 1978; Rossman et al. 1990, Couch dan Kohn 2002). Pyricularia grisea adalah penyebab penyakit blas pada rumput Digitaria sanguinalis (Ou 1985), Digitaria horizontalis dari Brazil, Digitaria smutzi dari
Jepang, Digitaria sp. dari USA dan Cina dengan Magnaporthe grisea sebagai
teleomorfnya (Couch dan Kohn 2002).
Peritesium M. grisea dapat dibentuk oleh dua isolat anamorf serasi yang
diperoleh dari sumber bercak blas yang sama pada padi (Hayashi et al. 1997).
Teleomorf ini hanya dibentuk di laboratorium, sedangkan persilangan anamorf dari padi dengan anamorf dari D. sanguinalis tidak menghasilkan peritesium.
menempatkan spesies ini sebagai nama spesies yang berbeda. Teleomorf P. oryzae adalah Magnaporthe oryzae B. Couch dan M. oryzae ditempatkan sebagai
anggota spesies M. grisea spesies kompleks (Couch & Kohn 2002). Peritesium
dapat dibentuk secara in vitro dan in planta pada persilangan antara anamorf dari
padi, tetapi tidak pernah ditemukan di lapang (Silue & Notteghem 1990, Hayashi
et al. 1997).
Pengenalan spesies filogenetik (phylogenetic species recognition=PSR,
Taylor et al. 2000) berdasarkan pendekatan molekuler dapat memisahkan
spesimen cendawan blas dari padi dengan spesimen cendawan blas dari Digitaria ciliaris di Filipina (Borromeo et al. 1993) atau dari D. sanguinalis (Couch &
Kohn 2002). Masing-masing spesimen berturut-turut diidentifikasi sebagai P. oryzae dan P. grisea. PSR memperjelas taksonomi genus dan merupakan alat kuat
untuk pembatasan spesies cendawan (Balajee et al. 2009).
Pendekatan molekuler multilokus (ITS-rDNA, actin, β-tubulin, dan calmodulin) menunjukkan bahwa P. grisea adalah spesies cryptic, dan
berkembang melalui spesiasi yang terus menerus (Hirata et al. 2007). Pemisahan
secara molekuler didukung oleh penelitian tentang kisaran inang. Di Filipina, isolat-isolat Pyricularia bersifat spesifik inang, isolat dari padi tidak mampu
menginfeksi D. ciliaris (Mackill & Bonman 1986), begitu juga tidak terjadi
infeksi silang oleh isolat dari padi ke D. sanguinalis atau sebaliknya (Kato et al.
2000). Kebanyakan spesimen Pyricularia dari padi selalu berbeda dari Pyricularia dari rumput yang tumbuh di dekat padi maupun dari populasi isolat
dari rumput di tempat berbeda (Borromeo et al. 1993). Sebaliknya, pendekatan
molekuler multilokus (ITS-rDNA, actin, β-tubulin, dan calmodulin) menunjukkan bahwa P. grisea dan P. oryzae adalah kelompok monofiletik (Hirata et al. 2007).
Gen rRNA merupakan kandidat yang baik untuk studi hubungan filogenetik (Guarro et al. 1999), karena merupakan gen penyandi non-protein
yang mempunyai banyak salinan dalam genom (White et al. 1990, Guarro et al.
1999), dan membuat homogen melalui evolusi dan hampir selalu diperlakukan sebagai gen dengan lokus tunggal (Guarro et al. 1999). Bagian molekul yang
sangat konservatif ini menyediakan sebagai referensi studi perbedaan evolusioner (Guarro et al. 1999). Diantara gen yang konservatif tersebut terdapat internal
transcribed spacer (ITS) yang tidak konservatif, dapat bervariasi (White et al.
1990, Guarro et al. 1999). Analisis filogenetik interspesies atau tingkat takson
yang lebih tinggi umumnya menggunakan sekuen gen rRNA, termasuk daerah ITS1 dan ITS2, intergenic spacer (IGS), 5.8S rRNA, 18S rRNA, dan 26S rRNA.
Gen rRNA sangat konservatif dalam satu spesies, tetapi dapat juga sangat bervariasi di antara spesies (Summerbel et al. 2005). Variasi situs enzim restriksi
juga ditemukan dalam anggota populasi, seperti mutasi yang berulang-ulang pada situs enzim restriksi EcoRI dalam IGS dari rDNA (Capossela et al. 1992).
Studi sekuen rDNA memiliki dampak sistematik paling besar sampai saat ini, yaitu dapat membedakan sampai tingkat strain, dan untuk mengelompokkan organisme yang morfologinya hanya memberikan sedikit informasi, misalnya organisme uniseluler (Hillis & Dixon 1991). Beberapa metode molekuler telah digunakan untuk mengetahui hubungan evolusioner, namun sekuen nukleotida paling banyak digunakan daripada metode molekuler lainnya, karena perbedaan atau tingkat kesamaannya dapat dinyatakan dengan tepat. Selain itu, data yang diperoleh juga akan membentuk database untuk rujukan berikutnya (Summerbel et al. 2005).
Pada penelitian ini, Pyricularia dapat ditemukan pada rumput D. ciliaris
di sekitar percobaan padi yang sedang terserang penyakit blas secara alami.
Pyricularia juga selalu ditemukan sepanjang waktu pada Panicum repens di
sawah Sukabumi yang merupakan daerah endemik blas (Bustaman & Mahrup 2004). Hubungan filogenetik antara Pyricularia dari kedua inang yang berada di
Jawa Barat belum diketahui. Oleh karena itu penelitian ini bertujuan untuk menganalisis hubungan filogenetik antara cendawan blas dari rumput D. ciliaris
dan Panicum repens terhadap cendawan blas dari padi yang tumbuh berdekatan
melalui sekuen ITS beserta 5.8S rDNA. Penelitian ini diharapkan mendapatkan informasi khususnya hubungan filogenetik antara Pyricularia dari rumput D. ciliaris dengan tanaman padi yang secara tiba-tiba terserang penyakit blas di
ladang percobaan dan kaitannya dengan penamaan spesies patogennya, serta hubungan filogenetik Pyricularia dari Panicum repens dan padi di sawah
Bahan dan Metode
Tempat. Penelitian dilaksanakan di Laboratorium Genetika Cendawan dan Biorin di Pusat Penelitian Sumberdaya Hayati dan Bioteknologi (PPSHB) IPB.
Kultur Cendawan. Semua isolat yang dianalisis berasal dari kultur konidium tunggal hasil penelitian sebelumnya (Bab 3), terdiri atas lima isolat cendawan blas, yaitu Pyricularia d4 dan ok6, masing-masing berasal dari daun
rumput D. ciliaris. dan daun padi var. Kencana bali yang berada pada lokasi
(ladang di Jasinga Bogor) dan waktu yang sama (September 2005). Isolat lainnya adalah Pyricularia pr10.a.S4 dan ou6.S4, masing-masing berasal dari daun
rumput Panicum repens dan daun padi (varietas tidak diketahui) yang diperoleh
dari lokasi (sawah di Sukabumi) dan waktu yang sama (Mei 2008). Semua isolat disimpan pada medium Potato Dextrosa Agar (Difco).
Isolasi DNA. DNA genom cendawan diisolasi dari miselium yang ditumbuhkan pada 25 mL medium cair (5 g L-1 sukrosa, 2 g L-1 ekstrak khamir, dan 2 g L-1 pepton, modifikasi Crawford et al. 1986) selama enam hari pada mesin
pengocok. Miselium dipanen dan diisolasi genomnya menurut prosedur yang dijelaskan oleh Raeder dan Broda (1985) pada volume lebih besar dan sedikit modifikasi. Miselium digerus dalam mortar steril sampai berbentuk pasta. Pasta disuspensikan dalam 4 mL larutan penyangga ekstrak (200 mM Tris HCl pH 8.5; 250 mM NaCl; 25 mM EDTA; 0.5% SDS). Sebanyak 2.8 mL fenol dan 1.2 mL campuran kloroform dan isoamil alkohol (CIA=24:1) ditambahkan ke dalam suspensi dan suspensi dibolak-balik secara perlahan. Suspensi disentrifugasi selama 30 menit pada 4,000 rpm dengan suhu 6 °C. Fase cairan bagian atas segera dipindahkan ke tabung baru dan dipresipitasi dengan menambahkan 1x volume isopropanol dingin. Hasil presipitasi disentrifugasi selama 20 menit pada 4,000 rpm dengan suhu 6 °C. Endapan dibilas menggunakan etanol dingin konsentrasi 70% dan disentrifugasi kembali selama 10 menit. Endapan dikeringkan menggunakan pompa vakum selama 15 menit, dan dilarutkan dalam 100 uL TE 1x (10 mm Tris HCl pH 8, 1 mmol EDTA), serta ditambahkan 0.2x volume RNAse 20 mg mL-1. Larutan diinkubasi semalam pada 37 °C, kemudian ditambahkan 900 uL TE 1x dan larutan diekstrak kembali melalui penambahan 1x
volume CIA, dan disentrifugasi selama 10 menit pada 4,000 rpm dengan suhu 6 °C. Cairan bagian atas dipresipitasikan kembali melalui penambahan isopropanol dingin seperti tahapan sebelumnya sampai diperoleh endapan yang dilarutkan dalam 100 uL TE 1x. DNA yang dianalisis memiliki tingkat kemurnian (A260/A280) 1.6-1.9.
DNA cendawan hasil isolasi diamplifikasi melalui PCR dengan menggunakan sepasang primer yang telah digunakan pada penelitian sebelumnya (Bab 4), yaitu its1 dan its4 (White et al. 1990), dengan susunan nukleotida sebagai
berikut: its1: F:5’TCCGTAGGTGAACCTGCGG 3’ its4: R:5 TCCTCCGCTTATTGATATGC 3’
Organisasi ITS berdasarkan data GeneBank dengan nomor akses AB026819 (Sone et al. 2000) disajikan pada Gambar 12. Primer its1 menempel di ujung 3’ gen 18S
rDNA pada nukleotida posisi 2162-2180 dan primer its4 menempel pada ujung 5’ gen 26S rDNA pada nukleotida posisi 2685-2704.
Total reaksi PCR sebanyak 40 μL, mengandung sekitar 200 ng DNA genom cetakan; 20 μL 2xPCR master mix (0.05 unit μL-1 Taq DNA polymerase, 4 mM MgCl, 0.4 mM masing-masing dNTP), dan 1.2 ρmol masing-masing primer. Program PCR meliputi pradenaturasi pada suhu 95 °C selama lima menit, dilanjutkan 30 siklus pada suhu 95 °C selama 30 detik, suhu pelekatan (annealing) primer 52 °C selama satu menit. Progam selanjutnya adalah
pemanjangan (elongation) pada suhu 72 °C selama dua menit. Tahap akhir proses
PCR pada suhu 72 °C selama lima menit, dan pendinginan 20°C selama 10 menit. Untuk mengetahui keberhasilan proses PCR maka produk PCR divisualisasi melalui elektroforesis pada gel agarosa 1% (w/v) dalam TAE 1x, dan dilanjutkan perendaman gel dalam 0.5 μg mL-1 etidium bromida. Produk PCR dikirim ke PT Genetika Science Indonesia sebagai institusi penerima jasa layanan sequencing. Konstruksi pohon filogenetik
Sekuen nukleotida berdasarkan primer its1 dan primer its4 disejajarkan kemudian diedit menggunakan piranti lunak Bioedit dengan mengacu pada kromatogramnya. Selanjunya keseluruhan sekuen nukleotida d4 sebagai perwakilan sampel dianalisis lebih lanjut dengan mencari kesamaannya menggunakan program basic local alignment search tool (BLAST) di
http://blast.ncbi.nlm.nih.gov. Sekuen hasil BLAST dipilih hanya pada nomor akses yang telah dipublikasi. Sekuen yang digunakan untuk mengkonstruksi filogram dibatasi, yaitu hanya sekuen ITS1, 5.8S rDNA, dan ITS2. Filogram dibuat dengan bantuan piranti lunak ClustalX dan program Phylogenetic Analysis Using Parsimony (PAUP) version 4.0b10 for 32-bit Microsoft Windows
(Swofford 2002). Filogram dikonstruksi melalui distance pada metode heuristic.
Untuk mengetahui tingkat kepercayaan setiap percabangan dilakukan bootstrap
1000 kali.
Hasil
Hasil amplifikasi dengan menggunakan primer its1 dan its4 pada 4 isolat (d4, pr10.a.S4, ok6, dan ou6.S4) diperoleh sekuen DNA berukuran 543 pb. Sekuen tersebut terdiri atas bagian hilir 18S rDNA berukuran 30 pb, bagian ITS1 berukuran 123 pb, bagian 5.8S rDNA berukuran 158 pb, bagian ITS2 berukuran 172 pb, dan bagian hulu 26S rDNA berukuran 60 pb (Gambar 24). Sekuen ITS1 dan 5.8S rDNA pada tiga isolat (d4, ok6, dan ou6.S4) ialah sama. Sebaliknya sekuen pr10.a.S4 berbeda enam nukleotida terhadap d4, atau ok6, atau ou6.S4. Perbedaan tersebut berada pada bagian 5.8S rDNA sebanyak satu nukleotida dan pada bagian hulu 26S rDNA sebanyak lima nukleotida (Gambar 24).
Hasil BLAST keseluruhan sekuen hasil amplifikasi primer its1 dan its4 dari Pyricularia d4 (sekuen sama dengan ok6, ataupun ou6.S4) umumnya
memiliki kesamaan 99% (e-value 0 dan query coverage 100%) dengan cendawan
penyebab penyakit blas pada padi, Eleusine coracana, Setaria italica, Stenotaphrum secundatum, dan Festuca arundinacea. Cendawan pada
masing-masing inang tersebut di data GeneBank memiliki nama M. oryzae dan M. grisea.
Berdasarkan Couch dan Kohn (2002) maka beberapa nomor akses yang bernama
M. grisea dinyatakan sebagai M. oryzae.
Pyricularia d4 memiliki kesamaan 100% (e-value 0 dan query coverage
100%) dengan M. oryzae Ken54-20 (AB274418, Hirata et al. 2007) pada padi dari
Jepang (Tabel 15). Sedangkan tingkat kesamaan d4 dengan cendawan blas asal padi Indonesia (AB274421, Hirata et al. 2007) sebesar 99% (e-value 0 dan query coverage 100%). Tingkat kesamaan dari keseluruhan sekuen d4 (hasil amplifikasi
1 90 d4=ok6=ou6.S4 tccgtaggtgaacctgcggAGGGATCATTA CTGAGTTGAAAAACTCCAACCCCTGTGAACATAACCTCTGTCGTTGCTTCGGCGGGCACG pr10.a.S4 tccgtaggtgaacctgcggAGGGATCATTACTGAGTTGAAAAACTCCAACCCCTGTGAACATAACCTCTGTCGTTGCTTCGGCGGGCACG
primer its1 91 180 d4=ok6=ou6.S4 CCCGCCGGAGGTTCAAAACTCTTATTTTTTCCAGTATCTCTGAGCCTGAAAGACAAATAATCA
AAACTTTCAACAACGGATCTCTTGGTT pr10.a.S4 CCCGCCGGAGGTTCAAAACTCTTATTTTTTCCAGTATCTCTGAGCCTGAAAGACAAATAATCA AAACTTTCAACAACGGATCTCTTGGTT 181 270 d4=ok6=ou6.S4 CTGGCATCGATGAAGAACGCAGCGAAATGCGATAAGTAATGTGAATTGCAGAATTCAGTGAATCATCGAATCTTTGAACGCA C ATTGCGC pr10.a.S4 CTGGCATCGATGAAGAACGCAGCGAAATGCGATAAGTAATGTGAATTGCAGAATTCAGTGAATCATCGAATCTTTGAACGCA G ATTGCGC 271 360 d4=ok6=ou6.S4 CCGCCGGTATTCCGGCGGGCATGCCTGTTCGAGCGTCATTT CAACCCTCAAGCCTCGGCTTGGTGTTGGGGCGCCCGGGCCCTCCGCGGC pr10.a.S4 CCGCCGGTATTCCGGCGGGCATGCCTGTTCGAGCGTCATTT CAACCCTCAAGCCTCGGCTTGGTGTTGGGGCGCCCGGGCCCTCCGCGGC 361 450 d4=ok6=ou6.S4 CCGGGGCCCCCAAGTTCATCGGCGGGCTCGTCGGTACACTGAGCGCAGTAAAACGCGGTAAAACGCGAACCTCGTTCGGATCGTCCCGGC pr10.a.S4 CCGGGGCCCCCAAGTTCATCGGCGGGCTCGTCGGTACACTGAGCGCAGTAAAACGCGGTAAAACGCGAACCTCGTTCGGATCGTCCCGGC 451 543 d4=ok6=ou6.S4 GTGCTCCAGCCGCTAAACCCCCAATTTTTTAA AGGTTGACCTCGGATCAGGTAGGAATACCCGCTGAACTTAA gcatatcaataagcggagga pr10.a.S4 GTGCTCCAGCCGCTAAACCCCCAATTTTTTAAAGGTTGACATCGGATCAAGTAAGAATACCCGCGAAACTTAAgcatatcaataagcggagga
primer its4 Gambar
24 Seku en nu kleotida ba g ian hilir 18 S rDNA, d ae rah IT S b eserta 5.8S rDN A , d an ba g ian hulu 26S rD N A pada Py ricularia dari D . c iliaris (d4 ), P . re p ens (p r10.a. S 4 ) dan p adi ( ok6, ou6.S4 ). Ket: __: bag
ian hilir 18S rDNA,
merah : 5.8S rDNA, italik : bag ian h ulu 26S rDNA, : I T S2 , : I T S1, : variasi nukleotida
sanguinalis hanya 95%, (e-value 0 dan query coverage 97%), dan pada D. horizontalis sebesar 93% (e-value 0 dan query coverage 97%).
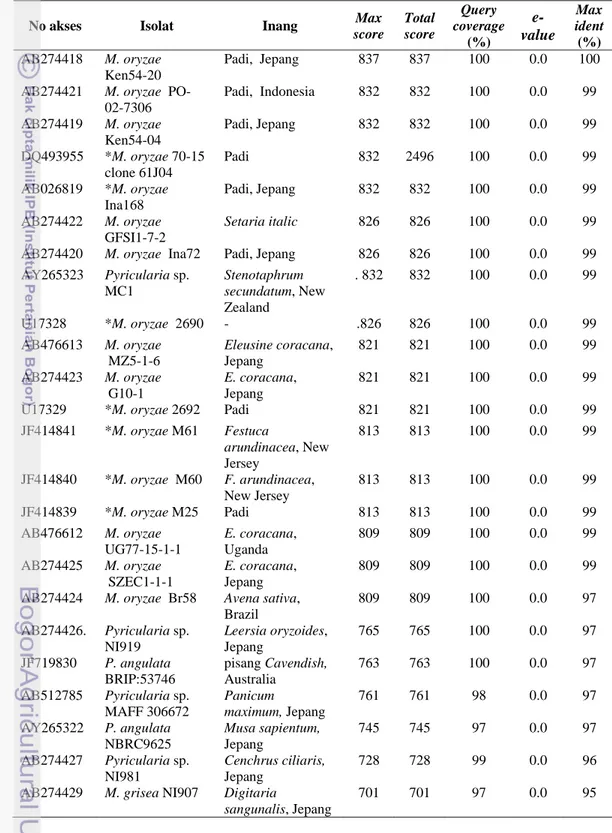
Tabel 15 Hasil BLAST sekuen ITS beserta 5.8S rDNA (hasil amplifikasi primer universal its1 dan its4) Pyricularia d4 asal rumput Digitaria ciliaris No akses Isolat Inang Max
score Total score Query coverage (%) e- value Max ident (%) AB274418 M. oryzae Ken54-20 Padi, Jepang 837 837 100 0.0 100
AB274421 M. oryzae PO-
02-7306 Padi, Indonesia 832 832 100 0.0 99 AB274419 M. oryzae Ken54-04 Padi, Jepang 832 832 100 0.0 99 DQ493955 *M. oryzae 70-15 clone 61J04 Padi 832 2496 100 0.0 99 AB026819 *M. oryzae Ina168 Padi, Jepang 832 832 100 0.0 99 AB274422 M. oryzae GFSI1-7-2 Setaria italic 826 826 100 0.0 99
AB274420 M. oryzae Ina72 Padi, Jepang 826 826 100 0.0 99
AY265323 Pyricularia sp. MC1 Stenotaphrum secundatum, New Zealand . 832 832 100 0.0 99 U17328 *M. oryzae 2690 - .826 826 100 0.0 99 AB476613 M. oryzae MZ5-1-6 Eleusine coracana, Jepang 821 821 100 0.0 99 AB274423 M. oryzae G10-1 E. coracana, Jepang 821 821 100 0.0 99
U17329 *M. oryzae 2692 Padi 821 821 100 0.0 99
JF414841 *M. oryzae M61 Festuca arundinacea, New Jersey 813 813 100 0.0 99 JF414840 *M. oryzae M60 F. arundinacea, New Jersey 813 813 100 0.0 99 JF414839 *M. oryzae M25 Padi 813 813 100 0.0 99 AB476612 M. oryzae UG77-15-1-1 E. coracana, Uganda 809 809 100 0.0 99 AB274425 M. oryzae SZEC1-1-1 E. coracana, Jepang 809 809 100 0.0 99
AB274424 M. oryzae Br58 Avena sativa,
Brazil 809 809 100 0.0 97 AB274426. Pyricularia sp. NI919 Leersia oryzoides, Jepang 765 765 100 0.0 97 JF719830 P. angulata BRIP:53746 pisang Cavendish, Australia 763 763 100 0.0 97 AB512785 Pyricularia sp. MAFF 306672 Panicum maximum, Jepang 761 761 98 0.0 97 AY265322 P. angulata NBRC9625 Musa sapientum, Jepang 745 745 97 0.0 97 AB274427 Pyricularia sp. NI981 Cenchrus ciliaris, Jepang 728 728 99 0.0 96
AB274429 M. grisea NI907 Digitaria
sangunalis, Jepang
Tabel 15 Hasil BLAST sekuen ITS beserta 5.8S rDNA (hasil amplifikasi primer universal its1 dan its4) Pyricularia d4 asal rumput Digitaria ciliaris (Lanjutan)
No akses Isolat Inang Max score Total score Query coverage (%) e-value Max ident (%) AY265324 Pyricularia sp. MC2 Digitaria sangunalis, New Zealand 697 697 97 0.0 95
AB274428 M. grisea Dig41 D. sangunalis,
Jepang
695 695 97 0.0 95
AB274430 M. grisea Br33 Digitaria
horizontalis, Brazil
660 660 97 0.0 93
Hubungan filogenetik keempat isolat pada penelitian ini (d4, ok6, pr10.a.S4, dan ou6.S4) serta sekuen dari beberapa nomor akses hasil BLAST terpilih (hanya pada nomor akses yang telah dipublikasi) ditampilkan sebagai
filogram. Pyricularia angulata digunakan sebagai outgroup pada filogram
(Gambar 25). Keempat isolat tersebut berada pada clade P. oryzae. Spesies
Pyricularia dari inang padi, Eleusine coracana, Setaria italica, Stenotaphrum
secundatum, dan Festuca arundinacea adalah kelompok monofiletik, dan
membentuk sister clade dengan spesies Pyricularia pada jenis inang D.
sanguinalis dan D. horizontalis yang bernama P. grisea.
Sekuen ITS beserta 5.8S rDNA dari Pyricularia asal rumput (d4 dan pr10.a.S4) pada penelitian ini tidak mampu memisahkannya dengan Pyricularia asal padi (ok6 dan ou6.S4) dari dua lokasi di Jawa Barat. Pada dua lokasi tersebut tampak terjadi infeksi silang antara Pyricularia asal rumput dan padi. Sebaliknya, secara filogenetik bahwa sekuen ITS beserta 5.8S rDNA nukleus pada Pyricularia
asal Digitaria sanguinalis dan Digitaria horizontalis mampu memisahkannya
terhadap Pyricularia asal padi dan Graminae yang bernilai ekonomi. Pemisahan
antara P. grisea dan P. oryzae yang membentuk sister clade tersebut sangat kuat karena nilai bootstrapnya 97%. Berdasarkan prioritas dalam hukum tata nama bahwa P. oryzae adalah sinonim P. grisea. Oleh karena itu khususnya Pyricularia yang berasal dari D. ciliaris ditempatkan sebagai P. grisea dengan teleomorfnya adalah M. grisea. Hal yang sama juga diterapkan pada pr10.a.S4, yaitu sebagai P. grisea, meskipun secara filogenetik isolat tersebut menempati clade P. oryzae.
*: nama spesies merujuk Couch dan Kohn (2002), pada nomor akses di National Center for
Pembahasan
Sekuen ITS beserta 5.8S rDNA dari d4 dan ok6 memiliki kesamaan 100%, sehingga posisinya pada clade yang sama, yaitu pada P. oryzae. Kedua sampel diperoleh pada lokasi dan waktu yang sama. Pada lokasi tersebut kemungkinan terjadi aliran genetik Pyricularia, namun tidak diketahui arah alirannya antara cendawan blas pada rumput D. ciliaris dan padi. Lokasi tersebut bukan area produksi padi, dan di sekitarnya tidak tampak area penanaman padi. Sebelum bulan September 2005 pada lokasi yang sama pernah digunakan sebagai
10-3 perbedaan 54 65 60 55 56 81 88 95 100 99 99 100 97 97 87
Gambar 25 Filogenetik berdasarkan sekuen ITS beserta 5.8S rDNA pada cendawan blas asal rumput dan padi yang tumbuh berdekatan pada dua lokasi di Jawa Barat terhadap data GeneBank. Nilai bootstrap 1000x yang lebih kecil dari 50% tidak ditunjukkan; * nama spesies merujuk Couch dan Kohn (2002), pada nomor akses di National Center for Biotechnology Information (NCBI) tertulis sebagai M. Grisea; : isolat pada penelitian ini.
tempat percobaan padi yang tidak berkaitan dengan penyakit blas (Trikoesoemaningtyas 2011, komunikasi pribadi). Diperkirakan bahwa inokulum awal pada lokasi kemungkinan terbawa benih padi yang ditanaman sebelum Agustus 2005. Inokulum kemudian mampu menginfeksi rumput tertentu di sekitar tanaman padi. Pada waktu ladang tidak sedang digunakan sebagai tempat percobaan, maka patogen blas bertahan di rumput-rumput sebagai inang alternatifnya. Selanjutnya patogen menginfeksi inang utamanya, yaitu padi rentan penyakit blas yang ditanam pada bulan Agustus 2005. Salah satu padi rentan tersebut adalah varietas Kencana bali.
Aliran genetik cendawan blas pada P. repens dan padi juga tampak pada
sawah di Sukabumi yang merupakan daerah endemik blas. Meskipun cendawan blas pada P. repens (pr10.a.S4) memiliki perbedaan lima nukleotida pada hilir
26S rDNAnya, dan satu nukleotida pada 5.8S rDNA dengan cendawan blas dari padi (ou6.S4) yang berada di sekitarnya. Keduanya tidak memiliki perbedaan pada daerah ITS. Variasi pada sekuen ITS dapat ditemukan pada anggota populasi cendawan (White et al. 1990). Hal ini menunjukkan bahwa dalam spesies sama
dapat memiliki variasi sekuen ITS, sehingga perbedaan beberapa nukleotida pada isolat-isolat dari rumput maupun padi dari lokasi berbeda masih dalam kisaran spesies yang sama. Variasi nukleotida tersebut karena ITS pada rDNA nukleus merupakan unit berulang (high copy number), sehingga kemungkinan terdapat
variasi sekuen ITS pada lokus yang berbeda, dan sekuen ITS tidak konservatif, paling cepat berubah (White et al. 1990). Sebaliknya pada anggota populasi
cendawan lain dapat ditemukan sangat sedikit (satu nukleotida) variasi sekuen ITS (Chen et al. 2001, Korabecná et al. 2003, Hinrikson et al. 2005).
Sekuen ITS beserta 5.8S rDNA tidak dapat memisahkan semua sampel, baik berasal dari rumput maupun padi yang digunakan pada penelitian ini. Oleh karena itu, data tersebut dapat digunakan untuk menyatakan bahwa P. grisea juga
dapat digunakan sebagai nama Pyricularia pada padi untuk sementara waktu
sampai data sekuen lokus actin, ß-tubulin, dan calmodulin diperoleh. Selain itu juga perlu menganalisis persilangan antara strain tersebut dengan isolat fertil yang hermaprodit asal padi untuk mendukung konsep spesies Biologi.
Hubungan filogenetik yang sangat dekat pada semua sampel pada penelitian ini menunjukkan bahwa ada aliran genetik Pyricularia antara pada
rumput dan padi, baik pada lokasi yang sama maupun berbeda. Sedangkan aliran genetik Pyricularia pada D. ciliaris (d4) terhadap ok6 pada lokasi dan waktu yang
sama dapat terjadi secara langsung maupun tidak langsung. Arah penularannya tidak dapat ditentukan antara kedua inang itu. Kemampuan d4 asal D. ciliaris
untuk berganti inang ke padi melalui injeksi pada penelitian sebelumnya (Bab 4) tidak dapat menggambarkan kemampuan infeksi di alam. Inokulasi melalui injeksi merupakan modifikasi dari metode Punch (Ono et al. 2001). Sebelumnya
dilaporkan bahwa cendawan blas pada rumput yang tumbuh di sekitar pertanaman padi di Filipina tidak menjadi sumber inokulum penyakit blas padi (Borromeo et al. 1993). Kato et al. (2000) juga tidak menemukan penularan Pyricularia antara
pada padi dengan Digitaria sanguinalis, Digitaria horizontalis, dan Digitaria smutsii di agrosistem alami.
Berdasarkan data GeneBank yang disertakan dalam filogram, satu lokus,
yaitu sekuen ITS rDNA dapat memisahkan spesies Pyricularia yang berada pada D. sanguinalis, dan D. horizontalis terhadap Pyricularia pada padi (memisah
dengan nilai bootstrap 97%). Sebaliknya menurut Hirata et al. (2007), analisis satu
lokus maupun 4 lokus (sekuen ITS rDNA, actin, ß-tubulin, dan calmodulin) tidak dapat menyelesaikan kontroversi spesiasi antara P. grisea dan P. oryzae.
Monofiletik juga ditemukan pada Pyricularia dari 14 jenis gulma padi, termasuk D. ciliaris dan padi di Filipina, yaitu memiliki kemiripan hasil hibridisasi dengan
probe rDNA (Borromeo et al. 1993).
Monofiletisme pada kedua spesies Pyricularia juga ditemukan oleh
Couch dan Kohn (2002). Hanya pada saat itu Couch dan Kohn (2002) mengesampingkan penemuannya pada Pyricularia asal Digitaria yang memiliki
sekuen seperti P. oryzae. Mereka menganggap terdapat kesalahan pelabelan
ataupun suatu kejadian yang jarang. Inang selain padi yang dilaporkan sebagai inang P. oryzae adalah Eleusine coracana (finger millet), Eleusine indica, Eragrostis curvula, Lolium perenne, Setaria sp. Pemisahan P. grisea dengan P. oryzae berdasarkan substitusi beberapa nukleotida pada actin, ß-tubulin, dan
L. hexandra dan P. repens. Sedangkan Pyricularia dari padi berasal dari Setaria millet (Couch et al. 2005). Oleh karena itu Pyricularia pr10.a.S4 pada penelitian
ini juga dapat ditempatkan sebagai P. oryzae.
Disisi lain yang perlu mendapat perhatian dengan berkembangnya pendekatan spesies, yaitu kemungkinan perubahan genetik yang terjadi pada waktu patogen melakukan infeksi silang ke spesies yang berbeda. Pada penelitian ini ditemukan bahwa pergantian inang dapat menginduksi keragaman genetik (Bab 4). Pergantian inang d4 ke P. repens menghasilkan mutasi transisi dua
nukleotida pada ITS. Selain itu juga menghasilkan perubahan genetik yang dideteksi melalui AFLP, dan rep-Pot2. Inang rentan juga dapat menginduksi keragaman genetik inokulum, yaitu genotipe Cut1, PWL, AFLP, dan rep-Pot2. Tingkat perubahan genotipe AFLP dari d4 setelah menginfeksi Panicum repens,
dan padi Kencana bali sangat berbeda dibandingkan d4 setelah menginfeksi padi Cisokan. Padi Kencana bali sangat rentan terhadap penyakit blas. Sedangkan padi Cisokan bersifat moderat resisten terhadap penyakit blas jika dilihat berdasarkan tingkatan nilai padi diferensial Indonesia untuk menentukan ras fisiologi P. oryzae
(Mogi et al. 1991) .
Simpulan
Hasil amplifikasi menggunakan primer its1 dan its4 pada empat isolat
Pyricularia dari rumput dan padi (d4, pr10.a.S4, ok6, dan ou6.S4) diperoleh
sekuen DNA berukuran 543 pb. Sekuen tersebut terdiri atas bagian hilir 18S rDNA, ITS1, 5.8S rDNA, ITS2, dan bagian hulu 26S rDNA. Isolat d4 dari rumput
D. ciliaris dan ok6 dari padi var. Kencana bali dari lokasi dan waktu yang sama,
serta ou6.S4 asal padi dari lokasi dan waktu berbeda memiliki sekuen yang sama. Sebaliknya sekuen pr10.a.S4 berbeda beberapa nukleotida terhadap d4, ok6, atau ou6.S4.
Sekuen ITS beserta 5.8S rDNA tidak dapat memisahkan d4 dan pr10.a.S4 yang berasal dari rumput terhadap ok6 dan ou6.S4 yang berasal dari padi. Kesemuanya memiliki hubungan filogenetik sangat dekat dengan P. oryzae dari
padi. Berdasarkan prioritas maka d4 dan pr10.a.S4 sebagai P. grisea. Sedangkan
ok6 dan ou6.S4 masih dapat juga disebut sebagai P. grisea berdasarkan kesamaan