KERAGAMAN GEN DIACYLGLYCEROL
ACYLTRANSFERASE 1 (DGAT1) PADA POPULASI
SAPI PERAH DI KABUPATEN ENREKANG
SKRIPSI
Oleh
AWAL REZKI AWAN
I 111 11 010
FAKULTAS PETERNAKAN
UNIVERSITAS HASANUDDIN
MAKASSAR
2015
KERAGAMAN GEN DIACYLGLYCEROL
ACYLTRANSFERASE 1 (DGAT1) PADA POPULASI
SAPI PERAH DI KABUPATEN ENREKANG
SKRIPSI
Oleh
AWAL REZKI AWAN
I 111 11 010
Skripsi sebagai Salah Satu Syarat untuk Memperoleh
Gelar Sarjana Peternakan pada Fakultas Peternakan
Universitas Hasanuddin
FAKULTAS PETERNAKAN
UNIVERSITAS HASANUDDIN
MAKASSAR
2015
KATA PENGANTAR
Puji dan syukur penulis panjatkan ke hadirat Allah SWT, karena atas berkat rahmat dan taufik-Nya sehingga dapat menyelesaikan skripsi ini dengan judul “Keragaman Gen Diacylglycerol Acyltransferase 1 (DGAT1) pada Populasi Sapi Perah di Kabupaten Erekang”.
Penulis dengan rendah hati mengucapkan terima kasih kepada semua pihak yang telah membantu dalam menyelesaikan skripsi ini kepada:
1. Ibu Prof. Rr. Sri Rachma AB., M. Sc, Ph. D selaku Pembimbing Utama dan bapak Prof. Dr. Ir. Lellah Rahim, M.Sc. selaku Pembimbing Anggota, atas segala bantuan dan keikhlasannya untuk memberikan bimbingan, nasehat dan saran-saran sejak awal penelitian sampai selesainya penulisan skripsi ini.
2. Kedua orang tua tercinta ayahanda Syamsur Adis, ibunda Suwarni Syam dan Tante Hasnah Syam yang memberikan cinta kasih dukungan mental dan memberikan doa restunya dan saudaraku Muh. Rafdy Fauzan dan Nasylah Maulidya Syam yang telah memberikan motivasi untuk selalu lebih semangat.
3. Bapak Prof. Dr. Ir. H. Sudirman Baco, M.Sc selaku Dekan Fakultas Peternakan Universitas Hasanuddin.
4. Ibu Prof. Dr. drh. Hj. Ratmawati Malaka, M. Sc selaku Wakil Dekan I, Ibu Ir. Hastang, M.Si selaku Wakil Dekan II, Bapak Prof. Dr. Ir. Jasmal A Syamsu, M.Si selaku Wakil Dekan III Fakultas Peternakan Universitas Hasanuddin.
5. Bapak Prof. Dr. Ir. Ambo Ako, M.Sc., Bapak Dr. Muh . Ihsan A. Dagong, S.Pt., M. Si., selaku dosen pembahas yang telah banyak memberikan saran-saran dan masukan untuk perbaikin skripsi ini.
6. Ibu Prof. Rr. Sri Rachma AB., M. Sc, Ph. D selaku Penasehat Akademik yang memberikan bimbingannya.
7. Bapak Dr. Muh . Ihsan A. Dagong, S.Pt., M. Si., terima kasih atas bimbingannya selama penulis melakukan penelitian.
8. Sahabat-sahabat Nurjannah S. Pt, Mutmainnah, Mutiara Hikma S. Pt, Arra Musyarrafah, Mardhatilla Utami S. Pt, A. Pancawati S. Pt, Nurmulyaningsih S. Pt, Magfira Nur S. Pt, Kurniah Kamaruddin S. Pt, Musfira Jafar, Rizka Isnaini HS, Hj.Suci Ramadhani, Armi Aulia Utami S. Pt, Muh. Shoalihin Saleh Husain S.Pt, Andi Zuaib, Fadly Hidayat Ilyas, Nur Ahmad S. Pt, Khairun Nur Karimuddin, Nur Fajri Syam, Budi Utomo, S. Pt., Ardi S. Pi, Zulkifli SP serta Pondok Faisal terima kasih atas segala cinta, pengorbanan, bantuan, pengertian, candatawa, serta kebersamaannya selama ini.
9. Keluargan besar “SOLANDEVEN” khususnya kelas “PROTEK”. Keluarga Besar Himpunan Mahasiswa Produksi Ternak serta rekan-rekan asisten Ilmu Kesehatan Ternak, terima kasih atas kenangan yang telah terukir selama penulis bersama kalian.
10. Kepada teman-teman Penelitian Genetika Molekuler, Kak Abduh, Mardha, Fira, Umma, Inci, Nia, dan Evi terima kasih atas bantuan dan perhatiannya selama penelitian dan penyelesaian skripsi.
11. Laboratorium Terpadu Peternakan UNHAS, Kak Nurul Purnomo, Kak Tri terima kasih atas bantuan dan perhatiannya selama penelitian dan penyelesaian skripsi. 12. Teman-teman KKN Gelombang 87 Geng Carigadis “Takbir, Dede, Imy, Dila, Irma,
Ayu, Ros” dan teman-teman sekecamatan Awangpone Kabupaten Bone.
13. Semua pihak yang tidak dapat penulis sebut satu persatu, terima kasih banyak atas segala bantuannya.
Penulis menyadari bahwa penyusunan skripsi ini masih terdapat kekurangan dan kesalahan. Penulis mengharapkan kritikan dan saran yang sifatnya membangun demi kesempurnaan skripsi ini.
Makassar, Oktober 2015
ABSTRAK
AWAL REZKI AWAN (I 111 11 010). Keragaman Gen Diacylglyserol
Acyltransferase 1 (DGAT1) pada Populasi Sapi Perah di Kabupaten Enrekang.
Dibimbing oleh SRI RACHMA APRILITA BUGIWATI dan LELLAH RAHIM. Kualitas susu secara genetik dipengaruhi oleh gen Diacylgliserol acyltransferase 1 (DGAT1). Oleh karena itu, diperlukan upaya untuk mengidentifikasi keragaman gen DGAT1 agar nantinya dapat dilakukan seleksi induk sapi perah yang dapat menghasilkan anak betina yang memiliki gen penghasil susu dengan kadar lemak tinggi. Penelitian ini bertujuan untuk mengidentifikasi keragaman DGAT1 pada populasi sapi perah di Kabupaten Enrekang. Bahan utama dari penelitian ini adalah sampel darah induk sapi perah jenis Fries Holland di Kabupaten Enrekang Kecamatan Cendana (50 ekor) dan Kecamatan Angeraja (30 ekor). Metode yang digunakan dalam penelitian ini meliputi koleksi sampel darah, ekstraksi darah, PCR, dan kemudian hasil PCR dipotong dengan enzim restriksi EaeI. Hasil yang diperoleh dari penelitian ini yaitu dari 80 sampel ditemukan 45 sampel heterozigot dan 35 sampel sampel homozigot. Hasil penelitian ini menyimpulkan bahwa populasi sapi perah di Kabupaten Enrekang bersifat polimorfik, terdapat dua tipe alel, yaitu K dan A. frekuensi alel K (0,72%) lebih tinggi dibanding freuensi alel A (0,28%).
ABSTRACT
AWAL REZKI AWAN (I 111 11 010). Diversity of Diacylglyserol Acyltransferase 1
Gene (DGAT1) in Dairy Cattle From Enrekang Regency. Supervised SRI RACHMA
APRILITA BUGIWATI dan LELLAH RAHIM.
The quality of milk genetically influenced by Diacylgliserol acyltransferase 1 gene (DGAT1). Therefore, it is necessary to identify the diversity of DGAT1 gene that later can to do the selection process of cattle who can produce a calves who has high fat content milk production. This study aims to identified the diversity of DGAT1 of dairy cattle poluation in Enrekang. The main ingredient of this study was a dairy holding a blood sample types Fries Holland in Enrekang District of Cendana (50 samples) and Angngerajas District (30 samples). The method used in this study are collection of blood samples, blood extraction, PCR, and then the PCR product was cut with restriction enzymes named EaeI. From the 80 samples was found 45 samples heterozygous and 35 samples homozygous. The conclution of this research are the cattle population in Enrekang was polymorphic, there were two allele type, Allele K and A. Frequency of allele K (0,72%) is higher than allele A (0,28%).
DAFTAR ISI
KATA PENGANTAR ... i
DAFTAR ISI ... ii
DAFTAR TABEL ... iii
DAFTAR GAMBAR ... iv
PENDAHULUAN ... 1
TINJAUAN PUSTAKA Keragaman Genetik ... 3
Penanda DNA Terciri (Marker Assisted Selection) ... 4
Gen Diacylglyserol Acyltransferase 1 (DGAT1) ... 5
METODE PENELITIAN Waktu dan Tempat ... 8
Materi Penelitian ... 8
Tahapan Penelitian ... 9
Analisis Data ... 11
HASIL DAN PEMBAHASAN Amplifikasi dan pendeteksian keragaman Gen DGAT1 ... 13
Frekuensi genotipe dan alel ... 16
Nilai heterozigositas ... 17
Keseimbangan Hardy-Weinberg ... 19
KESIMPULAN DAN SARAN ... 21
LAMPIRAN ... 25 RIWAYAT HIDUP ... 27
DAFTAR TABEL
No. Teks Halaman 1. Sequen primer beserta enzim restriksi endonuklease untuk
PCR-RFLP ... 8
2. Frekuensi genotip dan alel gen DGAT1 ... 16
3. Nilai heterozigositas harapan dan pengamatan gen DGAT1 ... 17
DAFTAR GAMBAR
No. Teks Halaman 1. Hasil amplifikasi dan pendeteksian keragaman gen DGAT1 pada
mesin PCR ... 13 2. Posisi penempelan primer forward dan reverse serta situs pemotongan
PENDAHULUAN
Kabupaten Enrekang Sulawesi Selatan merupakan salah satu daerah yang terkenal dengan populasi sapi perahnya. Peternakan sapi perah di Kabupaten Enrekang dimulai sejak tahun 1981 melalui proyek Crash Program oleh Dinas Pertanian dan Peternakan setempat berupa bantuan sapi perah jenis Sahiwal Cross dan Santa Gertrudis dari Selandia Baru. Namun usaha peternakan sapi perah mengalami stagnasi, populasi hanya bertambah 60 ekor hingga tahun 1991. Melalui teknologi inseminasi buatan, pengadaan sapi perah bantuan pemerintah daerah, dan swadaya masyarakat, populasi sapi perah mengalami peningkatan hingga mencapai 110 ekor pada tahun 2001 dan pada tahun 2011 populasi sapi perah mencapai 1.065 ekor (Hatta, 2013). Peningkatan populasi sapi perah di Kabupaten Enrekang berdampak pada peningkatan produksi air susu. Produktivitas air susu sapi perah di Kabupaten Enrekang rata-rata 6-8 liter per ekor per hari (Amrawaty dan Sirajuddin, 2014). Akan tetapi, produksi susu sapi perah yang diperoleh peternak tidak dipasarkan dalam bentuk susu segar, melainkan dalam bentuk produk dangke karena dianggap lebih menguntungkan dari segi ekonomi.
Dangke merupakan suatu produk olahan sejenis keju lunak berbahan dasar air susu ternak yang diolah secara tradisional melalui teknik penggumpalan dengan campuran enzim papain. Dangke dibuat dengan cara memanaskan air susu dengan api kecil sampai mendidih, kemudian ditambahkan koagulan berupa getah pepaya (enzim papain) sehingga terjadi penggumpalan. Enzim secara alamiah akan mengubah air susu menjadi
padat akibat terjadinya pemisahan protein dan air (Kesuma, dkk., 2013). Kualitas dari produk dangke sangat dipengaruhi oleh kualitas air susu.
Strzałkowska, et al., (2005) menyatakan bahwa kadar lemak dalam susu yang merupakan penentu kualitas air susu dipengaruhi oleh gen Diacylgliserol
acyltransferase (DGAT1). Kualitas susu sapi perah di Kabupaten Enrekang jika ditinjau
dari kadar lemaknya memiliki kadar lemak rata-rata 3,34%, sedangkan kadar lemak susu sapi perah berdasarkan SNI 01-3141-1998 yaitu minimum 3,0% (Irfan, 2011).
Gen DGAT1 merupakan gen yang mengontrol kadar lemak air susu. Oleh karena itu, diperlukan upaya untuk mengidentifikasi keragaman gen DGAT1 agar nantinya dapat dilakukan seleksi induk sapi perah yang dapat menghasilkan anak betina yang memiliki gen penghasil susu dengan kadar lemak tinggi. Berdasarkan uraian tersebut maka perlu dilakukan penelitian untuk mengidentifikasi keragaman gen DGAT1 dengan menggunakan teknik molekuler PCR-RFLP (Polymerase Chain Reaction-Restriction
Fragment Length Polymorphism) pada populasi sapi perah di Kabupaten Enrekang.
Penelitian ini bertujuan untuk mengidentifikasi keragaman DGAT1 pada populasi sapi perah di Kabupaten Enrekang.
Kegunaan penelitian ini diharapkan dapat memberikan informasi genetik mengenai keragaman alel gen DGAT1 yang dapat dimanfaatkan dalam proses seleksi induk sapi perah untuk menghasilkan anak betina yang memiliki gen penghasil susu dengan kadar lemak tinggi.
TINJAUAN PUSTAKA
Keragaman Genetik
Keanekaragaman genetik adalah keanekaragaman individu dalam satu jenis makhluk hidup dan menjadi ciri-ciri yang terdapat dalam suatu populasi serta mengakibatkan variasi antar individu sejenis. Keragaman genetik antar individu dalam populasi kadangkala cukup besar (Indrawan, Primack, dan Supriatna, 2007). Keragaman genetik terjadi tidak hanya antar bangsa tetapi juga di dalam satu bangsa yang sama maupun antar individu di dalam populasi (Handiwirawan dan Subandriyo, 2004). Keragaman genetik atau polimorfisme genetik adalah terdapatnya lebih dari satu bentuk atau macam genotipe di dalam populasi. Sumber keragaman ini dapat disebabkan oleh adanya pengulangan urutan sekuen, insersi, delesi, dan rekombinasi (Kirby,1990).
Ukuran tinggi rendahnya keragaman genetik dalam suatu kelompok atau populasi dapat dilihat berdasarkan nilai heterozigositas. Semakin tinggi derajat heterozigositas suatu populasi maka daya tahan hidup populasi tersebut akan semakin tinggi. Derajat heterozigositas adalah rataan presentase lokus heterozigositas tiap individu atau rataan presentase individu heterozigot dalam populasi (Nei dan Kumar, 2000).
Frekuensi genotipe dalam suatu populasi yang cukup besar akan selalu dalam keadaan seimbang bila tidak ditemukan seleksi, migrasi, mutasi dan genetik drift. Selain itu, silang luar dan silang dalam juga mempengaruhi frekuensi genetik.
Keragaman genetik antara subpopulasi dapat diketahui dengan melihat persamaan dan perbedaan frekuensi alel diantara subpopulasi (Li, et al., 2000).
Studi tentang variasi genetik pada suatu organisme terutama pada hewan ternak baik inter maupun antar jenis organisme adalah sangat penting karena berhubungan dengan variasi pada fenotip. Variasi fenotip yang terjadi bisa disebabkan karena adanya variasi genetik atau variasi lingkungan atau karena variasi lingkungan dan genetik. Pengetahuan tentang variasi genetik mempunyai sejumlah aplikasi yang bermanfaat. Aplikasi dari variasi genetik ini misalnya untuk mengidentifikasi hewan dan mencari asal usulnya, mengetahui hubungan kekerabatan dan pemetaan gen (Lelana, dkk., 2003). Penanda DNA Terciri (Marker Assisted Selection)
Perkembangan ilmu pengetahuan dan teknologi biologi molekuler, khususnya terhadap materi kimia genetik (DNA dan RNA), teknologi PCR dan elektroforesis telah menghasilkan penemuan berbagai rangkaian materi genetik sebagai penanda genetik (genetic marker) untuk sifat ekonomi yang memiliki nilai ekonomi tinggi, asal usul dan kekerabatan suatu individu atau bangsa ternak tertentu (Sari, dkk., 2014). Pada studi keragaman genetik, penanda morfologi dan penanda molekuler telah banyak digunakan antara lain untuk mengidentifikasi genetik individu, estimasi keragaman populasi, diferensiasi populasi, menghitung jarak genetik dan hubungan genetik antar subpopulasi (Sumadi, dkk., 2008). Penggunaaan Penanda MAS (Marker Assisted Selection) didasarkan pada gagasan bahwa terdapat gen yang memegang peranan utama dan menjadi sasaran atau target secara spesifik dalam seleksi (Van der Warf, 2000).
Penggunaan Penanda MAS pada sapi dapat menunjang cara seleksi konvensional yang berdasarkan fenotipe, sebab seleksi dilakukan pada arah molekuler sehingga tidak terpengaruh lingkungan. Pemarka DNA memiliki keunggulan karena sifatnya sangat polimorfik dan beberapa pemarka DNA antara lain Restriction Fragments Lengths
Polymorphisms (RFLP), Mikrosatelit, dan sidik jari DNA (Sumadi, dkk., 2008).
Kemajuan ilmu pengetahuan dan teknologi bidang genetika molekuler dan biologi molekuler dari waktu ke waktu diharapkan dapat memberikan kontribusi signifikan pada kemajuan dan perkembangan dunia peternakan khususnya program pemuliabiakan. Salah satu alternatif seleksi dengan menggunakan marker gen adalah alternatif bioteknologi untuk memproduksi ternak pembawa sifat yang diinginkan (sesuai dengan marker gen tersebut). MAS terbukti mampu meningkatkan nilai genetik ternak dalam program pemuliaan ternak. Identifikasi marka genetik yang bermanfaat merupakan langkah awal dan kritis untuk mendapatkan marka pembantu seleksi (Dedi, dkk., 2008).
Gen Diacylgliserol acyltransferase 1 (DGAT1)
Gen DGAT1 merupakan gen yang mempengaruhi kandungan lemak dalam susu. Kandungan lemak dalam susu berpengaruh terhadap kualitas susu, semakin tinggi kadar lemak susu maka kualitas susu akan semakin baik (Mohammed, et al., 2015). Suatu studi pemetaan lokus sifat kuantitatif pada sapi menghasilkan identifikasi polimorfisme dalam pengkodean gen untuk diacyilglycerol acyltransferase1 (DGAT1), yang merupakan kunci enzim dalam sintesis trigliserida dan diduga memiliki pengaruh
yang kuat terhadap persentase lemak susu dan karakteristik produksi susu lainnya (Winter, et al., 2002).
Kandungan lemak dalam susu diatur oleh gen DGAT1 yang terdapat pada bagian lokus sifat kuantitatif di kromosom 14 pada sapi. Urutan DNA dari gen DGAT1 menunjukkan adanya perubahan frekuensi yang signifikan di beberapa posisi variabel antara kelompok hewan dengan nilai-nilai pemuliaan tinggi dan rendah untuk kandungan lemak susu pada jenis yang berbeda. Gen DGAT1 mengkodekan enzim acyl-CoA yang berperan penting dalam metabolisme sel diasilgliserol dalam proses fisiologis, seperti penyerapan lemak usus, lipoprotein, pembentukan jaringan adiposa dan dalam proses laktasi (Strzałkowska, et al., 2005). Gen DGAT1 adalah gen mikrosomal yang memainkan peranan penting dalam metabolisme gliserolipid dan dapat memodifikasi komposisi asam lemak di jaringan adiposa dan otot rangka yang menyebabkan bertambah atau berkurangnya asam lemak jenuh serta mengubah metabolisme trigliserida dalam kelenjar susu (Mercade, et al., 2005).
Berdasarkan hasil penelitian Utama (2013) pada populasi sapi perah di Balitnak dan BIB Lembang bahwa gen DGAT1 bersifat polimorfik terletak di kromosom autosom ke-14 dengan panjang total 411 (pasang basa). Produk amplifikasi atau amplikon yang diperoleh memiliki panjang 411 pb. Amplikon tersebut terletak pada posisi basa ke-10 232 sampai basa ke-10 644. Alel yang didapat dari populasi ini yaitu alel K dan A.
Hasil identifikasi keragaman ruas gen DGAT1 pada (Balai Besar Pembibitan Ternak Unggul Sapi Perah (BBPTU SP) Baturraden dan Balai Pengembangan dan
Pembibitan Sapi Perah (BPPT SP) Cikole, menunjukkan bahwa ruas gen DGAT1 bersifat polimorfik karena ditemukan dua tipe alel, yaitu alel K dan A. Frekuensi genotipe KA (75%) pada populasi yang diamati lebih tinggi dibanding dengan frekuensi genotip KK (25%). Frekuensi alel K pada ruas gen DGAT1 tinggi (0,531-0,844) di semua populasi dibandingkan dengan frekuensi alel A. Sapi dengan genotipe KA menghasilkan asam nervonat lebih tinggi dibandingkan genotipe KK (P<0,05). Asam nervonat merupakan salah satu jenis dari asam lemak tidak jenuh tunggal (mono unsaturated fatty acid), sehingga gen DGAT1 mempunyai peluang untuk dijadikan marka pembantu seleksi (Sari, dkk., 2014).
METODE PENELITIAN
Waktu dan Tempat
Penelitian ini dilaksanakan pada bulan Juni 2015 di Kabupaten Enrekang (pengambilan sampel) dan untuk tahapan ekstraksi DNA, PCR dan analisis data dilaksanakan di Laboratorium Bioteknologi Terpadu Fakultas Peternakan Universitas Hasanuddin, Makassar.
Materi Penelitian
Bahan utama dari penelitian ini adalah sampel darah 80 ekor induk sapi perah jenis Fries Holland di Kabupaten Enrekang Kecamatan Cendana (50 ekor) dan Kecamatan Angeraja (30 ekor). Bahan pendukung antara lain: enzim restriksi HaeIII, bahan ekstraksi DNA (lysis buffer, proteinaseK, wash buffer I, wash buffer II, elution buffer, ethanol absolute 96%), bahan PCR (dNTP mix, MgCl2, enzim Taq DNA polymerase), bahan elektroforesis (tris base, asam borat, agarose, Na2 EDTA, ethidium bromide, marker DNA, DNA loading dye), tissue, plastik mika dan primer gen DGAT1.
Tabel 1. Sequen primer beserta enzim restriksi endonuklease untuk PCR-RFLP Primer Sekuen DNA Enzim
Restriksi
Panjang PCR
Sumber DGAT1 F:5’-GCACCATCCCTTCCTCAAG-3’
R:5’- GGAAGCGCTTTCGGATG -3’ EaeI 411 pb Trzałkowska, et al,
2005 F = Forward, R = Reverse
Tahapan Penelitian
1. Koleksi Sampel Darah
Sampel darah diperoleh dari 80 ekor sapi perah di Kabupaten Enrekang. Pengambilan darah sebanyak 2 ml melalui vena jugularis dilakukan pada tiap ekor sapi perah yang ditampung pada tabung vacutainer yang telah berisi antikoagulan EDTA untuk mencegah penggumpalan darah.
2. Ekstraksi DNA
Sebanyak 200 µl sampel darah dilisiskan dengan menambahkan 400 µl larutan
lysis buffer dan 20 µl proitenase K (10 mg/ml), kemudian diinkubasi pada suhu 56 oC
selama 60 menit di dalam waterbath shaker. Setelah inkubasi, larutan kemudian ditambahkan 200 µl Ethanol absolute 96% dan disentrifugasi 6.000 x g selama satu menit.
Pemurnian DNA dilakukan dengan metode spin column dengan menambahkan 500 µl larutan pencuci wash buffer 1 pada yang kemudian dilanjutkan dengan sentrifugasi pada 8.000 X g selama satu menit. Setelah supernatannya dibuang, DNA kemudian dicuci lagi dengan 500 µl wash buffer II dan disentrifugasi pada 12.000 x g selama tiga menit. Setelah supernatannya dibuang, DNA kemudian dilarutkan dalam 200 µl elution buffer dan disentrifugasi pada 8.000 x g selama satu menit untuk selanjutnya DNA hasil ekstraksi ditampung dan disimpan pada suhu -20 oC.
agarose 1,5 % dengan buffer 1 × TBE (89 mM Tris, 89 mM asam borat, 2 mM Na2EDTA) yang mengandung 100 ng/ml ethidium bromide lalu divisualisasi pada UV
transiluminator (gel documentation system). Teknik PCR
Komposisi reaksi PCR dikondisikan pada volume reaksi 25 µl yang terdiri atas 100 ng DNA, 0,25 mM masing-masing primer DGAT1 forward dan reverse, 150 µM dNTP, 2,5 mM Mg2+, 0,5 Taq DNA polymerase dan 1 × buffer. Kondisi PCR mulai
dengan denaturasi awal pada suhu 94 oC × 4 menit, diikuti dengan 34 siklus berikutnya
masing-masing denaturasi 94 oC × 30 detik, dengan suhu annealing yaitu: 50 oC × 30
detik, yang dilanjutkan dengan ekstensi: 72 oC × 90 detik, yang kemudian diakhiri
dengan satu siklus ekstensi akhir pada suhu 72 oC selama 10 menit dengan
menggunakan mesin PCR. Produk PCR kemudian di elektroforesis pada gel agarose 1.5 % dengan buffer 1 x TBE (89 mM Tris, 89 mM asam borat, 2 mM Na2 EDTA) yang mengandung 100 ng/ml ethidium bromide. Kemudian divisualisasi pada UV transiluminator (gel documentation system).
Produk PCR yang diperoleh dari masing-masing gen target kemudian dianalisis menggunakan RFLP melalui pemotongan menggunakan enzim restriksi EaeI yang memiliki situs pemotongan pada gen DGAT1. Sebanyak 5 l DNA produk PCR ditambahkan 0,3 l enzim restriksi (5U) ; 0,7 l buffer enzim dan 1lmilique water sampai volume 7 l, selanjutnya dilakukan inkubasi selama 18 jam pada suhu 37 ºC.
Analisis Data
Keragaman genotipe tiap individu dari total 80 ekor sapi perah ditentukan dari pita-pita DNA gen yang ditemukan. Masing-masing sampel dibandingkan berdasarkan ukuran (marker) yang sama dan dihitung frekuensi alelnya. Frekuensi alel bisa dihitung dengan menggunakan rumus Nei dan Kumar (2000) dalam Yulianty (2013), sebagai berikut :
𝑋𝑖 = ( 2𝑛𝑖𝑖+ ∑𝑗≠𝑖 𝑛𝑖𝑗) 2𝑛
Keterangan :
Xi = frekuensi alel ke -i
nii = jumlah sampel yang bergenotip ii ( homozigot) nij = jumlah sampel yang bergenotip ij ( heterozigot) n = jumlah sampel
Hardy-Weinberg (HWE) dengan uji chi-square (X2) menurut Hartl (1988)
dalam Yulianty (2013), sebagai berikut :
𝑋2 = ∑(𝑂𝑖− 𝐸𝑖) 2 𝐸𝑖
Keterangan : χ² = chi-square
Oi = jumlah pengamatan genotipe ke-i
Nilai heterozigositas pengamatan (Ho) dan heterozigositas harapan (He) berdasarkan rumus heterozigositas Nei dan Kumar dihitung dengan menggunakan software PopGene32 versi 1.31 (Yeh, Yang, and Boyle, 1999) dalam Yulianty (2013), sebagai berikut :
Keterangan:
Ho = heterozigositas pengamatan di antara populasi He = heterozigositas harapan di antara populasi Wk = ukuran relatif populasi
HASIL DAN PEMBAHASAN
Amplifikasi dan Pendeteksian Keragaman Gen DGAT1
Amplifikasi gen DGAT1 pada populasi sapi perah di Kabupaten Enrekang berhasil dilakukan dengan menggunakan teknik PCR-RFLP. Hasil amplifikasi dan identifikasi keragaman gen DGAT1 pada gel agarose 1,5% dapat dilihat pada Gambar 1.
(a) (b)
Gambar 1. Hasil amplifikasi (a) dan pendeteksian keragaman (b) gen DGAT1 pada mesin PCR,
M: marker; Nomor 1-7: Amplikon gen DGAT1
Gambar 1. menunjukkan bahwa panjang fragmen gen DGAT1 yaitu 411 pb. Hal ini sesuai dengan pendapat Sari, dkk. (2014) bahwa panjang produk hasil amplifikasi ruas gen DGAT1 adalah 411 pb yang terletak pada exon 8. Menurut Winter et al. (2002) bahwa deteksi variasi alel dari gen DGAT1 pada produk PCR berada pada 411
pb dari DNA genom sapi. Posisi mutasi ekson ke-8, posisi basa ke-10 menyebabkan perubahan adenin menjadi guanin (A→G) atau mutasi transisi dan basa ke-10 menyebabkan perubahan adenin menjadi sitosin (A→C) atau mutasi transversi.
Proses PCR yang dilakukan menggunakan suhu annealing 50 0C selama 30
detik. Yusuf (2010) menyatakan bahwa waktu annealing yang bisa digunakan dalam PCR adalah 30 sampai dengan 45 detik. Semakin panjang ukuran primer, semakin tinggi temperaturnya. Kisaran temperatur penempelan yang digunakan adalah antara 36 sampai dengan 72 0C, namun suhu yang biasa digunakan yaitu antara 50 sampai 60
0C.
Keberhasilan teknik PCR lebih didasarkan kepada kesesuaian primer dan efisiensi dan optimasi proses PCR. Primer yang tidak spesifik dapat menyebabkan teramplifikasinya daerah lain dalam genom yang tidak dijadikan sasaran atau sebaliknya tidak ada daerah genom yang teramplifikasi. Proses penempelan primer pada utas DNA yang sudah terbuka memerlukan suhu optimum, sebab suhu yang terlalu tinggi dapat menyebabkan amplifikasi tidak terjadi atau sebaliknya suhu yang terlalu rendah menyebabkan primer menempel pada sisi lain genom yang bukan sisi homolognya (Suryanto, 2003).
Berdasarkan Gambar 1. ditemukan dua tipe alel yaitu K dan A dan dua tipe genotipe yaitu KK dan KA. Hasil ini dapat dikatakan beragam karena ditemukan 2 jenis alel. Hal ini sesuai dengan pendapat Nei dan Kumar (2000) yang menyatakan bahwa suatu populasi dikatakan beragam jika memiliki dua atau lebih alel dalam satu lokus dengan frekuensi kurang dari satu (100%). Utama (2013) juga menemukan hal yang
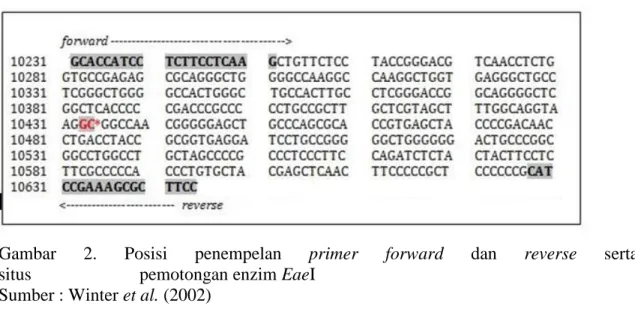
serupa dengan penelitian ini yaitu alel K dan alel A pada gen DGAT1 berhasil diidentifikasi menggunakan enzim restriksi EaeI. Alel K tidak memiliki situs mutasi GC*GGCC, sehingga tidak terpotong oleh enzim. Panjang fragmennya sama dengan amplikon, yakni 411 pb. Fragmen alel A terpotong oleh enzim karena memiliki situs mutasi GC*GGCC, sehingga terbagi menjadi dua fragmen. Panjang masing-masing fragmennya, yakni 411 pb (KK), dan 203 dan 208 pb (KA).
Posisi penempelan primer gen DGAT1 dan pemotongan oleh enzim EaeI dapat dilihat pada Gambar 2.
Gambar 2. Posisi penempelan primer forward dan reverse serta situs pemotongan enzim EaeI
Sumber : Winter et al. (2002)
Penentuan genotip gen DGAT1 pada sapi perah dalam penelitian ini menggunakan metode PCR-RFLP dengan EaeI sebagai enzim pemotong. Letak/runutan sequens DNA gen DGAT1 dari primer yang dipakai dengan mengguanakan enzim restriksi EaeI dapat dilihat pada Gambar 2. yaitu mengenali situs pemotongan GC*GGCC. Hal ini sesuai dengan penelitian Kong et al. (2007) bahwa enzim restriksi
Frekuensi Genotipe dan Alel
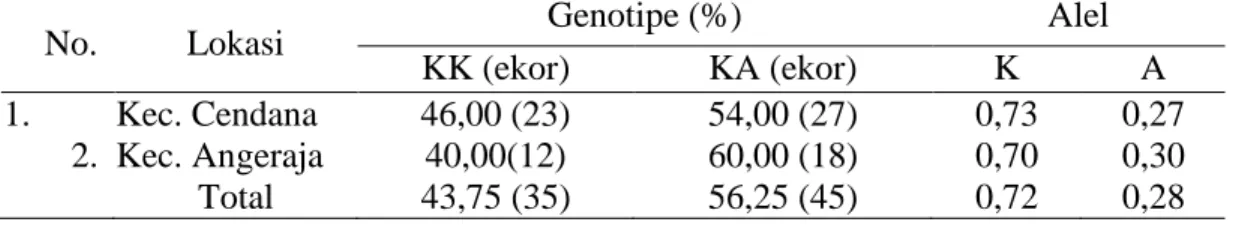
Hasil analisis frekuensi genotipe dan alel pada fragmen gen DGAT1 pada sapi perah dapat dilihat pada Tabel 2.
Tabel 2. Frekuensi Genotipe dan Alel Gen DGAT1 pada Populasi Sapi Perah No. Lokasi Genotipe (%) Alel
KK (ekor) KA (ekor) K A 1. Kec. Cendana 46,00 (23) 54,00 (27) 0,73 0,27
2. Kec. Angeraja 40,00(12) 60,00 (18) 0,70 0,30 Total 43,75 (35) 56,25 (45) 0,72 0,28
Hasil pada Tabel 2. memperlihatkan bahwa total frekuensi genotipe KA (56,25%) lebih tinggi dibanding genotipe KK (43,75%), sedangkan genotipe AA tidak ditemukan pada populasi sapi perah. Proses perkawinan pada sapi perah di Kabupaten Enrekang umumnya dilakukan secara inseminasi buatan (IB) dan diduga pejantan yang digunakan hanya memiliki genotipe homozigot (KK) sehingga genotipe homozigot (AA) tidak ditemukan. Kondisi seperti ini juga didapat dalam penelitian Sari, dkk. (2014) yang mendapatkan frekuensi genotipe KA yaitu 75% lebih tinggi dibandingkan dengan frekuensi genotipe KK yaitu 25% dan tidak ditemukan genotipe AA.
Ferekuensi alel yang diperoleh dari penelitian ini ada dua jenis yaitu alel K (0,72) lebih tinggi dibanding alel A (0,28). Hal ini terjadi karena aliran alel K dalam populasi sapi perah yang lebih banyak. Hal ini dibuktikan dengan beberapa penelitian sejenis yang menemukan alel K lebih banyak dibanding alel A. Dalam Penelitian Utama (2013) menemukan frekuensi alel K (0,66) lebih tinggi dibanding alel A(0,34).
Kondisi seperti ini juga didapat dalam penelitian Sari, dkk (2014) yang menemukan frekuensi alel K (0,64) lebih tinggi dibanding alel A (0,36).
Gen DGAT1 pada populasi sapi FH yang diamati bersifat polimorfik karena frekuensi alel yang ditemukan berada dibawah 0,99. Hal ini sesuai dengan pendapat Nei dan Kumar (2000) yang menyatakan bahwa frekuensi alel adalah frekuensi relatif dari suatu alel dalam populasi atau jumlah suatu alel terhadap jumwlah total yang terdapat dalam suatu populasi. Suatu alel dikatakan polimorfik jika memiliki frekuensi alel sama dengan atau berada dibawah 0,99.
Keragaman gen DGAT1 dapat dijadikan sebagai informasi acuan untuk program seleksi sapi perah karena gen tersebut berperan dalam mengatur kadar dan komposisi asam lemak susu. Sapi dengan genotipe KA menghasilkan asam nervonat lebih tinggi dibandingkan genotipe KK (P<0,05). Asam nervonat merupakan salah satu jenis dari asam lemak tidak jenuh tunggal (mono unsaturated fatty acid), sehingga gen DGAT1 mempunyai peluang untuk dijadikan marka pembantu seleksi (Sari, dkk., 2014). Dapat dikatakan bahwa alel yang berperan dalam proses pembentukan air susu yang memiliki kadar lemak yang baik yaitu alel K. Hal ini sesuai dengan penelitian Utama (2013), yang menemukan bahwa sapi perah yang bergenotipe AA menghasilkan susu dengan asam lemak tak jenuh yang tinggi.
Nilai heterozigositas
Hasil analisis nilai heterozigositas pengamatan (Ho) dan heterozigositas harapan (He) gen DGAT1 dapat dilihat pada Tabel 3.
Tabel 3. Nilai Heterozigositas pengamatan (Ho) dan heterozigositas harapan (He) DGAT1
No Lokasi N (ekor) Ho He 1. Kec. Cendana 50 0.5306 0.3939 2. Kec. Angeraja 30 0.6000 0.4271
Berdasarkan data pada Tabel 3. bahwa nilai heterozigositas pengamatan (Ho) lebih tinggi dibanding heterozigositas harapan (He) pada kedua populasi sapi perah. Hal ini menunjukkan bahwa nilai Ho yang didapatkan cukup tinggi karena nilai yang didapat berada diatas 0,50. Nilai Ho yang tinggi menunjukkan keragaman yang tinggi pada suatu populasi. Hal ini sesuai dengan pendapat Javanmard, et al., (2005) yang menyatakan bahwa nilai heterozigositas harapan yang tinggi (Ho>0,50) menunjukkan tingginya keragaman gen pada suatu polulasi. Utama (2013) juga menemukan hal serupa dengan penelitian ini yaitu nilai Ho dari populasi pengamatan lebih tinggi dibanding nilai He. Menurut Tambasco, et al., (2003) bahwa perbedaan antara nilai heterozigositas pengamatan (Ho) dan nilai heterozigositas harapan (He) dapat dijadikan indikator adanya ketidakseimbangan genotipe pada populasi yang diamati. Nilai Ho dan He menjadi penciri tinggi rendahnya variasi gen dalam populasi. Semakin tinggi nilai heterozigositas pengamatan maka semakin tinggi pula keragaman yang ada dalam suatu populasi. Sebaliknya, semakin rendah nilai heterozigositas pengamatan semakin rendah pula keragaman dalam suatu populasi.
Keseimbangan Hardy-Weinberg
Suatu populasi dikatakan berada dalam keseimbangan Hardy-Weinberg yaitu jika frekuensi genotipe dan frekuensi alel selalu konstan dari generasi ke generasi berikutnya. Hal ini terjadi sebagai penggabungan gamet secara acak dalam populasi yang besar (Vasconcellous et al., 2003).
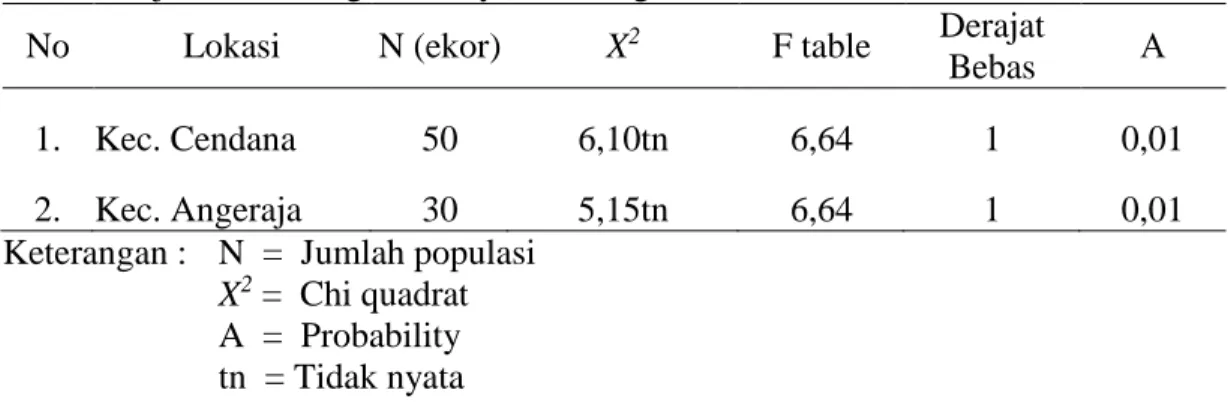
Hasil pengujian keseimbangan Hardy-Weinberg pada populasi sapi perah di Kabupaten Enrekang dilakukan dengan menggunakan uji chi-square dapat dilihat pada Tabel 4.
Tabel 4. Uji Keseimbangan Hardy-Weinberg
No Lokasi N (ekor) X2 F table Derajat
Bebas Α 1. Kec. Cendana 50 6,10tn 6,64 1 0,01 2. Kec. Angeraja 30 5,15tn 6,64 1 0,01 Keterangan : N = Jumlah populasi
X2 = Chi quadrat A = Probability tn = Tidak nyata
Pengujian keseimbangan Hardy-Weinberg pada populasi sapi perah dilakukan dengan menggunakan uji chi-square untuk mengetahui kesesuaian data pengamatan dengan hukum Hardy-Weinberg. Nilai Chi-square pada kedua populasi square (6,10 dan 5,15) tidak berbeda nyata (P>0,01) dapat dilihat pada Tabel 4. dimana F.hitung lebih kecil daripada F.Tabel artinya nilai tersebut berada dalam kesetimbangan Hardy- Weinberg. Suatu popuasi dikatakan sesuai dengan kesetimbangan Hardy-Weinberg yaitu jika frekuensi genotype dan frekuensi alel selalu konstan dari generasi ke generasi berikutnya. Ketidakseimbangan Hardy-Weinberg terjadi disebabkan karena adanya
seleksi, terjadi arus gen (migrasi) secara tidak seimbang, mutasi tidak seimbang, dan terjadi perkawinan tidak acak (Aryulina, dkk., 2006). Hukum keseimbangan Hardy-Weinberg menyatakan bahwa frekuensi alel dan frekuensi genotipe dalam suatu populasi yang cukup besar akan tetap konstan dari satu generasi ke generasi jika dalam populasi tersebut terjadi perkawinan secara acak (random mating), tidak ada seleksi, mutasi, migrasi dan genetic drift. Kesetimbangan Hardy- Weinberg berhubungan erat dengan frekuensi genotipe dan frekuensi alel (Nei dan Kumar, 2000).
KESIMPULAN DAN SARAN
Kesimpulan
Keragaman gen DGAT pada populasi sapi perah di Kabupaten Enrekang dapat diidentifikasi menjadi dua jenis alel, yaitu alel K dan A. Frekuensi alel K lebih tinggi dibanding alel A.
Saran
Perlu dilakukan penelitian lebih lanjut untuk mencari hubungan variasi alel-alel yang ditemukan dengan peningkatan kadar lemak pada populasi sapi perah yang diamati.
DAFTAR PUSTAKA
Amrawaty. H., dan S. Nurani, 2014. Aspek-aspek pengembangan usaha sapi perah di Provinsi Sulawesi Selatan. Buletin Peternakan. Dinas Peternakan dan Kesehatan Hewan Sulawesi Selatan.
Aryulina, C. Muslim, S. Manaf, dan E. Winarni. 2006. Biologi 3. Erlangga. Jakarta. Dedi, A. Dudi, A. Johar, H. Nena, dan S. Cece. 2008. Identifikasi gen IGF dan
hubungannya dengan pertumbuhan dan prolifikasi sebagai dasar seleksi bibit domba Garut berkelanjutan di kelompok peternak tunas Rahayu Wanaraja Garut. Prooceding Seminar Nasional Domba dan Kambing. Fakultas Peternakan. Universitas Padjajaran, Bandung.
Handiwirawan dan Subandriyo. 2004. Potensi Keragaman Sumberdaya Genetik Sapi Bali. Balai Penelitian Ternak. Prooceding Lokakarya Nasional Sapi Potong. Bogor.
Hatta, W. 2013. Survei Potensi Pengembangan Dangke Susu Sapi sebagai Alternatif Dangke Susu Kerbau di Kabupaten Enrekang, Sulawesi Selatan.Laporan Penelitian. Program Doktor PS Kesmavet Institut Pertanian Bogor. Bogor.
Indrawan, Primack, dan Supriatna. 2007. Biologi Konservasi. Yayasan Obor Indonesia. Jakarta.
Irfan, M. 2011. Kualitas Susu Sapi Perah pada Pemberian Pakan Tepung Daun Murbei (Morus Alba L). Skripsi. Fakultas Peternakan Universitas Hasanuddin, Makassar. Javanmard A, Asadzadeh N, Banabazi MH, and Tavakolian J. 2005. The Allele and
genotype frequencies of bovine pituitary specific transcription factor and leptin genes in iranian cattle and buffalo populations using PCR-RFLP. Iranian J Biotechnol. 3:104-108
Kesuma, M. Suranto, N. Ahmad, dan M. Anang. 2013. Dangke dari susu dengan waktu inkubasi berbeda pasca perendaman dalam larutan laktoferin. Jurnal Aplikasi Teknologi Pangan. 2(3): 155-158.
Kirby. 1990. DNA Fingerprinting. Stockton Press. New York
Kong, J. Oh, J. Lee, D. Yoon, Y. Choi, B. Cho, H. Lee, and G. Jeon. 2007. Association of sequence variations in DGAT1 gene with economic traits in Hanwoo (Korean cattle). Asian-Aust. J. Anim. Sci. 20 (6): 817-820.
Lelana, N.E., Sutarno, dan N. Etikawati. 2003. Identifikasi polimorfisme pada fragmen ND-5 DNA mitokondria sapi Benggala dan Madura dengan teknik PCR-RFLP. Biodiversitas. 4(1):1-6.
Li, K. Li, B. Fan, Y. Gong, S. Zhao, Z. Peng, dan B. Liu, 2000. The genetic diversity of seven pigs breeds in China, estimated by means of microsatellites. J. Anim. Sci. 9:1193-1195.
Mercade, A. Sanchez, and J.M. Folch. 2005. Exclusion of the Acyl CoA: diacylglycerol Acyltransferase 1 Gene (DGAT1 ) as a candidate for a fatty acid composition QTL on porcine chromosome 4:departament de cie` ncia animal i dels aliments, Facultat de Veterinaria, Universitat Auto` noma de Barcelona, Bellaterra 08193, Spain. Original article. 122:161-164.
Mohammed, A. Siham, Rahamtalla, S. Salah, A. Ahmed, Elhafiz, M. Bakhiet, Dousa, M. Khalid, Elamin, and M. Ahmed . 2015. DGAT gene in dairy cattle. Global Jurnal of Animal Sciencific Research. Department of Animal Production, Genetics and Animal Breeding, Faculty of Agricultural Technology and Fish Sciences. Alneelain University. 3(1):191-198.
Nei, M., dan S. Kumar. 2000. Molecular Evolution and Phylogenetics. Oxford University Press, New York.
Sari, C. Sumantri, I. Mathius, dan A. Anggraeni. 2014. Polimorfisme gen diasilgliserol asiltransferase1 dan asosiasinya dengan komponen asam lemak susu sapi perah Friesian Holstein. Jurnal JITV. Jurusan Ilmu Produksi dan Teknologi Peternakan, Institut Pertanian Bogor. 19(3):159-167.
Strzałkowska, E. Siadkowska, K. Słoniewski, J. Krzyżewski, and L. Zwierzchowski. 2005. Effect of the DGAT1 gene polymorphism on milk production traits in Black-and-White (Friesian) cows. Polish Academy of Sciences Institute of Genetics and Animal Breeding, Animal Science Papers and Reports. Poland. 23 (3): 189-197.
Sumadi, E. Hartatik, S. Romjali, Subandriyo, Subandiyah, dan Hartati. 2008. Identifikasi Karakteristik Genetik Sapi PO dan Silangannya di Peternakan Rakyat. Kerjasama Kemitraan Penelitian Pertanian dengan Perguruan Tinggi (KKP3T). Fakultas Peternakan UGM. Yogyakarta.
Suryanto, Dwi. 2003. Melihat Keanekaragaman Organisme Melalui Beberapa Teknik Genetika Molekuler. Program Studi Biologi Fakultas Matematika Dan Ilmu Pengetahuan Alam Universitas Sumatera Utara. Medan.
Tambasco, D. D., C. C. P. Paz, M. Tambasco-Studart, A. P. Pereira, M. M. Alencar, A. Freitas, L. L. Countinho, I. Packer and L. Regitano. 2003. Candidate genes for growth traits in beef cattle Bos Taurus x Bos Indicus. J. Anim. Bred. Genet. 120: 51-60
Utama, R. 2013. Identifikasi Keragaman Gen Dgat1|Eaei pada Sapi Friesian Holstein dengan Metode PCR-Rflp. Skripsi. Institut Pertanian Bogor. Bogor.
Van der Warf J. 2000. An overview of animal breedings programs. Identifiying and Incorporating Genetic Markers and Majors Genes in Animal Breeding Program. University of New England, England.
Vasconcellos, D. Talhari, A. Pereira, L. Coutinho, and, L. Reginato. 2003. Genetic characterization of Aberden Angus cattle using molecular. Genet. Mol. Biol. 26: 133-137.
Winter, A. Wolfgang, A. Fabian, Werner, K. Sonja, K. Srinivas, D. Gregor, B. Johannes, James, E. Womack, G. Thaller, and R. Fries. 2002. Association of a lysine-232/alanine polymorphism in a bovine gene encoding acyl-CoA:diacylglycerol acyltransferase (DGAT1) with variation at a quantitative trait locus for milk fat content. Journal of NATL Academy Sci. 99(14): 9300–9305. Yulianty. 2013. Keragaman Gen GH (growth hormone) pada Populasi Kambing Kacang
di Kabupaten Jeneponto. Skripsi. Fakultas Peternakan Universitas Hasanuddin, Makassar.
Yusuf. Polymerase Chain Reaction (PCR). 2010. Staf Pengajar Jurusan Kesehatan Masyarakat FIKK Universitas Negeri Gorontalo. Saintek. 5(6).
Lampiran Dokumentasi Penelitian
KOLEKSI SAMPEL DARAH DAN DNA
EKST RAKSI DNA
TEKNIK PCR – RFLP
PROSES
RIWAYAT HIDUP
AWAL REZKI AWAN (I111 11 010) lahir di Bulukumba, pada
tanggal 12 Juli 1994 dari pasangan Syamsur Adis dan Suwarni Syam. Penulis menyelesaikan Pendidikan Sekolah Dasr Negeri 20 Manyampa pada tahun 2005, kemudian melanjutkan ke Sekolah Menengah Pertama di SMP Negeri 1 Bulukumba, tamat pada tahun 2008 dan melanjutkan sekolah ke Sekolah Menengah Atas di SMA Negeri 1 Bulukumba pada tahun 2011. Pada tahun yang sama pula, penulis melanjutkan pendidikan ke Perguruan Tinggi Negeri dan lulus melalui Jalur Undangan di Program Studi Peternakan, Fakultas Peternakan, Universitas Hasanuddin, Makassar. Selama kuliah penulis pernah menjadi Asisten di Laboratorium Kesehatan Ternak. Penulis juga merupakan anggota Himpunan Mahasiswa Produksi Ternak Universitas Hasanuddin (HIMAPROTEK-UH).