Lampiran 1. Bentuk Umum Dari PROC MIXED
PROC MIXED pilihan-pilihan ;
BY nama-nama peubah ;
CLASS nama-nama peubah ;
ID nama-nama peubah;
MODEL peubah respon = nama-nama peubah / pilihan-pilihan ;
RANDOM nama-nama peubah / pilihan-pilihan ;
REPEATED nama-nama peubah / pilihan-pilihan ;
PARMS (nilai yang tercantum) ... / pilihan-pilihan ;
PRIOR sebaran / pilihan-pilihan ;
CONTRAST 'label' nama-nama peubah faktor tetap | nama-nama peubah faktor acak /
pilihan-pilihan
;
ESTIMATE 'label' nama-nama peubah nil ifaktor tetap | nama-nama peubah nilai factor acak /
pilihan-pilihan
;
LSMEANS ; nama-nama peubah / pilihan-pilihan ;
MAKE 'tabel' OUT=SAS-data-set ;
WEIGHT peubah;
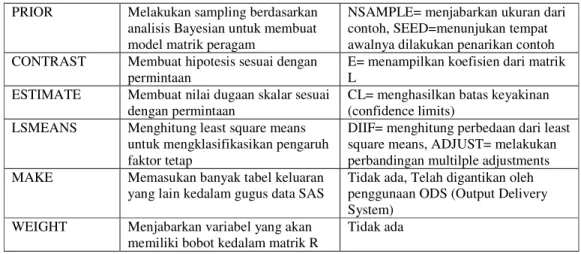
Lampiran 2. Fungsi dari masing-masing pernyataan yang digunakan dalam PROC MIXED
Pernyataan
Fungsi
Pilihan-pilihan penting
PROC MIXED
Menunjukan prosedur
DATA= nama file data SAS,
METHOD=metode yang akan dipakai
dalam pendugaan
BY
Melakukan analisis yang terpisah
dari observasi yang terpisah untuk
masing-masing grup
Tidak ada
CLASS
Menyatakan variabel kualitatif yang
menyusun variabel indikator dalam
matrik indikator
Tidak ada
ID
Mendaftarkan variabel tambahan
yang akan dimasukkan dalam tabel
nilai dugaan
Tidak ada
MODEL
Menjabarkan peubah bebas dan
faktor tetap yang menyusun matrik
X
S = meminta solusi untuk parameter
faktor tetap, DDFM= menjabarkan
metode pembilang bagi derajat bebas.
RANDOM
Menjabarkan faktor acak yang
menyusun matrik Z dan G
SUBJECT=membuat blok dalam
doagonal matrik, TYPE=menjabarkan
struktur peragam, S= meminta solusi
untuk parameter pengaruh acak, G =
menampilkan dugaan dari matrik G
REPEATED
Membangun matrik R
SUBJECT=membuat blok dalam
diagonal matrik, TYPE=menjabarkan
struktur peragam, R= menampilkan
dugaan untuk blok dalam matrik R,
Group= memungkinkan adanya
keheterogenan dalam subjek, LOCAL=
menambahkan matrik diagonal
kedalam matrik R
PARMS
Menjabarkan jaringan dari nilai
inisial untuk parameter peragam
(covariance)
HOLD dan NOITER= mengatur
parameter peragam atau rasio dari
parameter peragam tetap konstan,
PDATA= membaca nilai inisialdari
gugus data SAS
PRIOR
Melakukan sampling berdasarkan
analisis Bayesian untuk membuat
model matrik peragam
NSAMPLE= menjabarkan ukuran dari
contoh, SEED=menunjukan tempat
awalnya dilakukan penarikan contoh
CONTRAST
Membuat hipotesis sesuai dengan
permintaan
E= menampilkan koefisien dari matrik
L
ESTIMATE
Membuat nilai dugaan skalar sesuai
dengan permintaan
CL= menghasilkan batas keyakinan
(confidence limits)
LSMEANS
Menghitung least square means
untuk mengklasifikasikan pengaruh
faktor tetap
DIIF= menghitung perbedaan dari least
square means, ADJUST= melakukan
perbandingan multilple adjustments
MAKE
Memasukan banyak tabel keluaran
yang lain kedalam gugus data SAS
Tidak ada, Telah digantikan oleh
penggunaan ODS (Output Delivery
System)
WEIGHT
Menjabarkan variabel yang akan
memiliki bobot kedalam matrik R
Tidak ada
Lampiran 3. Jenis-jenis keluaran (output) dari PROC MIXED beserta fungsinya masing-masing.
Jenis Tabel
Fungsi
Tabel “Model Information”
Menampilkan model yang sesuai dengan percobaan,
variable-variabel yang dipakai dan metode yang sesuai
untuk data tersebut.
Tabel “Class Level Information”
Menampilkan banyaknya taraf yang dijelaskan dalam
pernyataan Class. Kita bisa menggunakan table ini untuk
memastikan apakah data yang kita masukan sudah benar.
Tabel “Dimention”
Menampilkan ukuran dari matrik-matrik yang termasuk
dalam model liniear campuran. Table ini bisa berguna
untuk menentukan waktu dalam proses pengolahan bagi
CPU dan keperluan dalam memori.
Tabel “Covariance Parameter
estimates”
Menampilkan hasil dugaan ragam dari model
Tabel Fitting Information”
Berisi beberapa informasi mengenai model yang cocok
dan juga nilai yang dihasilkan oleh restricted/ residual
likelihood.
Tabel “Type 3 test of Fixed Effects”
Menampilkan uji signifikansi dari pengaruh yang
disebutkan dalam pernyataan MODEL, nilai F-statistik
dan p-value tipe ke-3 yang sama dengan yang dihasilkan
oleh PROC GLM.
Lampiran 4. Analisis Ragam Individu (Rancangan Acak Kelompok), satu untuk setiap lima lokasi
(L1 sampai L5), data dari pengujian tujuh genotipe jahe putih kecil
Sumber
Keragaman
Derajat
Bebas
Jumlah Kuadrat
Kuadrat tengah
Lokasi Sukamulya
Blok
2
130.92
65.46
Genotipe
6
376.73
62.79
Galat
12
183.18
15.27
Total
20
690.84
Lokasi Wado
Blok
2
4.020
2.010
Genotipe
6
214.363
35.727
Galat
12
47.400
3.950
Total
20
265.783
Lokasi Malangbong
RESI3 Pe rc en t 10 5 0 -5 -10 99.9 99 95 90 80 70 60 50 40 30 20 10 5 1 0.1 Mean 0.026 6.344132E-16 StDev 2.713 N 105 KS 0.096 P-Value
Probability Plot of RESI 3
Normal
Obs er vat ion Or der
St a nd ar di ze d R es id u al 100 90 80 70 60 50 40 30 20 10 1 4 3 2 1 0 -1 -2 -3 -4
R es iduals Ver s us t he Or der of t he Data
(response is Y)
Blok
2
102.14
51.07
Genotype
6
50.88
8.48
Galat
12
206.83
17.24
Total
20
359.86
Lokasi Garut
Blok
2
17.06
13.30
Genotipe
6
79.79
8.53
Galat
12
301.50
25.13
Total
20
398.36
Lokasi Majalengka
Blok
2
6.723
3.361
Genotipe
6
17.896
2.983
Galat
12
26.744
2.229
Total
20
51.363
Lampiran 5. Hasil Uji Asumsi Data Jumlah Anakan Jahe Putih Kecil di Lima Lokasi.
Uji Kenormalan Galat
Uji Kebebasan Galat Percobaan
Fit t ed Value St an da rd iz ed R es id ua l 30 25 20 15 10 5 4 3 2 1 0 -1 -2 -3 -4
R esiduals Ver sus the Fitted Values
(response is Y) 0.6 0.5 0.4 0.3 0.2 0.1
95% Confidence Intervals for Sigmas
P-Value : 0.000 Test Statistic: 6.352 Levene's Test P-Value : 0.000 Test Statistic: 26.829 Bartlett's Test Factor Levels L5 L4 L3 L2 L1
Pengujian Kehomogenan Ragam Galat di Masing-Masing Lokasi
Uji Kehomogenan Ragam Galat
Lampiran 6. Hasil transformasi Box-Cox
5 4 3 2 1 0 -1 -2 -3 -4 -5 30 20 10 0 95% Confidence Interval S tD ev Lambda
Last Iteration Info
3,191 3,189 3,190 0,056 0,000 -0,056 StDev Lambda Up Est Low
Box-Cox Plot for Y
RESI4 Pe rc en t 0.8 0.6 0.4 0.2 0.0 -0.2 -0.4 -0.6 -0.8 99.9 99 95 90 80 70 60 50 40 30 20 10 5 1 0.1 Mean >0.150 -1.05736E-16 StDev 0.2281 N 105 KS 0.069 P-Value Pr obability Plot of R ES I 4 Normal
Obser vat ion Or der
St an da rd iz ed R es id ua l 100 90 80 70 60 50 40 30 20 10 1 4 3 2 1 0 -1 -2 -3 -4
R esiduals Ver sus the Or der of the Data
(response is log y) Fit t ed Value St an da rd iz ed R es id ua l 3.5 3.0 2.5 2.0 1.5 4 3 2 1 0 -1 -2 -3 -4
R esiduals Ver sus the Fitted Values
(response is log y)
Lampiran 7. Hasil uji asumsi data jumlah anakan jahe setelah transformasi.
Uji Kenormalan Galat Percobaan
Uji Kebebasan Galat Percobaan
Lampiran 8. Output Proc Mixed untuk menguji pengaruh faktor lokasi dan genotipe dengan
asumsi ragam galat berbeda antar lokasi.
The Mixed Procedure Model Information
Data Set WORK.COBA Dependent Variable Y
Covariance Structure Variance Components Group Effect Lokasi
Estimation Method REML Residual Variance Method None Fixed Effects SE Method Model-Based Degrees of Freedom Method Satterthwaite
Class Level Information Class Levels Values
Lokasi 5 L1 L2 L3 L4 L5 Genotip 7 JPK1 JPK2 JPK3 JPK4 JPK5 JPK6 JPK7 r 3 1 2 3 Dimensions Covariance Parameters 5 Columns in X 63 Columns in Z 0 Subjects 105
Max Obs Per Subject 1
Observations Used 105
Observations Not Used 0
Total Observations 105 Iteration History
Iteration Evaluations -2 Res Log Like Criterion 0 1 375.47372103
1 1 354.34877593 0.00000000 Convergence criteria met.
Covariance Parameter Estimates Cov Parm Group Estimate Residual Lokasi L1 15.2653 Residual Lokasi L2 3.9500 Residual Lokasi L3 17.2358 Residual Lokasi L4 25.1252 Residual Lokasi L5 2.2287 Fit Statistics
Res Log Likelihood -177.2 Akaike's Information Criterion -182.2 Schwarz's Bayesian Criterion -188.8 -2 Res Log Likelihood 354.3
Null Model Likelihood Ratio Test DF Chi-Square Pr > ChiSq
4 21.12 0.0003 Type 3 Tests of Fixed Effects Num Den Effect DF DF F Value Pr > F Lokasi 4 24.3 39.50 <.0001 r(Lokasi) 10 12 1.92 0.1414 Genotip 6 41.3 0.82 0.5584 Lokasi*Genotip 24 24.3 3.30 0.0023 Contrasts Num Den Label DF DF F Value Pr > F L1 vs L2 1 17.8 66.00 <.0001 L1 dan L2 vs L3 1 18.6 41.39 <.0001
Lampiran 9. Output Proc Mixed untuk menguji pengaruh faktor lokasi dan genotipe dengan
asumsi ragam galat berbeda antar grup hasil revisi.
The Mixed Procedure Model Information Data Set WORK.COBA Dependent Variable Y
Covariance Structure Variance Components Group Effect grup
Estimation Method REML Residual Variance Method None Fixed Effects SE Method Model-Based Degrees of Freedom Method Satterthwaite
Class Level Information Class Levels Values
Lokasi 5 L1 L2 L3 L4 L5 Genotip 7 JPK1 JPK2 JPK3 JPK4 JPK5 JPK6 JPK7 Ulangan 3 1 2 3 grup 3 1 2 3 Dimensions Covariance Parameters 3 Columns in X 63 Columns in Z 0 Subjects 105
Max Obs Per Subject 1
Observations Used 105
Observations Not Used 0
Total Observations 105 Iteration History
Iteration Evaluations -2 Res Log Like Criterion 0 1 375.47372103
1 1 355.36248870 0.00000000
Convergence criteria met. Covariance Parameter Estimates
Cov Parm Group Estimate Residual grup 1 16.2506 Residual grup 2 3.0893 Residual grup 3 25.1252
Fit Statistics
Res Log Likelihood -177.7 Akaike's Information Criterion -180.7 Schwarz's Bayesian Criterion -184.7 -2 Res Log Likelihood 355.4
Null Model Likelihood Ratio Test DF Chi-Square Pr > ChiSq 2 20.11 <.0001
Type 3 Tests of Fixed Effects Num Den Effect DF DF F Value Pr > F Lokasi 4 32.1 35.43 <.0001 Ulangan(Lokasi) 10 19.7 1.85 0.1168 Genotip 6 41.5 0.82 0.5583 Lokasi*Genotip 24 32.1 3.45 0.0006 Contrasts Num Den Label DF DF F Value Pr > F L1 vs L2 1 32.8 65.58 <.0001 L1 dan L2 vs L3 1 25.8 43.26 <.0001
Lampiran 10. Output Proc Mixed untuk menguji pengaruh lokasi dan genotipe hasil transformasi
.The Mixed Procedure Model Information
Data Set WORK.COBA Dependent Variable Y
Covariance Structure Diagonal Estimation Method REML Residual Variance Method Profile Fixed Effects SE Method Model-Based Degrees of Freedom Method Residual
Class Level Information Class Levels Values Lokasi 5 A B C D E Genotip 7 JPK1 JPK2 JPK3 JPK4 JPK5 JPK6 JPK7 r 3 1 2 3 Dimensions Covariance Parameters 1 Columns in X 63 Columns in Z 0 Subjects 1
Max Obs Per Subject 105
Number of Observations Read 105
Number of Observations Used 105 Number of Observations Not Used 0
Covariance Parameter Estimates Cov Parm Estimate Residual 0.01702
Fit Statistics
-2 Res Log Likelihood -21.7 AIC (smaller is better) -19.7 AICC (smaller is better) -19.7 BIC (smaller is better) -17.6
Type 3 Tests of Fixed Effects Num Den Effect DF DF F Value Pr > F Lokasi 4 60 28.64 <.0001 r(Lokasi) 10 60 2.12 0.0365 Genotip 6 60 1.27 0.2851 Lokasi*Genotip 24 60 1.91 0.0225