TAKSONOMI NUMERIK
Oleh :
Nama : Kasriati Heruningsih
NIM : B1J011155
Kelompok : 3 Rombongan : I
Asisten : Siska Damayanti
LAPORAN PRAKTIKUM BAKTERIOLOGI
KEMENTERIAN PENDIDIKAN DAN KEBUDAYAAN UNIVERSITAS JENDERAL SOEDIRMAN
FAKULTAS BIOLOGI PURWOKERTO
I. PENDAHULUAN
A. Latar Belakang
Klasifikasi dan identifikasi merupakan dua hal yang memiliki perbedaan, namun pada dasarnya saling berhubungan dalam taksonomi. Klasifikasi dapat diidentifikasikan sebagai penyusunan suatu organisme kedalam suatu kelompok taksonomi (taksa) berdasarkan persamaan atau hubungan. Klasifikasi mikroorganisme prokariota seperti bakteri dapat diketahui berdasarkan pengalaman dan juga teknik observasi, sifat biokimia, fisiologi, genetik dan morfologi yang merupakan ciri khas untuk kemudian dapat menggambarkan sebuah takson. Mikroorganisme memiliki cakupan yang sangat luas dan terdiri dari berbagai kelompok serta jenis, sehingga diperlukan suatu cara pengelompokan atau pengklasifikasian (Sembiring, 2003).
Taksonomi merupakan suatu langkah dalam pengelompokan jasad hidup ke dalam kelompok atau takson yang sesuai. Taksonomi dapat dilakukan secara numerik ataupun secara fenetik. Taksonomi secara numerik (numerical taxonomy) adalah taksonomi yang dikelompokkan berdasarkan pada informasi sifat suatu organisme yang dikonversikan kedalam bentuk yang sesuai untuk analisis numerik dan dibandingkan menggunakan computer. Sebaiknya 50 atau beberapa ratus karakter yang dapat dibandingkan, karakter tersebut di antaranya adalah karakter morfologi, biokimiawi, dan fisiologi. Koefisien asosiasi ditentukan diantara karakter-karakter yang dimiliki oleh dua atau lebih organisme (Felsenstein, 2004).
Pengklasifikasian bakteri memiliki beberapa kesulitan, kriteria dalam klasifikasi bakteri berbeda dengan mengklasifikasikan tumbuhan tingkat tinggi ataupun hewan tingkat tinggi. Hal ini didasarkan terutama pada sifat-sifat marfologinya. Klasifikasi bakteri didasarkan pada sebagiam sifat-sifat morfologi dan sifat-sifat fisiologinya termasuk imunologi. Pada dasarnya bakteri ketika di bawah mikroskop menunjukkan bentuk morfologi yang sama, namun sifat-sifat fisiologi mereka berlainan antara yang satu dengan yang lain. Ada beberapa golongan bakteri yang sama bentuknya, namun yang berlainan fungsi dalam
melangsungkan metabolisme. Ada pula suatu golongan yang dapat menyebabkan suatu penyakit, sedang golongan yang lain tidak, sehingga dari karakter tersebut bakteri dapat diklasifikasikan berdasarkan sifat-sifat morfologi (Harly, 2005).
B. Tujuan
Tujuan dari praktikum taksonomi numerik adalah untuk dapat mengetahui cara dan tahapan analisis kekerabatan bakteri dengan metode taksonomi numerik.
II. MATERI DAN METODE
A. Materi
Bahan dan alat yang digunakan dalam praktikum ini adalah hasil karakter mikroba yang diujikan dan laptop dengan program excel, PFE, MVSP, Paintshop Pro dan Words.
B. Metode
Cara kerja yang dilakukan dalam praktikum ini adalah :
Pemasukan data unit karakter ke dalam matriks n x t. 1. Buka program Excell.
2. Buka file baru (click new).
3. Label OTU diketikan pada kolom (sejumlah strain uji n).
4. Label unit karakter diketikan pada baris (row) sebanyak karakter uji (t).
5. Masing-masing nilai (+) atau (-) dimasukkan pada cell yang sesuai. 6. Matriks n x t selesai disusun, selanjutnya dicopykan ke PFE dengan
cara menghighligt seluruh matriks dan kemudian click copy. 7. Program excel diminimize.
Preparasi data dalam matriks n x t dengan program PFE. 1. Program PFE dibuka.
2. File baru dibuka dan click new.
3. Click paste untuk mengkopikan file data dari excel.
4. Pada baris pertama ketik : *L t n Nama Data yang akan dianalisis. 5. Data (+) dan (-) berturut-turut dikonversikan menjadi 1 dan 0 dengan
Replace All dari menu Edit.
6. Selanjutnya data dirapikan supaya lurus dalam baris dan kolom dengan jarak atau spasi.
7. Save file dalam format *.mvs dalam direktori MVSP, kemudian PFE diminimize.
Analisis data dengan program MVSP untuk mengkonstruksi matriks similaritas dan dengan dendogram.
1. Program MVSP dibuka.
2. Click file open, pilih data yang disimpan dengan format : *.mvs. 3. Select Analysis, pilih Clustering analysis.
4. Muncul kotak dialog, pada menu Option pilih Clustering method : Default UPGMA.
5. Pada similarity or distance, pilih jaccard coefficient (SJ) atau simple
matching coefficient (SSM).
6. Pada menu advanced : relust to display, checklist (√) semua lalu klik Ok.
7. Save file : Nama*.mvd, lalu klik save.
8. Print screen dendogram dan data hasil analisis cluster ke Ms. Word. 9. Blok data hasil analisis clusternya, lalu copykan ke Ms. Excel.
10. Buat data sorted dan unsorted dengan membandingkan tingkat similaritas tiap group.
11. Hitung indeks similaritasnya dengan rumus =Correl(data unsorted;data sorted)*100, lalu enter. Atau dengan rumus manual, yaitu :
SSM =
x 100% SJ = x 100%
III. HASIL DAN PEMBAHASAN
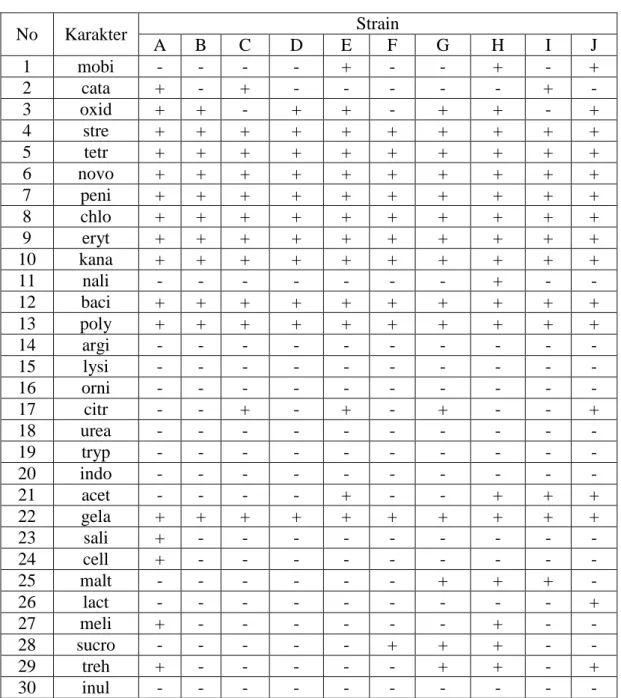
A. Hasil Tabel 1. Data Karakter Mikroba
No Karakter Strain A B C D E F G H I J 1 mobi - - - - + - - + - + 2 cata + - + - - - + - 3 oxid + + - + + - + + - + 4 stre + + + + + + + + + + 5 tetr + + + + + + + + + + 6 novo + + + + + + + + + + 7 peni + + + + + + + + + + 8 chlo + + + + + + + + + + 9 eryt + + + + + + + + + + 10 kana + + + + + + + + + + 11 nali - - - + - - 12 baci + + + + + + + + + + 13 poly + + + + + + + + + + 14 argi - - - - 15 lysi - - - - 16 orni - - - - 17 citr - - + - + - + - - + 18 urea - - - - 19 tryp - - - - 20 indo - - - - 21 acet - - - - + - - + + + 22 gela + + + + + + + + + + 23 sali + - - - - 24 cell + - - - - 25 malt - - - + + + - 26 lact - - - + 27 meli + - - - + - - 28 sucro - - - + + + - - 29 treh + - - - + + - + 30 inul - - - -
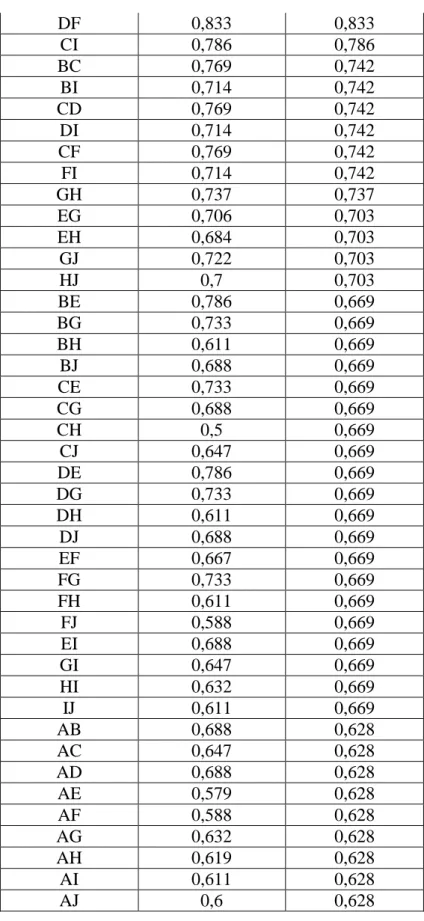
Tabel 2. Data Unsorted dan Sorted Jaccard Coeficient.
unsorted sorted
BD 1 1
EJ 0,875 0,875
DF 0,833 0,833 CI 0,786 0,786 BC 0,769 0,742 BI 0,714 0,742 CD 0,769 0,742 DI 0,714 0,742 CF 0,769 0,742 FI 0,714 0,742 GH 0,737 0,737 EG 0,706 0,703 EH 0,684 0,703 GJ 0,722 0,703 HJ 0,7 0,703 BE 0,786 0,669 BG 0,733 0,669 BH 0,611 0,669 BJ 0,688 0,669 CE 0,733 0,669 CG 0,688 0,669 CH 0,5 0,669 CJ 0,647 0,669 DE 0,786 0,669 DG 0,733 0,669 DH 0,611 0,669 DJ 0,688 0,669 EF 0,667 0,669 FG 0,733 0,669 FH 0,611 0,669 FJ 0,588 0,669 EI 0,688 0,669 GI 0,647 0,669 HI 0,632 0,669 IJ 0,611 0,669 AB 0,688 0,628 AC 0,647 0,628 AD 0,688 0,628 AE 0,579 0,628 AF 0,588 0,628 AG 0,632 0,628 AH 0,619 0,628 AI 0,611 0,628 AJ 0,6 0,628
Unsorted sorted BD 1 1 BF 0,933 0,933 DF 0,933 0,933 EJ 0,933 0,933 CI 0,9 0,9 BC 0,9 0,883 BI 0,867 0,883 CD 0,9 0,883 CF 0,9 0,883 DI 0,867 0,883 FI 0,867 0,883 BG 0,867 0,847 CG 0,833 0,847 FG 0,833 0,847 GI 0,8 0,847 BE 0,9 0,833 CE 0,867 0,833 DE 0,9 0,833 EF 0,833 0,833 EG 0,847 0,833 EI 0,833 0,833 BJ 0,833 0,833 CJ 0,8 0,833 DJ 0,833 0,833 FJ 0,767 0,833 GJ 0,833 0,833 IJ 0,767 0,833 AB 0,833 0,779 AC 0,8 0,779 AD 0,833 0,779 AE 0,733 0,779 AF 0,767 0,779 AG 0,767 0,779 AI 0,767 0,779 AJ 0,733 0,779 AH 0,733 0,767 BH 0,767 0,767 CH 0,667 0,767 DH 0,767 0,767 EH 0,8 0,767
FH 0,767 0,767
GH 0,833 0,767
HI 0,767 0,767
HJ 0,8 0,767
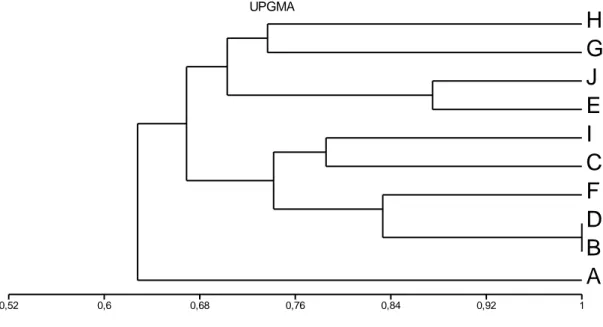
Gambar 1. Hasil Dendogram Jaccard Coeficient.
Gambar 2. Hasil Dendogram Simple Matching Coeficient.
UPGMA Jaccard's Coefficient
A
B
D
F
C
I
E
J
G
H
0,52 0,6 0,68 0,76 0,84 0,92 1 UPGMASimple Matching Coefficient
A
B
D
F
C
I
G
E
J
H
0,76 0,8 0,84 0,88 0,92 0,96 1 Indeks similaritas SJ dan SSM. SJ = Correl(Unsorted;sorted) x 100% = 82,3 %. SSM = Correl(Unsorted;sorted) x 100% = 85 %. B. Pembahasan
Taksonomi numerik didefinisikan sebagati metode evaluasi kuantitatif mengenai kesamaan atau kemiripan sifat antar golongan organisme, dan penataan golongan-golongan itu melalui suatu analisis yang dikenal sebagai “analisis kelompok” (cluster analysis) ke dalam kategori takson yang lebih tinggi atas dasar kesamaan-kesamaan tadi. Taksonomi numerik didasarkan atas bukti-bukti fenetik, artinya didasarkan atas kemiripian yang diperlihatkan obyek studi yang diamati dan dicatat serta bukan atas dasar kemungkinan-kemungkinan perkembangan filogenetiknya. Kegiatan-kegiatan dalam taksonomi numerik bersifat emperik dan data serta kesimpulannya selalu dapat diuji kembali melalui observasi dan eksperimen (Tjitrosoepomo, 1993).
Analisis taksonomi numerik harus diputuskan dari unit-unit taksonomi tingkat terendah yang dikaji dalam OTU’s (Opertional Taxonomic Unit). OTU’s dapat merupakan tumbuhan individual, pemisahan populasi dari jenis yang sama, pemisahan jenis dalam satu genus, pemisahan genus dan sebagainya. Selain hal tersebut, karakteristik yang tepat harus diseleksi untuk menunjukkan perbandingan OTU’s. Karakter-karakter tersebut diperoleh dari berbagai alat morfologis yang ada.
Ada dua metode yang dapat digunakan untuk mengetahui hubungan kekerabatan di antara organisme, yaitu metode fenetik dan metode filogenetik. Dan pada penelitian ini, penulis menggunakan metode fenetik atau dikenal dengan taksonomi numerik. Taksonomi numerik dikembangkan oleh Sokal dan Sneath (1963), yang didasarkan pada prinsip Adansonian, prinsip-prinsip tersebut yaitu :
1. Semakin banyak informasi yang terdapat dalam taksa dan semakin banyak karakter yang mendasarinya, maka semakin baik klasifikasi yang dihasilkan
2. Bersifat apriori, artinya setiap karakter memiliki nilai atau bobot yang sama dalam membentuk taksa alami
3. Semua persamaan antar dua taksa merupakan fungsi dari persamaan individual pada semua karakter di mana keduanya dibandingkan
4. Taksa yang berbeda dapat terjadi karena korelasi karakter yang berbeda-beda dalam kelompok yang dipelajari.
5. Taksonomi merupakan ilmu empiris.
6. Klasifikasi didasarkan pada persamaan fenetik.
Menurut Tjitrosoepomo (1993), langkah-langkah pengklasifikasian menggunakan metode taksonomi numerik meliputi :
a. Pemilihan obyek studi.
Pemilihan obyek studi dapat berupa varietas, jenis dan seterusnya. Yang penting untuk diperhatikan ialah bahwa unit-unit yang dijadikan obyek-obyek studi harus benar mewakili golongan organisme yang sedang diteliti. Unit terkecil sebagai obyek studi disebut unit taksonomi operasional (OTU’s).
b. Pemilihan ciri-ciri yang akan diberi angka (skor).
Ciri atau karakter yang dipilih untuk pemberian angka masing-mamsing diberi kode dan selanjutnya disusun dalam bentuk tabel atau matriks. c. Pengukuran kemiripan.
Kemiripan ditentukan dengan membandingkan tiap ciri pada masing-masing unit taksonomi operasional.
d. Analisis kelompok (cluster analysis).
Matriks dari sifat yang sama ditata kembali, sehingga OTU’s yang mempunyai kemiripan dapat dikelompokkan menjadi satu. Kelompok-kelompok itu disebut fenon dan dapat ditata secara hierarki dalam suatu diagram yang disebut dendogram.
Setelah klasifikasi dilakukan, ciri-ciri yang digunakan ditelaah kembali untuk menentukan ciri yang paling konstan dan bernilai untuk pembuatan kunci identifikasi
Menurut Weier (Riana, 2007) diagram percabangan yang sering disebut dengan dendogram yang dihasilkan oleh analisis kelompok adalah suatu metode yang digunakan untuk menggambarkan hubungan suatu analisis fenetik. Sedangkan analisis kelompok merupakan suatu metode yang dikelompokkan atau klaster dari OTU’s yang mempunyai koefisiensi similaritas yang tinggi untuk menggambarkan tingkat yang dapat diterapkan dalam hierarki taksonomi, kemudian dapat dikemas seperti genera dan lain-lain.
Pengelompokan OTU’s disusun berdasarkan kemiripan dalam suatu metode yang disebut cluster analysis. Dunn dan Everitt (1980), menyebutkan beberapa metode cluster analysis meliputi :
a. Single linkage clustering.
Metode ini membandingkan antara dua klaster atau kelompok berdasarkan koefisien similaritas maupun disimilaritasnya.
b. Complete-linkage clustering.
Metode ini tidak hanya dapat digunakan untuk membandingkan koefisien similaritas atau disimilaritas antara dua klaster tetapi dapat digunakan untuk membandingkan dengan kelompok similaritas atau disimilaritas yang terbesar atau terkecil.
c. Group average clustering
Metode ini membandingkan rata-rata koefisien similaritas atau disimilaritas antara dua klaster dan juga dengan rata-rata koefisien similaritas atau disimilaritas semua OTU’s.
d. Centroid clustering
Metode analisis ini dengan mencari nilai tengah dan jarak antar group OTU’s.
Menurut Ningrum (2012), analisis fenetik berdasarkan pada similaritas keseluruhan yaitu pasangan OTU’s diperbandingkan dari keseluruhan fakta-fakta yang tersedia dan suatu koefisien similaritas yang dideterminasi. Ada tiga metode
utama yang banyak digunakan dalam menghitung persamaan fenetik di antara unit taksonomi yaitu :
1. Koefisien asosiasi.
Koefisien ini merupakan metode yang paling sederhana dan menunjukkan sifat yang diekspresikan sebagai pernyataan yang bersifat positif atau negative.
2. Koefisien korelasi.
Koefisien ini merupakan proporsionalitas dan independensi antara pasangan vector-vektor OTU’s.
3. Pengukuran jarak di antara unit taksonomi.
Pengukuran jarak ini menggunakan ruang multi dimensi dengan satu dimensi untuk setiap sifat.
Prosedur kerja taksonomi numeric diawali dengan mebuka program Excell. Kemudian buka file baru (click new) dan ketikan label OTU pada kolom (sejumlah strain uji n). Lalu label unit karakter diketikan pada baris (row) sebanyak karakter uji (t). Masing-masing nilai (+) atau (-) dimasukkan pada cell yang sesuai. Kemudian matriks n x t yang telah selesai disusun, selanjutnya dicopykan ke PFE dengan cara menghighligt seluruh matriks dan kemudian click copy. Selanjutnya buka program PFE dan click new untuk membuka file baru. Click paste untuk mengkopikan file data dari excel yang telah disusun tadi. Pada baris pertama ketik : *L t n Nama Data yang akan dianalisis. Data (+) dan (-) berturut-turut dikonversikan menjadi 1 dan 0 dengan Replace All dari menu Edit. Selanjutnya data dirapikan supaya lurus dalam baris dan kolom dengan jarak atau spasi. Save file dalam format *.mvs dalam direktori MVSP, kemudian PFE diminimize.
Langkah selanjutnya adalah membuka program MVSP dan Click file open, pilih data yang disimpan dengan format : *.mvs. Kemudian select Analysis, pilih Clustering analysis. Muncul kotak dialog, pada menu Option pilih Clustering method : Default UPGMA. Pada similarity or distance, pilih jaccard coefficient (SJ) atau simple matching coefficient (SSM). Pada menu advanced : relust to
display, checklist (√) semua lalu klik Ok. Kemudian simpan file dengan format nama*.mvd, lalu klik save. Print screen dendogram dan data hasil analisis cluster
ke Ms. Word. Blok data hasil analisis clusternya, lalu copykan ke Ms. Excel. Buat data sorted dan unsorted dengan membandingkan tingkat similaritas tiap group. Hitung indeks similaritasnya dengan rumus =Correl(data unsorted;data sorted)*100, lalu enter.
Hasil dendogram SJ dengan SSM menujukkan perbedaan, yaitu pada
dendogram SJ, isolate G berkerabat dekat dengan isolate H dan isolate A berada
dalam outgroup yang memiliki kekerabatan yang paling jauh dari isolate yang lain. Pada dendogram SSM, isolate G justru lebih dekat kekerabatannya dengan
isolate C dan I. Isolate H justru berada dalam outgroup yang kekerabatannya jauh dari isolate yang lain. Nilai indeks similaritas SJ menunjukkan angka sebesar
82,3%, sedangkan nilai indeks similaritas SSM sebesar 85%. Hal tersebut
menunjukkan bahwa hasil dendogram sesuai dengan tingkat kekerabatan isolate tersebut. Menurut Raj et al. (2011), metode perhitungan Jaccard hanya didasarkan atas kesamaan morfologi pada setiap strain yang dibandingkan. Menurut Mulumba dan Kakudidi (2011), perhitungan dengan menggunakan SSM
didasarkan atas kesamaan dan perbedaan semua karakter yang didapat.
Koefisien Jaccard (Jaccard coefficient) akan mengabaikan karakter-karakter yang tidak ada pada kedua organisme, nilai-nilai tersebut diatur untuk membentuk matriks kesamaan (similarity matrix) dimana organisme dengan kesamaan tinggi dikelompokkan bersama dalam fenon (phenons) dan perbedaan (significance). Fenon tidak selalu jelas terlihat, namun fenon dengan kesamaan 80% seringkali dianggap satu spesies (bakteri) (Felsenstein, 2004). Simple Matching Coeficient digunakan sebagai ukuran kemiripan strain yang diamati (Felsenstein, 1981).
IV. KESIMPULAN DAN SARAN
A. Kesimpulan
Berdasarkan hasil dan pembahasan diperoleh kesimpulan sebagai berikut :
1. Tahapan analisis kekerabatan dengan taksonomi numeric, dilakukan dengan membuat data pada program excel. Selanjutnya dkonversikan datanya pada program PFE dan dibuat dendogramnya pada program MVSP. Lalu dihitung besar indeks similaritasnya.
2. Nilai indeks similaritas SJ menunjukkan angka sebesar 82,3%, sedangkan
nilai indeks similaritas SSM sebesar 85%. Hal tersebut menunjukkan bahwa
hasil dendogram sesuai dengan tingkat kekerabatan isolate tersebut.
B. Saran
Sebaiknya praktikum taksonomi numeric tidak dilakukan waktu malam hari. Sehingga praktikan dapat mengikuti rangkaian praktikum secara tertib dan kondusif.
DAFTAR REFERENSI
Dunn, G., & B.S. Everitt. (1982). An Introduction to Mathematical Taxonomy. New York : Cambridge University Press.
Felsenstein, J. 1981. Evolutionary trees from DNA sequences: A maximum likelihood approach. J Mol Evol 17: 368-376
Felsenstein, J. 2004 Inferring Phylogenies. Sunderland, MA: Sinauer Associates. Harly, J. P. 2005. Laboratory Exorcises in Microbiology sixth Edition. McGraw
Hill Companies, inc, 1211, Avence of the Amonical. New York.
Mulumba, John Wasswa dan Kakudidi, Esezah. Infraspecific Delimitation of Acacia Senegal (fabaceae) in Uganda. American Journal of Plant Sciences, 2011, 2, 345-353. Makerere University, Kampala, Uganda. Ningrum, S.U. 2012. Variasi Morfologi dan Hubungan Fenetik Populasi Sukun
(Artocarpus altilis (Parkinson) Fosberg) di Hutan Penelitian Balai Besar Penelitian Bioteknologi dan Pemuliaan Tanaman Hutan (BBPBPTH) Playen, Gunung Kidul. Universitas Negeri Yogyakarta.
Raj, L. Joelri Michael., Britto, S.J., Prabhu, S dan Senthilkumar, S.R. 2011. Identification of Agronomically Valuable Species of Crotalaria Based On Phenetics. ABJNA;2011;25;840-847. Thiruchirappalli 620 002. South India.
Riana Wijayanti. (2007). “Karakterisasi, Klasifikasi dan Hubungan Kekerabatan Berdasarkan Ciri Vegetatif Berbagai Kultivar Pisang Kepok (Musa paradisicca L) di Kebun Plasma Nutfah Pisang Giwangan, Yogyakarta”. Skripsi. Yogyakarta : FMIPA Universitas Negeri Yogyakarta.
Sembiring. 2003. “Kinerja Keuangan, Political Visibility, Ketergantungan pada Hutang, dan Pengungkapan Tanggung Jawab Sosial Perusahaan.”, Simposium Nasional Akuntansi 6
Sokal, R.R. and Sneath, P.H.A. 1963. Principles of Numerical Taxonomy. San Fransisco : WH Freeman and Company.
Tjitrosoepomo, Gembong. 1993. Taksonomi Tumbuhan (Spermatophyta). UGM. Yogyakarta.