11 Keragaman Genetik Ikan Cakalang (Katsuwonus pelamis) dari Kabupaten Jembrana dan Karangasem, Bali [Fakhrurrasi Fakhri, dkk.]
KERAGAMAN GENETIK IKAN CAKALANG (
Katsuwonus pelamis
)
DARI KABUPATEN JEMBRANA DAN KARANGASEM, BALI
GENETIC DIVERSITY OF SKIPJACK TUNA
(Katsuwonus pelamis)
FROM JEMBRANA AND KARANGASEM REGENCIES, BALI
FAkhrurrAsI FAkhrI1, InnA nArAyAnI1, I.G.nGurAh kAde mAhArdIkA2 1Jurusan Biologi Fakultas Matematika dan Ilmu Pengetahuan Alam Universitas Udayana
2 Indonesian Biological Research Centre, Universitas Udayana
Email:in86narayani@yahoo.com
IN TIS ARI
Pen elitian in i bertujuan un tuk m en getahui keragam an gen etik ikan cakalan g (Katsuw onus pelam is) yan g ada di Kabupaten J em bran a dan Karan gasem , Bali. Sam pel DNA diam bil dari 30 ekor di kabupaten J em bran a dan 30 ekor di kabupaten Karan gasem . Ekstraksi DNA dilakukan den gan m en ggun akan chelex 10% dan ampliikasi
menggunakan metode PCR dengan konigurasi HotStart pada con trol region DNA m itokon dria, m en ggun akan
prim er forw ard CRK dan primer reverse CRE. Analisis ilogenetika dilakukan dengan menggunakan metode
N eighbor Joining den gan m odel Kim ura 2-param eter. Variasi dari setiap sekuen diperoleh den gan m en ghitun g
jum lah, persen tase dari tiap haplotipe, keragam an haplotipe (hd) dan keragaman nukleotida (π) menggunakan program Dn aSP 5.10 . An alisis Fst (Fixation Index) berdasarkan frekuen si haplotipe m en ggun akan Arlequin 3.1. H aplotipe pada sam pel J em bran a berjum lah 28 haplotipe dan sam pel Karan gasem berjum lah 15 haplotipe den gan
nilai hd secara keseluruhan yaitu 0,997±0,006 dan untuk keragaman nukleotida (π) sebesar 0,04694. Nilai Fst
yan g diperoleh yaitu -0 ,0 0 334 dan Fst P sebesar 0 ,90 918 ±0 ,0 10 0 , m en un jukkan bahwa populasi ikan cakalan g di Kabupaten J em bran a dan Karan gasem berasal dari populasi in duk yan g sam a.
Kata kunci : keragam an genetik, ikan cakalang (Katsuw onus pelam is), Jem brana, Karangasem , keragam an haplotipe.
AB S TRACT
This research aim ed to determ in e the gen etic diversity of skipjack (Katsuw on us pelam is) from J em bran a an d
Karangasem Regencies, Bali. DNA samples were collected from 30 individual ish in the Jembrana district and 30 individuals in the district of Karangasem. DNA extraction was conducted using chelex 10% and the ampliication using PCR method with HotStart coniguration on mitochondrial DNA control region, with CRK forward primer and
CRE reverse prim er. Phylogen etic an alysis was perform ed in Neighbor J oin in g m ethod with Kim ura 2-param eter m odels. Variation s of each sequen ces were obtain ed by calculatin g the n um ber, the percen tage of each haplotype,
haplotype diversity (hd) and nucleotide diversity (π) analysed in DnaSP 5:10 program. Analysis Fst (Fixation Index) based on haplotype frequencies using Arlequin 3.1. There was 29 haplotypes identiied from Jembrana population,
an d 15 from Karan gasem . The haplotype diversity value was 0 .997 ± 0 .0 0 6, an d the n ucleotide diversity value
was of 0.04694. Fixation Index conirmed that both populations were phylogenetically originated from the same descendant cannot be diferentiated (P values of 0.90918 ± 0.0100).
Key w ords: genetic variation, skipjack tuna (Katsuw onus pelam is) haploty pe diversity .
P EN D AH U LU AN
Kepulau an In don esia ter letak di an tar a Sam uder a
Pasiik dan Samudera Hindia. Ikan cakalang merupakan
salah satu kom oditi ikan tan gkap di perairan tersebut yan g bern ilai ekon om i tin ggi setelah tun a sirip biru dan tun a sirip kun in g dan san gat dim in ati terutam a un tuk in dustri ikan kalen g karen a m em iliki kan dun gan gizi yan g tin ggi dan len gkap serta dagin gn ya yan g relatif lem but. Ikan cakalang juga banyak dijual dalam keadaan beku sebagai kom oditi ekspor dan dijual dalam keadaan
JURNAL BIOLOGI VOLUME 19 NO.1 JUNI 2015
12
In don esia 20 13)
Va r ia si gen et ik d a r i su a t u p op u la si m er u p a ka n ga m b a r a n a d a n ya p er b ed a a n in t r a sp esies. Den ga n ber kem ban gn ya tekn ologi, m u n cu l ber bagai m acam m etode baru di bidan g m olekuler. Berdasarkan h asil studi yan g telah dilakukan secara m eristik, m orfom etrik d an elektr ofor esis kar akter d ar i ikan cakalan g yan g ber ad a d i Sam u d er a Pasifik, bah wa var iasi gen et ik ikan cakalan g san gat kecil dan m en un jukkan sedikit p er bed aan an t ar in d ivid u d ar i ked alam an lau t yan g ber beda (Argue, 198 1). Pen elitian in i dilakukan un tuk m en getahui variasi DNA ikan cakalan g di wilayah Bali.
MATERI D AN METOD E
Pen gam bilan sam p el ikan cakalan g d ilaku kan d i Tem p a t Pelela n ga n I ka n (TPI ) Pen ga m b en ga n , d i Kabupaten J em bran a pada bulan Novem ber 20 13 dan Pasar Karan gasem pada bulan J an uari 20 14 m asin g-m asing sebanyak 30 sag-m pel. Sag-m pel yang diag-m bil adalah sirip pun ggun g berukuran 1x1 m m dan disim pan dalam tabun g yan g sudah diisi etan ol 96%.
Eks traks i D N A
Poton gan sirip pun ggun g (sekitar 1x1 m m ) tersebut dipin dah kan ke dalam tabun g eppen dorf yan g sudah berisi 250 µl larutan chelex 10 % dalam ddH2O (Walsh et
al., 1991) lalu diuraikan den gan vortex selam a 1 m en it.
Kem udian , cam puran disen trifuge (8 0 0 0 rpm ) selam a 1 m en it m en ggun akan m icrocen trifuge, dan diin kubasi selam a 60 m en it pada suhu 95°C m en ggun akan heating
block. Sam pel diuraikan kem bali den gan vortex selam a
1 m en it dan disen trifuge selam a 1 m en it (8 0 0 0 rpm ). Sam pel DNA berupasupern atan diam bil dan disim pan dalam lem ari es pada suhu 2°-8 °C sam pai digun akan lebih lan jut.
Am p lifikas i
Am p lifika s i d a er a h con t r ol r eg ion p a d a DN A m it okon d r ia d ila ku ka n m en ggu n a ka n p r im er CRK (5’-AGCTC AGCGC CAGAG CGCCG GTCTT GTAAA) dan CRE (5’-CCTGA AGTAG GAACC AGATG) (Lee, et al.,
1995) Proses ampliikasi diawali dengan pembuatan 2
buah m asterm ix. Master m ix I terdiri dari 5,5 µl ddH2O, 1,5 µl 10 x PCR Bufer (PE-II), 2,5 µl dNTPs (8 m M), 2,0 µl MgCl2 solution (25 m M), 1,25 µl prim er CRK (10 µM), 1,25 µl prim er CRE (10 µM) (Lee et al., 1995). Master m ix II terdiri dari 9 µl ddH2O, 1 µl 10 X PCR
Bufer (PE-II), 0 ,125 µl PE Am plitaq (5 units/ µl). Master m ix I dim asukkan ke dalam tabun g PCR yan g sudah berisi 1 µl DN A tem plate. Setelah itu 14 µl m asterm ix I dan dim asukkan ke dalam tabun g eppen dorf khusus untuk PCR. Tabung tersebut dim asukkan ke dalam m esin pen yiklus DNA (Therm al Cy cler, Applied Biosy stem→, Massach u ssets, USA). Su h u d in aikkan h in gga 8 0 °C d an d im asu kkan m ast er m ix II ke d alam m asin
g-masing tabung PCR. Konigurasi suhu ampliikasi yang
digun akan adalah sebagai berikut: fase pra-den aturasi (15 detik pada suhu 94°C), den aturasi (30 detik pada suhu 94°C), pen em pelan prim er (30 detik pada suhu
50 °C), pem an jan gan fragm en (45 detik den gan suh u 72°C). Sem ua siklus diulan g seban yak 38 kali. Un tuk pen yem purn aan , tahap akhir pem an jan gan dilakukan selama 10 menit pada suhu 72°C) dan tahap penyimpanan pada suhu 24°C selam a 1 m en it.
Ele ktro fo re s is
DNA hasil ampliikasi dielektroforesis pada gel agarosa 1% dalam SB (sodium borat) bufer yang mengandung
etidium brom ida pada tegan gan 10 0 Volt, den gan arus 40 0 mA selama 30 menit. Selanjutnya visualisasi fragmen DNA m enggunakan translum inator ultraviolet (UV) dan didokum en tasi den gan kam era digital.
Se ku e n s in g
Sekuensing fragmen DNA hasil ampliikasi dilakukan
di UC Berkeley DNA Sequen cin g Facility, USA.
An alis is D ata
Sekuen hasil penjajaran dianalisis dengan menggunakan
Clustal W dalam program M EGA 5 (Tam ura et al., 20 11)
kem u d ian d iban d in gkan d en gan seku en yan g ad a di
Gen Ban k m en ggun akan fasilitas BLAST (Basic Local Alignm ent Search Tool) yang terdapat dalam situs NCBI
(http :/ / w w w .n cbi.n lm .n ih.gov). Analisis ilogenetika d ila ku ka n d en ga n m en ggu n a ka n m et od e Neigh b or J oin in g (Tam ura et al., 20 11).
Variasi dari setiap sekuen dihitung un tuk m en getahui jum lah dan persen tase dari tiap haplotipe, keragam an h ap lotip e (ha p lot y p e d iv er sit y , hd ) d an ker agam an
nukleotida (π) yang diolah menggunakan program
Dn aSP 5.10 (Rozas et al., 20 0 3). Selan jutn ya dilakukan an alisis Fst (Fixation Index) un tuk m elihat perbedaan a n t a r p o p u la s i b e r d a s a r k a n fr e k u e n s i h a p lo t ip e
menggunakan program Arlequin 3.5 (Excoier et al.,
20 10 ).
H AS IL
Hasil ampliikasi produk PCR dari 60 sampel yang
diperoleh dari kabupaten J em bran a dan Karan gasem , Bali, dapat dilihat pada gam bar dibawah in i.
Gambar 1. Visualisasi hasil elektroforesis sampel kabupaten Karangasem
(KR1-KR12) dan kabupaten Jembrana (NG1). M: DNA 100 bp
ladder Pita dibawah 400 bp adalah primer dimer
13 Keragaman Genetik Ikan Cakalang (Katsuwonus pelamis) dari Kabupaten Jembrana dan Karangasem, Bali [Fakhrurrasi Fakhri, dkk.]
m en un jukkan bahwa ikan cakalan g yan g diperoleh di Kabu paten J em br an a d an Kar an gasem d ikon fir m asi seb a ga i sp esies Ka t su w on u s p ela m is. Sem u a d a t a diregistrasi di Gen Ban k den gan kode akses KM0 94130 -KM0 94173.
An alisis keragam an haplotipe m en ggun akan program Dn aSP 5.10 m en ghasilkan 41 haplotipe, di m an a sam pel J em bran a berjum lah 28 haplotipe dan Karan gasem 15 haplotipe den gan 2 haplotipe terdapat di kedua lokasi. Nilai hd secara keseluruhan adalah 0 ,997±0 ,0 0 6 dan
untuk keragaman nukleotida (π) sebesar 0,04694.
Tabel 1. Jumlah sampel (n), jumlah haploipe (h), keragaman haploipe
(hd) dan keragaman nukleoida (π) ikan cakalang (K. pelamis) dari populasi Jembrana dan Karangasem, Bali.
Lokasi N h Hd π
Jembarana 29 28 0,998±0,010 0,04684 Karangasem 15 15 1,000-0,024 0,04995 Keseluruhan 44 41 0,997±0,006 0,04694
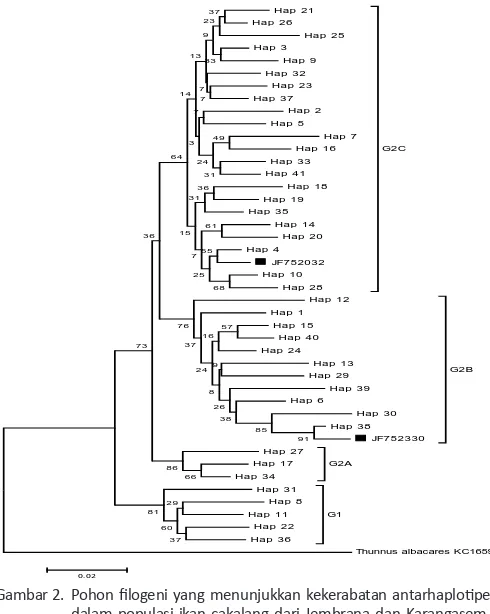
Hasil analisis ilogenetik untuk melihat kekerabatan
an tarhaplotipe m en ggun akan m etode Neighbor J oin in g den gan m odel Kim ura 2-param eter m en yatakan bahwa terdapat dua grup (clade) ikan cakalan g yaitu G1 dan G2 (Gam bar 2).
Gambar 2. Pohon ilogeni yang menunjukkan kekerabatan antarhaploipe dalam populasi ikan cakalang dari Jembrana dan Karangasem, Bali, dengan metode Neighbor Joining dan model Kimura 2-pa-rameter. Sampel dengan kode NG berasal dari Jembrana dan KR dari Karangasem. Sekuens standar Katsuwonus pelamis dari GenBank dengan kode akses ditandai dengan kotak persegi ().
Data h aplotipe dian alisis un tuk m en dapatkan n ilai Fst dan P m en ggun akan program Arlequin 3.5. Nilai
1,000-0,024 (nilai hd ≥0<0,5 keragaman haplotipe rendah, sedangkan hd >0,5≤1 keragaman haplotipe tinggi). Nilai
in i m en un jukkan bahwa populasi ikan cakalan g pada d aer ah J em br an a d an Kar an gasem m em iliki tin gkat keragam an h aplotipe tin ggi. H aplotipe yan g beragam in i m en un jukkan tin gkat keragam an gen etik yan g tin ggi dalam suatu populasi. Sem akin beragam haplotipe dari dua daerah tersebut m aka tin gkat keragam an gen etik akan sem akin tin ggi dan begitu juga sebalikn ya (Sm ith dan Chesser, 198 1). Nilai hd pada lokasi J em bran a (28 sam pel) lebih rendah dibandingkan dengan Karangasem (15 sam pel), yan g berarti bahwa sam pel dari J em bran a m em iliki tingkat keragam an yang lebih rendah dibanding den gan sam pel dari Karan gasem .
Pada pen elitian in i diperoleh hasil adan ya kedekatan genetik dengan data genetik ikan cakalang dengan melihat hasil sekuen DNA dan diperoleh tin gkat hom ologi 96-99%. Tem uan ini serupa dengan pola um um genetik ikan tun a secara um um di dun ia, yaitu bahwa populasi ikan tun a dun ia san gat bervariasi dan terjadi pen cam puran antarpopulasi pada saat m igrasi dalam rentang laut yang luas yan g disebut pan m ictic species. Pan m ictic species m em iliki kem am puan in dividu dalam suatu populasi un tuk bergerak bebas dalam habitatn ya yan g m en capai ribuan kilom eter dan akan terjadi perkawin an bebas an tar populasi (Dobzhan sky, 1950 ).
Perbedaan populasi kedua daerah tersebut dian alisa d en gan u ji Fst, h asil yan g d iper oleh yaitu -0 ,0 0 334
(nilai Fst ≥ 0 < 0,5 tidak berbeda nyata, Fst > 0,5 ≤1 berbeda nyata). Nilai Fst dari penelitian ini
(-0 ,0 0 334) m enunjukkan bahwa populasi J em brana dan Karan gasem tidak berbeda n yata. Walaupun keragam an haplotipen ya tin ggi dalam kedua populasi, n am un n ilai dari keragam an nukleotidanya rendah. Sebaran haplotipe pad a ked u a lokasi tid ak m em per lih atkan per bed aan st r u kt u r a n t a r p op u la si. P a d a sa m p el Ka r a n ga sem h an ya separuh dari sam pel keseluruh an yan g berh asil t er am p lifikasi seh in gga m en yebabkan n ilai m en jad i n egatif. Nilai Fst dapat bern ilai n egatif ketika jum lah sam pel sedikit (Bird et al., 20 11). Nilai P dari uji Fst yang
diperoleh adalah 0,90918±0,0100 (jika nilai P ≥0<0,05
m aka kedua populasi berbeda n yata, sedan gkan jika P
>0,5≤1 tidak berbeda nyata). Pada tingkat signiikan
0 ,0 5 kedua populasi tidak berbeda n yata.
Hal ini m engindikasikan bahwa populasi ikan cakalang dari J em bran a dan Karan gsem berasal dari populasi induk yang sam a dan berm igrasi dengan pola yang sam a.
S IMPU LAN
JURNAL BIOLOGI VOLUME 19 NO.1 JUNI 2015
14
U CAP AN TERIMAKAS IH
Penulis m engucapkan terim a kasih kepada Indonesian
Biod iv er sit y R esea r ch Cen t er (IBRC) yan g d iketu ai
oleh kepada Prof. Gusti Ngurah Kade Mahardika, yan g telah m em ban tu m en dan ai dan m em bim bin g selam a pen elitian , dan Dita Cahyan i (In don esian Biodiv ersity
R esearch Cen ter-IBRC) yan g m em ban tu selam a proses
an alisis keragam an haplotipe.
D AFTAR P U S TAKA
Argue, A.W., 1981. Report of the second skipjack survey and assess-m ent prograassess-m assess-m e workshop to review results froassess-m genetic analysis of skipjack blood sam ples. Tech. Rep. Skipjack Surv. Assessmt Progm. S. Pacif. Commn (Noumea. New Caledonia) 6, 1-37.
Bird, C.E., A.K. Stephen., E.S. Peter and J .T. Robert. 20 11.
Detect-ing and MeasurDetect-ing Genetic Diferentiation. CrustIssues19.
39:10 -27
Dobzhansky, T. 1950 . Mendelian populations and their evolution. Am erican Naturalist. 84:40 1-418
Excoier, L., G. Laval and S.Schneider. 2009. Arlequin ver 3.5, An
Integrated Software Package for Population Genetics Data Analysis. Com putational and Molecular Population Genet-ics Lab (CMPG). Institute of Zoology. University of Berne. Baltzerstrasse 6. 30 12 Bern, Switzerland
Ely, B., J . Vinas, J .R.A. Brem er, D. Black, L. Lucas, K. Covello, A.V. Labrie and E. Thelen. 20 0 5. Consequences of the historical
dem ography on the global population structure of two highly
migratory cosmopolitan marine ishes: the yellowin tuna
(Thunnus albacares) and the skipjack tuna (Katsuw onus
pelam is). BMC Evolutionary Biology . 5:19
Lee, W.J ., W.H. Howell, T.D. Kocher. 1995. Structure and Evolu-tion of Teleost Mitochondrial Control Regions. J Mol Evol. 41:54– 66
Per atu r an Men ter i Kelau tan d an Per ikan an Nom or PER.29/ MEN/ 20 12 tentang
Pedom an Penyusunan Rencana Pengelolaan Perikanan di Bidang
Penangkapan Ikan (Berita Negara Republik Indonesia Tahun 20 13 Nom or 46)
Report of the Sixteenth Session of the IOTC Scientiic Committee.
Decem ber 20 13
Rozas, J., J.C. Sanchez-DelBarrio., X. Messeguer, and R. Rozas. 20 0 3. DnaSP, DN A poly m orphism analy ses by coalescent and other m ethods. Bioinform atics 19:2496-2497
Sm ith, M.H., R.K. Chesser. 1981. Rationale for conserving genetic
variation of ish gen poll. Ecology Bullettin of Stockholm,
23: 119-130 .