Klustering Data Ekspresi Gen dengan Metoda-metoda
Berbasis Dekomposisi Nilai Singular
Studi Kasus: Data Ekspresi Gen Kanker Paru
Evi Noviani
1, Yoga Satria Putra
1, Kuntjoro Adji Sidarto
21
FMIPA Universitas Tanjungpura Pontianak 2
FMIPA Institut Teknologi Bandung [email protected]
Abstrak.Pada penelitian ini telah dikelompokkan data ekspresi gen kanker paru dengan memanfaatkan dekomposisi nilai singular. pasien kanker yang tergolong pada sub tipe
kanker paru yang sama dikelompokkan pada cluster yang sama berdasarkan data ekpresi
gen yang berupa matriks berukuran puluhan ribu sampai ratusan ribu. Pembentukan
cluster dilakukan dengan terlebih dahulu memodelkan ke dalam permasalahan optimisasi yaitu meminimumkan kesalahan penempatan pasien pada suatu kelompok, atau maksimumkan ketepatan dalam menempatkan pasien pada suatu kelompok. Masalah minimisasi/maksimisasi tersebut dapat diselesaikan dengan mengambil nilai singular kanan pertama dari dekomposisi nilai singular matriks data yang telah dinormalisasi. Dari proses ini didapatkan beberapa kelompok penderita kanker paru. Data ekspresi gen kanker paru telah dikelompokkan juga dengan menggunakan SVD-gaps. SVD-gaps ini
mengambil k vektor singular kanan pertama, yang kemudian dicari selisih antara elemen
vektor singular yang telah diurutkan. Dengan toleransi tertentu, maka selisih ini akan menentukan apakah dibentuk kelompok baru atau tidak. SVD-gaps menghasilkan 11 kelompok pasien kanker paru-paru.
Kata Kunci.SVD-gaps, Dekomposisi Nilai Singular, Data Ekspresi Gen, Klustering.
PENDAHULUAN
Rangkaian Deoxyribonucleic acid
(DNA) merekam setiap karakteristik dan sifat setiap mahluk hidup. Gen yang dikodekan dalam DNA berperan sebagai pesan di dalam sel yang memberitahu bagaimana sel berperilaku. Gen yang berbeda memberitahu sel bagaimana membuat protein yang berbeda. Satu kode gen untuk satu protein. Setiap sel memiliki banyak gen dan karena itu dapat membuat banyak protein yang berbeda. Beberapa protein mengontrol bagaimana sel berperilaku. Contohnya protein yang memberitahu sel untuk mereproduksi dengan membagi dirinya menjadi dua[1].
Dewasa ini informasi yang terkandung dalam DNA yang nantinya akan menghasilkan protein tertentu dapat diukur oleh teknologi microarray. Data
microarrayini menyajikan data tingkat ekspresi gen yang direpresentasikan melalui titik-titik warna.Satu sampel pada data microarrayterdiri dari ribuan atau
puluhan ribu gen. Pada pengolahan data
microarrayinilah menjadi hal yang menarik manakala didapatkan informasi penting dari data yang berukuran besar.
Data ekspresi gen yang dihasilkan dari data microarray juga dapat mengukur ekspresi manakala terjadi mutasi pada gen. Mutasi pada gen berarti bahwa gen tersebut telah rusak atau hilang. Sebuah mutasi dapat berarti bahwa terlalu banyak protein dibuat atau protein tidak dibuat sama sekali[1]. Seringkali,
mutasi yang menyebabkankanker adalah mutasi padagen-gen yangmengatur pertumbuhan sel[2].
Data level ekspresi gen manusia berukuran relatif besar, sesuai dengan jumlah gen pada manusia. Jadi melalui level ekspresi setiap gen ini diperlukan suatu metoda sedemikian sehingga data
mereka mempunyai karakteristik yang sama dan akan terbagi dalam kelompok yang berbeda manakala karakteristiknya berbeda.
Terdapat beberapa metode untuk mengklusterkan data dengan ukuran relatif besar. Diantaranya adalah matrix Factorisation[3], dan Dekomposisi Nilai Singular (Singular Value Decomposition/ SVD)[4,5, 6, 7]. Pada pencitraan digital, dekomposisi nilai singular telah digunakan. Pada pengiriman citra digital, reduksi dimensi pada data, sehingga hanya beberapa data saja yang digunakan akan tetapi gambar yang dikirim hampir sama dengan gambar asli, sangat menguntungkan terutama pada pemakaian memori.
Pada penelitian ini data ekspresi gen yang berukuran relatif besar akan diklusterkan dengan teknik-teknik yang menggunakan dekomposisi nilai singular. Algoritma akan diimplementasikan pada data ekspresi gen pasien kanker paru-paru[8].Garber mengelompokan data
microarray pasienkanker paru dengan menggunakan teknik hierarchical clustering. Data yang dipublikasikan oleh Garber inilah yang akan disimulasikan dengan menggunakan teknik yang menggunakan dekomposisi nilai singular.
METODE PENELITIAN
Misalkan diberikan suatu matriks data ekspresi gen, sebut , dengan ukuran
. Dengan menyatakan banyaknya
gen dan menyatakan banyaknya pasien yang akan dikelompokkan. Elemen matriks pada baris dan kolom , , menyatakan level ekspresi gen pada pasien
Data ekspresi gen dapat dinyatakan ke dalam graf bipartit dengan gen dan sampel masing-masing di kelompok titik yang berbeda [6].Bobot pada sisi yang menghubungkan antara gen dan sampel bernilai positif jika gen i relatif
over-expressed di sampel j, dan bernilai negatif jika gen i relatif under-expressed di sampel j.
Tujuan graf-bipartit tersebut adalah ingin membagi himpunan G(gen) kedalam 2 atau lebih grup, dan membagi himpunan S(sampel) kedalam 2 atau lebih grup, sehingga untuk masing-masing grup dan sampel level ekspresinya memiliki sifat hampir sama. Hal ini dikarenakan gen berkaitan yang terlibat dalam suatu proses akan aktif di himpunan sampel tertentu yang memiliki sifat hampir sama[6].
Misalkan adalah vektor indikator apakah gen i dimasukkan ke G1 ( )atau G2 ( ). Dan
misalkan pula adalah vektor indikator apakah sampel j dimasukkan ke
S1 ( ) atau S2 ( ).Tujuan
dari pengelompokkan ini adalah diinginkan ketika
, dan diinginkan ,
maka , ,dan . Dengan klustering ini diharapkan dapat memaksimalkan ketepatan dalam menempatkan gen dan sampel pada grup yang sesuai. Secara matematis dapat dituliskan sebagai berikut:
{ } { }
∑ ∑ (1)
Ketika aij> 0 maka tempatkan gen i dan sampel j di grup yang sama piqi= 1. Dan ketika aij< 0 maka tempatkan gen i dan sampel j di grup lain yang berbeda
piqi= -1.Dengan dimana
( ) ∑ | | dan
dengan (
) ∑ | |. Matriks
menunjukkan setiap entri di dipangkatkan . Untuk selanjutnya, menunjukkan setiap elemennya dipangkatkan k, yaitu .
Sehingga masalah optimisasi (1) tersebut dapat dituliskan sebagai berikut:
Pada pengolahan data selanjutnya digunakan normalisasi data terlebih dahulu, yakni dan
. Secara biologi, normalisasi data
dapat menghilangkan efek karena adanya perbedaaan kondisi saat eksperimen dan dilakukan sedemikian sehingga penekanan ada pada pengelompokan(bi-clustering) data [9].
HASIL DAN PEMBAHASAN
Pada penelitian ini akan dibahas implementasi dengan menggunakan algoritma dengan memanfaatkan hasil dari solusi analitik yang dibuat Higham, untuk selanjutnya disebut sebagai algoritma Higham. Untuk selanjutnya akan dibahas juga klustering dengan SVD-gaps pada data kanker paru-paru. SVD gaps pertama kali diperkenalkan oleh Douglas [5], yang menggunakannya untuk mengklusterkan data Yahoo!.
Klustering Dengan Algoritma Higham
Masalah klustering (2) dapat diselesaikan dengan teorema berikut[7]:
Teorema
Masalah ‖ ‖ ‖ ‖dapat
diselesaikan dengan mengambil
( ) dan
( ) dengan dan adalah
vektor singular kiri dan kanan kesatu dari
( ) ( ) .[7]
Berdasarkan teorema tersebut, didapat algoritma sebagai berikut[10]:
1. Input matriks
2. Hitung jumlah total ekspresi dari nilai mutlak dari elemen di setiap baris ( ) dan setiap kolom ( ). 3. Bentuk vektor dari jumlah total ekspresi baris ( ) dan kolom ( )
4. Bentuk matriks diagonal dengan
elemen diagonal utama adalah akar entri dari vektor dan , yang
dinotasikan dan
5. Hitung matriks .
6. Hitung bentuk dekomposisi nilai singular dari , ambil vektor singular kiri dan kanan Pertama. Hitung dan
sebagai solusi dari masalah
clustering.Plot atau juga
melibatkan singular kedua dan ketiga sebagai visualisasi hasil pengelompokan sampel data.
Penyelesaian di atas berlaku untuk matriks ekspresi gen dengan elemen positif, negatif atau nol. Sedangkan khusus untuk matriks dengan elemen tak negatif, telah disimulasikan oleh Noviani,et. Al pada kankerkanker Leukemia[11].
Klustering Dengan Svd-Gaps
Matriks data ekspresi gen, , dinormalisasi terlebih dahulu, baru kemudian dicari dekomposisi nilai singularnya. SVD yang digunakan adalah
truncated SVD, yakni hasil dekomposisinya hanya diambil vektor saja. Nilai ditentukan yaitu pada saat nilai singular mengalami lengkungan (elbow).Hal ini berarti bahwa hanya diambil vektor singular yang memiliki pengaruh cukup besar terhadap data.Berikut algoritma SVD gaps yang digunakan pada penelitian ini:
1. Tentukan [ ] 2. Untuk i = 1 : k,
3. Untuk , pisahkan dan tentukan selisih(gaps) diantara vektor singular kananyang telah diurutkan.. 4. Jika gaps antara baris dan dari
cukup besar, lebih dari sama dengan toleransi, maka bagi A dengan baris yang sesuai (columns).
5. Buat vektor kolom yang mengandung nama-nama cluster
numerik dari untuk semua kolom. 6. Setelah menemukan untuk semua
, bandingkan pola nama
Jika kolom dan memiliki pola nama
cluster yang sama dalam , maka kolom dan termasuk kedalam cluster yang sama. Toleransi yang digunakan untuk penentuan kluster baru pada penelitian ini adalah zscore dari selisih antara nilai vektor singular yang telah diurutkan lebih dari 3,5.
Implementasi Algoritma
Algoritma Higham dan SVD gaps pertama-tama diimplementasikan pada matriks dengan aturan sebagai berikut:
{ secara random dengan menggunakan distribusi uniform ( ).Sedangkan
menyatakan nilai yang dipilih secara
random mengikuti distribusi normal dengan rataan 0 dan standar deviasi 1.
Matriks di atas kemudian diacak kolom dan barisnya, kemudian diterapkan algoritma Higham dan SVD-gaps. Hasil algoritma tersebut dapat dilihat pada Gambar 1.
Gambar 4Hasil algoritma higham dan svd-gaps pada data simulasi
Pada Gambar 1 (a) disajikan matriks awal yang dibentuk ( ).
Kemudian matriks diacak baris dan kolomnya dan disajikan dalam Gambar 1(b). Matriks hasil acak inilah yang akan diterapkan algoritmaHigham dan SVD-gaps. Dapat dilihat pada Gambar 1 (c) dan (d) matriks data dapat diurutkan kembali. Matriks terdiri dari tiga submatriks yang relatif berbeda dengan entri yang lain. Gambar 1(c) merupakan matriks hasil
pengurutan kembali dengan menggunakan algoritma Higham. Sedangkan Gambar 1(d) merupakan matriks hasil pengurutan dengan menggunakan SVD-gaps.
Pada Gambar 1 dapat terlihatbahwa dengan algoritma Higham dan SVD-gaps, blok matriks dapat disusun kembali menjadi tiga. Hal ini menunjukkan bahwa dari data yang ada dapat dikelompokkan menjadi tiga kluster.
Untuk selanjutnya, dilakukan simulasi pada data kanker paru-paru. Data ekspresi gen kanker paru-paru yang akan diolah, terlebih dahulu diubah menjadi bentuk matriks data. Entri pada baris i dan kolom
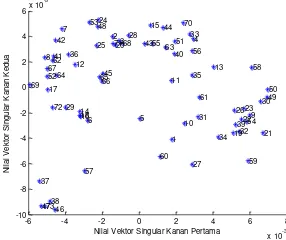
j matriks tersebut menunjukkan ekspresi gen i pada pasien j. Pada Gambar 2 dapat dilihat hasil simulasi dengan menggunakan algoritma Higham.
Gambar 5Nilai vektor singular pertama yang telah diurutkan dengan algoritma higham
Gambar6Nilai vektor Singular Pertama yang telah diurutkan dengan algoritma Higham
Jika diperhatikan, data-data pada Gambar 3 akan sulit untuk menentukan pasien termasuk kluster mana. Oleh karena itu, selanjutnya klustering dicoba dengan menggunakan SVD-gaps.
Dengan menggunakan algoritma pada SVD-gaps dapat diketahui bahwa pasien kanker paru-paru terbagi menjadi 11 kluster. Pasien normal termasuk dalam satu kluster. Sedangkan kluster 3 didominasi oleh pasien Adenocarsinoma. Hasil penghitungan dapat dilihat pada Tabel 1.
TABEL 3Hasil klustering pasien kanker paru
Nomor
Nilai Vektor Singular Kanan Pertama
Nomor pasien normal terkelompokkan menjadi satu kelompok. Sedangkan kluster 3 didominasi oleh pasien adenocarsinoma. Kluster 8 hanya terdiri dari pasien LCLC.
Pada pembagian kluster dengan SVD-gaps tersebut, dapat terlihat pada Tabel 1 terdapat kluster yang hanya terdiri dari satu anggota.Terdapat pasien SCC tergolong pada kluster 3 yang anggota klusternya didominasi pasien Adeno. Yang menyebabkan hal ini terjadi sangat dipengaruhi oleh penentuan toleransi yang digunakan untuk pembentukan suatu kluster. Pada penelitian ini digunakan nilai
zscore 3,5. Selain penentuan toleransi gaps, hasil klustering juga dipengaruhi pemilihan nilai k pada saat penentuan
truncated-SVD.
KESIMPULAN
Data ekspresi gen telah dapat dikelompokkan dengan menggunakan teknik dekomposisi nilai singular. Dengan menggunakan algoritma Higham belum ada aturan mekanisme suatu pasien termasuk kluster mana, akan tetapi penentuan kluster dilakukan secara subjektif dengan melihat plot nilai vektor singular kanan pertama. Hal ini akan efektif ketika data yang diteliti nilai vektor singular kanannya antara kluster yang satu dengan yang lainnya terpisah sangat jelas. Tetapi untuk data kanker paru pada penelitian ini hampir tidak dapat dibedakan antara kluster yang satu dengan yang lain. Berbeda halnya dengan algoritma Higham, pada algoritma SVD-gaps sudah ada kriteria penentuan suatu kluster, yaitu melalui besarnya toleransi pada selisih antara nilai vektor singular kanan. Setiap pasien sudah ditetapkan termasuk kluster mana. Namun demikian,
untuk memperbaiki ketepatan dalam menentukan kluster diperlukan kajian mengenai besarnya toleransi ini dan penentuan sampai dimensi berapa harus dihitung truncated-SVDnya.
UCAPAN TERIMA KASIH
Penelitian ini merupakan bagian dari Penelitian Pekerti tahun 2012 yang dibiayai Dikti.Terima kasih penulis ucapkan kepada Jurusan Matematika dan Fakultas MIPA Universitas Tanjungpura dan Dept. Matematika FMIPA ITB serta cancer-starts#how_starts. Akses tanggal 30 April 2013
_____, The Relationship Between DNA
and Cancer.
http://www.foundationmedicine.com/patients-dna-cancer.php. Akses tanggal 30 April 2013
Brunet, JP., Pablo Tamayo, T.R. Golub, & J.P. Mesirov. (2004). Metagenes and Molecular Pattern Discovery Using Matrix Factorization. Procidings of The National Academy of Sciences:
101.p. 4164-4169.
Noviani, Evi & Putra,Y. S., (2010), Pengklasteran Pasien Kanker Leukemia Berdasarkan Data Ekspresi Gen dengan Menggunakan Dekomposisi Nilai Singular. Journal of Mathematics and Its Applications (Limits): 7, p. 49-56 Douglas, E.P. (2008), Clustering datasets
Mathematics, The Graduate school of the college of charleston.
Higham, Desmond J, Gabriela K., J. Keith Vass. 2005. Analysis of the singular value decomposition as a tool for processing
microarray expression data. In: Proceedings of ALGORITMY 2005, 13-18 March 2005, p.250-259, Podbanské, Slovakia.
Higham, Desmond J, Gabriela K., J. Keith Vass. 2007. Spectral Analysis of Two-signed Microarray Expression Data.
Mathematical Medicine and Biology:
24, p. 131-148
Garber, M. E., et.al.,(2001). Diversity of Gene Expression in Adenocarcinoma of The Lung. Procidings of The
National Academy of Sciences: 98, p. 13784–13789.
Kluger, Y., R Basri, J.T Chang, et al.(2003). Spectral Biclustering of Microarray Data: Coclustering Genes and Conditions. Genome Research.13, 703-716.
Noviani, Evi, K. A. Sidarto, Y. S. Putra, (2012). Pengelompokan Pasien Kanker Liver Berdasarkan Data Ekspresi Gen dengan Struktur Papan Catur. Prosiding KNM XVI- 3-6 Juli 2012- UNPAD, Jatinangor.