92
Segmentasi Jaringan Otak Putih, Jaringan Otak Abu-Abu, dan Cairan Otak dari
Citra MRI Menggunakan Teknik K-Means Clustering
Nurhasanah
Jurusan Fisika F.MIPA Universitas Tanjungpura
email : [email protected]
Abstrak
Magnetic Resonance Imaging (MRI) adalah teknik pencitraan medis yang digunakan dalam radiologi untuk memvisualisasi struktur internal secara rinci. Segmentasi jaringan otak putih, jaringan otak abu-abu dan cairan otak penting dilakukan untuk meningkatkan pemahaman tentang pathophysiology beberapa gangguan neurologis. Oleh karena itu, dibutuhkan teknik segmentasi citra untuk mensegmentasi citra jaringan otak lebih akurat dan efisien. Penelitian ini mendesain dan mengembangkan program berdasarkan algoritma K-Means clustering dengan menggunakan informasi yang saling melengkapi yang tersedia pada citra T1, T2 dan PD dari MRI. Algoritma K-means clustering dipilih karena sederhana, mudah diimplementasikan, dan mampu menangani data outlier. Gabungan dari ketiga citra MRI tersebut akan disegmentasi menjadi jaringan otak putih, jaringan otak abu-abu dan cairan otak secara otomatis setelah melalui pre-processing. Waktu segmentasi juga dihitung. Dihasilkan program segmentasi citra MRI menggunakan teknik K-means clustering yang mudah diimplementasikan dan metodenya bekerja secara efektif untuk mengklasifikasi jaringan otak putih, jaringan otak abu-abu dan cairan otak.
Kata kunci : Magnetic Resonance Imaging, K-Means clustering, jaringan otak
1. Pendahuluan
Magnetic Resonance Imaging (MRI)
adalah
teknik
pencitraan
medis
yang
digunakan
dalam
radiologi
untuk
memvisualisasikan struktur internal secara
rinci. Alat ini menghasilkan kontras yang baik
sehingga berguna pada pencitraan otak, otot,
jantung, dan kanker dibandingkan dengan
teknik pencitraan medis yang lain seperti
computed tomography (CT) atau sinar-X.[1]
Segmentasi jaringan otak pada citra
Magnetic Resonance (MR) merupakan isu
penting dalam analisis beberapa penyakit otak
(gangguan
neurologis),
seperti
multiple
sclerosis atau penyakit Alzheimer. Segmentasi
jaringan otak putih, jaringan otak abu-abu dan
cairan otak dilakukan untuk meningkatkan
pemahaman tentang pathophysiology beberapa
gangguan neurologis.[2] Hal ini penting untuk
mendefinisikan batas-batas organ secara jelas,
karena ini digunakan untuk perhitungan dosis
dari setiap treatment.[3]
Penelitian
ini
mendesain
dan
mengembangkan
program
segmentasi
berdasarkan algoritma K-Means clustering
dengan menggunakan informasi yang saling
melengkapi yang tersedia pada citra T1, T2
dan PD dari MRI. Gabungan dari ketiga citra
tersebut akan disegmentasi menjadi jaringan
otak putih, jaringan otak abu-abu dan cairan
otak (CSF) secara otomatis setelah melalui
pre-processing
.
2. Dasar Teori
Magnetic Resonance Imaging (MRI)
adalah suatu alat kedokteran di bidang
pemeriksaan
diagnostic
radiologi,
yang
menghasilkan rekaman gambar potongan
penampang tubuh/organ manusia dengan
menggunakan medan magnet berkekuatan
antara 0,064 – 1,5 tesla (1 tesla = 1000 Gauss)
dan resonansi getaran terhadap inti atom
hidrogen.[4]
Citra
MRI
konvensional
memberikan informasi morfologi berupa citra
T1, T2 dan PD-weighted. Ketiga citra tersebut
memberikan informasi tentang sifat fisik air
pada jaringan. T1, spin-lattice relaxation time,
berbanding terbalik dengan jumlah gerakan
molekul dalam jaringan pada frekuensi
resonansi. T2, spin-spin relaxation time,
berbanding terbalik dengan jumlah gerakan
dalam jaringan pada frekuensi di bawah dan
sama dengan frekuensi resonansi. Selanjutnya
PD (proton density) menyediakan gambar
kepadatan proton. Ketiga citra tersebut
memberikan informasi yang berbeda dan
saling melengkapi. Ketiga pengukuran berbeda
ini memberikan perbedaan tingkat kontras dari
berbagai jenis jaringan lunak pada otak
manusia.
2.1 Pre-processing
Pre-processing
merupakan
proses
yang digunakan untuk meningkatkan kualitas
tampilan citra agar memiliki format yang lebih
baik sehingga citra tersebut menjadi lebih
mudah diolah lebih lanjut.
Perbaikan
kualitas
citra
(image
enhancement) adalah proses memperjelas dan
mempertajam fitur tertentu dari citra agar citra
lebih mudah dipersepsi atau dianalisis lebih
teliti. Secara matematis, image enhancement
dapat diartikan sebagai proses mengubah citra
f(x,y) menjadi f’(x,y) sehingga ciri-ciri yang
terlihat pada f(x,y) lebih ditonjolkan. Image
enhancement tidak meningkatkan kandungan
informasi, melainkan jangkauan dinamis dari
ciri agar bisa dideteksi lebih mudah dan tepat.
2.2 Segmentasi
Segmentasi citra merupakan pusat (a
central preoccupation) dalam analisis citra.
Proses segmentasi membagi citra menjadi
bagian-bagian dimana bagian-bagian tersebut
dapat dipandang sebagai objek-objek mandiri
yang dapat dianalisa.
Segmentasi citra merupakan teknik
untuk membagi suatu citra menjadi beberapa
daerah (region) dimana setiap daerah memiliki
kemiripan atribut.[5] Atribut yang paling dasar
untuk
segmentasi
adalah
amplitudo
pencahayaan (luminance) citra untuk gambar
monokrom dan komponen warna untuk
gambar berwarna. Tepi gambar dan tekstur
juga
merupakan
atribut
berguna
untuk
segmentasi.
Segmentasi
hanya
membagi
gambar, tetapi tidak berusaha untuk mengenali
segmen satu per satu atau hubungan mereka
satu sama lain.
Segmentasi yang akan di bahas di sini
yang berdasarkan clustering. Segmentasi ini
menggunakan
data
multidimensi
untuk
mengelompokkan
pixel citra ke dalam
beberapa cluster. Pada umumnya pixel
di-cluster berdasarkan kedekatan jarak
antar-pixel. Keberhasilan dari proses segmentasi
berbasis cluster ditentukan oleh keberhasilan
dalam
mengelompokkan
fitur-fitur
yang
berdekatan ke dalam satu cluster.
2.3 K-Means Clustering
K-Means
merupakan
salah
satu
metode data clustering non hirarki yang
berusaha mempartisi data yang ada ke dalam
satu atau lebih cluster/kelompok. Metode ini
mempartisi data ke dalam cluster/kelompok
sehingga data yang memiliki karakteristik
yang sama dikelompokkan ke dalam satu
cluster yang sama dan data yang mempunyai
karakteristik yang berbeda dikelompokkan ke
dalam kelompok yang lain.[6]
K-means
mengelompokkan
objek
menjadi K cluster. Metode ini akan mencari
pusat cluster dan batas-batas cluster melalui
proses perulangan (iterative). Kedekatan atau
kemiripan (similarity) suatu objek dengan
objek lain atau dengan pusat cluster dihitung
dengan menggunakan fungsi jarak. Pada
umumnya
K-means
menggunakan
jarak
Euclidean
untuk
menghitung
kemiripan
tersebut. K-Means mampu meminimalkan
rata-rata jarak setiap data ke claster-nya. Metode
ini dikembangkan oleh J. MacQueen pada
tahun 1967.
Algoritma
K-means
dipengaruhi
jumlah pusat cluster, pemilihan inisial pusat
cluster, bagaimana sampel diambil, dan sifat
geometri
dari
data.
Proses
clustering
menggunakan metode K-Means ini dilakukan
dengan algoritma dasar sebagai berikut :[7]
1. Menentukan jumlah cluster.
2. Mengalokasikan data ke dalam cluster
secara random
3. Menghitung centroid/rata-rata dari data
yang ada di masing-masing cluster
4. Mengalokasikan masing-masing data ke
centroid/rata-rata terdekat
Kembali ke langkah 3, apabila masih ada
data yang berpindah cluster atau apabila
perubahan nilai centroid, ada yang di atas nilai
threshold yang ditentukan atau apabila
perubahan nilai pada objective function yang
digunakan di atas nilai threshold yang
ditentukan.
3. Metode Penelitian
3.1 Desain Program
Pengolahan citra di sini dilakukan melalui
tahap pre-processing, proses clustering dan
pemisahan objek. Secara garis besar rancangan
program ditunjukkan pada Gambar 1.
Pre-processing
merupakan
proses
yang
digunakan untuk meningkatkan kualitas citra
agar dapat menghasilkan segmentasi yang
terbaik. Program ini akan melakukan
pre-processing yang menggunakan thresholding
(pengambangan),
erosion,
dilation
dan
histogram equalization.
Proses thresholding adalah proses untuk
mengubah gambar yang memiliki tingkat
warna
abu-abu
menjadi
gambar
biner
berdasarkan suatu nilai tertentu yang menjadi
tolok ukurnya. Proses pengambangan citra
grayscale untuk menghasilkan citra biner
adalah sebagai berikut.
g(x,y)=
(1)
Dengan g(x,y) adalah citra biner dari citra
grayscale f(x,y), dan T menyatakan nilai
ambang. Nilai T pada gambar tersebut
menunjukkan batas yang menjadi tolok ukur
pengubahan nilai tiap pixel, apakah menjadi 0
(hitam) atau 255 (putih).
Selanjutnya kombinasi dari operasi erosi
(erosion)
dan
operasi
dilasi
(dilation)
dilakukan. Proses ini disebut proses opening
yang secara matematis dapat dinyatakan
dengan :
0(A,B) = AoB = D(E(A,B),B) (2)
Algoritma histogram equalization,
mulai dari pengambilan nilai untuk histogram,
kemudian perhitungan histogram menjadi
histogram
yang
ter-equalize,
hingga
pengubahan pada tiap pixel pada gambar agar
histogram dari gambar tersebut menjadi
histogram yang ter-equalize. Teknik ini
melakukan distribusi ulang terhadap distribusi
intensitas dari histogram awal. Histogram
puncak dan lembah hasil ekualisasi akan
digeser atau lebih disebarkan (spreading).
Nilai piksel baru n(g) dinyatakan sebagai
berikut,
(3)
dimana, N menyatakan banyaknya pixel pada
citra, g menyatakan nilai gray level awal yang
nilainya dari 1…L-1(L adalah nilai gray level
maksimum), dan c(g) menyatakan banyaknya
pixel yang memiliki nilai sama dengan g atau
kurang. Secara matemtis dinyatakan sebagai
(4)
dengan h(i) menyatakan histogram awal.
Gambar 1
Bagan Aplikasi Secara Garis Besar
Proses clustering di sini dilakukan
dengan mengklasifikasi karakteristik citra
berdasarkan K-Means clustering. Jumlah klas
dalam klasifikasi ini terdiri dari 4 klas, yaitu
klas 1 untuk latar belakang, klas 2 untuk cairan
otak (CSF), klas 3 untuk jaringan otak
abu-abu, dan klas 4 untuk jaringan otak putih.
Secara garis besar proses clustering
menggunakan metode K-Means ditunjukkan
pada gambar 2. Proses pemisahan citra
dilakukan
dengan
thresholding
(pengambangan). Seperti pada persamaan (1).
Proses ini dilakukan berdasarkan hasil
clustering.
Gambar 2 Flowchart K-Means Clustering
3.2 Pengujian Program
Pengujian program dilakukan dengan
meng-input-kan file citra MRI kepala yang
terdiri dari PD, T1 dan T2 ke dalam program
yang telah dibuat. Citra yang diinput ke dalam
program seperti yang terlihat pada gambar 3.
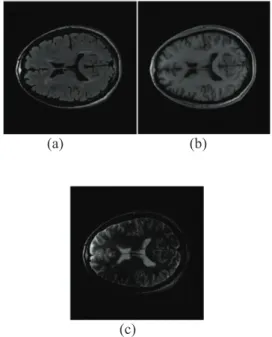
(a) (b)
(c)
Gambar 3 Citra MRI: (a) PD (b) T1 (c) T2
4. Hasil dan Pembahasan
4.1. Pengujian Pre-Processing
Pre-processing merupakan kumpulan
dari proses yang digunakan untuk dapat
menghasilkan
segmentasi
yang
terbaik.
Program ini akan digunakan pre-processing
yang menggunakan thresholding, erosion,
dilation dan histogram equalization. Untuk
menghindari misclassification, citra selain
jaringan otak harus dihilangkan. Proses
thresholding dan opening dilakukan untuk
menghilangkan citra tulang dan citra selain
otak lainnya.
Operasi
erosi
berguna
dalam
menghilangkan
objek-objek
kecil
yang
terdapat pada citra sedangkan operasi dilasi
memperbesar batas dari objek yang ada
sehingga objek terlihat semakin besar. Proses
ini disebut proses opening yang bertujuan
mencegah penurunan ukuran objek secara
keseluruhan. Proses opening secara matematis
dapat dinyatakan dengan :
0(A,B) = AoB = D(E(A,B),B)
Hasil penghilangan citra tulang dapat
dilihat pada gambar 4a. Kemudian citra otak
dipertegas
dengan
peningkatan
kontras
menggunakan
algoritma
histogram
equalization. Teknik ini melakukan distribusi
ulang terhadap distribusi intensitas dari
histogram awal. Hasil perbaikan citra pada
tahap ini dapat dilihat pada gambar 4b.
(a) (b)
Gambar 4 (a) Hasil Penghilangan Citra Tulang (b) Hasil Perbaikan Kualitas Citra
4.
2. Pengujian Proses clustering
Proses clustering dilakukan dengan
mengklasifikasi intensitas citra berdasarkan
K-Means cluster. Metode ini mengalokasikan
data items ke masing-masing cluster secar
a
unsupervised dan menentukan jumlah cluster
yang paling sesuai dengan data yang dianalisa
secara supervised.
Setiap piksel citra dalam proses
clustering ditandai menjadi 4 klas, yaitu klas 1
untuk latar belakang, klas 2 untuk cairan otak
(CSF), klas 3 untuk jaringan otak abu-abu, dan
klas 4 untuk jaringan otak putih.[8] Hasil
pengujian proses clustering pada program
segmentasi ini dapat dilihat pada gambar 5.
Gambar 5 Hasil clustering berdasarkan K-means
clustering
4.3. Pengujian Proses Pemisahan
Proses pemisahan citra dilakukan
dengan thresholding (pengambangan). Proses
pengambangan
dilakukan
terhadap
citra
menggunakan
nilai
ambang
tertentu
berdasarkan hasil clustering. Proses ini akan
menghasilkan citra biner, yaitu citra yang
memiliki dua nilai tingkat keabuan yaitu hitam
dan putih. Proses ini bertujuan untuk
menampilkan tiap-tiap klas yang telah dibuat.
Hasil pengujian proses pemisahan dapat dilihat
pada gambar 6.
Selain menguji program segmentasi
apakah sesuai dengan algoritma yang telah
dibuat juga dilakukan perhitungan waktu yang
dibutuhkan mulai dari pre-processing hingga
selesainya segmentasi. Perhitungan waktu ini
dilakukan untuk mengetahui apakah proses
segmentasi berdasarkan K-means clustering
efektif
untuk
dilakukan.
Waktu
yang
dibutuhkan
untuk
menyelesaikan
proses
segmentasi hanya sekitar 10,94 detik.
Oleh karena itu program segmentasi
yang telah dibuat cukup efektif karena secara
qualitative, hasil segmentasi lebih teliti
dibandingkan
dengan
metode
Minimum
Distance Classifier dan Maximum Distance
Classifier karena tiap data dikelompokkan
menjadi k kelompok dengan cara
memindah-mindahkan data dari kelompok yang satu ke
kelompok
yang
lain
sehingga
tercapai
komponen kesalahan yang minimum. Selain
itu, metode yang biasa digunakan oleh para
ahli adalah metode manual yang membutuhkan
waktu
paling
sedikit
3
jam[9]
dan
menghasilkan pengukuran volume tumor yang
tidak dapat dipercaya dan sensitif error (error
sensitive).[10] Sedangkan program ini hanya
membutuhkan sekitar 10,94 detik untuk tiap
citra.
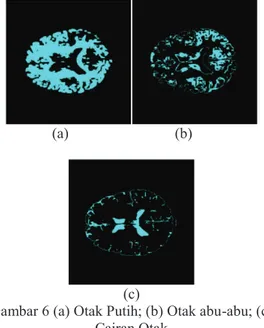
(a) (b)
(c)
Gambar 6 (a) Otak Putih; (b) Otak abu-abu; (c) Cairan Otak
5. Kesimpulan
Dari penelitian ini dapat diperlihatkan
bahwa
program
segmentasi
citra
MRI
menggunakan algoritma K-Means clustering
berhasil membagi irisan citra MRI kepala
menjadi 4 klas, yaitu klas 1 untuk latar
belakang, klas 2 untuk cairan otak (CSF), klas
3 untuk jaringan otak abu-abu, dan klas 4
untuk jaringan otak putih. Keuntungan
program segmentasi dengan algoritma
K-Means clustering mudah diimplementasikan,
cepat, dan memiliki kemampuan untuk
menangani data outlier serta kompleksitas
waktunya linear. Hasil klasifikasi berdasarkan
K-Means clustering dipengaruhi oleh besarnya
kontras citra, penentuan jumlah cluster yang
paling cocok dan besarnya pixel citra yang
digunakan.
Daftar pustaka
[1]. http://en.wikipedia.org/wiki/Magnetic_resona nce_imaging, November 2010
[2]. Cercignani, M., Inglese, M., Zajdel, M. Z., dan Filippi, M. (2001). Segmenting Brain White Matter, Gray Matter and Cerebro-spinal Fluid Using Diffusion tensor-MRI Derived Indices. Magnetic Resonance Imaging, 19, 1167-1172.
[3]. Kalet, I. J., and Seymour, M. M. A. (1997) : The Use of Medical Images in Planning and Delivery of Radiation Therapy, Journal of The
American Medical Informatics Association, 4,
327-339.
[4]. Stark, David D. (1988) : Magnetic Resonance
Imaging, The CV Mosby Company, Toronto.
[5]. Putra, D. (2010) : Pengolahan Citra Digital, Penerbit Andi, Yogyakarta.
[6]. Agusta, Y. (2007) : K-Means – Penerapan, Permasalahan dan Metode Terkait. Jurnal
Sistem dan Informatika, 3, 47-60.
[7]. MacQueen, J. B. (1967) : Some Methods for classification and Analysis of Multivariate Observations, Proceedings of 5-th Berkeley
Symposium on Mathematical Statistics and
Probability, Berkeley, University of
California Press, 1, 281-297.
[8]. Bartlett, T., Vannier, M., Keel, D.Mc., Gado, M., Hildebolt, C., dan Walkup, R. (1994). Interactive Segmentation of Cerebral Gray Matter, White Matter, and CSF : Photographic and MR Images. Comp. Med. Graphics, 18, 449-460.
[9]. Mancas, M., Gosselin, B., dan Macq, B. (2005) : Segmentation Using a Region Growing Thresholding, Proc. Of the Electronic Imaging Conference of the International Society for Optical Imaging (SPIE/EI 2005), San Jose (California, USA).
[10]. Dai, D., Condon, B., Hadley, D., Rampling, R., Teasdale, G. (1993). Intracranial deformation caused by brain tumors : assessment of 3-D surface by magnetic resonance imaging. IEEE Transactions on
Medical Imaging, 12, 693 – 702.
[11]. Ardisasmita, M.S. Metoda Segmentasi Citra Resonansi Magnetik Otak Menggunakan Sistem Pengkodean Neurofuzzy. Pusat Pengembangan Teknologi Informatika dan Komputasi, BATAN.
[12]. Gonzalez, R.C., Woods, R.E. (2002) : Digital
Image Processing Second Edition, Prentice
Hall, New Jersey.
[13]. Sakas, G., dan Pommert, A. (2006) : Processing and Segmentation of 3D Images, 17-25 dalam Schlegel, W., Bortfeld, T., dan Grosu, A.-L. New Technologies in Radiation
Oncology, Springer, Germany.
[14]. Wijaya, M.C., dan Prijono, A. (2007) :
Pengolahan Citra Digital menggunakan Matlab, Penerbit Informatika, Bandung.
[15]. Tanabe, J. L., Amend, D., Scuff, N., DiSclafani, V., Ezekiel, F., Norman, D., Fein, G., dan Weiner, M.W. (1997). Tissue Segmentation of The Brain in Alzheimer Disease. Am. J. Neuroradiol, 18, pp. 115-123.