ASAL NIGERIA BERDASARKAN ANALISIS MARKA
Simple Sequence Repeats (SSR)
ZULHERMANA
SEKOLAH PASCASARJANA
INSTITUT PERTANIAN BOGOR
Dengan ini saya menyatakan bahwa tesis Keragaman Genetik Intra dan
Interpopulasi Kelapa Sawit (Elaeis guineensis Jacq.) Pisifera Asal Nigeria
Berdasarkan Analisis Marka Simple Sequence Repeats (SSR) adalah karya
saya dengan arahan dari komisi pembimbing dan belum diajukan dalam bentuk
apapun kepada perguruan tinggi manapun. Sumber informasi yang berasal atau
dikutip dari karya yang diterbitkan maupun tidak diterbitkan dari penulis lain telah
disebutkan dalam teks dan dicantumkan dalam Daftar Pustaka di bagian akhir
tesis ini.
Bogor, Juli 2009
Zulhermana
ZULHERMANA. 2009. Intra and Interpopulation Genetic Diversity Based
on Simple Sequence Repeats (SSR) Markers Analysis of Oil Palm (Elaeis
guineensis Jacq.) Pisiferas Originated from Nigeria. Under direction of SUDARSONO and DWI ASMONO.
The objectives of this experiment were to determine intra and inter population genetic diversity of TxP family and tissue culture clones of pisifera palm collections originated from Nigeria that have been used as pollen sources for producing oil palm’s DxP commercial.
Intra and interpopulation genetic diversity of Nigeria’s pisifera analisis in this experiment was assessed using 12 loci of oil palm’s specific SSR markers. Results of the experiment indicated out of 12 SSR marker loci evaluated, two loci were monomorphic in all pisifera palms evaluated while 10 loci were polymorphic. The average alele numbers of the marker in the pisifera populations were 3.7 aleles per locus.
The result showed that out of six different clonal populations of pisiferas palm analyze, intrapopulation of clone 22, 24 and 32 showed uniform alele profiles in almost all SSR marker loci tested, indicating the clonal nature of the population members. However, intrapopulation of clone 14, 23 and 33 showed diversity among individuals within population, indicating possibilities of either existance of somaclonal variation or mislabelled individuals. The results also showed that intrapopulation of four population of Nigeria pisifera’s TxP family were all on genetically diverse.
Interpopulation analysis showed that all of Nigeria’s pisiferas both clones and TxP family were band together as a cluster at 0,50 coefficient similarity value. However, interpopulation of Nigeria’s pisifera showed interrelated among population of clone and TxP family. Based on 12 loci of SSR markers data the pisifera clones were shown to have high similarity to a number of individual of the TxP pisifera population. The interrelation among Nigeria’s pisifera population indicating that there are genetic relationship among Nigeria’s pisiferas family.
Based on general combining ability analysis in the traits have been observed, result showed that TxP family 320 from family 24 of Nigeria’s pisifera have been selected as pollen sources for producing commercial DxP oil palm. All the Nigeria’s pisiferas palm have been selected by family and individual palm selection’s method and result showed that all the individual palm selected evenly distributed throughout the population group of TxP family 320 on the dendogram of UPGMA analysis.
Genetic diversity analysis based on SSR marker can be used to give an accurate information of genetic relatedness of oil palm germplasm and the molecular information can also be used as a tool for selection in order to maintain genetic variability to determine breeding activity for the future.
RINGKASAN
ZULHERMANA. 2009. Keragaman Genetik Intra dan Interpopulasi Kelapa
Sawit (Elaeis guineensis Jacq.) Pisifera Asal Nigeria Berdasarkan Analisis
Marka Simple Sequence Repeats (SSR). Dibawah bimbingan SUDARSONO
dan DWI ASMONO.
Perkebunan kelapa sawit di Indonesia terus mengalami peningkatan, jika pada tahun 1970 hanya 133.000 ha, pada tahun 2008 telah mencapai 7,16 juta ha dan diperkirakan pada tahun 2009 luas areal pengembangan akan terus mengalami peningkatan yang ditunjukkan dengan permintaan benih untuk tanam baru dan tanam ulang mencapai hingga 150 juta benih di tahun 2009. Untuk memenuhi benih tersebut, kelapa sawit pisifera sebagai tetua jantan penghasil serbuk sari merupakan sumber genetik yang berperan penting dalam membentuk turunan yang unggul dan berkualitas.
Sumber genetik ini perlu mendapat perhatian, tidak hanya dalam bentuk mengumpulkan dan memelihara, tetapi juga mengkarakterisasi keragaman genetik, mengevaluasi sifat-sifat yang dikehendaki dan memanfaatkannya untuk pemuliaan tanaman. Bertitik tolak dari hal itu maka penelitian ini dilakukan dengan tujuan untuk menganalisis keragaman genetik intra dan interpopulasi kelapa sawit (Elaeis guineensis Jacq.) pisifera yang berasal dari Nigeria. Kelapa sawit pisifera tersebut digunakan sebagai sumber serbuk sari untuk menghasilkan benih Dura x Pisifera komersial.
Salah satu penelitian dilakukan untuk membandingkan penggunaan dua marka molekular, RAPD dan SSR untuk menganalisis keragaman genetik pisifera kelapa sawit yang berasal dari Nigeria. Hasil analisis UPGMA menunjukkan bahwa marka RAPD dan SSR mampu memisahkan individu pisifera Nigeria yang berasal dari TxP famili dan klon. Marka RAPD mengelompokan seluruh pisifera Nigeria pada tingkat kesamaan 0,83 sedangkan marka SSR pada koefisien 0,68. Ketika analisis dilakukan menggunakan marka RAPD dan SSR, seluruh pisifera klon membentuk satu kelompok pada tingkat kesamaan 1,00 hal ini mengindikasikan bahwa seluruh klon yang dianalisis benar-benar seragam
Berdasarkan keunggulan dari marka SSR yang bersifat kodominan, tingkat polimorfisme yang tinggi, penafsiran hasil yang sederhana dan reprodusibilitas yang tinggi maka marka SSR ini lebih lanjut digunakan untuk menganalisis keragaman genetik kelapa sawit pisifera Nigeria.
Penelitian analisis keragaman genetik intra dan interpopulasi kelapa sawit pisifera Nigeria ini dilakukan menggunakan 12 marka SSR. Hasil penelitian menunjukkan bahwa dari 12 marka yang digunakan, 10 marka bersifat polimorfis dan 2 marka yang lain bersifat monomorfis. Jumlah alel yang dihasilkan adalah 3,7 alel perlokus.
klon 14 dan 23 yang secara genetik berbeda dengan yang lain, dengan perbedaan satu lokus dari 12 lokus yang dianalisis. Adanya keragaman ini kemungkinan disebabkan oleh terjadinya variasi somaklonal. Sedangkan pada populasi klon 23 dan 33 juga terdapat masing-masing satu individu yang berbeda dengan yang lain, dengan perbedaan lima dan sepuluh lokus dari 12 lokus yang dianalisis. Hal ini kemungkinan disebabkan oleh mislabelling pada saat kultur.
Analisis intrapopulasi empat pisifera Nigeria TxP famili yang dilakukan juga menunjukkan adanya keragaman pada seluruh populasi. Populasi TxP 317 membentuk satu kelompok pada tingkat kesamaan 0,72 sedangkan populasi TxP 318 membentuk kelompok pada koefisien 0,50. Populasi TxP 319 membentuk kelompok pada koefisien 0,85 dan populasi TxP 320 membentuk kelompok pada koefisien 0,78.
Analisis interpopulasi pisifera Nigeria secara umum menunjukkan bahwa seluruh kelapa sawit pisifera asal Nigeria membentuk satu kelompok pada tingkat kesamaan 0,65. interpopulasi pisifera Nigeria dapat dibedakan atas empat kelompok yaitu kelompok pisifera TxP famili 319, kelompok pisifera TxP famili 318, kelompok pisifera TxP 320 dan kelompok Klon 33 dan14. Serta terdapat kelompok lain yang sangat berbeda yaitu kelompok klon 23 dan TxP 318/56.
Hasil uji keturunan (progeny test) dari lima famili DxP test cross terbaik dari masing-masing famili pisifera Nigeria menunjukkan bahwa pisifera Nigeria famili 24 menunjukkan keragaaan yang terbaik untuk karakter, pertambahan
tinggi (HI) sebesar 45 cm/tahun, tandan buah segar (FFB) sebesar 202 kg/pokok/tahun, total produk ekonomi (TEP) sebesar 54,30% dan
peningkatan total produk ekonomi seluruh pisifera (%TEP-all) sebesar 127,08%. Nilai daya gabung umum (GCA) tertinggi untuk karakter-karakter komponen minyak menyebar merata pada seluruh famili pisifera Nigeria. Pisifera Nigeria famili 14 menunjukkan rasio minyak per tandan (O/B) yang tertinggi dengan nilai 27,84%, famili 22 menunjukkan rasio buah pertandan (F/B) yang tertinggi dengan nilai 66,40%, famili 23 menunjukkan rasio kernel pertandan (K/B) yang tertinggi dengan nilai 5,23%, famili 24 menunjukkan rasio minyak per mesokarp segar (O/WM) yang tertinggi dengan nilai 53,47% dan famili 32 menunjukkan rasio mesokarp perbuah (M/F) yang tertinggi dengan nilai 81,20%. Sedangkan nilai GCA untuk karakter tandan buah segar (FFB), pertumbuhan meninggi (HI) dan total ekonomi produk (TEP) yang tertinggi terdapat pada pisifera Nigeria famili 24 dengan nilai masing-masing sebesar 172 kg/pokok/tahun, 52 cm/tahun dan 46,42%.
Dari serangkaian penelitian yang telah dilakukan dalam pengkajian keragaman genetik berdasarkan marka molekuler terhadap sumber plasma nutfah kelapa sawit pisifera Nigeria ini, disarankan analisis marka molekuler dapat diikutsertakan sebagai salah satu perangkat seleksi dalam menyusun program pemuliaan kelapa sawit di masa depan. Informasi marka molekular berupa keragaman dan jarak genetik juga dapat membantu dalam pengkayaan basis genetik. Analisis keragaman genetik kelapa sawit menggunakan marker SSR ini dapat digunakan sebagai salah satu perangkat seleksi dalam pemeliharaan keragaman genetik yang tersedia, memberikan informasi yang akurat mengenai tingkat kekerabatan genetik, monitoring keseragaman di antara dan di dalam populasi klon serta pendeteksian kultur yang tercampur (mislabelling).
©Hak Cipta Milik IPB, tahun 2009
Hak Cipta dilindungi Undang-Undang
1. Dilarang mengutip sebagian atau seluruh karya tulis ini tanpa mencantumkan atau menyebutkan sumbernya.
a. Pengutipan hanya untuk kepentingan pendidikan, penelitian,
penulisan karya ilmiah, penyusunan laporan, penulisan kritik, atau tinjauan suatu masalah.
b. Pengutipan tersebut tidak merugikan kepentingan yang wajar IPB. 2. Dilarang mengumumkan dan memperbanyak sebagian atau seluruh karya tulis
ASAL NIGERIA BERDASARKAN ANALISIS MARKA
Simple Sequence Repeats (SSR)
ZULHERMANA
Tesis
sebagai salah satu syarat untuk memperoleh gelar
Magister Sains
pada Sekolah Pascasarjana Institut Pertanian Bogor
SEKOLAH PASCASARJANA
INSTITUT PERTANIAN BOGOR
Asal Nigeria Berdasarkan Analisis Marka Simple Sequence Repeats (SSR)
Nama : Zulhermana
NRP : A151060101
Program Studi : Agronomi
Disetujui
Komisi Pembimbing
Prof. Dr. Ir. Sudarsono, MSc Dr. Ir. Dwi Asmono, MS, APU Ketua Anggota
Diketahui
Ketua Program Studi Agronomi Dekan Sekolah Pascasarjana
Dr. Ir. Munif Ghulamahdi, MS Prof. Dr. Ir. Khairil A. Notodipuro, MS
Puji beriring syukur penulis panjatkan kehadirat Allah SWT atas segala
karunia-Nya sehingga penulis dapat menyelesaikan penelitian ini dengan judul
”Keragaman Genetik Intra dan Interpopulasi Kelapa Sawit (Elaeis guineensis Jacq.) Pisifera Asal Nigeria Berdasarkan Analisis Marka Simple Sequence Repeats (SSR)” sesuai dengan waktu yang telah ditetapkan. Pendidikan dan penelitian ini
merupakan program pengembangan riset berkelanjutan dari PT Bina Sawit
Makmur, PT Sampoerna Agro Tbk. dan seluruh pembiayaannya didanai
sepenuhnya oleh PT bina Sawit Makmur, PT Sampoerna Agro Tbk.
Penulis mengawali penelitian ini dengan tanpa dasar pengetahuan akan
teknis dan analisis molekuler. Namun Alhamdulillah penelitian ini dapat
diselesaikan dengan baik. Untuk itu penulis mengucapkan terima kasih yang
sebesar-besarnya kepada Bapak Prof. Dr. Ir. Sudarsono, MSc dan Bapak Dr. Ir.
Dwi Asmono, MS, APU selaku pembimbing yang telah banyak memberikan
masukan dan arahan mulai dari pemahaman tentang teknik dan analisis molekuler,
perencanaan, pelaksanaan hingga terselesaikannya penelitian ini dengan sangat
baik.
Ucapan terima kasih yang tidak berhingga secara khusus penulis sampaikan
kepada Bapak Dr. Ir. Dwi Asmono, MS, APU selaku Direktur Riset
PT Sampoerna Agro Tbk. yang peduli terhadap peningkatan sumber daya manusia
Indonesia, penulis bersyukur menjadi salah seorang yang diberi kesempatan untuk
meningkatkan potensi diri melalui jenjang akademik. Terima kasih secara khusus
juga penulis haturkan kepada Bapak Allan Goh yang telah memberikan
kesempatan dan motivasi kepada penulis sehingga kesempatan yang tidak terduga
ini dapat dijalani.
Kepada segenap jajaran Direksi PT Sampoerna Agro Tbk. penulis ucapkan
terima kasih yang tidak terhingga atas motivasi serta dukungan dana dan fasilitas
dalam menjalani pendidikan pasca sarjana ini. Kepada Staf dan Karyawan
PT Bina Sawit Makmur, PT Sampoerna Agro Tbk, penulis juga mengucapkan
terima kasih yang sebesar-besarnya atas pemikiran, sumbang saran dan bantuan
Departemen Agronomi dan Hortikultura, Fakultas Pertanian IPB yang dikordinir
oleh Bapak Prof. Dr. Ir. Sudarsono, MSc dan seluruh staf tehnisi di laboratorium,
untuk ini penulis haturkan terima kasih. Kepada seluruh teman-teman di
Laboratorium Biologi Molekuler Tanaman, saya ucapkan terima kasih atas
bantuan saran, tenaga dan motivasinya. Kepada seluruh team di statistical unit dan breeding unit kebun Surya Adi, PT Bina Sawit Makmur, terima kasih atas bantuan data dan pengiriman sampel daunnya. Semoga tetap menjadi team yang solid dan
sukses selalu. Tak lupa kepada seluruh team purchasing department dan payroll department PT Sampoerna Agro Tbk. yang membantu penyediaan bahan-bahan penelitian dan pengaturan pembiayaan penelitian ini, penulis ucapkan terima kasih
karena tanpa bantuan teman-teman penelitian ini tidak akan dapat berjalan dengan
baik.
Kepada motivator sejati, istri tercinta Zubaidah Harahap dan anak-anakku
M. Aulia Khairu Rizqy Sembiring dan Rifqy Arikin Halim Sembiring, penulis
ucapkan terima kasih karena selalu memberi dorongan semangat dan doa, walau
kadang terabaikan. Khusus kepada Ibunda tercinta Almh. Siti Rukiah br. Tarigan
penulis haturkan doa dan terima kasih karena cita-cita beliau menjadi semangat
kepada penulis untuk terus maju walaupun jenjang yang dicapai saat ini tidak
pernah terbayangkan beliau. Kepada Ayahanda serta seluruh keluarga terima
kasih atas dukungan dan doanya.
Penulis menyadari sepenuhnya bahwa tesis ini masih jauh dari sempurna,
terutama keterbatasan informasi dan waktu penelitian. Namun demikian, penulis
berharap semoga tesis ini bermanfaat kepada pembaca dan semua pihak yang
membutuhkannya.
Bogor, Juli 2009
ZULHERMANA SEMBIRING dilahirkan di Kabanjahe Kabupaten Karo
Sumatera Utara pada tanggal 15 Pebruari 1970 sebagai putra pertama dari
ayahanda Y. Heryanto Sembiring dengan ibunda Almh. Siti Rukiah Br. Tarigan.
Pada tanggal 16 Pebruari 2003 penulis menikah dengan Zubaidah Harahap, dan
telah dikaruniai dua orang putra bernama M. Aulia Khairu Rizqy Sembiring dan
Rifqy Arikin Halim Sembiring.
Pendidikan dasar dan menengah diselesaikan di kota Medan, Sumatera
Utara; yaitu Sekolah Dasar Negeri No 060448 Medan (1983), Sekolah Menengah
Tingkat Pertama Negeri 8 Medan (1986), Sekolah Menengah Tingkat Atas
Negeri 1 Medan (1989). Gelar sarjana pertanian (S1) diperoleh dari Fakultas
Pertanian (Jurusan Budidaya Pertanian, Program Studi Pemuliaan Tanaman)
Universitas Sumatera Utara di Medan (1995) dengan predikat sangat memuaskan.
Pada tanggal 3 Juli 1995 penulis diterima bekerja di PT Tania Selatan, salah
satu perusahaan perkebunan di Sumatera Selatan sebagai Asisten Lapangan.
Pada tahun 2003 penulis ditugaskan sebagai research officer kebun induk PT Bina Sawit Makmur, Selapan Jaya Group. Dan pada tahun 2006 penulis diberi
kesempatan untuk mengikuti pendidikan Pasca Sarjana di Institut Pertanian Bogor
pada program studi Agronomi. Sampai saat ini penulis bertugas sebagai
xi
DAFTAR ISI
Halaman
DAFTAR TABEL ... xiii
DAFTAR GAMBAR ... xiv
DAFTAR LAMPIRAN ... xvi
DAFTAR SINGKATAN ... xvii
PENDAHULUAN ... 1
Latar Belakang ... 1
Tujuan ... 5
Manfaat ... 6
TINJAUAN PUSTAKA ... 7
Kelapa Sawit ... 7
Pemuliaan Kelapa Sawit ... 13
Marka Molekuler ... 18
EFEKTIFITAS PENGGUNAAN MARKA RAPD DAN SSR DALAM ANALISIS KERAGAMAN GENETIK SEMBILAN AKSESI KELAPA SAWIT (Elaeis guineensis Jacq.) PISIFERA ASAL NIGERIA ... 19
Abstrak… ... 19
Abstract ... 20
Pendahuluan ... 21
Bahan dan Metode ... 23
Hasil dan Pembahasan ... 26
Kesimpulan ... 35
KERAGAMAN GENETIK INTRA DAN INTERPOPULASI KELAPA SAWIT (Elaeis guineensis Jacq.) PISIFERA KLON ASAL NIGERIA BERDASARKAN ANALISIS MARKA SSR ... 36
Abstrak… ... 36
Abstract ... 37
Pendahuluan ... 38
Bahan dan Metode ... 40
Hasil dan Pembahasan ... 42
xii
Halaman
KERAGAMAN GENETIK INTRA DAN INTERPOPULASI KELAPA SAWIT (Elaeis guineensis Jacq.) PISIFERA TxP FAMILI ASAL
NIGERIA BERDASARKAN ANALISIS MARKA SSR ... 53
Abstrak… ... 53
Abstract ... 54
Pendahuluan ... 55
Bahan dan Metode ... 57
Hasil dan Pembahasan ... 59
Kesimpulan ... 68
KAITAN ANTARA KERAGAMAN GENETIK INTRA DAN INTERPOPULASI SAWIT (Elaeis guineensis Jacq.) PISIFERA ASAL NIGERIA DENGAN KARAKTER UTAMA SELEKSI ... 69
Abstrak… ... 69
Abstract ... 70
Pendahuluan ... 71
Bahan dan Metode ... 73
Hasil dan Pembahasan ... 76
Kesimpulan ... 83
PEMBAHASAN UMUM ... 84
KESIMPULAN DAN SARAN ... 88
DAFTAR PUSTAKA ... 89
xiii
DAFTAR TABEL
Halaman
1. Jenis primer dan urutan sekuen primer acak, jumlah marka RAPD dan ukuran marka RAPD yang dihasilkan oleh masing-masing primer ... 26 2. Nilai tingkat kemiripan antar empat individu ramet klon pisifera dan
lima individu dari famili TxP berdasarkan data marka RAPD ... 28 3. Nama primer, urutan sekuen primer, jumlah alel total dan alel
polimorfik dalam analisis marka SSR ... 30 4. Nilai tingkat kemiripan antar empat individu ramet klon pisifera dan
lima individu dari famili TxP berdasarkan data marka SSR ... 31 5. Hasil perbandingan analisis marka RAPD dan marka SSR dari
sembilan aksesi pisifera Nigeria ... 33 6. Nama lokus, urutan basa dan jumlah alel dari 12 marka SSR yang
digunakan dalam penelitian analisis keragaman genetik intra dan inter populasi kelapa sawit pisifera klon Nigeria ... 42 7. Jumlah alel dan nilai polimorfisme dari 13 primer SSR yang
digunakan dalam penelitian analisis keragaman genetik intra dan inter populasi kelapa sawit pisifera klon Nigeria . ... 43 8. Data keragaman intrapopulasi pisifera klon Nigeria yang dianalisis
menggunakan 12 marka SSR ... 46 9. Data perbedaan jumlah lokus intrapopulasi pisifera klon Nigeria dari
12 lokus yang diuji ... 47 10. Nama lokus, urutan basa dan jumlah alel dari 13 primer SSR yang
digunakan dalam penelitian analisa keragaman genetik intra dan interpopulasi kelapa sawit pisifera TxP famili ... 59 11. Jumlah alel dan nilai polimorfisme dari 13 primer SSR.yang
digunakan dalam penelitian analisa keragaman genetik intra dan interpopulasi kelapa sawit pisifera TxP famili ... 60 12. Data koefisien kemiripan masing-masing populasi TxP family yang
membentuk satu kelompok ... 61 13. Data koefisien kemiripan masing-masing populasi TxP famili yang
membentuk keragaman ... 61 14. Data performance 5 (lima) individual DxP test cross terbaik dari
6 (enam) famili pisifera origin Nigeria. ... 77 15. Data performance 5 (lima) famili DxP test cross terbaik dari 6 (enam)
xiv
DAFTAR GAMBAR
Halaman
1. Tanaman kelapa sawit komersial yang telah berbuah, yang merupakan persilangan antara dura x pisifera (DxP) dengan tetua pisifera yang digunakan berasal dari Nigeria ... 5 2. Tipe pembungaan monoecious pada tanaman kelapa sawit. Bunga
jantan (bj) dan bunga betina (bb) dalam dua tandan yang terpisah ... 6 3. Gambar bunga jantan dan bunga betina kelapa sawit. (a) Tandan bunga
jantan kelapa sawit yang sedang antesis dan (b) Tandan bunga betina kelapa sawit yang siap diserbuki ... 6 4. Tenera yang merupakan persilangan tetua betina dura dengan tetua jantan pisifera ... 8 5. Keragaan DxP test cross dengan pejantan Nigeria. (a) Tanaman
dengan tipe buah virescence, (b) Tanaman dengan tipe buah nigrescence, (c) Tandan dan buah virescence, (d) Tandan dan buah nigrescence ... 10 6. Metode seleksi yang melibatkan dua heterotik group: Group A tetua
betina dura dan Group B tetua jantan pisifera ... 14 7. Dendrogram hasil analisis UPGMA pada sembilan aksesi
pisifera Nigeria menggunakan marka RAPD yang dihasilkan dari lima primer acak. ... 28 8. Contoh visualisasi marka RAPD yang dihasilkan dengan
menggunakan primer acak, OPR-11. ... 29 9. Dendrogram hasil analisis UPGMA pada sembilan aksesi
pisifera Nigeria menggunakan marka SSR yang dihasilkan dari lima primer spesifik. ... 32 10. Visualisasi DNA hasil amplifikasi plasma nutfah kelapa sawit pisifera
Nigeria menggunakan primer SSR, P-9 dan P-11. ... 32 11. Dendrogram analisis UPGMA populasi pisifera klon menggunakan
12 primer SSR. ... 45 12. Visualisasi profil pita hasil elektroforesis DNA kelapa sawit populasi
klon 33 dan klon 14 menggunakan primer SSR 1 dan 7 ... 48 13. Dendrogram analisis UPGMA populasi pisifera klon dan
keterkaitannya dengan pisifera TxP famili menggunakan 12 primer SSR ... 50 14. Dendrogram analisis UPGMA populasi pisifera TxP 318
menggunakan 12 primer SSR ... 62 15. Dendrogram analisis UPGMA populasi pisifera TxP 320
menggunakan 12 primer SSR ... 63 16. Visualisasi profil pita hasil elektroforesis DNA kelapa sawit populasi
xv
17. Dendrogram analisis UPGMA populasi pisifera TxP famili dan keterkaitannya dengan pisifera seluruh pisifera Nigeria menggunakan 12 primer SSR ... 66 18. Dendrogram keterkaitan hasil analisis UPGMA dari 12 primer SSR
xvi
DAFTAR LAMPIRAN
Halaman
1. Silsilah populasi pisifera origin Nigeria (GHA 608) ... 97 2. Prosedur baku pembuatan larutan kimia dan ekstraksi DNA daun
kelapa sawit ... 98 3. Prosedur baku pembuatan larutan kimia dan elektroforesis horizontal
DNA kelapa sawit ... 110 4. Prosedur baku analisis SSR kelapa sawit ... 116 5. Prosedur pengolahan data molekuler menggunakan program
NTSYSpc versi 2.02 ... 133 6. Dendogram analisis UPGMA terhadap pisifera Nigeria menggunakan
xvii
DAFTAR SINGKATAN
AFLP : amplified fragment length polymorpism
ALJ : asam lemak jenuh
ALTJ : asam lemak tak jenuh
BC : backcross
BI : Bunch index
bp : basepair
BSM : Bina Sawit Makmur
CD : crown desease
CIRAD : centre de cooperation internationale en recherche
agronomiquepour le developpement
CPO : crude palm oil
CTAB : cetyl-trimethyl-ammoniumbromide
D : Dura
dATP : 2’-deoxyadenosine 5’-triphosphate
dCTP : 2’-deoxycytidine 5’-triphosphate
dGTP : 2’-deoxyguanosine 5’-triphosphate
DNA : deoxyribonucleic acid
dNTP : 2’-deoxy any base 5’-triphosphate
dTTP : 2’-deoxythymidine 5’-triphosphate
DxP : Dura x Pisifera
FAD : fatty acid desaturase
FIPS : family and individual palm selection
GCA : general combining ability
GHA : Ghana
IPC : Integral plate chamber
Jacq. : Jacquin (Nicolaus Joseph von Jacquin)
KIAA : kloroform : isoamilalkohol
LDM : Leaf dry matter
xviii
nig : nigrescence
P : Pisifera
PCR : polymerase chain reaction
PKO : palm kernel oil
PVPP : polyvinilpolypyrrolidone
QTL : quantitative trait loci
RAPD : random amplified polymorphic DNA
RFLP : ristriction fragment length polymorphisms
RRS : recurrent reciprocal selection
SCA : specific combining ability
SJ : Sriwijaya
SSR : simple sequence repeats
TAE : [Tris]-[Acetic Acid Glacial]-[EDTA]
Taq : Thermus aquaticus
TBS : tandan buah segar
TE : [Tris]-[EDTA]
TEP : Total Economic Product
TxP : Tenera x Pisifera
TxT : Tenera x Tenera
UPGMA : unweighted pair group method with arithmetic
UV : ultra violet
PENDAHULUAN
Latar Belakang
Produktivitas kelapa sawit sebagai komoditi penghasil devisa terus
mengalami peningkatan. Bila pada tahun 1978, tingkat produksi CPO di Indonesia
hanya 501.284 ton, maka pada tahun 2008 tingkat produksi CPO telah mencapai
19,8 juta ton. Dari sisi luas areal, perkebunan kelapa sawit di Indonesia yang pada
tahun 1970 hanya 133.000 ha dan pada tahun 2008 telah mencapai 7,16 juta ha.
Diperkirakan pada tahun 2009 luas areal pengembangan akan tetap mengalami
peningkatan. Permintaan benih untuk tanam baru dan tanam ulang pada tahun
2009 mencapai 150 juta benih. Devisa yang diperoleh dari ekspor 11,9 juta ton
minyak kelapa sawit dan turunannya pada tahun 2007 mencapai US$ 7,9 milyar.
Usaha perkebunan tersebut menyerap tenaga kerja sebanyak 3,3 juta kepala
keluarga (Dirjen Bun, 2008).
Kelapa sawit pisifera sebagai tetua jantan penghasil serbuk sari merupakan
sumber genetik yang berperan penting dalam membentuk turunan yang unggul
dan berkualitas. Sumber genetik kelapa sawit pisifera ini perlu mendapat
perhatian, tidak hanya dalam bentuk mengumpulkan dan memelihara, tetapi juga
mengkarakterisasi keragaman genetik, mengevaluasi sifat-sifat yang dikehendaki
dan memanfaatkannya untuk pemuliaan tanaman (Bennet 1993). Kelapa sawit
pisifera asal Nigeria merupakan salah satu tetua jantan penghasil serbuk sari yang
digunakan untuk produksi benih kelapa sawit DxP komersial. Hasil uji progeni
DxP test cross yang dilaksanakan di lahan S3 (kurang subur) di Sumatera Selatan menggunakan pisifera Nigeria (GHA 608) memperlihatkan hasil
dengan rerata produksi minyak 7,3 ton/tahun, rendemen 26,3% serta kecepatan
meninggi 56 cm/tahun pada TM 3-7 (BSM 2007).
Guna mendukung upaya pemberdayaan potensi plasma nutfah pada program
seleksi maka mutlak diperlukan kelengkapan informasi yang berkaitan dengan
berbagai karakter morfologi maupun genetiknya. Informasi genetik sangat
bermanfaat untuk memberi kelengkapan informasi tanaman dan mampu
memberi gambaran yang akurat tentang perbedaan genetik individu, baik pada
tingkat spesies maupun dengan kerabat jauhnya. Menurut Tanksley (1983),
penanda molekuler dapat mendeteksi variasi genetik dan polimorfismenya tidak
dipengaruhi oleh lingkungan.
Marka SSR untuk kelapa sawit pertama kali dikembangkan oleh CIRAD
Perancis. Bilotte et al. (2001) berdasarkan hasil analisis data multivariat melaporkan kemampuan marka SSR yang sangat efisien untuk menunjukkan
struktur keragaman genetik genus Elaeis sesuai dengan daerah asalnya. Berdasarkan tingkat variabilitas aleliknya yang tinggi, marka SSR dapat menjadi
perangkat yang sangat bermanfaat untuk kajian genetik genus Elaeis, antara lain untuk identifikasi plasma nutfah dan pemetaan genetik intra atau interspesifik.
Sanghai-Maroof et al. (1994) mengemukakan beberapa alasan pemakaian SSR yaitu; (1) melimpah, (2) terdistribusi dengan seragam, (3) sangat polimorfis, (4)
kodominan, (5) dihasilkan dengan cepat melalui PCR, (6) relatif sederhana untuk
ditafsirkan, dan (7) mudah diakses oleh laboratorium lain melalui publikasi
sekuen primer. Karena itu marka SSR ini dapat digunakan untuk mendeteksi
keragaman genetik populasi tanaman yang berkerabat dekat dengan lebih baik
dibandingkan dengan marka molekuler yang lain. Singh et al. (2007) juga menjelaskan bahwa marka SSR dapat digunakan untuk pengendalian mutu dalam
memproduksi klon kelapa sawit melalui kultur jaringan dalam skala komersial.
Penerapan marka SSR sebagai pelacak DNA sangat efektif untuk:
(1) mengidentifikasi klon, (2) mendeteksi tercampurnya kultur, (3) memonitor
keseragaman garis keturunan dan (4) mengkonfirmasikan identitas ramet untuk
recloning.
Karakterisasi keragaman genetik secara molekuler terhadap sumber plasma
nutfah dapat membantu pemulia menyeleksi progenitor dari populasi dasar untuk
menyusun program pemuliaan. Keragaman genetik dan jarak genetik yang
ditentukan berdasarkan marka molekuler juga dapat membantu dalam pengkayaan
basis genetik. Marka molekuler dapat juga bermanfaat untuk mengevaluasi
duplikat dan defisiensi khusus dalam bank plasma nutfah sehingga menghasilkan
strategi pemeliharaan dan pengelolaan koleksi yang efisien. Data marka
untuk meminimalkan jumlah pemeliharaan keturunan yang tidak perlu dalam bank
plasma nutfah dan memudahkan akses pemulia terhadap bank plasma.
Karakterisasi molekuler dapat membantu menyeleksi pohon-pohon yang dapat
digunakan sebagai ortet. Hal ini akan sangat bermanfaat bila sudah diketahui
secara jelas keterkaitan (linkage) antara lokus marka molekuler dan lokus penentu sifat kuantitatif yang mempunyai nilai ekonomi tinggi, seperti kandungan minyak
buah. Oleh karena itu, analisis linkage antara marka molekuler dan lokus-lokus sifat kuantitatif (QTL) menjadi fokus penelitian masa depan (Setiyo et al. 2001).
Tujuan dan Manfaat Penelitian
Tujuan dari penelitian ini adalah: (1) Mengevaluasi keragaman genetik
plasma nutfah intra dan interpopulasi TxP famili kelapa sawit pisifera Nigeria,
(2) Mengevaluasi keragaman genetik plasma nutfah kelapa sawit intrapopulasi
klon pisifera Nigeria dan (3) Melihat keterkaitan komponen vegetatif dan
generatif serta keragaman genetik pisifera origin Nigeria.
Penelitian ini diharapkan dapat memberikan manfaat sebagai: (1) Bahan
informasi yang akurat mengenai tingkat kekerabatan genetik plasma nutfah
pisifera Nigeria, (2) Dasar bagi kepentingan penetapan aktivitas program
pemuliaan kelapa sawit di masa datang dan upaya melakukan konservasi sumber
daya genetik kelapa sawit, (3) Dasar seleksi dan pelestarian serta pemeliharaan
plasma nutfah yang potensial dan (4) Deteksi dini serta konfirmasi asal tanaman
TINJAUAN PUSTAKA
Kelapa Sawit
Asal
Tanaman kelapa sawit (Elaeis guineensis Jacq.) berasal dari Afrika Barat dan ada beberapa bukti kuat yang mendukungnya. Di Abydos (3000 SM)
ditemukan lemak dalam kendi yang terkubur di makam, yang diduga berasal dari
kelapa sawit. Fosil polen mirip dengan polen kelapa sawit yang dipelihara saat ini
ditemukan di Afrika Barat dari jaman Miocene dan dari lapisan yang lebih muda
di delta Niger, serta bukti lingustik yang menyebutkan ditemukannya spesies
pohon mirip kelapa sawit. Elaeis oleifera atau Elaeis melanococca merupakan spesies kelapa sawit yang banyak tumbuh di Amerika. Ada pendapat lain bahwa
kelapa sawit berasal dari Amerika yang kemudian dibawa ke Afrika. Ada dua
alasan yang mendukung bahwa kelapa sawit berasal dari Amerika, yaitu (1) Palma
tersebut tumbuh di area pantai Brazil dan (2) Seluruh genera berasal dari Amerika.
Ketika Colombus menemukan Amerika, diyakini bahwa kelapa sawit sudah
tumbuh di Amerika. Akan tetapi, tidak ada catatan otentik tentang hal itu (Hartley
1988).
Tanaman kelapa sawit diintroduksi ke Indonesia pada tahun 1848.
Sebanyak empat bibit kelapa sawit ditanam di Kebun Raya Bogor. Dari keempat
bibit tersebut, dua bibit diintroduksi dari Bourbon atau Mauritius pada
bulan Pebruari 1848, dau bibit yang lain diintroduksi dari Amsterdam pada
bulan Maret 1848 (Pamin 1998).
Botani
Kelapa sawit (Elaeis guineensis Jacq.), berasal dari bahasa Yunani, yaitu
elaion yang berarti minyak dan guineensis yang menunjukkan bahwa tanaman kelapa sawit berasal dari pantai Guinea Afrika Barat, sedangkan Jacq., adalah singkatan dari nama belakang Nicolaus Josef von Jacquin, orang yang memberi
nama kelapa sawit secara botani (Hartley 1977). Tanaman ini memiliki genom
Tanaman kelapa sawit tergolong monokotil. Akarnya terdiri atas akar
primer, sekunder, tersier dan kuarter serta merupakan akar serabut yang sebagian
besar berada dekat permukaan tanah dengan kedalaman 15-30 cm. Batangnya
tegak tidak bercabang, berdiameter 40-75 cm dan dengan tinggi batang dalam
pembudidayaan tidak lebih dari 15-18 m (Gambar 1). Daunnya majemuk dengan
pelepah daun tersusun melingkari batang berbentuk spiral. Panjang pelepah daun
mencapai 9 m dan panjang helaian daun mencapai 1.2 m dengan jumlah 100-160
pasang. Untuk perkebunan kelapa sawit, jumlah pelepah daun yang dipertahankan
sekitar 30-50 pelepah (Hartley 1977).
Tipe pembungaan kelapa sawit adalah monoecious, berarti bunga jantan dan betina ada di satu tanaman, tetapi pada tandan yang berbeda (Gambar 2). Bentuk
bunga jantan dan bunga betina kelapa sawit dapat dilihat pada Gambar 3.
Rasio bunga jantan terhadap betina dapat dipengaruhi keadaan iklim. Pada musim
Gambar 2. Tipe pembungaan monoecious pada tanaman kelapa sawit. Bunga jantan (bj) dan bunga betina (bb) dalam dua tandan yang terpisah.
Gambar 3. Gambar bunga jantan dan bunga betina kelapa sawit. (a) Tandan bunga jantan kelapa sawit yang sedang antesis dan (b) Tandan bunga betina kelapa sawit yang siap diserbuki.
kemarau biasanya bunga jantan yang mendominasi sedangkan pada musim
penghujan bunga betina yang mendominasi. Kadangkala dijumpai bunga
hermaprodit pada tanaman kelapa sawit muda yang berumur sekitar 2-4 tahun,
bunga ini akan menyusut atau hilang sejalan dengan bertambahnya umur tanaman.
Pada setiap ketiak pelepah daun kelapa sawit tumbuh hanya satu tandan bunga,
a
b
bj
dapat berupa bunga jantan atau bunga betina. Periode antesis bunga jantan dan
reseptif bunga betina tidak bersamaan sehingga memungkinkan terjadinya
penyerbukan silang antar pohon kelapa sawit. Buah kelapa sawit merupakan buah
batu yang terdiri atas kulit buah, daging buah, cangkang dan inti yang tersusun
dalam satu tandan. Minyak sawit sebagian besar (20-27%) terdapat pada perikarp
(kulit buah) dan mesokarp (daging buah) sedangkan pada bagian inti hanya
mengandung sedikit minyak (4-6%) (Hartley 1977).
Berdasarkan ketebalan cangkangnya, kelapa sawit dapat dibedakan menjadi
kelapa sawit tipe dura, pisifera, dan tenera dengan ciri-ciri sebagai berikut :
a) Dura: persentase mesokarp terhadap buah bervariasi antara 35-55%,
meskipun ada yang mencapai 65%; ketebalan cangkang 2-8 mm; tidak
mempunyai lingkar serabut di sekeliling inti; inti relatif besar dan rendemen
minyak relatif rendah (17-18%). Penampang biji dura dapat dilihat pada
Gambar 4. Dura sengat baik digunakan sebagai induk betina dalam produksi
benih komersial.
b) Pisifera: tidak mempunyai cangkang; cangkang digantikan oleh lingkar
serabut di sekeliling inti; persentase mesokarp terhadap buah sangat besar dan
rendemen minyak sangat tinggi (45-50%). Penampang biji pisifera dapat
dilihat pada Gambar 4. Pisifera disebut juga sebagai pohon betina yang steril
karena sebagian besar tandan aborsi pada awal perkembangannya. Sehingga ia
digunakan sebagai induk jantan dalam produksi benih komersial.
c) Tenera: merupakan hasil persilangan dura dengan pisifera; banyak ditanam
secara komersil di perkebunan dan mempunyai karakteristik gabungan dari
kedua induk ura dan pisifera. Ketebalan cangkang 0.4-4 mm; di sekelilingnya
ada lingkar serabut dan perbandingan mesokarp terhadap buahnya cukup
tinggi mencapai (60-96%). Tenera menghasilkan tandan relatif lebih banyak
dibandingkan dura, walaupun ukuran tandannya lebih kecil dari dura.
Rendemen minyak mencapai 22-24% (Soehardjo et al. 1996). Penampang biji tenera dapat dilihat pada Gambar 4. Tenera merupakan tanaman kelapa sawit
komersial yang ditanam untuk menghasilkan minyak sawit.
Sifat ketebalan cangkang pada masing-masing tipe kelapa
Gambar 4. Tenera yang merupakan persilangan tetua betina dura dengan tetua jantan pisifera.
(Sh+ dan Sh-) yang berekspresi kodominan. Secara teoritis bila pohon dura
(Sh+ Sh+) disilangkan dengan pohon tenera (Sh+ Sh-) maka dalam proses
reproduksinya, pohon dura akan menyumbangkan satu jenis gamet (Sh+)
sedangkan pohon tenera menyumbangkan dua jenis gamet (Sh+ dan Sh-). Dalam
proses penyerbukan dan pembuahan, gamet dari masing-masing tetua akan
berpadu bebas sehingga pada turunannya akan terbentuk 50% tipe dura dan
50% tipe tenera. Tetapi variasi ketebalan cangkang yang terlihat pada
masing-masing tipe disebabkan oleh perbedaan perkembangan lignifikasi cangkang yang
diwariskan secara kuantitatif dan dikendalikan oleh banyak gen (Corley et al. 1978). Tenera lebih disukai untuk digunakan sebagai bahan tanaman komersial
(Setiyo et al. 2001). Karena mempunyai proporsi kandungan minyak di dalam mesokarpnya 30% lebih besar dari dura. Untuk mendapatkan 100% tenera (DxP)
maka tetua betina tipe dura (DxD) disilangkan dengan tetua jantan tipe pisifera
(TxP) (Gambar 4).
Dura (Sh
+Sh
+)
X
Pisifera (Sh
-Sh
-)
Pisifera Nigeria
Kelapa sawit pisifera Nigeria merupakan salah satu sumber tetua jantan
penghasil serbuk sari yang digunakan untuk produksi benih kelapa sawit DxP
unggul untuk skala komersial. Pisifera Nigeria yang ada di PT Bina Sawit
Makmur berasal dari Pusat Penelitian Kade di Ghana yang dihasilkan melalui
kerja sama Wonkkyo-Appiah pada tahun 1978. Tetua betina pisifera Nigeria yang
digunakan untuk menghasilkan (GHA 608) berasal dari Calabar, sedangkan tetua
jantannya berasal dari keturunan Ufama dan Aba (BSM 2004). Dari serangkaian
penelitian yang dilakukan di ASD Costa Rica diketahui kinerja material GHA 608
yang baik, yaitu pertambahan meninggi yang lambat dan produksi tandan serta
ekstraksi minyak yang tinggi dibanding materi genetik pisifera lainnya. Penelitian
lanjutan yang dilakukan di Indonesia juga menunjukkan bahwa DxP testcross
menggunakan pisifera Nigeria (GHA 608) yang ditanam di lahan S3 (kurang
subur) di Sumatera Selatan memperlihatkan hasil yang baik dengan rataan
produksi minyak 7,3 ton per tahun, rendemen minyak 26,3% dan kecepatan
meninggi 56 cm/tahun pada TM 3-7 (BSM 2007).
Benih kelapa sawit DxP unggul dengan pejantan pisifera Nigeria
ini telah dilepas oleh Menteri Pertanian Republik Indonesia melalui SK
No. 435/Kpts/LB.320/7/2004 dan diberi nama DxP Sriwijaya 1. Populasi pisifera
Nigeria yang ada di PT Bina Sawit Makmur saat ini terdiri atas pisifera dari famili
TxP dan pisifera klon. Saat ini sebagai pejantan penghasil serbuk sari yang
digunakan hanyalah pisifera Nigeria dari famili TxP, sedangkan pisifera Nigeria
yang berasal dari klon belum digunakan sebagai pejantan penghasil serbuk sari
secara komersial karena masih perlu penelitian lebih lanjut berupa studi pewarisan
genetik, fisiologi, maupun analisis molekuler (DNA) untuk mengkonfirmasi
identitas dan normalitas pisifera dan turunan DxP-nya (BSM 2007).
Karakteristik morfologi DxP testcross menggunakan sumber serbuk sari pisifera Nigeria ini menghasilkan dua tipe warna buah (Gambar 5) yaitu tipe
Gambar 5. Keragaan DxP test cross dengan pejantan Nigeria. (a) Tanaman dengan tipe buah virescence, (b) Tanaman dengan tipe buah nigrescence, (c) Tandan dan buah virescence, (d) Tandan dan buah nigrescence.
Karakteristik lain dari DxP test cross dengan sumber serbuk sari pisifera Nigeria adalah pertumbuhan meninggi yang relatif lambat, dengan kecepatan
meninggi 56 cm per tahun berdasarkan data dari tanaman hingga berumur 9 tahun
yang ditanam pada lahan S-3 (kurang subur), jenis tanah alluvial (aquic kandiudultc, plinthaquic kandiudults) dengan iklim yang relatif kering dan
distribusi curah hujan yang tidak merata sepanjang tahun di daerah Sumatera
Selatan (BSM 2007). Karakteristik sekunder tipe buah virescence dan pertumbuhan meninggi yang lambat ini cukup memberikan nilai tambah yang
bermanfaat dalam budidaya kelapa sawit.
Sampai saat ini untuk produksi benih DxP komersial di PT Bina Sawit
Makmur, PT Sampoerna Agro Tbk. hanya digunakan pejantan pisifera Nigeria
yang berasal dari famili TxP. Salah satu kerugian penggunaan famili TxP sebagai
pejantan (tanaman tipe pisifera) karena 50% yang lain akan menjadi tanaman tipe
tenera yang tidak digunakan sebagai pejantan. Pisifera Nigeria yang berasal dari
a
b
d
perbanyakan klonal masih belum digunakan secara karena kekhawatiran akan
timbulnya abnormalitas pembungaan, yaitu kemunculan buah mantel pada turunan
yang dihasilkan. Berbeda dengan famili TxP yang hanya 50%-nya pisifera, semua
individu dalam klon pisifera adalah tanaman pisifera. Hal ini merupakan nilai
positif penggunaan pisifera klon dalam produksi kelapa sawit DxP secara
komersial.
Serangkaian penelitian untuk membuktikan keberadaan abnormalitas
pembungaan tersebut masih terus dilakukan untuk mengevaluasi efektifitas
penggunaan pejantan klon pisifera Nigeria dalam memproduksi DxP testcross. Salah satu keunggulan dari pejantan klon pisifera Nigeria adalah populasi
tanamannya relatif seragam dan bentuk buah yang seluruhnya bertipe virescence. Penelitian berbasis molekuler diharapkan dapat membantu mempercepat
penggunaan pejantan klon pisifera Nigeria untuk merakit varitas unggul kelapa
sawit DxP pada skala komersial (BSM 2007)
Pemuliaan Kelapa Sawit
Tujuan Pemuliaan
Pemuliaan kelapa sawit Indonesia menurut Asmono et al. (2005) umumnya ditujukan untuk menghasilkan bahan tanaman kelapa sawit unggul yang memiliki
produktivitas minyak tinggi dan karakteristik sekunder (auxiliary traits) tertentu dan spesifik seperti kualitas minyak, fenologi, ketahanan terhadap cekaman biotik
atau cekaman abiotik.
a) Perbaikan CPO
Pemuliaan untuk perbaikan kandungan CPO menjadi perhatian utama
seluruh lembaga riset kelapa sawit. Hal ini tidak terlepas dari nilai keunggulan
kompetitif kelapa sawit yang mampu menghasilkan minyak dalam
kuantitas lebih tinggi jika dibandingkan dengan tanaman penghasil
minyak lainnya. Untuk perbaikan produktivitas CPO, seleksi ditekankan
pada komponen-komponen utama yang terkait dengan produksi tandan
b) Perbaikan PKO
Minyak inti sawit (PKO) mengandung asam laurat yang berkisar antara
41-55% sehingga dapat dijadikan sebagai salah satu alternatif bahan
baku industri oleokimia. Seiring dengan pengembangan industri hilir kelapa
sawit, permintaan terhadap PKO akan terus meningkat. Saat ini, produksi
rata-rata PKO dari bahan tanaman kelapa sawit komersial hanya sebesar
0,28 ton/ha/tahun. Seleksi dilakukan untuk memperoleh bahan tanaman yang
memiliki persentase inti per buah di atas 10%. Melalui perbaikan persentase
inti per buah dari 5 % menjadi lebih dari 10%, diharapkan dapat meningkatkan
produksi minyak inti menjadi 0,5-1,0 ton/ha/tahun.
c) Kultivar yang Seragam
Peningkatan produksi minyak kelapa sawit per satuan luas, telah dapat
dilakukan dengan menggunakan bahan tanaman klonal. Peningkatan produksi
terjadi karena bahan tanaman klonal diharapkan mempunyai keseragaman
fenotipe di lapangan. Dalam hal ini, induk yang diperbanyak secara klonal
adalah 5% terbaik dari populasi tanaman unggul.
d) Perbaikan asam lemak tak jenuh (ALTJ)
Kepedulian akan kesehatan mendorong pemulia kelapa sawit untuk menaruh
perhatian yang lebih serius terhadap perbaikan kualitas minyak, terutama
kandungan ALTJ dan β karoten, tokoferol serta tokotrienol. Program silang
balik (back cross) antara E. oleifera dan E. guineensis dengan sasaran utama memindahkan alel bermanfaat yang berasosiasi dengan ALTJ dari E. oleifera
ke E. guineensis saat ini terus dilakukan. e) Perbaikan fenologi tanaman.
Pengembangan kultivar dengan karakter batang yang pendek dan tajuk yang
kompak sangat diinginkan karena meningkatkan umur ekonomis dan efisiensi
manajemen tanaman.
f) Toleransi terhadap cekaman biotik dan abiotik
Sejalan dengan meningkatnya intensitas penanaman kembali dan perluasan
areal kelapa sawit ke areal baru dengan tanah yang marjinal, di masa yang
akan datang dibutuhkan bahan tanaman yang memiliki toleransi terhadap
ketahanan terhadap ganoderma dan bahan tanaman yang memiliki sifat toleran terhadap cekaman kekeringan serta toleran terhadap tanah masam
(gambut) merupakan bahan tanaman yang perlu dikembangkan.
Metode Pemuliaan
Asmono et al. (2005) juga menjelaskan bahwa plasma nutfah yang mempunyai keragaman genetik tinggi menjadi bekal utama bagi lembaga riset
yang bekerja untuk pemuliaan kelapa sawit Indonesia. Plasma nutfah tersebut
diperlukan untuk perakitan dan perbanyakan varietas, yang dapat dilakukan
dengan beberapa strategi yaitu; seleksi berulang timbal balik (Recurrent Reciprocal Selection, RRS), seleksi famili dan individu (Family and Individual Palm Selection, FIPS), silang balik, biak sel dan jaringan, serta MAS ( marker-assisted breeding).
a) RRS (Recurrent Reciprocal Selection)
Penggunaan RRS diilhami oleh Comstock dan Robinson (1949) yang
memperkenalkan alat bantu seleksi dengan sasaran utama meningkatkan
alel-alel bermanfaat, mempertahankan keragaman genetik, dan mengeksploitasi
heterosis. Sejalan dengan temuan dua gugus heterotik pada kelapa sawit,
dura dan pisifera, Gascon et al. (1989) menyarankan penggunaan metode RRS untuk memperbaiki produktivitas minyak tanaman kelapa sawit.
Efektivitas program RRS untuk mengeksploitasi heterosis pada kelapa sawit
telah dibuktikan oleh Gascon et al. (1989). Hasil pengujian di Pantai Gading menunjukkan bahwa hasil siklus ke-1 RRS yang dilakukan mampu
meningkatkan produktivitas minyak sebesar 18%. Pada akhir siklus ke-2
RSS, produktivitas minyak meningkat 36%, relatif terhadap rataan
produktivitas minyak pada populasi dasar DxP pra-RRS. Penerapan strategi
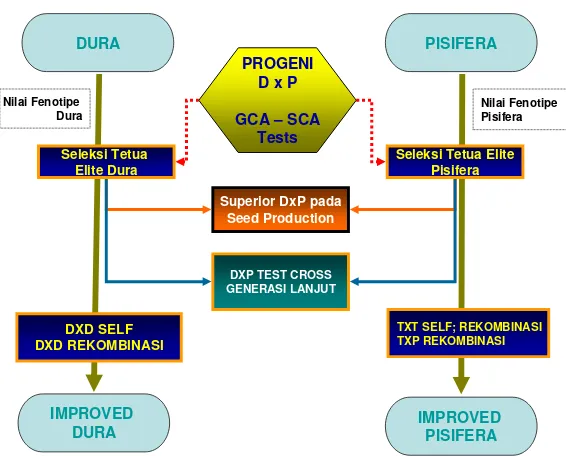
RRS menurut Asmono et al. (2005) melibatkan dua heterotik group yaitu, Group A yang mencakup materi tetua betina dura dan Group B tetua jantan,
pisifera dari famili tenera/pisifera (Gambar 6). Dari populasi dasar yang
telah diseleksi dilakukan suatu tahapan evaluasi untuk menganalisis
dan menentukan individu tanaman terbaik yang dilihat berdasarkan
Gambar 6. Metode seleksi yang melibatkan dua heterotik group: Group A tetua betina dura dan Group B tetua jantan pisifera.
keturunan (progeny test) untuk mengetahui daya gabung umum (GCA) dan daya gabung khusus (SCA) dari tetua (progenitor) masing-masing persilangan
yang diuji. Dari hasil pengujian keturunan diperoleh data yang menunjukkan
potensi dan daya gabung dari tetua-tetua yang digunakan. Berdasarkan data
tersebut dilakukan seleksi untuk menentukan tetua terpilih yang dapat
dijadikan sebagai pohon induk untuk produksi benih komersial. Selain
penentuan pohon induk untuk benih komersial, pada tahapan seleksi ini juga
dipilih tetua-tetua terpilih yang akan direkombinasikan (saling silang antar
tetua DxP dan antar tetua TxT) untuk mencari segregan dan rekombinan
dengan potensi yang lebih baik pada siklus pemuliaan berikutnya. Pemilihan
tetua yang terpilih akan direkombinasikan berdasarkan atas data hasil uji
keturunan. Melalui segregasi dan rekombinasi diharapkan dapat terbentuk
populasi dasar baru dengan sifat-sifat yang lebih baik dari populasi dasar
sebelumnya.
b) FIPS (Family and Individual Palm Selection)
Prosedur pemuliaan yang lain adalah dengan menerapkan strategi seleksi
yang didasarkan pada seleksi famili dan individu, yang lazim disebut Family
Seleksi Tetua Elite Dura
Seleksi Tetua Elite Pisifera
DXD SELF DXD REKOMBINASI
TXT SELF; REKOMBINASI TXP REKOMBINASI
Superior DxP pada Seed Production
DXP TEST CROSS GENERASI LANJUT
Nilai Fenotipe Dura
Nilai Fenotipe Pisifera
PROGENI D x P
GCA – SCA Tests
DURA PISIFERA
IMPROVED
and Individual Palm Selection (FIPS). Menurut Asmono et al. (2005) seleksi dan rekombinasi dilakukan pada famili dura, sedangkan untuk
pengujian dura-dura tersebut disilangkan dengan tester berupa pisifera
unggul. Tujuan utama dari penggunaan FIPS adalah untuk memperbaiki
produksi CPO. Prosedur seleksi ini juga dilakukan untuk memperbaiki sifat
sekunder, seperti pertumbuhan meninggi yang lambat. Keberadaan varietas
yang mengandung CPO tinggi dan mempunyai pertumbuhan meninggi yang
lambat diharapkan dapat meningkatkan nilai ekonomi kelapa sawit.
c) Biak Sel dan Jaringan.
Peningkatan produksi minyak kelapa sawit per satuan luas areal juga dapat
dilakukan dengan menggunakan material kelapa sawit klonal hasil kultur
jaringan. Pengembangan klon melalui teknologi kultur jaringan ini masih
terus dilakukan. Hasil pengamatan di lapang pada percobaan PPKS
menunjukkan bahwa tanaman klon asal kultur jaringan mampu menghasilkan
tandan buah segar (TBS) 30-40% lebih tinggi dari produksi TBS tanaman asal
benih (Latief et al. 2003). Peningkatan produksi terjadi karena keseragaman tanaman klonal dan karena penggunaan pohon induk terpilih dari 5% terbaik
populasi DxP hasil seleksi RRS. Namun demikian kendala terbesar yang
dihadapi bahan tanaman asal kultur jaringan adalah keberadaan tandan buah
yang abnormal (mantled).
d) Silang Balik (Backcross). Backcross merupakan prosedur umum yang digunakan untuk mentransfer karakter-karakter spesifik dari satu spesies ke
spesies lainnya. Saat ini dikenal dua spesies utama pada kelapa sawit:
E. guineensis yang berasal dari Afrika dan E. Oleifera yang berasal dari Amerika. Kelapa sawit komersial yang dikenal saat ini, E. guineensis, memiliki berbagai keunggulan, utamanya kandungan CPO yang tinggi.
Namun demikian, ada beberapa kelemahan diantaranya komponen penting,
seperti kandungan asam lemak tak jenuh (ALTJ), pada E. guineensis umumnya sangat rendah (hanya 40-60 %) dengan pertumbuhan meninggi
yang relatif cepat. Di sisi lain, E.oleifera dikenal sebagai spesies kelapa sawit yang memiliki kandungan CPO sangat rendah, persentase ALTJ sangat tinggi
lembaga riset dengan menggunakan metode backcross, saat ini berupaya untuk mentransfer karakter unggul E. oleifera, utamanya ALTJ tinggi, ke
E, guineensis. Tujuan utamanya adalah untuk menghasilkan kelapa sawit unggul yang mempunyai kandungan CPO sekaligus ALTJ yang tinggi.
d) Marker-Assisted Selection (MAS).
Untuk memecahkan kendala inefisiensi program pemuliaan diperlukan
pendekatan baru dengan sasaran memperpendek siklus seleksi. Salah satu
upaya yang dapat dilakukan adalah dengan menggabungkan teknologi marka
molekuler ke dalam kegiatan seleksi, atau lazim disebut marker-assisted selection (MAS). Secara empiris maupun teoritis MAS efektif dan mampu memperpendek siklus seleksi pada berbagai tanaman. Integrasi marka
molekuler ke dalam program seleksi membawa dua implikasi penting bagi
pemuliaan tanaman kelapa sawit. Pertama, pengurangan jumlah siklus seleksi
sejalan dengan peningkatan efektifitas seleksi. Kedua, pengurangan waktu
yang diperlukan untuk uji keturunan di dalam satu siklus seleksi, karena siklus
seleksi berikutnya dapat dilakukan tanpa harus menunggu tanaman mencapai
puncak usia menghasilkan. Pada tanaman kelapa sawit, secara normal satu
siklus seleksi memerlukan waktu antara 7-10 tahun. Jika marka molekuler
mampu mendeteksi keunggulan suatu karakter sejak dini, maka siklus seleksi
berikutnya dapat dimulai pada saat tanaman mulai belajar menghasilkan yaitu
umur 2-3 tahun (Asmono et al. 2005).
Marka Molekuler
Potensi
Keragaman genetik secara konvensional dapat terjadi karena segregasi,
rekombinasi atau mutasi alami. Dengan kemajuan teknologi, keragaman
genetik juga dapat diinduksi melalui variasi somaklonal, perlakuan radiasi
sinar gamma, fusi protoplas dan rekayasa genetika. Informasi mengenai
keragaman genetik plasma nutfah perlu diketahui karena sangat penting untuk
Keragaman genetik juga sangat diperlukan dalam pengembangan program
pemuliaan tanaman (Bennet 1993).
Pemuliaan tanaman yang dilakukan dengan teknik bantuan molekuler
(molecular breeding) merupakan kegiatan pemuliaan tanaman bantuan yang melibatkan pemakaian marka DNA untuk memfasilitasi proses pemuliaan
tersebut. Berdasarkan sejarahnya, para pemulia tanaman mengandalkan fenotipe
tanaman dalam rangka pengembangan kultivar tanaman dengan sifat-sifat yang
unggul. Para pemulia dapat menggunakan teknik molekuler sebagai alat untuk
melengkapi teknik pemuliaan klasik (Forbes 2000).
Sekarang, teknologi marka molekuler mengandalkan amplifikasi sejumlah
kecil DNA melalui polymerase chain reaction (PCR). Fragmen yang teramplifikasi dipisahkan melalui gel elektroforesis dan divisualisasikan melalui
pewarnaan dengan pewarna spesifik untuk DNA. Dengan marka molekuler,
proses seleksi dapat dipercepat. Selain itu, lokus DNA yang bertanggung jawab
terhadap sifat kuantitatif tertentu dapat dipetakan (Jung 1999).
Potensi penggunaan marka sebagai alat untuk melakukan karakterisasi
genetik tanaman telah dikenal sejak puluhan tahun lalu. Marka bisa dikategorikan
sebagai marka morfologi, sitologi, dan yang terbaru adalah marka molekuler
(Moritz dan Hillis 1996). Informasi genetik tanaman dapat diduga dengan
menggunakan marka molekuler, seperti isozim, RFLP, RAPD, SSR, AFLP, dan
yang lainnya (Plieske dan Struss 2001).
SSR (simple sequence repeats)
Dalam DNA pada individu eukariot terdapat tiga kelas pengulangan fraksi
DNA, yaitu fraksi sangat berulang (highly repeated fraction), fraksi berulang secara moderat (moderately repeated fraction), dan fraksi tidak berulang (nonrepeated fraction). Fraksi sekuen sangat berulang terdiri atas satelit DNA, minisatelit DNA, dan mikrosatelit DNA. Pengulangan sekuennya tersusun secara
tandem. Satelit DNA terdiri atas sekuen-sekuen pendek dengan ukuran 5-10 bp
yang jumlah pengulangannya sangat banyak sehingga membentuk cluster sangat besar dan panjang DNA-nya dapat mencapai 100 juta bp. Minisatelit DNA,
mengandung 1000-3000 pengulangan. Mikrosatelit DNA terdiri atas
sekuen-sekuen pendek dengan ukuran 2-5 bp dan berada pada cluster yang rata-rata pengulangannya maksimum 100 kali (Karp 1996). Sekuen berulang
sederhana yang dimiliki mikrosatelit atau SSR, tersebar secara acak dalam genom
eukariot.
Saghai-Maroof et al. (1994) mengemukakan beberapa alasan pemakaian SSR untuk analisis molekular yaitu: (1) melimpah, (2) terdistribusi dengan
seragam, (3) sangat polimorfis, (4) kodominan, (5) dihasilkan dengan cepat
melalui PCR, (6) relatif sederhana untuk ditafsirkan, dan (7) mudah diakses oleh
laboratorium lain melalui publikasi sekuen primer. Bahkan Powell et al. (1996) membuktikan bahwa dari empat marka molekuler yang diuji (RFLP, RAPD,
AFLP dan SSR) marka SSR memiliki kandungan informasi (kemampuan untuk
membedakan genotipe) yang paling tinggi untuk mengevaluasi plasma nutfah
kedelai dibandingkan dengan marka molekuler yang lain .
Penerapan SSR pada Tanaman Kelapa Sawit
Marka SSR untuk kelapa sawit pertama kali dikembangkan oleh CIRAD
Perancis. Bilotte et al. (2001) melaporkan hasil pengembangan marka SSR kelapa sawit berlangsung langkah demi langkah, mulai dari penapisan pustaka
SSR yang diperkaya dengan unit pengulangan (GA)n, (GT)n, dan (CCG)n, sampai
kepada karakterisasi akhir 21 lokus SSR. Juga telah dilaporkan tentang sekuen
primer, estimasi kisaran ukuran alel, dan heterosigositas yang diharapkan pada
E. guineensis dan E. oleifera. Analisis data multivariat menunjukkan kemampuan marka SSR yang sangat efisien untuk mengevaluasi struktur keragaman genetik
genus Elaeis. Keberadaan variabilitas alelik yang tinggi mengindikasikan bahwa penggunaan SSR pada E. guineensis akan menjadi perangkat yang sangat bermanfaat untuk kajian genetik, termasuk identifikasi varietas dan pemetaan
AKSESI KELAPA SAWIT (Elaeis guineensis Jacq.) PISIFERA
ASAL NIGERIA
Abstrak
Tujuan penelitian ini adalah untuk membandingkan keefektifan marka RAPD dan SSR untuk analisis genetik sembilan pokok kelapa sawit pisifera yang berasal dari Nigeria (pisifera Nigeria). Sembilan aksesi pisifera
Nigeria (5 aksesi berasal dari pisifera famili TxP dan 4 aksesi dari pisifera klon) digunakan dalam penelitian ini. Untuk menghasilkan marka RAPD digunakan lima primer acak RAPD dan untuk menghasilkan marka SSR digunakan lima pasang primer spesifik SSR.
Hasil penelitian menunjukkan bahwa dari lima primer acak yang diuji terhadap pisifera Nigeria yang diuji, empat primer menghasilkan marka RAPD yang polimorfis. Seluruh primer menghasilkan 16 marka RAPD dan hanya empat (25%) yang polimorfis pada pisifera Nigeria. Jumlah rata-rata marka RAPD yang dihasilkan adalah 3,2 marka tiap marka per primer sedangkan jumlah rata-rata marka yang polimorfis adalah 0,8 marka per primer. Hasil juga menunjukkan bahwa seluruh primer spesifik (100%) menghasilkan marka SSR yang polimorfis pada seluruh pisifera Nigeria yang diuji. Jumlah rata-rata alel yang dihasilkan adalah 2,6 alel per primer sedangkan jumlah rata-rata alel yang polimorfis adalah 1,0.
Marka RAPD dan SSR mampu menunjukkan identitas dari empat ramet pisifera klon sebagai satu genotype, hal ini menunjukkan bahwa keempat ramet tersebut benar-benar berasal dari sumber klonal. Di samping itu marka RAPD dan SSR mampu mengidentifikasi secara tepat aksesi pisifera TxP yang secara genetik berbeda, menunjukkan bahwa pisifera TxP merupakan segregan atau rekombinan. Hasil analisis UPGMA menggunakan marka RAPD menempatkan pisifera klon pada kemiripan 0,83 – 0,91 terhadap aksesi pisifera TxP famili, sementara marka SSR menempatkannya pada 0,63 – 0,84. Sebagai tambahan SSR marker merupakan marka kodominan, lebih polimorfik, mudah ditafsirkan dan menunjukkan reprodusibilitas yang lebih tinggi dari pada marka RAPD. Karena itu, marka SSR dianjurkan untuk digunakan pada kajian keragaman genetik kelapa sawit.
EFFECTIVENESS OF RAPD AND SSR MARKERS FOR
GENETIC ANALYSIS OF NINE PISIFERA OIL PALM
(Elaeis guineensis Jacq.) ORIGINATED FROM NIGERIA
Abstract
The objectives of this experiment were to compare effectiveness of RAPD and SSR markers for genetic analysis of nine pisifera oil palm originated from Nigeria (pisifera Nigeria). Nine accessions of pisifera Nigeria (5 accessions of TxP pisifera family and 5 accessions of pisifera clone) were used. Five random primers were used to generated RAPD markers and five specific primers were used for SSR markers.
Results of the experiment indicated four out of five evaluated random primers generated polymorphic RAPD markers in the pisifera Nigeria. All primers generated a total of 16 RAPD markers and only four of them (25%) were polymorphic in the pisifera Nigeria. The average number of generated RAPD markers was 3.2 markers per primer while the average number of polymorphic marker per primer was only 0.8. Results also indicated all specific primers (100%) generated polymorphic SSR markers in the pisifera Nigeria. The average number was 2.6 alleles per primer while the average number of polymorphic alleles per primer was 1,0.
Either RAPD or SSR markers was able to indicate the identity of four ramets of pisifera clone as single genotype, indicating they were clonal materials. On the other hand, either RAPD or SSR marker correctly identified the TxP pisifera accessions as genetically different, indicating they were segregants or recombinants. The result of UPGMA analysis using RAPD marker positioned the pisifera clone at 0.83 – 0.91 similarity to accession of TxP pisifera family while using SSR marker they were at 0.63 – 0.84. This data indicated that SSR was more informatic than RAPD marker. In addition SSR marker was codominant, more polymorphic, easier to interpret and showed higher reproducibility than RAPD marker. Therefore, SSR marker was suggested for oil palm genetic diversity studies.
Pendahuluan
Kelapa sawit tipe pisifera merupakan tetua jantan penghasil serbuk sari
yang berperan penting dalam membentuk turunan yang unggul dan berkualitas.
Pisifera Nigeria yang dikoleksi oleh PT Bina Sawit Makmur dihasilkan
secara generatif melalui persilangan tenera (GHA 608) x pisifera (GHA 608).
Dari persilangan ini menghasilkan pohon tipe pisifera sebesar 50% dari populasi
bibit hasil persilangan. Sebagian pisifera Nigeria milik PT Bina Sawit Makmur
juga berasal dari perbanyakan vegetative melalui teknik kultur jaringan
yang melibatkan tetua pisifera GHA 608 sebagai sumber eksplan (ortet).
Dari kultur jaringan ini menghasilkan 100% pohon pisifera (ramet) yang seragam
(BSM 2007). Berdasarkan asal usulnya, pisifera hasil persilangan TxP secara
genetik akan beragam sedangkan pisifera klon secara genetik seragam.
Keragaman atau keseragaman masing-masing pisifera Nigeria tersebut perlu
dianalisis lebih lanjut.
Ada beberapa pendekatan yang dapat dilakukan untuk mengevaluasi
keragaman genetik pada tanaman yaitu melalui informasi berdasarkan marka
morfologi, sitologi dan molekuler. Marka berbasis protein (enzim) meskipun
relatif cepat, murah dan mudah namun masih memiliki tingkat polimorfisme yang
terbatas (Meunier 1992). Marka molekular berbasis DNA mampu menjadi
alternatif yang lebih baik untuk mengkarakterisasi populasi tanaman karena
polimorfismenya lebih tinggi, konsisten dan tidak dipengaruhi faktor lingkungan
(Rafalski et al. 1994; Wickneswari 1996).
Studi genetik berbasis molekuler pada tanaman kelapa sawit yang
telah dilakukan diantaranya kajian genom kelapa sawit menggunakan
restriction fragment length polymorphism (RFLP), random amplification of polymorphic DNA (RAPD) dan amplified fragment length polimorphism (AFLP) (Rajanaidu et al. 1995; Singh dan Cheah 1996), studi keragaman genetik 241 aksesi E. oleifera dari Amerika dan 38 aksesi E. guineensis dari Afrika menggunakan RFLP dan AFLP (Barcelos 1998), studi pembentukan peta pautan
kelapa sawit (Irwansyah et al. 2004), karakterisasi 21 lokus marka
simple sequence repeats (SSR) pada kelapa sawit (Bilotte et al. 2001) dan peta pautan genetik kelapa sawit berbasis SSR (Bilotte et al 2005). Marka SSR juga telah digunakan sebagai prosedur pengendalian mutu dalam memproduksi klon
kultur jaringan kelapa sawit dalam skala komersial (Singh et al. 2007).
Marka RAPD merupakan salah satu marka DNA yang menggunakan
prinsip kerja polymerase chain reaction (PCR) untuk mengamplifikasi sekuen DNA tertentu secara in-vitro. Marka RAPD merupakan marka genetik yang relatif sederhana, mudah dalam penyiapannya, memberikan hasil lebih cepat dan
menghasilkan marker yang relatif tidak terbatas jumlahnya sehingga sangat
membantu untuk analisis keragaman genetik tanaman yang informasi tentang
DNA genomnya tidak diketahui (Asmono et al. 2000).
Mikrosatelit, yang juga dikenal dengan simple sequence repeats (SSR) merupakan DNA berulang yang sub unitnya terdiri atas 1-6 nukleotida.
Mikrosatelit diketahui tersebar secara merata pada genom eukariot. Marka
mikrosatelit merupakan marka DNA yang memiliki beberapa keunggulan, yaitu:
sangat polimorfis, jumlahnya melimpah, pewarisannya bersifat kodominan,
analisisnya sederhana dan mudah ditranfer melalui publikasi sekuen. Sebagai
marka kodominan yang lokus spesifik, marka SSR secara luas telah digunakan
sebagai alat untuk identifikasi genotipe dan kajian genetika populasi pada
tanaman. (Saghai-Maroof et al., 1994; Smith et al., 1997; Bilotte et al., 2001; Singh et al., 2007).
Dengan tersedianya berbagai marka yang ditunjukkan marka molekuler
berbasis DNA sebagai alat bantu untuk analisis keragaman genetik tersebut
selayaknya dievaluasi efektifitasnya pada berbagai tanaman yang bernilai
ekonomi. Penelitian ini bertujuan untuk mengevaluasi efektifitas penggunaan
marka RAPD dan marka SSR untuk analisis keragaman genetik plasma nutfah
kelapa sawit pisifera Nigeria. Hasil penelitian ini diharapkan dapat memberikan
informasi awal guna mendapatkan marka yang efektif dan efisien untuk analisis
Bahan dan Metode
Tempat, Waktu dan Bahan Tanaman
Penelitian dilaksanakan di Laboratorium Biologi Molekuler, Departemen
Agronomi dan Hortikultura, Fakultas Pertanian, Institut Pertanian Bogor. Sampel
daun tanaman diambil dari Kebun Induk PT Bina Sawit Makmur, Sumatera
Selatan. Penelitian dilaksanakan mulai bulan November 2007 sampai dengan
April 2009.
Bahan tanaman yang digunakan untuk analisis keragaman genetik berupa
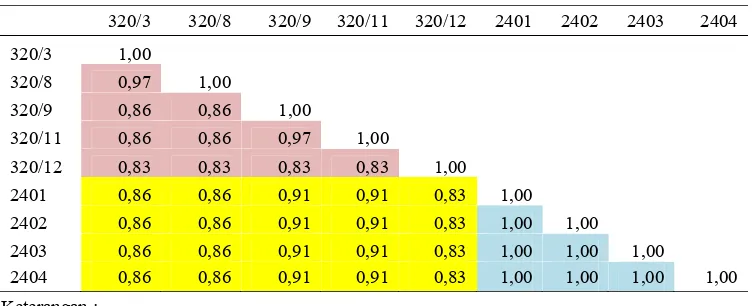
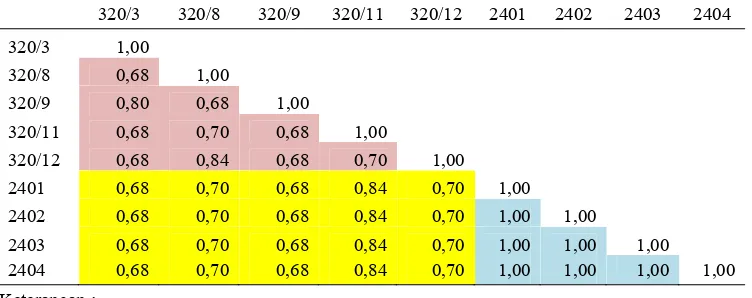
sampel daun tanaman kelapa sawit (Elaeis guineensis Jacq.) pisifera Nigeria famili TxP No. 24 yang terdiri atas lima nomor aksesi (320/3, 320/8, 320/9,
320/11 dan 320/12) dan pisifera klon yang terdiri atas empat ramet (2401, 2402,
2403 dan 2404). Pengambilan sampel daun mengacu pada metode yang
dikembangkan oleh Toruan-Mathius et al. (1996).
Isolasi DNA
DNA genomik diisolasi dari jaringan daun pertama (daun tombak) kelapa
sawit dilakukan mengikuti metode CTAB yang dikembangkan oleh Orozco
Castillo et al.(1993). Modifikasi dengan penambahan PVP (polyvinylpyrrolidone) 50 mg dan 2-Mercaptoethanol 10 µl ke dalam larutan penyangga. Konsentrasi dan
kemurnian DNA dapat ditentukan dengan UV-spektrofotometer. Tingkat
kemurniaan DNA yang cukup memadai untuk analisis lanjutan sesuai yang
ditetapkan Sambrook et al. (1987) adalah jika nilai absorban pada panjang gelombang (λ) 260 dan 280 nm berkisar 1,7 – 2,0.
Keragaman genetik berdasarkan marka RAPD
Protokol reaksi amplifikasi diadaptasi dari prosedur yang dikembangkan
oleh William et al. (1990). Reaksi amplifikasi dilakukan dengan Perkin Elmer Gene Amp PCR System 2400. Untuk satu kali PCR dengan volume akhir 25 µl, ke dalam tabung PCR 0.2 ml ditambahkan reaksi 14.3 µl aquabidestilata (ddH2O)
steril; 2.5 µl Taq buffer 10x; 2.5 µl MgCl2 1.5 mM; 2.5 µl dNTP 10 mM;
2 µl DNA 25 ng/µl. Tahapan PCR diatur sebagai berikut: (1) tahapan
pra-amplifikasi pada suhu 94ºC selama 2 menit; (2) tahapan amplifikasi sebanyak
45 siklus masing-masing siklus terdiri dari tiga tahapan yaitu, (a) pemisahan utas
ganda cetakan DNA menjadi utas tunggal (denaturasi) pada 94ºC selama 1 menit,
(b) penempelan primer pada utas tunggal DNA (primer annealing) pada 36ºC selama 1 menit dan (c) pemanjangan utas nukleotida baru (primer extension) pada 72ºC selama 2 menit; serta (3) tahapan pasca-amplifikasi yaitu pemanjangan utas
tunggal DNA tahap akhir (final extention) pada 72ºC selama 4 menit dan pendinginan pada suhu ruang atau suhu simpan 4ºC.
DNA hasil amplifikasi PCR yang didapat ditambahkan 2 µl loading buffer
dan potongan DNA-nya dipisahkan dengan elektroforesis gel agarosa 1.4% (w/v)
menggunakan larutan penyangga TAE 1x. Setelah elektroforesis gel agarosa
diberi pewarnaan (staining) dengan merendam ke dalam larutan etidiumbromida 5 µg/l selama 30 menit dan dibilas (destaining) dengan aquades selama 20 menit. Pita DNA divisualisasikan di atas UV-transluminator (panjang gelombang 312
nm) dan didokumentasikan dengan kamera.
Keragaman genetik berdasarkan marka SSR
Amplifikasi DNA mengikuti metode yang dikembangkan oleh Bilotte et al. (2001) dengan menggunakan Perkin Elmer Gene Amp PCR System 2400. Tahapan PCR diatur sebagai berikut: (1) tahapan pra-amplifikasi pada 94ºC
selama 1 menit, (2) tahapan amplifikasi sebanyak 35 siklus masing-masing siklus
terdiri atas tiga tahapan yaitu (a) pemisahan utas ganda cetakan DNA menjadi utas
tunggal (denaturasi) pada 94ºC selama 30 detik, (b) penempelan primer pada utas
tunggal DNA (primer annealing) pada 52ºC selama 1 menit, dan (c)