LAMPIRAN 2. Lembar Penjelasan dan Persetujuan (Informed Consent)
LEMBARAN PENJELASAN
HUBUNGAN EKSPRESI BIOFILM BAKTERI DENGAN KULTUR BAKTERI DAN ANALISIS UJI KEPEKAAN ANTIBIOTIK PADA PENDERITA
RINOSINUSITIS KRONIS
Bapak/Ibu yang terhormat, nama saya dr. Silvia, Peserta Program Pendidikan Dokter Spesialis Ilmu Kesehatan Telinga Hidung Tenggorok Fakultas Kedokteran Universitas Sumatera Utara. Saat ini saya sedang melakukan penelitian untuk tesis saya yang berjudul Hubungan Ekspresi Biofilm Bakteri dengan Kultur Bakteri dan Analisis Uji Kepekaan Antibiotik pada Penderita Rinosinusitis Kronis, atau dengan istilah lain apakah ditemukan biofilm bakteri pada sinus yang terinfeksi yang mengakibatkan penyakit rinosinusitis kronis seperti yang Bapak/Ibu derita serta adakah hubungannya dengan kultur bakteri, jenis bakteri apa yang dapat menyebabkan rinosinusitis kronis baik dengan biofilm ataupun tidak dan antibiotik apa yang sensitif untuk penderita rinosinusitis kronis baik dengan biofilm ataupun tidak.
Dalam penelitian ini Bapak/Ibu akan menjalani pemeriksaan THT berdasarkan gejala dan tanda yang dialami. Apabila telah disarankan untuk menjalani tindakan bedah sinus endoskopik fungsional (BSEF) yaitu suatu tindakan operasi yang menggunakan tehnik minimal invasif memakai alat endoskopi, maka sebelumnya saya melakukan wawancara, mengambil data-data mengenai hasil pemeriksaan Bapak/Ibu dan saya meminta izin untuk mengambil daging dari hasil operasi bedah sinus tersebut untuk dilakukan pemeriksaan apakah dalam daging tersebut terdapat biofilm bakteri serta
usapan pada daerah karang hidung bagian tengah untuk dilakukan pemeriksaan bakteri apa yang dijumpai serta antibiotik apa yang tepat untuk digunakan. Melalui hasil pemeriksaan tersebut dapat diketahui ada tidaknya infeksi yang disebabkan oleh biofilm bakteri serta jenis bakteri apa yang dijumpai dan antibiotik apa yang tepat digunakan untuk Bapak/Ibu, sehingga dapat mengetahui keadaan penyakit rinosinusitis akibat biofilm serta hubungannya dengan kultur bakteri dan analisis uji kepekaan antibiotik di RSUP. H. Adam Malik Medan dan RS. Haji Mina Medan.
Sebelum memulai wawancara, saya mengucapkan terimakasih yang sebesar-besarnya kepada Bapak/Ibu atas kesediaannya menjadi Responden. Perlu saya jelaskan bahwa penelitian ini akan saya gunakan untuk mengetahui diagnosa, perjalanan penyakit, dan penatalaksanaan yang tepat untuk Bapak/Ibu serta untuk penyusunan penelitian tesis Saya dan tidak untuk keperluan yang lain.
Untuk keakuratan data dan informasi yang saya kumpulkan maka saya sangat berharap agar bapak/ibu bersedia memberikan jawaban yang sejelas-jelasnya sesuai dengan apa yang bapak/ibu ketahui, alami dan rasakan sehubungan dengan judul penelitian saya.
Pada penelitian ini identitas Anda disamarkan. Hanya dokter peneliti, anggota peneliti dan anggota komisi etik yang bisa melihat data Anda. Kerahasiaan data Anda akan dijamin sepenuhnya. Bila data Anda dipublikasi kerahasiaannya tetap dijaga.
Partisipasi Anda dalam penelitin ini bersifat sukarela. Tidak terjadi perubahan mutu pelayanan dari dokter Anda bila Anda tidak bersedia mengikuti penelitian ini. Anda akan tetap mendapatkan pelayanan kesehatan standar rutin sesuai dengan prosedur pelayanan. Sebagai tanda terima kasih kami akan memberikan makan siang dan biaya ganti transportasi kepada Anda.
Mudah-mudahan informasi yang saya sampaikan sudah cukup jelas. Bila demikian saya harapkan Bapak/Ibu dapat membubuhkan tandatangan pada bagian bawah lembaran ini sebagai tanda persetujuan dan wawancara akan segera kita mulai.
Bila ada keluhan setelah dilakukannya tindakan, maka Bapak/Ibu dapat menghubungi saya di nomor 081396666003. Peneliti akan bertanggung jawab dan membantu mengatasi keluhan Anda.
Lembar Persetujuan Setelah Penjelasan (Informed Consent)
Saya yang bertanda tangan di bawah ini :
Nama : ... Umur : ... Jenis Kelamin : ... Alamat : ...
Setelah mendapat penjelasan dan memahami dengan penuh kesadaran mengenai penelitian ini, maka dengan ini saya menyatakan bersedia untuk ikut serta. Apabila dikemudian hari saya mengundurkan diri dari penelitian ini, maka saya tidak akan dituntut apapun.
Demikian surat pernyataan ini saya buat, agar dapat dipergunakan bila diperlukan.
Medan, 20
Saksi Peserta penelitian
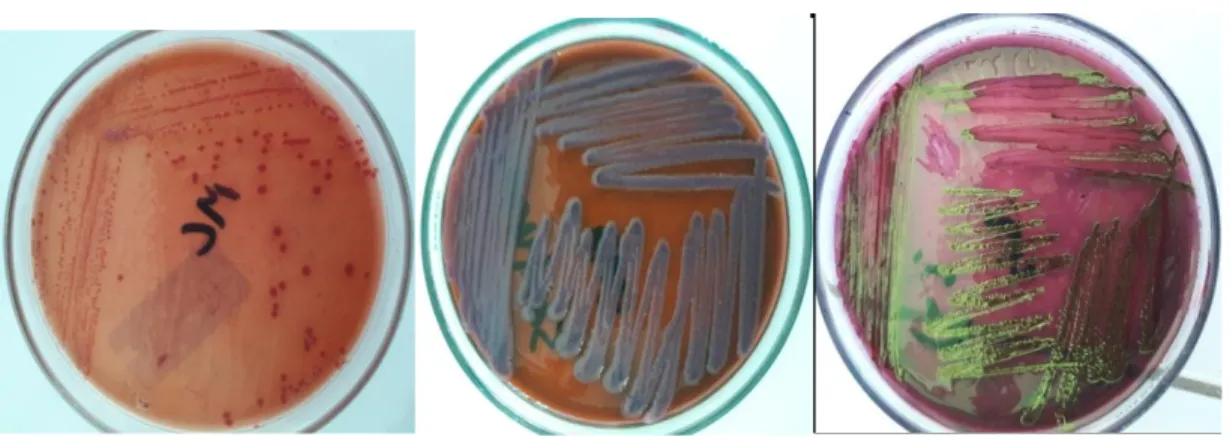
LAMPIRAN 3. Pemeriksaan Kultur Bakteri
Gambar 7.1. Hasil Pemeriksaan Kultur Bakteri
Gambar 7.2. Gambaran Mikroskopis, Kanan: batang gram negatif, Kiri: coccus gram positif
LAMPIRAN 4. Data Output OUTPUT ANALISIS Frequency Table jenis_kelamin Frequenc y Percent Valid Percent Cumulative Percent Valid pria 18 56.3 56.3 56.3 wanita 14 43.8 43.8 100.0 Total 32 100.0 100.0 Descriptives Statistic Std. Error usia Mean 37.44 2.763 95% Confidence Interval for Mean
Lower Bound 31.80 Upper Bound 43.07 5% Trimmed Mean 37.28 Median 37.00 Variance 244.319 Std. Deviation 15.631 Minimum 10 Maximum 70 Range 60 Interquartile Range 25 Skewness .100 .414 Kurtosis -.737 .809 merokok Frequenc y Percent Valid Percent Cumulative Percent Valid tidak 23 71.9 71.9 71.9 ya 9 28.1 28.1 100.0 Total 32 100.0 100.0
tersumbat Frequenc y Percent Valid Percent Cumulative Percent Valid tidak 2 6.3 6.3 6.3 ya 30 93.8 93.8 100.0 Total 32 100.0 100.0 sekret Frequenc y Percent Valid Percent Cumulative Percent Valid tidak 8 25.0 25.0 25.0 ya 24 75.0 75.0 100.0 Total 32 100.0 100.0 nyeri Frequenc y Percent Valid Percent Cumulative Percent Valid tidak 10 31.3 31.3 31.3 ya 22 68.8 68.8 100.0 Total 32 100.0 100.0 penciuman Frequenc y Percent Valid Percent Cumulative Percent Valid tidak 15 46.9 46.9 46.9 ya 17 53.1 53.1 100.0 Total 32 100.0 100.0 polip Frequenc y Percent Valid Percent Cumulative Percent Valid tidak 21 65.6 65.6 65.6 ya 11 34.4 34.4 100.0 Total 32 100.0 100.0
bakteri Frequenc y Percent Valid Percent Cumulative Percent Valid positif 21 65.6 65.6 65.6 negatif 11 34.4 34.4 100.0 Total 32 100.0 100.0 jenis_kelamin * bakteri Crosstab bakteri Total positif negatif jenis_kelami n pria Count 12 6 18 Expected Count 11.8 6.2 18.0 % within jenis_kelamin 66.7% 33.3% 100.0% % within bakteri 57.1% 54.5% 56.3% wanita Count 9 5 14 Expected Count 9.2 4.8 14.0 % within jenis_kelamin 64.3% 35.7% 100.0% % within bakteri 42.9% 45.5% 43.8% Total Count 21 11 32 Expected Count 21.0 11.0 32.0 % within jenis_kelamin 65.6% 34.4% 100.0% % within bakteri 100.0% 100.0% 100.0% Chi-Square Tests Value df Asymp. Sig. (2-sided) Exact Sig. (2-sided) Exact Sig. (1-sided) Pearson Chi-Square .020a 1 .888 Continuity Correctionb .000 1 1.000 Likelihood Ratio .020 1 .888
Fisher's Exact Test 1.000 .590
Linear-by-Linear
Association .019 1 .890
a. 1 cells (25.0%) have expected count less than 5. The minimum expected count is 4.81.
b. Computed only for a 2x2 table Risk Estimate
Value
95% Confidence Interval Lower Upper Odds Ratio for
jenis_kelamin (pria / wanita)
1.111 .256 4.824
For cohort bakteri =
positif 1.037 .623 1.725
For cohort bakteri =
negatif .933 .358 2.436 N of Valid Cases 32 merokok * bakteri Crosstab bakteri Total positif negatif meroko k tidak Count 16 7 23 Expected Count 15.1 7.9 23.0 % within merokok 69.6% 30.4% 100.0% % within bakteri 76.2% 63.6% 71.9% ya Count 5 4 9 Expected Count 5.9 3.1 9.0 % within merokok 55.6% 44.4% 100.0% % within bakteri 23.8% 36.4% 28.1% Total Count 21 11 32 Expected Count 21.0 11.0 32.0
% within merokok 65.6% 34.4% 100.0% % within bakteri 100.0% 100.0% 100.0% Chi-Square Tests Value df Asymp. Sig. (2-sided) Exact Sig. (2-sided) Exact Sig. (1-sided) Pearson Chi-Square .563a 1 .453 Continuity Correctionb .113 1 .737 Likelihood Ratio .551 1 .458
Fisher's Exact Test .681 .362
Linear-by-Linear
Association .545 1 .460
N of Valid Cases 32
a. 1 cells (25.0%) have expected count less than 5. The minimum expected count is 3.09.
b. Computed only for a 2x2 table Risk Estimate
Value
95% Confidence Interval Lower Upper Odds Ratio for
merokok (tidak / ya) 1.829 .374 8.937 For cohort bakteri =
positif 1.252 .658 2.384
For cohort bakteri =
negatif .685 .263 1.783
N of Valid Cases 32
Case Processing Summary bakter
i
Cases
Valid Missing Total
N Percent N Percent N Percent
usia positif 21 100.0% 0 0.0% 21 100.0%
negatif 11 100.0% 0 0.0% 11 100.0%
a negatif 11 100.0% 0 0.0% 11 100.0% Descriptives
bakteri Statistic
Std. Error
usia positif Mean 37.76 3.490
95% Confidence Interval for Mean
Lower Bound 30.48 Upper Bound 45.04 5% Trimmed Mean 37.54 Median 37.00 Variance 255.790 Std. Deviation 15.993 Minimum 10 Maximum 70 Range 60 Interquartile Range 25 Skewness .002 .501 Kurtosis -.441 .972 negatif Mean 36.82 4.721 95% Confidence Interval for Mean
Lower Bound 26.30 Upper Bound 47.34 5% Trimmed Mean 36.58 Median 32.00 Variance 245.164 Std. Deviation 15.658 Minimum 16 Maximum 62 Range 46 Interquartile Range 29 Skewness .336 .661 Kurtosis -1.195 1.279 lama_gejal a positif Mean 35.14 8.730 95% Confidence Interval for Mean
Lower
Upper Bound 53.35 5% Trimmed Mean 32.21 Median 15.00 Variance 1600.32 9 Std. Deviation 40.004 Minimum 3 Maximum 120 Range 117 Interquartile Range 50 Skewness 1.232 .501 Kurtosis .168 .972 negatif Mean 15.55 3.423 95% Confidence Interval for Mean
Lower Bound 7.92 Upper Bound 23.17 5% Trimmed Mean 15.11 Median 12.00 Variance 128.873 Std. Deviation 11.352 Minimum 3 Maximum 36 Range 33 Interquartile Range 20 Skewness .353 .661 Kurtosis -1.126 1.279 Tests of Normality bakter i Kolmogorov-Smirnova Shapiro-Wilk Statistic df Sig. Statistic df Sig.
usia positif .100 21 .200* .978 21 .897 negatif .166 11 .200* .944 11 .573 lama_gejal a positif .276 21 .000 .774 21 .000 negatif .226 11 .121 .872 11 .082
*. This is a lower bound of the true significance. a. Lilliefors Significance Correction
T-Test Group Statistics bakteri N Mean Std. Deviation Std. Error Mean usia positif 21 37.76 15.993 3.490 negatif 11 36.82 15.658 4.721
Independent Samples Test Levene's
Test for Equality
of Variance
s t-test for Equality of Means
F Sig. t df Sig. (2-tailed ) Mean Differe nce Std. Error Differen ce 95% Confidence Interval of the Difference Lower Upper usi a Equal variances assumed .06 4 .80 3 .16 0 30 .874 .944 5.911 -11.12 9 13.016 Equal variances not assumed .16 1 20.80 9 .874 .944 5.871 -11.27 2 13.160 Mann-Whitney Test Ranks bakter i N Mean Rank Sum of Ranks lama_gejal a positif 21 17.43 366.00 negati f 11 14.73 162.00 Total 32
Test Statisticsa lama_gejal a Mann-Whitney U 96.000 Wilcoxon W 162.000 Z -.784
Asymp. Sig. (2-tailed) .433 Exact Sig.
[2*(1-tailed Sig.)] .457
b
a. Grouping Variable: bakteri b. Not corrected for ties. Crosstabs
Notes
Output Created 08-JAN-2017 11:43:40
Comments
Input Data C:\Users\User\Downloads\sp
ss tesis silvia tht edit.sav Active Dataset DataSet1
Filter <none>
Weight <none>
Split File <none> N of Rows in Working
Data File 32
Missing Value Handling
Definition of Missing User-defined missing values are treated as missing. Cases Used Statistics for each table are
based on all the cases with valid data in the specified range(s) for all variables in each table.
Syntax CROSSTABS
/TABLES=tersumbat sekret nyeri penciuman polip BY bakteri
/FORMAT=AVALUE TABLES
/STATISTICS=CHISQ RISK /CELLS=COUNT
EXPECTED ROW COLUMN /COUNT ROUND CELL.
Resources Processor Time 00:00:00.03
Elapsed Time 00:00:00.02
Dimensions
Requested 2
Cells Available 174734
Case Processing Summary Cases
Valid Missing Total
N Percent N Percent N Percent
tersumbat * bakteri 32 100.0% 0 0.0% 32 100.0% sekret * bakteri 32 100.0% 0 0.0% 32 100.0% nyeri * bakteri 32 100.0% 0 0.0% 32 100.0% penciuman * bakteri 32 100.0% 0 0.0% 32 100.0% polip * bakteri 32 100.0% 0 0.0% 32 100.0% tersumbat * bakteri Crosstab bakteri Total positif negatif tersumba t tidak Count 1 1 2 Expected Count 1.3 .7 2.0 % within tersumbat 50.0% 50.0% 100.0% % within bakteri 4.8% 9.1% 6.3% ya Count 20 10 30 Expected Count 19.7 10.3 30.0 % within tersumbat 66.7% 33.3% 100.0% % within bakteri 95.2% 90.9% 93.8% Total Count 21 11 32 Expected Count 21.0 11.0 32.0 % within tersumbat 65.6% 34.4% 100.0% % within bakteri 100.0% 100.0% 100.0%
Chi-Square Tests Value df Asymp. Sig. (2-sided) Exact Sig. (2-sided) Exact Sig. (1-sided) Pearson Chi-Square .231a 1 .631 Continuity Correctionb .000 1 1.000 Likelihood Ratio .220 1 .639
Fisher's Exact Test 1.000 .577
Linear-by-Linear
Association .224 1 .636
N of Valid Cases 32
a. 2 cells (50.0%) have expected count less than 5. The minimum expected count is .69.
b. Computed only for a 2x2 table Risk Estimate
Value
95% Confidence Interval Lower Upper Odds Ratio for
tersumbat (tidak / ya) .500 .028 8.853 For cohort bakteri =
positif .750 .183 3.068
For cohort bakteri =
negatif 1.500 .343 6.559 N of Valid Cases 32 sekret * bakteri Crosstab bakteri Total positif negatif
sekret tidak Count 5 3 8
Expected Count 5.3 2.8 8.0 % within sekret 62.5% 37.5% 100.0% % within bakteri 23.8% 27.3% 25.0% ya Count 16 8 24
Expected Count 15.8 8.3 24.0 % within sekret 66.7% 33.3% 100.0% % within bakteri 76.2% 72.7% 75.0% Total Count 21 11 32 Expected Count 21.0 11.0 32.0 % within sekret 65.6% 34.4% 100.0% % within bakteri 100.0% 100.0% 100.0% Chi-Square Tests Value df Asymp. Sig. (2-sided) Exact Sig. (2-sided) Exact Sig. (1-sided) Pearson Chi-Square .046a 1 .830 Continuity Correctionb .000 1 1.000 Likelihood Ratio .046 1 .831
Fisher's Exact Test 1.000 .575
Linear-by-Linear
Association .045 1 .832
N of Valid Cases 32
a. 1 cells (25.0%) have expected count less than 5. The minimum expected count is 2.75.
b. Computed only for a 2x2 table Risk Estimate
Value
95% Confidence Interval Lower Upper Odds Ratio for sekret
(tidak / ya) .833 .158 4.401
For cohort bakteri =
positif .938 .511 1.720
For cohort bakteri =
N of Valid Cases 32 nyeri * bakteri Crosstab bakteri Total positif negatif
nyeri tidak Count 7 3 10
Expected Count 6.6 3.4 10.0 % within nyeri 70.0% 30.0% 100.0% % within bakteri 33.3% 27.3% 31.3% ya Count 14 8 22 Expected Count 14.4 7.6 22.0 % within nyeri 63.6% 36.4% 100.0% % within bakteri 66.7% 72.7% 68.8% Total Count 21 11 32 Expected Count 21.0 11.0 32.0 % within nyeri 65.6% 34.4% 100.0% % within bakteri 100.0% 100.0% 100.0% Chi-Square Tests Value df Asymp. Sig. (2-sided) Exact Sig. (2-sided) Exact Sig. (1-sided) Pearson Chi-Square .123a 1 .725 Continuity Correctionb .000 1 1.000 Likelihood Ratio .125 1 .724
Fisher's Exact Test 1.000 .526
Linear-by-Linear
N of Valid Cases 32
a. 1 cells (25.0%) have expected count less than 5. The minimum expected count is 3.44.
b. Computed only for a 2x2 table Risk Estimate
Value
95% Confidence Interval Lower Upper Odds Ratio for nyeri
(tidak / ya) 1.333 .267 6.653
For cohort bakteri =
positif 1.100 .658 1.840
For cohort bakteri =
negatif .825 .276 2.469 N of Valid Cases 32 penciuman * bakteri Crosstab bakteri Total positif negatif penciuma n tidak Count 10 5 15 Expected Count 9.8 5.2 15.0 % within penciuman 66.7% 33.3% 100.0% % within bakteri 47.6% 45.5% 46.9% ya Count 11 6 17 Expected Count 11.2 5.8 17.0 % within penciuman 64.7% 35.3% 100.0% % within bakteri 52.4% 54.5% 53.1% Total Count 21 11 32 Expected Count 21.0 11.0 32.0 % within penciuman 65.6% 34.4% 100.0% % within bakteri 100.0% 100.0% 100.0%
Chi-Square Tests Value df Asymp. Sig. (2-sided) Exact Sig. (2-sided) Exact Sig. (1-sided) Pearson Chi-Square .014a 1 .907 Continuity Correctionb .000 1 1.000 Likelihood Ratio .014 1 .907
Fisher's Exact Test 1.000 .602
Linear-by-Linear
Association .013 1 .909
N of Valid Cases 32
a. 0 cells (0.0%) have expected count less than 5. The minimum expected count is 5.16.
b. Computed only for a 2x2 table Risk Estimate
Value
95% Confidence Interval Lower Upper Odds Ratio for
penciuman (tidak / ya)
1.091 .252 4.714
For cohort bakteri =
positif 1.030 .624 1.701
For cohort bakteri =
negatif .944 .361 2.473 N of Valid Cases 32 polip * bakteri Crosstab bakteri Total positif negatif
polip tidak Count 15 6 21
Expected Count 13.8 7.2 21.0 % within polip 71.4% 28.6% 100.0% % within bakteri 71.4% 54.5% 65.6% ya Count 6 5 11
Expected Count 7.2 3.8 11.0 % within polip 54.5% 45.5% 100.0% % within bakteri 28.6% 45.5% 34.4% Total Count 21 11 32 Expected Count 21.0 11.0 32.0 % within polip 65.6% 34.4% 100.0% % within bakteri 100.0% 100.0% 100.0% Chi-Square Tests Value df Asymp. Sig. (2-sided) Exact Sig. (2-sided) Exact Sig. (1-sided) Pearson Chi-Square .912a 1 .340 Continuity Correctionb .317 1 .573 Likelihood Ratio .898 1 .343
Fisher's Exact Test .442 .284
Linear-by-Linear
Association .884 1 .347
N of Valid Cases 32
a. 1 cells (25.0%) have expected count less than 5. The minimum expected count is 3.78.
b. Computed only for a 2x2 table Risk Estimate
Value
95% Confidence Interval Lower Upper Odds Ratio for polip
(tidak / ya) 2.083 .456 9.508
For cohort bakteri =
positif 1.310 .716 2.394
For cohort bakteri =
negatif .629 .246 1.603
Crosstabs
Notes
Output Created 08-JAN-2017 11:49:36
Comments
Input Data C:\Users\User\Downloads\sp
ss tesis silvia tht edit.sav Active Dataset DataSet1
Filter <none>
Weight <none>
Split File <none> N of Rows in Working
Data File 32
Missing Value Handling
Definition of Missing User-defined missing values are treated as missing. Cases Used Statistics for each table are
based on all the cases with valid data in the specified range(s) for all variables in each table. Syntax CROSSTABS /TABLES=biofilm BY bakteri /FORMAT=AVALUE TABLES /STATISTICS=CHISQ RISK /CELLS=COUNT
EXPECTED ROW COLUMN /COUNT ROUND CELL.
Resources Processor Time 00:00:00.02
Elapsed Time 00:00:00.01
Dimensions
Requested 2
Cells Available 174734
Case Processing Summary Cases
Valid Missing Total
N Percent N Percent N Percent
biofilm *
biofilm * bakteri Crosstabulation bakteri
Total positif negatif
biofilm tidak Count 6 5 11
Expected Count 7.2 3.8 11.0 % within biofilm 54.5% 45.5% 100.0% % within bakteri 28.6% 45.5% 34.4% ya Count 15 6 21 Expected Count 13.8 7.2 21.0 % within biofilm 71.4% 28.6% 100.0% % within bakteri 71.4% 54.5% 65.6% Total Count 21 11 32 Expected Count 21.0 11.0 32.0 % within biofilm 65.6% 34.4% 100.0% % within bakteri 100.0% 100.0% 100.0%
Chi-Square Tests Value df Asymp. Sig. (2-sided) Exact Sig. (2-sided) Exact Sig. (1-sided) Pearson Chi-Square .912a 1 .340 Continuity Correctionb .317 1 .573 Likelihood Ratio .898 1 .343
Fisher's Exact Test .442 .284
Linear-by-Linear
Association .884 1 .347
N of Valid Cases 32
a. 1 cells (25.0%) have expected count less than 5. The minimum expected count is 3.78.
b. Computed only for a 2x2 table Risk Estimate
Value
95% Confidence Interval Lower Upper Odds Ratio for
biofilm (tidak / ya) .480 .105 2.191 For cohort bakteri =
positif .764 .418 1.396
For cohort bakteri =
negatif 1.591 .624 4.057
N of Valid Cases 32
Personalia Penelitian
I. Peneliti Utama
Nama : dr. Silvia
Jabatan : PPDS T.H.T.K.L
Fakultas : Kedokteran
Perguruan Tinggi : Universitas Sumatera Utara Bidang Keahlian : T.H.T.K.L
Waktu Disediakan : 12 Jam / Minggu
II. Komisi Pembimbing
A. Nama : Prof. Dr. dr. Delfitri Munir, Sp.T.H.T.K.L (K)
NIP : 195401261984031001
Pangkat / Golongan : Pembina (IV/a)
Jabatan : Guru Besar
Fakultas : Kedokteran
Perguruan Tinggi : Universitas Sumatera Utara Bidang Keahlian : T.H.T.K.L
Waktu Disediakan : 6 Jam / Minggu
B. Nama : dr. Andrina YM. Rambe, Sp.T.H.T.K.L (K)
NIP : 197106221997032001
Pangkat / Golongan : Penata (III/c)
Jabatan : Lektor Kepala
Fakultas : Kedokteran
Perguruan Tinggi : Universitas Sumatera Utara Bidang Keahlian : T.H.T.K.L
Daftar Riwayat Hidup
Data Pribadi
Nama : dr. Silvia
Tempat / Tanggal lahir : Jakarta / 28 April 1984
Jabatan : PPDS T.H.T.K.L
Agama : Islam
Alamat Rumah : Komplek Tasbih Blok C No. 5 Medan
No. HP : 081396666003
Alamat e-mail : [email protected]
Instansi : Fakultas Kedokteran Universitas Sumatera Utara
Nama Orang Tua : 1. Ayah : Achmad Tasnimi 2. ibu : Alice