KERAGAMAN GEN MIOSTATIN (GDF
-
8) PADA SAPI
MADURA
IQBAL IMANNULLOH
DEPARTEMEN BIOLOGI
FAKULTAS MATEMATIKA DAN ILMU PENGETAHUAN ALAM
INSTITUT PERTANIAN BOGOR
ABSTRAK
IQBAL IMANNULLOH. Keragaman Gen Miostatin (GDF-8) pada Sapi Madura. Dibimbing oleh
ACHMAD FARAJALLAH dan RADEN RORO DYAH PERWITASARI.
Sapi madura merupakan salah satu sapi lokal Indonesia yang memiliki kemampuan
adaptasi terhadap iklim tropis di kepulauan Madura dan memiliki kualitas daging serta kulit yang
baik. Perkembangan dan diferensiasi massa otot rangka dikendalikan oleh gen miostatin atau
growth differentiation factor-8
(GDF-8). Penelitian ini dilakukan untuk mengetahui keragaman
gen miostatin (ekson 2 dan ekson 3) pada sapi madura dan dibandingkan dengan gen miostatin dari
genus
Bos
lainnya pada tingkat runutan nukleotida. Identifikasi varian gen miostatin dilakukan
terhadap 21 sampel DNA sapi madura dan perunutan nukleotida dilakukan terhadap amplikon
menggunakan metode sampel DNA
pooling
. Enam varian yang ditemukan pada ekson 2 yaitu
C1G
(Leu),
C41T
(Ala),
G239A
(Arg),
G266A
(Arg),
A268G
(Thr), dan
A331G
(Met), sedangkan
pada ekson 3 yaitu
G75A
,
G77A
,
T261C
,
C273T
,
A330C
(Ile), dan
T336C
(Thr). Analisis varian
menunjukkan bahwa empat varian pada ekson 3 hanya terdapat pada sapi madura, satu bersifat
missense
yaitu
G77A
(His -- Arg), tiga varian lainnya bersifat
nonsense
yaitu
G75A
(Glu),
T261C
(Ala), dan
C273T
(Cys). Enam varian pada ekson 2 dan dua varian pada ekson 3 memiliki
kesamaan nukleotida basa pada genus
Bos
lainnya, yaitu
C1G
(48%),
C41T
(64%),
G239A
(88%),
G266A
(92%),
A268G
(96%),
A331G
(92%),
A330C
(72,7%), dan
T336C
(36,4%). Varian yang
ditemukan pada sapi madura berbeda dengan varian yang menunjukkan fenomena
double
muscling
.
Kata kunci
: miostatin, ekson 2, ekson 3, varian, DNA
pooling
ABSTRACT
IQBAL IMANNULLOH. Diversity of Myostatin Gene (GDF-8) on Madura Cattle. Supervised by
ACHMAD FARAJALLAH and RADEN RORO DYAH PERWITASARI.
Madura cattle is one of Indonesian local cows that have an ability to adapt the tropical
climate in Madura island and produce good quality meats and skins. Development and
differentiation of muscle mass are controlled by myostatin gene or
growth differentiation factor-8
(GDF-8). This research aimed to estimate the diversity of myostatin gene (exon 2 and exon 3) in
madura cattle and compared it with myostatin gene from other
Bos
genus. The identification of
myostatin gene diversity was performed on 21 DNA samples from madura cattle and nucleotides
sequencing was conducted on the amplicon using DNA
pooling
sample methods. The six variants
of the exon 2 were
C1G
(Leu),
C41T
(Ala),
G239A
(Arg),
G266A
(Arg),
A268G
(Thr), and
A331G
(Met), whereas on exon 3 was
G75A
,
G77A
,
T261C
,
C273T
,
A330C
(Ile), and
T336C
(Thr). The
variance analysis showed that there were four variants of exon 3 that only found in a madura
cattle, one variant has
missense
characteristic, that is
G77A
(His -- Arg), and the three other
variants have
nonsense
characteristic, that are
G75A
(Glu),
T261C
(Ala), and
C273T
(Cys). The
six variants of exon 2 and two variants of exon 3 had a nitrogen base similarity with the other
Bos
genus, that are
C1G
(48%),
C41T
(64%),
G239A
(88%),
G266A
(92%),
A268G
(96%),
A331G
(92%),
A330C
(72,7%), and
T336C
(36,4%). The variants found in madura cattle are different
from variants that showed the
double muscling
phenomena.
KERAGAMAN GEN MIOSTATIN (GDF
-
8) PADA SAPI
MADURA
IQBAL IMANNULLOH
Skripsi
sebagai salah satu syarat untuk memperoleh gelar
Sarjana Sains pada
Departemen Biologi
DEPARTEMEN BIOLOGI
FAKULTAS MATEMATIKA DAN ILMU PENGETAHUAN ALAM
INSTITUT PERTANIAN BOGOR
Judul Skripsi : Keragaman Gen Miostatin (GDF-8) pada Sapi Madura
Nama
: Iqbal Imannulloh
NRP
: G34070079
Menyetujui:
Pembimbing I
Pembimbing II
Dr. Ir. Achmad Farajallah, M. Si
Dr. Ir. R. R. Dyah Perwitasari, M. Sc.
NIP. 19650427 199002 1 002
NIP. 19660403 199003 2 001
Mengetahui:
Ketua Departemen Biologi
Fakultas Matematika dan Ilmu Pengetahuan Alam
Institut Pertanian Bogor
Dr. Ir. Ence Darmo Jaya Supena
NIP. 19641002 198903 1 002
PRAKATA
Alhamdulillahirobbil’alamin
Segala puji dan syukur Penulis ucapkan bagi Allah yang telah melimpahkan
nikmat, karunia, anugrah, dan rahmat-Nya sehingga karya ilmiah yang berjudul
Keragaman Gen Miostatin (GDF-8) pada Sapi Madura dapat terselesaikan sebagai salah
satu syarat untuk memperoleh gelar Sarjana Sains di Departemen Biologi, Fakultas
Matematika dan Ilmu Pengetahuan Alam, Institut Pertanian Bogor.
Penulis mengucapkan terima kasih yang sebesar-basarnya kepada Bapak Dr. Ir.
Achmad Farajallah, M.Si dan Ibu Dr. Ir. R. R. Dyah Perwitasari, M.Sc selaku
pembimbing yang telah memberikan ilmu, pengarahan, dan bimbingannya sehingga
penelitian ini dapat terselesaikan. Serta kepada Dr. Ir. Iman Rusmana, M.Si selaku dosen
penguji yang turut memberikan kritik dan sarannya dalam laporan ini. Ucapan terima
kasih juga disampaikan kepada Kepala Bidang Pengembangan dan Usaha Peternakan,
Dinas Kelautan, Perikanan dan Peternakan Kab. Sampang Ir. Sri Wahyuni Yulianti yang
telah membantu dalam hal pengambilan sampel darah sapi madura serta kepada keluarga
tercinta, bapak, ibu, kakak, adik, dan feni shintarika atas segala doa yang tiada henti,
kasih sayang, dan dukungannya. Tidak lupa penulis ucapkan terima kasih kepada semua
keluarga besar zoologi (Mba Tini, Mba Ani, Pak Adi, Mba Kanthi, Mba Tetri, Kak Jazi,
Kak Uche, Mas Wildan, Pak Rizal, Mba Dea, I Made K, Raisa AS, Rindi, Bisri, Cahyo,
Chyntia, Nishe, Renny, dan Noe) yang telah berbagi ilmu dan segala dukungannya,
kepada sahabat seperjuangan (Remarchtito Ilkom44, Feri Bio44 dan Andra AGH44) atas
segala bantuan, nasehat, dan semangat yang selalu diberikan dalam penelitian ini, dan
kepada teman-teman Biologi angkatan 44, 45, dan 46 yang telah memberikan motivasi
kepada penulis.
Semoga karya ilmiah ini dapat bermanfaat dan menambah khasanah ilmu
pengetahuan kita semua. Saran dan kritik yang membangun sangat penulis harapkan agar
tulisan ini menjadi lebih baik.
Bogor, Januari 2012
RIWAYAT HIDUP
Penulis dilahirkan di Jakarta pada tanggal 31 Oktober 1988 dari Ayah Riyanto
dan Ibu Sumarni. Penulis merupakan anak kedua dari empat bersaudara.
Tahun 2007 penulis lulus dari SMA Negeri 51 Jakarta dan melanjutkan
pendidikan di Institut Petanian Bogor, Fakultas Matematika dan Ilmu Pengetahuan Alam,
Departemen Biologi melalui jalur penerimaan Undangan Seleksi Masuk IPB (USMI).
DAFTAR ISI
Halaman
DAFTAR TABEL ...ix
DAFTAR GAMBAR ...ix
DAFTAR LAMPIRAN ...ix
PENDAHULUAN
Latar Belakang... 1
Tujuan... 1
BAHAN DAN METODE
Lokasi dan Waktu ... 1
Sampel DNA... 2
Amplifikasi gen Miostatin ... 2
Elektroforesis dan Visualisasi DNA ... 2
Perunutan Nukleotida gen Miostatin ... 2
Analisis Runutan DNA ... 2
HASIL
Amplifikasi dan Visualisasi Fragmen DNA ... 2
Runutan gen Miostatin... 3
Analisis Varian Nukleotida... 4
PEMBAHASAN ... 4
SIMPULAN ... 6
SARAN ... 6
DAFTAR PUSTAKA ... 6
DAFTAR TABEL
Halaman
1 Resume hasil pensejajaran nukleotida ekson 2 dan ekson 3 yang berbeda terhadap beberapa ruas
nukleotida gen miostatin genus
Bos
...3
DAFTAR GAMBAR
Halaman
1 Hasil amplifikasi ekson 2 (A) dan ekson 3 (B) gen miostatin dalam PAGE 6% dengan
pewarnaan sensitif perak...3
2 Varian ekson 3 yang hanya terjadi pada sapi madura, (A) varian G75A dan G77A; (B) varian
T261C; dan (C) varian C273T...3
DAFTAR LAMPIRAN
Halaman
1 Posisi masing-masing pasangan primer pada peta gen miostatin (GDF8) genus
Bos
...9
2 Informasi runutan gen miostatin (GDF8) pada
Bos indicus
...9
3 Beberapa spesies pembanding yang digunakan dalam proses pensejajaran gen miostatin (GDF8)
ekson 2 dan ekson 3 ...11
PENDAHULUAN
Latar Belakang
Sapi merupakan salah satu hewan ternak
dari famili Bovidae. Sapi yang berkembang
saat ini berasal dari domestikasi
Bos
primigenius
.
Domestikasi
tersebut
menghasilkan dua jenis sapi, yaitu sapi tanpa
punuk (punggung bagian depan datar,
B.
taurus
) dan sapi berpunuk (punggung bagian
depan melengkung ke atas,
B. indicus
).
Persebaran
B. taurus
sebagian besar berada di
wilayah Eropa dan Afrika Barat sedangkan
B.
indicus
sebagian besar tersebar di wilayah
Asia bagian selatan dan Afrika.
Jenis sapi lain yang memiliki sejarah
berbeda dari keduanya adalah
B. javanicus
,
yang dikenal sebagai banteng.
Banteng
mengalami domestikasi langsung menjadi sapi
bali (Nijman
et al.
2003). Selain sapi bali, di
Indonesia bisa ditemukan beberapa sapi lokal
yang lain, misalnya sapi madura dan sapi
aceh. Uggla (2008) dan Mohamad
et al.
(2009) melaporkan bahwa sapi aceh berasal
dari keturunan
B. indicus
, sedangkan sapi
madura merupakan hasil persilangan banteng
dan sapi berpunuk atau
B. indicus
. Firdhausi
(2010) menggunakan asal sampel yang lebih
terkontrol dengan cakupan asal sampel sekitar
setengah luasan madura, berdasarkan DNA
mitokondria melaporkan bahwa sapi madura
terbagi menjadi dua tipe, yaitu tipe I berasal
dari keturunan induk betina banteng dan tipe
II berasal dari keturunan induk betina sapi
berpunuk.
Dilihat dari morfologinya, sapi madura
memiliki kesamaan dengan sapi bali, yaitu
kulit berwarna kecoklatan dengan motif putih
pada bagian pantat dan kaki. Adaptasi yang
lama di daerah tropis kepulauan Madura
menyebabkan sapi madura memiliki beberapa
sifat unggul, yaitu tahan terhadap kondisi
panas, mampu hidup baik dalam kondisi
makanan terbatas, resisten terhadap parasit
serta memiliki kualitas daging dan kulit yang
baik (Payne dan Hodges 1997).
Miostatin
atau
growth differentiation
factor-8
(GDF-8)
adalah
protein
yang
mengatur pertumbuhan otot rangka sebelum
dan setelah kelahiran.
Protein tersebut
merupakan salah satu anggota superfamili
transforming growth factor-
β
(TGf-
β) yang
mengontrol secara negatif pertumbuhan massa
otot, yaitu dengan cara menghambat aktifitas
miogenin. Inaktifasi miogenin mengakibatkan
mioblas tidak dapat berdiferensiasi menjadi
miotube yang akan berkembang menjadi serat
otot rangka (Thomas
et al.
2000).
Miostatin disandikan oleh gen miostatin.
Pada sapi, gen miostatin terletak di kromosom
nomor 2. Gen tersebut terdiri atas satu
promotor, tiga ekson dan dua intron.
Fenomena
double muscling
atau
muscular
hypertrophy
yang terjadi pada sapi belgian
blue dan piedmontese merupakan efek yang
ditimbulkan dari mutasi gen miostatin
(Oldham
et al.
2001). Mutasi gen miostatin
yang terjadi pada sapi belgian blue adalah
mutasi delesi 11 pb pada ekson 3 (McPherron
dan Lee 1997), sedangkan mutasi yang terjadi
pada
sapi
piedmontese
adalah
mutasi
substitusi transisi basa guanin (G) menjadi
basa adenin (A) pada ekson 3 yang mengubah
asam amino sistein (Cys) menjadi tirosin
(Tyr) (Kambadur
et al.
1997). Beberapa
varian gen miostatin juga dilaporkan bisa
mengganggu aktifitas miogenin sehingga
jumlah serat otot rangka bertambah banyak
(hiperplasia) dan/atau ukurannya bertambah
besar (hipertropi).
Pertumbuhan otot rangka yang cepat pada
sapi yang mengalami hiperplasia dan/atau
hipertropi menyebabkan varian gen miostatin
mempunyai prospek ekonomi yang sangat
besar. Oleh karena itu, pencarian varian gen
miostatin pada berbagai jenis ternak, hewan
peliharaan
dan
hewan-hewan
lainnya
termasuk manusia banyak dilakukan (domba,
Johnson
et al.
2005; anjing, Mosher
et al.
2007; ikan, Ostbye
et al.
2001; dan manusia,
Schuelke
et al.
2004). Beberapa mutan gen
miostatin juga dilaporkan mempengaruhi laju
pertumbuhan otot rangka pada kerbau Nellore
(Grisolia
et al.
2009) dan sapi Charolaise
(Dunner
et al.
2002).
Tujuan
Penelitian ini bertujuan untuk mengetahui
keragamangen miostatin (ekson 2 dan ekson
3) pada sapi madura yang dibandingkan
dengan beberapa anggota genus
Bos
lainnya.
BAHAN DAN METODE
Lokasi dan Waktu
Sampel DNA
Sampel DNA yang digunakan merupakan
ekstrak
DNA
sapi
madura
koleksi
Laboratorium Bagian Fungsi Hayati dan
Perilaku Hewan Departemen Biologi IPB.
Sampel yang digunakan berjumlah 21 sampel
terdiri atas sapi jantan (13 sampel) maupun
sapi betina (8 sampel).
Amplifikasi gen Miostatin
Amplifikasi ruas gen miostatin dilakukan
secara
in vitro
menggunakan mesin ESCO
Swift Maxi Thermal Cycler
. Amplifikasi ruas
ekson 2 gen miostatin menggunakan primer
forward
AF80 (5’-GCTGTTATGAATGAAA
TGCTAC) dan primer
reverse
AF81 (5’TTTT
ATTGGGTACAGGGCTAC).
Pasangan
primer
tersebut
mengapit
mulai
dari
nukleotida 2188 hingga nukleotida 2870 (
B.
taurus
, No. akses AB076403), dengan ukuran
amplikon sekitar 683 pb. Posisi penempelan
primer tersebut berada pada bagian akhir
intron 1 dan bagian awal intron 2. Sedangkan
amplifikasi ekson 3 menggunakan primer
forward
Luci 5 (5’-ATGTGACATAAGCAA
AATGATTAG) dan
reverse
Luci 6 (5’-CTTG
TGCTTAAGTGACTGTAG) yang mengapit
mulai dari nukleotida 4681 hingga nukleotida
5175 (
B. indicus
, No. akses AY794986),
dengan panjang amplikon sekitar 614 pb.
Pasangan primer tersebut menempel pada
bagian akhir intron 2 dan bagian awal
terminator gen miostatin (Lampiran 1).
Pereaksi
PCR dengan volume 25 μl
terdiri atas sampel DNA 2,5 μl (10
-100 ng),
DW steril 8 μl, masing
-masing primer
(
forward reverse
) 1 μl, dan
Kappa Taq
Readymix
12,5 μl.
Reaksi amplifikasi PCR
dilakukan dengan kondisi untuk kedua ruas
ekson gen miostatin adalah tahap
denaturasi
awal pada suhu 94
0C selama dua menit 30
detik; tahap kedua terdiri dari 30 siklus yang
masing-masing siklus terdiri dari
denaturasi
pada suhu 94
0C selama 30 detik, penempelan
primer (
annealing
) pada suhu 55
0-56
0C
selama 45 detik dan pemanjangan nukleotida
(
elongasi
) 72
0C selama satu menit; tahap
terakhir yaitu pemanjangan nukleotida akhir
(
post-elongasi
) selama dua menit 30 detik.
Elektroforesis dan Visualisasi DNA
Elektroforesis amplikon gen miostatin
dilakukan dengan metode
Polyacrilamide gel
Electrophoresis
(PAGE) 6% dalam bufer 1x
TBE (10 mM Tris-HCl, 1 M asam borat, dan
EDTA 0,1 mM) yang dijalankan pada
tegangan 250 volt
selama 30
menit.
Visualisasi pita DNA setelah elektroforesis
dilakukan dengan pewarnaan sensitif perak
(Byun
et al.
2009).
PerunutanNukleotida gen Miostatin
Perunutan nukleotida dilakukan terhadap
amplikon ekson 2 dan ekson 3
yang
menunjukkan pita tunggal dan berpita tebal di
atas gel akrilamid. Untuk itu, amplikon
dimurnikan kemudian amplikon disatukan
(DNA
pooling
) dan dijadikan cetakan dalam
proses perunutan menggunakan primer yang
sama dengan
amplifikasi awal. Proses
perunutan
(PCR
dan
elektroforesis)
menggunakan metode
sequencing big dye
terminator
yang dilakukan oleh Lembaga
Komersial jasa
sequencing
.
Analisis Runutan DNA
Hasil perunutan dari arah
forward
dan
reverse
digabung menjadi satu ruas DNA
kemudian diedit berdasarkan kromatogram
yang dihasilkan oleh mesin elektroforesis
sequencing
menggunakan program BioEdit
versi 6.0.7. Pengeditan runutan lebih lanjut
dilakukan
secara
manual
berdasarkan
penyandiannya menjadi polipeptida. Setelah
diedit, runutan nukleotida saling disejajarkan
dengan melibatkan beberapa runutan dari
genus
Bos
lainnya (Lampiran 3) menggunakan
ClustralW yang tertanam dalam MEGA versi
4.0.2
(
Moleculer
Evolutionary
Genetics
Analysis
).
HASIL
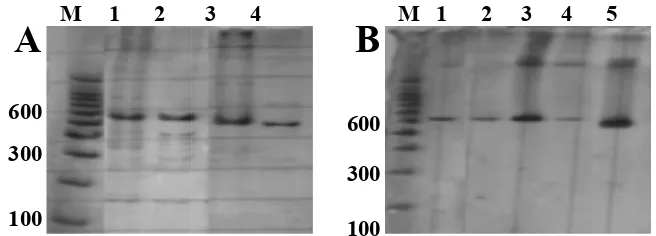
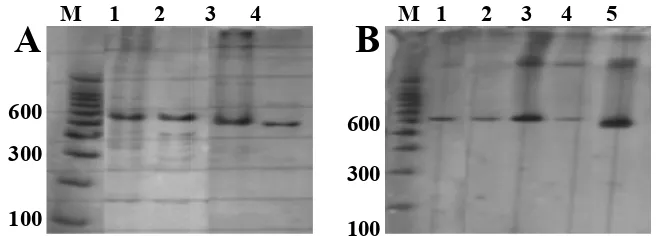
M 1 2
Gambar 1Hasil amplifikasi ekson
pewarnaan sensitif
madura.
Tabel 1. Resume hasil pense
beberapa ruas nukleotida
[image:11.612.145.473.80.198.2]Keterangan: Nomor posisi nukleotida
cetak tebal menunjukkan substitu
Gambar 2 Varian ekson 3 yan
varian T261C; dan
Runutan gen Miostatin
Runutan amplikon dari ara
reverse
yang digabung menjadi
DNA untuk ekson 2 dan ekson 3 berturut
yaitu sepanjang 683 nt
Pensejajaran dengan beberapa
miostatin genus
Bos
pemban
3)
menunjukkan
bahwa
sebenarnya untuk ekson 2 (La
ekson 3 (Lampiran 5) berturut
Spesies (No. Akses) /
Sampel
Sapi Madura
Bos taurus
(AF320998)
Bos taurus
(AB076403)
Bos indicus
(FJ752678)
Bos indicus
(EF438819)
Bos frontalis
(FJ752684)
Bos frontalis
(FJ752685)
Bos grunnies
(JN642607)
Bos grunnies
(EU372977)
600
300
100
A
A
M 1 2 3 4
M 1 2 3 4 5
plifikasi ekson 2 (A) dan ekson 3 (B) gen miostatin dalam PAGE
sensitif perak. Keterangan: M= marker 100 pb; 1, 2, 3, 4, 5= sampel
hasil pensejajaran nukleotida ekson 2 dan ekson 3 yang berbeda
uas nukleotida gen miostatin genus
Bos
.
posisi nukleotida dibaca secara vertikal di tiga baris pertama. Bagian
substitusi transversi.
ekson 3 yang hanya terjadi pada sapi madura, (A) varian G75A dan
C; dan (C) varian C273T.
dari arah
forward
dan
g menjadi satu ruas
n ekson 3 berturut-turut
683 nt dan 614 nt.
beberapa runutan gen
pembanding (Lampiran
bahwa
panjang
yang
on 2 (Lampiran 4) dan
berturut-turut yaitu 374
nt (124 asam amino) dan 381 nt
amino). Berdasarkan hasil pensejajaran
ruas ekson tersebut menunjukka
ekson 2 dan ekson 3 memiliki nukleoti
relatif stabil sebesar 98,4% dan
masing-masing enam varian terdiri
substitusi transversi dan lima
transisi, dengan posisi berbeda dari
varian (Tabel 1).
Ekson 2
Ekson 3
2
2
2
3
2
2
4
3
6
6
3
7
7
6
7
1
1
9
6
8
1
5
7
1
3
C
C G G A A
G G T C
C
T G G A A
A A C
T
C
C G G G A
A A C
T
G
C G G A A
A A C
T
G
C G G A A
A A C
T
(FJ752684)
G
C A A A A
A A C
T
(FJ752685)
G
T A G A A
A A C
T
(JN642607)
C
C G G A A
A A C
T
(EU372977)
G
C A A A G
A A C
T
300
100
600
C
B
B
PAGE 6% dengan
4, 5= sampel sapi
berbeda terhadap
pertama. Bagian yang di
G75A dan G77A; (B)
381 nt (127 asam
pensejajaran kedua
ukkan bahwa
memiliki nukleotida yang
dan ditemukan
varian terdiri atas satu
lima substitusi
dari tiap-tiap
2
3
3
7
3
3
3
0
6
C
A
T
T
A
C
T
A
C
T
C
T
T
A
C
T
A
T
T
A
C
T
A
C
[image:11.612.139.500.274.426.2] [image:11.612.124.504.462.583.2]Analisis Varian Nukleotida
Pada ekson 2, satu dari enam titik varian
termasuk substitusi transversi. Varian tersebut
yaitu
C1G
yang menyandikan asam amino
leusin. Lima titik varian lainnya termasuk
substitusi transisi yaitu
C41T
(Ala),
G239A
(Arg),
G266A
(Arg),
A268G
(Thr), dan
A331G
(Met). Pada ekson 3, satu titik varian
termasuk substitusi tranversi
A330C
(Ile),
sedangkan lima varian lainnya yaitu
G75A
,
G77A
,
T261C
,
C273T
, dan
T336C
(Tyr)
termasuk substitusi transisi.
Analisis lebih lanjut terhadap varian
tersebut menunjukkan bahwa empat dari 12
total varian merupakan varian yang hanya
terjadi pada sapi madura. Varian tersebut yaitu
G75A
,
G77A
,
T261C
, dan
C273T
. Varian
G75A
merupakan varian yang terjadi pada
posisi nukleotida 75 basa G terhadap basa A
(Gambar 2A). Varian tersebut bersifat
nonsense
karena tetap sebagai asam glutamat.
Varian
G77A
terjadi pada posisi nukleotida 77
basa G terhadap basa A (Gambar 2A). Varian
ini bersifat
missense
karena menyebabkan
perubahan histidin menjadi arginin. Lebih
lanjut, varian
T261C
terjadi pada posisi
nukleotida 261 basa T terhadap basa C
(Gambar 2B). Varian ini tetap menyandikan
asam amino alanin. Kemudian varian
C273T
terjadi pada posisi nukleotida 273 basa C
terhadap basa T yang tetap menyandikan
sistein (Gambar 2C).
Delapan varian lainnya merupakan varian
yang memiliki kesamaan basa nukleotida
terhadap beberapa genus
Bos
pembanding.
Varian
C1G
pada ekson 2 memiliki kesamaan
nukleotida basa C sebesar 48% terhadap
genus
Bos
pembanding, varian
C41T
memiliki
kesamaan nukleotida basa C sebesar 64%,
varian
G239A
memiliki kesamaan nukleotida
basa G sebesar 88%, varian
G266A
memiliki
kesamaan nukleotida basa G sebesar 92%,
varian
A268G
memiliki kesamaan nukleotida
basa A sebesar 96%, dan varian
A331G
memiliki kesamaan nukleotida basa A sebesar
92%. Sedangkan dua varian yang terdapat
pada ekson 3 yaitu varian
A330C
memiliki
kesamaan nukleotida basa A sebesar 72,7%
dan
varian
T336C
memiliki kesamaan
nukleotida basa T sebesar 36,4%. Kesamaan
nukleotida basa tersebut sebagian besar terjadi
pada
Bos taurus
dan
Bos indicus
pembanding.
PEMBAHASAN
Amplifikasi dan visualisasi untuk ekson 2
menghasilkan pita tunggal yang tebal dan
beberapa pita tambahan yang samar-samar
(Gambar
1A).
Pita
tambahan
tersebut
merupakan pengotor yang terdeteksi dalam
gel poliakrilamid setelah pewarnaan perak dan
tidak sampai mengganggu runutan amplikon.
Hal ini didukung dengan puncak kromatogram
yang jelas dengan jarak/spasi antar puncak
yang sebagian besar sama (Gambar 2).
Pewarnaan sensitif perak yang digunakan
untuk mendeteksi pita-pita DNA dalam gel
poliakrilamid sangat sesuai dengan volume
dan konsentrasi sampel yang sangat kecil
yaitu 2 μl
[10 ng] (Avise 1994). Hal tersebut
dikarenakan
pewarnaan
sensitif
perak
merupakan metode dengan sensitifitas yang
sangat tinggi dan cepat dalam mendeteksi
pita-pita DNA yang sangat kecil dengan
konsentrasi berkisar 10 ng (Byun
et al.
2009).
Hasil runutan dua amplikon dari arah
forward
dan
reverse
dengan hasil pensejajaran
ruas gen miostatin ekson 2 dan ekson 3
menunjukkan adanya perbedaan panjang
nukleotida. Perbedaan yang terdapat pada
ekson 2 berasal dari bagian akhir intron 1
sepanjang 158 nt dan bagian awal intron 2
sepanjang 127 nt (Lampiran 1). Sedangkan
pada ekson 3, perbedaan berasal dari bagian
akhir intron 2 sepanjang 108 nt dan bagian
awal terminator sepanjang 125 nt (Lampiran
1). Pada bagian intron-intron tersebut tidak
dilakukan analisis lebih lanjut karena ruas
intron
tidak
berperan
dalam
proses
penyandian asam amino (translasi) dalam hal
ini ekspresi dari gen miostatin.
Analisis
runutan
gen
miostatin
menunjukkan bahwa ekson 2 dan ekson 3
masing-masing menghasilkan enam varian
berturut-turut yaitu
C1G
,
C41T
,
G239A
,
G266A
,
A268G
,
A331G,G75A
,
G77A
,
T261C
,
C273T
,
A330C
dan
T336C
. Varian tersebut
ditunjukkan oleh adanya dua puncak pada
kromatogram yang saling tumpang tindih.
Puncak kromatogram pada varian ekson 3,
bukanlah sebagai
pengotor namun lebih
mengarah kepada varian (Gambar 2). Namun
lain halnya dengan beberapa puncak yang
terdapat pada ekson 2 selain enam puncak
yang
menunjukkan
varian
ekson
2.
Banyaknya puncak
pada latar belakang
kromatogram (tidak dilampirkan) diakibatkan
pengotor yang terbawa
saat amplifikasi
sampel. Hal ini mengakibatkan runutan ekson
2 diverifikasi lebih lanjut terhadap runutan
amplikon dari arah primer
forward
dan
reverse
untuk memastikan keakuratan runutan
tersebut.
diharapkan, karena menunjukkan adanya
varian pada ekson 2 dan ekson 3.
Puncak-puncak
tersebut
merupakan
hasil
dari
pembacaan mesin perunutan PCR dan
elektroforesis terhadap sampel yang dijadikan
dalam satu tabung (DNA
pooling
) yang sesuai
dengan masing-masing ekson. Teknik DNA
pooling
yang digunakan dalam penelitian ini
merupakan teknik yang dapat mendeteksi
varian pada suatu lokus namun varian tersebut
tidak dapat diketahui terjadi pada sampel yang
mana. Ini karena sampel-sampel tersebut
dijadikan dalam satu tabung (
pooling
)
sehingga teknik ini sangat hemat sebagai
penanda molekuler dan proses
screening
pada
sampel dapat terjadi secara cepat dan banyak
sampel. Secara umum, teknik DNA
pooling
untuk perunutan merupakan teknik dalam
mendeteksi
delesi, insersi dan substitusi
nukleotida (dikenal sebagai
Single Nucleotide
Polymorphisms
- SNPs).
Hasil perunutan amplikon ekson 2
(Lampiran 4) dan ekson 3 (Lampiran 5)
menunjukkan bahwa tidak ditemukan adanya
varian
yang
menyebabkan
terjadinya
pertambahan massa dan jumlah serat otot
rangka
(dikenal
double
muscling
atau
muscular hypertrophy
). McPherron dan Lee
(1997) melaporkan adanya delesi 11 pb pada
ekson 3 diantara nukleotida 821-831 dikenal
dengan
nt821(del11)
, mengakibatkan stop
kodon menjadi tidak dikenali sehingga protein
miostatin
tidak
dapat
diekspresikan.
Sedangkan Grobet
et al.
(1998) melaporkan
beberapa varian yang menyebabkan
double
muscling
terjadi pada ekson 2 yaitu delesi
tujuh pb dan digantikan dengan insersi 10 pb
pada posisi nukleotida ke-419 dikenal sebagai
nt419(del7-ins10)
, transisi basa C menjadi
basa T pada posisi nukleotida ke-610
(
Q204X
), dan transversi basa G menjadi basa
T pada posisi nukleotida ke-676 (E226X);
serta substitusi transisi basa G menjadi basa A
pada posisi nukleotida ke-938 (C313Y)
menyebabkan asam amino sistein (Cys)
berubah menjadi treonin (Thr). Varian yang
tidak menyebabkan
double muscling
juga
telah dilaporkan oleh Dunner
et al.
(2002)
pada ekson 2 yaitu substitusi transisi basa G
menjadi basa A pada posisi nukleotida ke-544
(
D182
) yang mengakibatkan perubahan asam
aspartat (Asp) menjadi asparagin (Asn) dan
substitusi transisi basa G menjadi basa A pada
posisi nukleotida ke-387 dikenal dengan
nt387(G-A)
.
Regulasi miostatin secara umum diawali
dengan pembentukan dan ekspresi sebagai
premiostatin yang belum aktif. Miostatin
menjadi aktif pada saat pasca-translasi dan
kemudian
berikatan
dengan
follistatin.
Kompleks miostatin dan follistatin ini akan
membentuk situs aktif jika berikatan dengan
activin reseptor IIB di jaringan otot. Reseptor
tersebut akan memberikan sinyal kerja ke
protein yang mengatur pengendalian otot
(miogenin), sehingga perkembangan jaringan
otot menjadi normal. Mutasi pada gen
miostatin menyebabkan perubahan jumlah
(hiperplasia) dan/atau ukuran serat otot
(hipertropi) maupun perubahan ikatan situs
aktif
dengan
activin
IIB
sehingga
menyebabkan fenomena
double muscling
(McNally 2004).
Pada penelitian ini, amplifikasi dan
perunutan gen miostatin menunjukkan bahwa
empat varian pada ekson 3 hanya terdapat
pada sapi madura, yaitu
G75A
,
G77A
,
T261C
,
dan
C273T
(Tabel 1). Meskipun varian
tersebut
berbeda
berdasarkan
basa
nukleotidanya, telaah lebih lanjut berdasarkan
asam amino yang disandikan ternyata tiga
varian, yaitu
G75A
,
T261C
, dan
C273T
memiliki asam amino yang sama dengan
genus
Bos
pembanding berturut-turut yaitu
asam glutamat (Glu), alanin (Ala), dan sistein
(Cys). Sedangkan pada varian
G77A
memiliki
perbedaan
asam
amino
karena
terjadi
perubahan dari histidin (His) menjadi arginin
(Arg). Arginin (Arg) dan histidin (His)
merupakan asam amino yang bersifat basa dan
mempunyai
gugus
amino
pada
rantai
sampingnya yang bermuatan positif serta
bersifat hidofilik. Adanya kesamaan asam
amino pada tiga varian ekson 3dikarenakan
posisi nukleotida basa pada tiga varian
tersebut terjadi pada basa ketiga (Lampiran 5)
sehingga asam amino yang disandikannya
tetap. Sedangkan posisi nukleotida basa pada
varian
G77A
terjadi pada basa kedua sehingga
terjadi
perbedaan
asam
amino
yang
disandikan. Asam amino yang berubah tidak
hanya terjadi pada perubahan nukleotida basa
di posisi kedua setiap kodonnya namun juga
dapat terjadi pada basa kesatu seperti pada
varian
C1G
,
A268G
dan
A330C
(Lampiran 4).
Dua varian lainnya (
G239A
dan
G266A
)
menyandikan asam amino arginin (Arg)
sedangkan
genus
Bos
pembandingnya
menyandikan lisin (Lys). Kedua asam amino
tersebut termasuk asam amino yang bersifat
basa, gugus amino pada rantai sampingnya
bermuatan positif dan bersifat hidrofilik.
Kesamaan nukleotida basa dan sifat asam
amino yang disandikannya terhadap beberapa
genus
Bos
pembanding sebagian besar terjadi
pada
Bos taurus
dan
Bos indicus
.
SIMPULAN
Perunutan (PCR dan elektroforesis)gen
miostatin pada sapi madura dengan teknik
sampel DNA
pooling
menunjukkan bahwa
ekson 2 dan ekson 3 masing-masing memiliki
enam varian. Empat varian pada ekson 3
(
G75A
,
G77A
,
T261C
, dan
C273T
) hanya
ditemukan pada sapi madura. Asam amino
pada varian
G77A
mengalami perubahan dari
histidin (His) menjadi arginin (Arg). Varian
yang ditemukan berbeda dengan varian yang
menyebabkan fenomena
double muscling
.
SARAN
Varian
G77A
pada ekson 3 gen miostatin
dapat digunakan sebagai penanda genetik
terhadap pertumbuhan rata-rata massa otot
rangka dan kualitas karkas.
DAFTAR PUSTAKA
Avise JC. 1994.
Molecular Markers, Natural
History and Evolution
. New York:
Chapman & Hall.
Byun SO, Fang Q, Zhou H, Hickford JGH.
2009. An effective method for
silver-staining DNA in large numbers of
polyacrylamide
gels.
Analytical
Biochemistry
385: 174 – 175.
Dunner S, Miranda ME, Amigues Y, Caon J,
Georges M, Hanset R, Williams J,
Menissier
F.
2002.
Haplotype
diversity of the myostatin
gene
among beef cattle breeds.
Genetics
Selection Evolution
35: 103 – 108.
Firdhausi NF. 2010. Asal Usul Sapi Madura
Berdasarkan
Penanda
DNA
Mitokondria. [Tesis] Bogor: Fakultas
Pascasarjana,
Institut
Pertanian
Bogor.
Grisolia AB, D’Angelo GT, Porto Neto LR,
Siqueira
F,
Garcia
JF.
2009.
Myostatin (GDF8) single nucleotide
polymorphisms in Nellore cattle.
Genetic and Molecular Research
8:
822 – 830.
Grobet L, Poncelet D, Royo LJ, Brouwers B,
Pirottin D, Michaux C, Ménissier F,
Zanotti M, Dunner S, Georges M.
1998. Molecular definition of an
allelic series of mutations disrupting
the myostatin function and causing
double
muscling
in
cattle.
Mammalian Genome
9: 210 – 213.
Johnson PL, McEwan JC, Dodds KG, Purchas
RW, Blair HT. 2005. A directed
search in the region of GDF8 for
quantitative
trait
loci
affecting
carcass traits in Texel sheep.
Journal
of Animal Science
83: 1988 – 2000.
Kambadur R, Sharma M, Smith TPL, Bass JJ.
1997.
Mutations
in
myostatin
(GDF8) in Double-Muscled Belgian
Blue
and
Piedmontese
Cattle.
Genome Research.
7: 910 – 915.
McNally
EM.
2004.
Powerful
genes-myostatin
regulation
of
human
muscle mass.
The New England
Journal of Medicine
350: 2642 –
2644.
McPherron AC, Lee SJ. 1997. Double
muscling in cattle due to mutations in
the myostatin gene.
Proceedings of
the National Academy of Sciences
.
USA 94: 12457 – 12461.
Mosher DS, Quignon P, Bustamante CD,
Sutter NB, Mellersh CS,Parker HG,
Ostrander EA. 2007. A mutation in
the myostatin gene increases muscle
mass
and
enhances
racing
performance in heterozygote dogs.
PLoS Genetics
3: 0779 – 0786.
Mohamad K, Olsson M, Tol HTA van, Mikko
S, Vlamings BH, Andersson G,
Martinez HR, Purwantara B, Paling
RW, Colenbrander B, Lenstra JA.
2009. On the origin of Indonesian
cattle.
PLoS ONE
4:1 – 5.
Oldham JM, Martyn JAK, Sharma M,
Jeanplong F, Kambadur R, Bass JJ.
2001.
Moleculer
expression
of
myostatin and MyoD is greater in
double-muscled
than
normal-muscled cattle fetuses.
American
Journalof Physiology - Regulatory,
Integrative
and
Comparative
Physiology
280: R1488 – R1493.
Ostbye TK,
Galloway TF, Nielsen C,
Gabestad I, Bardal T, Andersen O.
2001. The two myostatin genes of
Atlantic salmon (salmo salar) are
expressed in a variety of tissues.
European Journal of Biochemistry
268: 5249 – 5257.
Payne WJA, Hodges J. 1997.
Tropical Cattle:
Origins,
Breed,
and
Breeding
Policies
. Oxford: Blackwell Science
Ltd.
Schuelke M, Wagner KR, Stolz LE, Hübner
C, Riebel T, Kömen W, Braun T,
Tobin JF, Lee SJ. 2004. Myostatin
mutation
associated
with
gross
muscle hypertrophy in a child.
The
New England Journal of Medicine
350: 2682 – 2688.
Thomas M, Langley B, Berry C, Sharma M,
Kirk S, Bass J, Kambadur R. 2000.
Myostatin, a negative regulator of
muscle
growth,
function
by
inhibiting
myoblast
proliferation.
Journal Biochemistry
275: 40235 –
40243.
Lampiran 1. Posisi masing-masing pasangan primer pada peta gen miostatin (GDF8) genus Bos.
Pasangan primer
forward
AF80 dan
reverse
AF81 terhadap
Bos taurus
(No. akses
AB076403). Sedangkan pasangan primer
forward
Luci 5 dan
reverse
Luci 6 terhadap
Bos indicus
(No. akses AY794986)
Lampiran 2. Informasi runutan gen miostatin (GDF8) pada
Bos indicus
LOCUS AY794986 6686 bp DNA linear MAM 24-JAN-2007 DEFINITION Bos indicus myostatin gene, complete cds.
ACCESSION AY794986
VERSION AY794986.1 GI:55740411 KEYWORDS .
SOURCE Bos indicus (Bos taurus indicus) ORGANISM Bos indicus
Eukaryota; Metazoa; Chordata; Craniata; Vertebrata; Euteleostomi; Mammalia; Eutheria; Laurasiatheria; Cetartiodactyla; Ruminantia; Pecora; Bovidae; Bovinae; Bos.
REFERENCE 1 (bases 1 to 6686)
AUTHORS Tantia,M.S., Vijh,R.K., Kumar,S.T., Mishra,B. and Reecy,J.M. TITLE Comparative analysis of GDF 8 (myostatin) in Bos indicus and Bos taurus
JOURNAL DNA Seq. 17 (4), 311-313 (2006) PUBMED 17312952
REFERENCE 2 (bases 1 to 6686)
AUTHORS Tantia,M.S., Mishra,B., Bharani Kumar,S.T. and Vijh,R.K. TITLE Direct Submission
JOURNAL Submitted (26-OCT-2004) NATP, NBAGR, P B No. 129, Karnal, Haryana 132001, India
FEATURES Location/Qualifiers source 1..6686
/organism="Bos indicus" /mol_type="genomic DNA" /db_xref="taxon:9915"
mRNA join(<134..506,2371..2744,4778..>5158) /product="myostatin"
CDS join(134..506,2371..2744,4778..5158)
/note="similar to the product of GenBank Accession Number AB076403"
/codon_start=1 /product="myostatin" /protein_id="AAV63982.1" /db_xref="GI:55740412"
/translation="MQKLQISVYIYLFMLIVAGPVDLNENSEQKENVEKEGLCNACLW RENTTSSRLEAIKIQILSKLRLETAPNISKDAIRQLLPKAPPLLELIDQFDVQRDASS DGSLEDDDYHARTETVITMPTESDLLTQVEGKPKCCFFKFSSKIQYNKLVKAQLWIYL RPVKTPATVFVQILRLIKPMKDGTRYTGIRSLKLDMNPGTGIWQSIDVKTVLQNWLKQ PESNLGIEIKALDENGHDLAVTFPEPGEDGLTPFLEVKVTDTPKRSRRDFGLDCDEHS TESRCCRYPLTVDFEAFGWDWIIAPKRYKANYCSGECEFVFLQKYPHTHLVHQANPRG SAGPCCTPTKMSPINMLYFNGEGQIIYGKIPAMVVDRCGCS"
ORIGIN
1 agattcactg gtgtggcaag ttgtctctca gactgggcag gcattaacgt ttggcttggc 61 gttactcaaa agcaaaagaa aagtaaaagg aagaagtaag aacaagggaa aagattgtat 121 tgattttaaa accatgcaaa aactgcaaat ctctgtttat atttacctat ttatgctgat 181 tgttgctggc ccagtggatc tgaatgagaa cagcgagcag aaggaaaatg tggaaaaaga 241 ggggctgtgt aatgcatgtt tgtggaggga aaacactaca tcctcaagac tagaagccat 301 aaaaatccaa atcctcagta aacttcgcct ggaaacagct cctaacatca gcaaagatgc 361 tatcagacaa cttttgccca aggctcctcc actcctggag ctgattgatc agttcgatgt 421 ccagagagat gccagcagtg acggctcctt ggaagacgat gactaccacg ccaggacgga 481 aacggtcatt accatgccca cggagtgtga gtagtcctgc tggtgcagag caacgactct 541 gctgactgct gttctagtgt tcatgagaaa ccgatctatt ttcaggctct tttaacaagc 601 tgctggcttg tatgtaagga ggaggggaaa gagctttttt caagatttca tgagaaatag 661 accaatgaga ctgaaagctg ctactttatt tgtttcctta gagagctaaa aagctaaaaa
Intron 1
Intron 2
AF 80F
nt ke-2188
Luci 5F
nt ke-4681
AF 81R
nt ke-2870
Luci 6R
nt ke-5175
5161 tctatatttg gttcatagct tcctaaaaca tggaaggtct tcccctcaac aattttgaaa 5221 ctgtgaaatt atgtaccaca ggctataagc ctagagtatg ctacagtcac ttaagcacaa 5281 gctacagtat atgagctaaa aagagagaat atatgctatg gttggcattt aaccatcaaa 5341 acaaatcgta taataaaacg ttttatgatt tccagagttt ttgaactagg agatcaaatt 5401 ccatttatgt tcaaatatat cacaacacat gcaggtgaat gaaagcaatt ctccttgtct 5461 tctggtgaat taaaggagta tgctttaaaa tctatttctt tacagtttca cttaatattt 5521 acagaaaaat ctatatgtag tattggtaaa atgcagtatt gttatatacc attatttgaa 5581 acatccttaa acacttgaat ttatattgta tgatagcata cttggtaaga tgagattcca 5641 caaaataggg atggcacacc gtacgcaagt taccattcct atactgattg atacagtaca 5701 ttaacagttt ttgccaatgg tgctaataca ataggctgaa tggctgatgt tatcaggttt 5761 atcaagcaaa aaacgttcag gaaagtaata agtttctcct ttcttcaggt gcattttcac 5821 actcctccct atgggcaatg gatgttctat aaagaaagaa aactcatttt cctagaggtc 5881 tacattcaat tctgtagcat acttggagaa gctgcattga aaaggcagtc aaaaagtatt 5941 cattttggtc aaaatttcaa aattatagcc tgcctttgca atactgcagc ttttaggatg 6001 aaataatgga aatgactgat tctatcaata ttgtataaaa agattttgaa atagttgcat 6061 ttatataata tgtatacaat attgttttgt aaataaatgt ctcctttttt atttactttg 6121 gtatattttt acagtaagga catttcaaat taagtattaa ggcacaaaga catgtcatgt 6181 aggacataaa agcaaaagct tatattttgg agcaaattag ttgattaaat agtggtctta 6241 aaactccata tgctaatggt tagatggtta tattacaatc attttatatt tttttacatt 6301 attagcattc acttatggat tcatgatggc tgtataatgt gaatgtgaaa tttcaatggt 6361 ttactgtcat tgtattcaaa tctcaacgtt ccattatttt aatacttata aatattaagc 6421 ataccaaaat gatttaactc tattatctga aatcagaata ataaactgat gatatcttac 6481 aaattgttaa ttttatttta taatttgata atgaatatat ttctgcatat atttactact 6541 attttgtaaa tcaggatttt gttaatcaaa taaattgtac ttatgattaa gtgaaattat 6601 ttcttacatc caatgtgtag aaacaattta agttatatta aagtgttttc accttttttg 6661 aaagacaaca gtttcatgtt ataatg
Lampiran 3. Beberapa spesies pembanding yang digunakan dalam proses pensejajaran gen
miostatin (GDF8) ekson 2 dan ekson 3
No.
Spesies
Jenis
No. Akses
Keterangan
01.
Bos javanicus
Madura Cattle
-
ekson 2
02.
Bos javanicus
Madura Cattle
-
ekson 3
03.
Bos taurus
Japanese Black Cattle
AB076403
ekson 2 &ekson 3
04.
Bos taurus
Japanese Black Cattle
AB232690
ekson 2
05.
Bos taurus
Taurus Cattle
AF019761
ekson 2
06.
Bos taurus
Taurus Cattle
AF320998
ekson 2 & ekson 3
07.
Bos taurus
Korea native Cattle
AY160688
ekson 2 & ekson 3
08.
Bos indicus
Indicus Cattle
AY794986
ekson 2 & ekson 3
09.
Bos frontalis
Gayal (Gaur)
EF432555
ekson 3
10.
Bos indicus
Leiqiong & Menggu Cattle
EF438805
ekson 2 & ekson 3
11.
Bos indicus
Leiqiong & Menggu Cattle
EF438814
ekson 2 & ekson 3
12.
Bos taurus
Leiqiong & Menggu Cattle
EF467383
ekson 2 & ekson 3
13.
Bos taurus
Leiqiong & Menggu Cattle
EF467392
ekson 2 &ekson 3
14.
Bos grunniens
Domestic Yak
EU372977
ekson 2 & ekson 3
15.
Bos grunniens
Domestic Yak
EU926669
ekson 3
16.
Bos grunniens
Domestic Yak
EU926670
ekson 2 &ekson 3
17.
Bos taurus
Taurus Cattle
FJ752671
ekson 2 &ekson 3
18.
Bos taurus
Taurus Cattle
FJ752672
ekson 2 & ekson 3
19.
Bos indicus
Indicus Cattle
FJ752675
ekson 2 &ekson3
20.
Bos indicus
Indicus Cattle
FJ752676
ekson 2 & ekson 3
21.
Bos indicus
Indicus Cattle
FJ752679
ekson 2 & ekson 3
22.
Bos grunniens
Domestic Yak
FJ752681
ekson 2
23.
Bos grunniens
Domestic Yak
FJ752682
ekson 3
24.
Bos frontalis
Gayal (Gaur)
FJ752684
ekson 2 &ekson 3
25.
Bos frontalis
Gayal (Gaur)
FJ752685
ekson 2 &ekson 3
26.
Bos taurus
Chinese Bohai
12
Lampiran 4. Hasil pensejajaran ekson 2 gen miostatin (GDF8) sapi madura terhadap beberapa genus
Bos
(Nomor merujuk pada nama spesies yang ada di lampiran 3).
Baris pertama,kedua, dan ketiga menunjukkan nomor posisi nukleotida yang dibaca secara vertikal
111 111 111 122 222 222 223 333 333 333 444 444 444 455 555 555 556 666 666 666 777 777 777 788 888 888 889 999 999 999 123 456 789 012 345 678 901 234 567 890 123 456 789 012 345 678 901 234 567 890 123 456 789 012 345 678 901 234 567 890 123 456 789 01. CTG ATC TTC TAA CGC AAG TGG AAG GAA AAC CCA AAT GTT GCT TCT TTA AAT TTA GCT CTA AGA TAC AAT ACA ATA AAC TAG TAA AGG CCC AAC TGT GGA 03. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 04. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 05. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 06. ... ... ... ... ... ... ... ... ... ... ... ... ... .T. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 07. ... ... ... ... ... ... ... ... ... ... ... ... ... .T. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 08. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 10. G.. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 11. G.. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 12. G.. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 13. G.. ... ... ... ... ... ... ... ... ... ... ... ... .T. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 14. G.. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 16. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 17. G.. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 18. G.. ... ... ... ... ... ... ... ... ... ... ... ... .T. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 19. G.. ... ... ... ... ... ... ... ... ... ... ... ... .T. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 20. G.. ... ... ... ... ... ... ... ... ... ... ... ... .T. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 21. G.. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 22. G.. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 24. G.. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 25. G.. ... ... ... ... ... ... ... ... ... ... ... ... .T. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 26. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 27. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 28. ... ... ... ... ... ... ... ... ... ... ... ... ... .T. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 30. ... ... ... ... ... ... ... ... ... ... ... ... ... .T. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 31. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ...
13
111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 000 000 000 011 111 111 112 222 222 222 333 333 333 344 444 444 445 555 555 555 666 666 666 777 777 777 778 888 888 888 999 999 999 012 345 678 901 234 567 890 123 456 789 012 345 678 901 234 567 890 123 456 789 012 345 678 901 234 567 890 123 456 789 012 345 678 TAT ATC TGA GGC CTG TCA AGA CTC CTG CGA CAG TGT TTG TGC AAA TCC TGA GAC TCA TCA AAC CCA TGA AAG ACG GTA CAA GGT ATA CTG GAA TCC GAT 10. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 11. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 12. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 13. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 14. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 16. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 17. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 18. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 19. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 20. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 21. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 22. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 24. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 25. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 26. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 27. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 28. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 30. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 31. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ...14
122 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 900 000 000 001 111 111 111 222 222 222 233 333 333 334 444 444 444 555 555 555 566 666 666 667 777 777 777 888 888 888 899 999 999 901 234 567 890 123 456 789 012 345 678 901 234 567 890 123 456 789 012 345 678 901 234 567 890 123 456 789 012 345 678 901 234 567 CTC TGA AAC TTG ACA TGA ACC CAG GCA CTG GTA TTT GGC AGA GCA TTG ATG TGA AGA CAG TGT TGC AGA ACT GGC TCA AAC AAC CTG AAT CCA ACT TAG 20. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 21. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 22. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 24. ... ... ... ... ... ... ... ... ... ... ... ... ... .A. ... ... ... ... ... ... ... ... .A. ... ... ... ... ... ... ... ... ... ... 25. ... ... ... ... ... ... ... ... ... ... ... ... ... .A. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 26. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 27. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 28. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 30. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 31. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ...15
223 333 333 333 333 333 333 333 333 333 333 333 333 333 333 333 333 333 333 333 333 333 333 333 333 33990 000 000 000 111 111 111 122 222 222 223 333 333 333 444 444 444 455 555 555 556 666 666 666 777 77 890 123 456 789 012 345 678 901 234 567 890 123 456 789 012 345 678 901 234 567 890 123 456 789 012 34 GCA TTG AAA TCA AAG CTT TAG ATG AGA ATG GCC ATG ATC TTG CTG TAA CCT TCC CAG AAC CAG GAG AAG ATG GAC TG 31. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..
Lampiran 5. Hasil pensejajaran ekson 3 gen miostatin (GDF8) sapi madura terhadap beberapa genus
Bos
(Nomor merujuk pada nama spesies yang ada di lampiran 3).
Baris pertama,kedua, dan ketiga menunjukkan nomor posisi nukleotida yang dibaca secara vertikal
111 111 111 122 222 222 223 333 333 333 444 444 444 455 555 555 556 666 666 666 777 777 777 788 888 888 889 999 999 999 123 456 789 012 345 678 901 234 567 890 123 456 789 012 345 678 901 234 567 890 123 456 789 012 345 678 901 234 567 890 123 456 789 02. ACT CCT TTT TTA GAA GTC AAG GTA ACA GAC ACA CCA AAA AGA TCT AGG AGA GAT TTT GGG CTT GAT TGT GAT GAG CGC TCC ACA GAA TCT CGA TGC TGT 03. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 06. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 07. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 08. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 09. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 10. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 11. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 12. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 13. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 14. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 15. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 16. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 17. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 18. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 19. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 20. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 21. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 23. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 24. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 25. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 26. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ... 29. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..A .A. ... ... ... ... ... ... ...
16
111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 111 000 000 000 011 111 111 112 222 222 222 333 333 333 344 444 444 445 555 555 555 666 666 666 777 777 777 778 888 888 888 999 999 999 012 345 678 901 234 567 890 123 456 789 012 345 678 901 234 567 890 123 456 789 012 345 678 901 234 567 890 123 456 789 012 345 678 CGT TAC CCT CTA ACT GTG GAT TTT GAA GCT TTT GGA TGG GAT TGG ATT ATT GCA CCT AAA AGA TAT AAG GCC AAT TAC TGC TCT GGA GAA TGT GAA TTT 08. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 09. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 10. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 11. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 12. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 13. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 14. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 15. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 16. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 17. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 18. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 19. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 20. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 21. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 23. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 24. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 25. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 26. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... 29. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ...17
122 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 222 900 000 000 001 111 111 111 222 222 222 233 333 333 334 444 444 444 555 555 555 566 666 666 667 777 777 777 888 888 888 899 999 999 901 234 567 890 123 456 789 012 345 678 901 234 567 890 123 456 789 012 345 678 901 234 567 890 123 456 789 012 345 678 901 234 567 GTA TTT TTG CAA AAG TAT CCT CAT ACC CAT CTT GTG CAC CAA GCA AAC CCC AGA GGT TCA GCT GGC CCC TGC TGC ACT CCT ACA AAG ATG TCT CCA ATT 20. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..C ... ... ... ..T ... ... ... ... ... ... ... ... 21. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..C ... ... ... ..T ... ... ... ... ... ... ... ... 23. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..C ... ... ... ..T ... ... ... ... ... ... ... ... 24. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..C ... ... ... ..T ... ... ... ... ... ... ... ... 25. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..C ... ... ... ..T ... ... ... ... ... ... ... ... 26. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..C ... ... ... ..T ... ... ... ... ... ... ... ... 29. ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ... ..C ... ... ... ..T ... ... ... ... ... ... ... ...ABSTRAK
IQBAL IMANNULLOH. Keragaman Gen Miostatin (GDF-8) pada Sapi Madura. Dibimbing oleh
ACHMAD FARAJALLAH dan RADEN RORO DYAH PERWITASARI.
Sapi madura merupakan salah satu sapi lokal Indonesia yang memiliki kemampuan
adaptasi terhadap iklim tropis di kepulauan Madura dan memiliki kualitas daging serta kulit yang
baik. Perkembangan dan diferensiasi massa otot rangka dikendalikan oleh gen miostatin atau
growth differentiation factor-8
(GDF-8). Penelitian ini dilakukan untuk mengetahui keragaman
gen miostatin (ekson 2 dan ekson 3) pada sapi madura dan dibandingkan dengan gen miostatin dari
genus
Bos
lainnya pada tingkat runutan nukleotida. Identifikasi varian gen miostatin dilakukan
terhadap 21 sampel DNA sapi madura dan perunutan nukleotida dilakukan terhadap amplikon
menggunakan metode sampel DNA
pooling
. Enam varian yang ditemukan pada ekson 2 yaitu
C1G
(Leu),
C41T
(Ala),
G239A
(Arg),
G266A
(Arg),
A268G
(Thr), dan
A331G
(Met), sedangkan
pada ekson 3 yaitu
G75A
,
G77A
,
T261C
,
C273T
,
A330C
(Ile), dan
T336C
(Thr). Analisis varian
menunjukkan bahwa empat varian pada ekson 3 hanya terdapat pada sapi madura, satu bersifat
missense
yaitu
G77A
(His -- Arg), tiga varian lainnya bersifat
nonsense
yaitu
G75A
(Glu),
T261C
(Ala), dan
C273T
(Cys). Enam varian pada ekson 2 dan dua varian pada ekson 3 memiliki
kesamaan nukleotida basa pada genus
Bos
lainnya, yaitu
C1G
(48%),
C41T
(64%),
G239A
(88%),
G266A
(92%),
A268G
(96%),
A331G
(92%),
A330C
(72,7%), dan
T336C
(36,4%). Varian yang
ditemukan pada sapi madura berbeda dengan varian yang menunjukkan fenomena
double
muscling
.
Kata kunci
: miostatin, ekson 2, ekson 3, varian, DNA
pooling
ABSTRACT
IQBAL IMANNULLOH. Diversity of Myostatin Gene (GDF-8) on Madura Cattle. Supervised by
ACHMAD FARAJALLAH and RADEN RORO DYAH PERWITASARI.
Madura cattle is one of Indonesian local cows that have an ability to adapt the tropical
climate in Madura island and produce good quality meats and skins. Development and
differentiation of muscle mass are controlled by myostatin gene or
growth differentiation factor-8
(GDF-8). This research aimed to estimate the diversity of myostatin gene (exon 2 and exon 3) in
madura cattle and compared it with myostatin gene from other
Bos
genus. The identification of
myostatin gene diversity was performed on 21 DNA samples from madura cattle and nucleotides
sequencing was conducted on the amplicon using DNA
pooling
sample methods. The six variants
of the exon 2 were
C1G
(Leu),
C41T
(Ala),
G239A
(Arg),
G266A
(Arg),
A268G
(Thr), and
A331G
(Met), whereas on exon 3 was
G75A
,
G77A
,
T261C
,
C273T
,
A330C
(Ile), and
T336C
(Thr). The
variance analysis showed that there were four variants of exon 3 that only found in a madura
cattle, one variant has
missense
characteristic, that is
G77A
(His -- Arg), and the three other
variants have
nonsense
characteristic, that are
G75A
(Glu),
T261C
(Ala), and
C273T
(Cys). The
six variants of exon 2 and two variants of exon 3 had a nitrogen base similarity with the other
Bos
genus, that are
C1G
(48%),
C41T
(64%),
G239A
(88%),
G266A
(92%),
A268G
(96%),
A331G
(92%),
A330C
(72,7%), and
T336C
(36,4%). The variants found in madura cattle are different
from variants that showed the
double muscling
phenomena.
PENDAHULUAN
Latar Belakang
Sapi merupakan salah satu hewan ternak
dari famili Bovidae. Sapi yang berkembang
saat ini berasal dari domestikasi
Bos
primigenius
.
Domestikasi
tersebut
menghasilkan dua jenis sapi, yaitu sapi tanpa
punuk (punggung bagian depan datar,
B.
taurus
) dan sapi berpunuk (punggung bagian
depan melengkung ke atas,
B. indicus
).
Persebaran
B. taurus
sebagian besar berada di
wilayah Eropa dan Afrika Barat sedangkan
B.
indicus
sebagian besar tersebar di wilayah
Asia bagian selatan dan Afrika.
Jenis sapi lain yang memiliki sejarah
berbeda dari keduanya adalah
B. javanicus
,
yang dikenal sebagai banteng.
Banteng
mengalami domestikasi langsung menjadi sapi
bali (Nijman
et al.
2003). Selain sapi bali, di
Indonesia bisa ditemukan beberapa sapi lokal
yang lain, misalnya sapi madura dan sapi
aceh. Uggla (2008) dan Mohamad
et al.
(2009) melaporkan bahwa sapi aceh berasal
dari keturunan
B. indicus
, sedangkan sapi
madura merupakan hasil persilangan banteng
dan sapi berpunuk atau
B. indicus
. Firdhausi
(2010) menggunakan asal sampel yang lebih
terkontrol dengan cakupan asal sampel sekitar
setengah luasan madura, berdasarkan DNA
mitokondria melaporkan bahwa sapi madura
terbagi menjadi dua tipe, yaitu tipe I berasal
dari keturunan induk betina banteng dan tipe
II berasal dari keturunan induk betina sapi
berpunuk.
Dilihat dari morfologinya, sapi madura
memiliki kesamaan dengan sapi bali, yaitu
kulit berwarna kecoklatan dengan motif putih
pada bagian pantat dan kaki. Adaptasi yang
lama di daerah tropis kepulauan Madura
menyebabkan sapi madura memiliki beberapa
sifat unggul, yaitu tahan terhadap kondisi
panas, mampu hidup baik dalam kondisi
makanan terbatas, resisten terhadap parasit
serta memiliki kualitas daging dan kulit yang
baik (Payne dan Hodges 1997).
Miostatin
atau
growth differentiation
factor-8
(GDF-8)
adalah
protein
yang
mengatur pertumbuhan otot rangka sebelum
dan setelah kelahiran.
Protein tersebut
merupakan salah satu anggota superfamili
transforming growth factor-
β
(TGf-
β) yang