Kemampuan reproduksi merupakan salah satu ciri makhluk hidup. Reproduksi tingkat
sel merupakan dasar dari reproduksi makhluk hidup. Pada eukariot bersel tunggal,
sebagaimana juga pada bakteri, reproduksi sel sudah merupakan reproduksi makhluk hidup.
Pada eukariot bersel ganda reproduksi sel merupakan satu bagian dari proses pertumbuhan
dan perkembangan organisme. Pada titik tumbuh, seperti pada ujung akar atau pucuk, akan
terjadi pembelahan sel secara berkelanjutan.
Reproduksi selular akan diawali oleh reproduksi bahan genetik. Pada sel eukariot
reproduksi sel mengikuti urutan tahapan berikut: G1→S→G2→M (Gambar 1.7). Replikasi DNA, fase S, berjalan sebelum berlangsungnya pembelahan sel mitosis atau meiosis (fase
M). Pada fase S akan terjadi sintesis atau replikasi DNA kromosom, sehingga pada masuk ke
fase M (mitosis; meiosis) semua kromosom telah tergandakan.
Pada sebagian besar organisme, eukariot, prokariot, dan virus, DNA menjadi bahan
genetik; pada sebagian virus RNA menjadi bahan genetik. DNA genom diperbanyak dengan
cara replikasi, sedangan RNA genom virus diperbanyak dengan dua cara, replikasi dan
transkripsi balik. Pada bab ini akan dijelaskan mengenai replikasi bahan genetik organisme
pada tingkat molekular
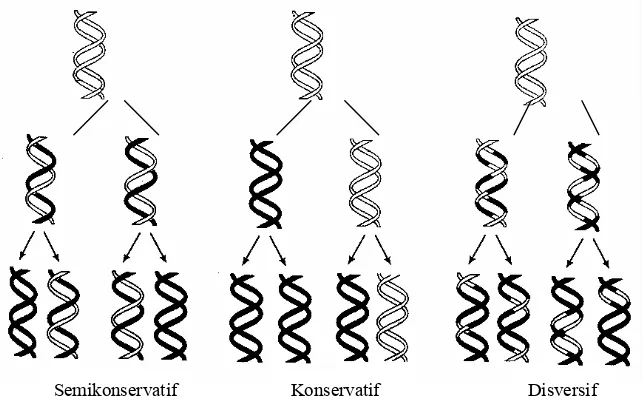
A. Replikasi Pola Semikonservatif
Watson dan Crick mengemukakan bahwa struktur heliks ganda DNA menunjang proses
reproduksi DNA melalu replikasi dengan pola semikonservatif. Pengertian replikasi
semikonservatif ialah : bahwa dalam proses pembentukan DNA dari kedua utasan
polinukleotida heliks ganda DNA hanya satu utasan yang disintesis sedangkan utasan yang
lainnya berasal dari molekul DNA terdahulu (Gambar 4.8 dan 4.11). Sebagai perbandingan
terhadap pola semikonservatif ini, pada Gambar 4.12 diperlihatkan dua pola yang lain, yaitu
pola konservatif dan pola dispersif, dan sudah terbukti bahwa pola koservatiflah yang benar.
Pola konservatif ternyata masih berlaku dalam proses reproduksi kromosom, yaitu digunakan
dalam replikasi genom virus RNA.
4
BAB
REPLIKASI
BAHAN GENETIK
Pola semikonservatif dibuktikan mula-mula oleh Mathew Meselson dan Francis Stahl
(1958). Mereka bekerja dengan bakteri E. coli telah menggunakan teknik radioisotop,
sentrifugasi, dan densitometer, dengan tujuan untuk membedakan jenis DNA serta
kuantitasnya. Pada garis besarnya yang mereka lakukan ialah menumbuhan E. coli pada
kemudian pada setiap generasi yang berurutan dilakukan pemeriksaan kromosomnya dan
dibandingkan satu generasi dengan yang lainnya
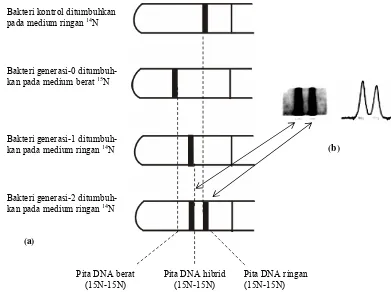
.Mula-mula bakteri ditumbuhkan secara berulang pada medium berat (radioisotop 15N)
sampai semua bakteri mengandung 15N pada DNAnya. Kultur bakteri ini disebut generasi-0.
Kemudian bakteri 15N ini dibiakkan pada medium ringan atau berisotop 14N dan turunannya
(generasi-1) dibiakkan lagi pada medium 14N menghasilkan generasi-2, dan selanjutnya
diulang lagi menghasilkan generasi-3, dan generasi-4 pada medium 14N.
Meselson dan Stahl telah mengisolasi DNA bakteri dari generasi-tersebut di atas dengan
teknik sentrifugasi kepekatan bertingkat, dan berhasil memisahkan DNA berdasarkan
jenisnya atau bobotnya, yaitu DNA berat 15N, DNA hibrid 15N-14N, dan DNA ringan 14N
(Gambar 4.12). Kuantitas DNA yang terdapat dalam tabung kemudian ditentukan dengan
bantuan teknik autoradiografi. DNA yang ada pada tabung sentrifugasi ditempelkan pada film
negatif, memberi kesempatan sinar dari radioisotop untuk membakar film, kemudian
kepekatan tanda yang terdapat pada foto digunakan sebagai penduga kuantitas DNA.
Densitometer dapat mengukur kepekatan DNA yang terdapat pada foto tersebut.
Gambar 4.1. Replikasi DNA mengikuti pola semikonservatif, yaitu dari dua utasan polinukleotida penyusun DNA hanya satu yang disintesis sedangkan yang satunya lagi berasal dari DNA tetuanya. Sebagai perbandingan digambarkan dua pola lain, yaitu pada pola konservatif kedua utasan DNA berasal dari generasi yang sama, sedangkan pada pola disversif, kedua utasan DNA merupakan campuran dari fragmen yang baru dan fragmen DNA lama
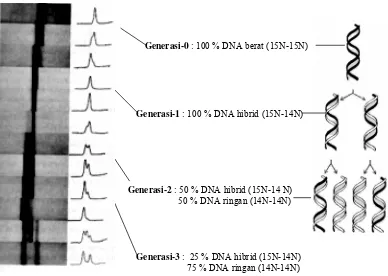
Bila pola semikonservatif itu benar maka seharusnya dari generasi-0 akan diperoleh
semua DNA bakteri mengandung 15N pada kedua utasannya, dan pada generasi-1 akan
diperoleh semua DNA dalam bentuk hibrid (15N-14N), satu utasan mengandung 15N dan
utasan lainnya mengandung 14N. Pada generasi-2 akan diperoleh dua jenis DNA yaitu
pertama DNA hibrid 15N 14N, dan yang kedua DNA dengan kedua utasannya yang
mengandung 14N. Kedua jenis DNA ini akan mempunyai nisbah (perbandingan) yang sama.
Hal ini terjadi karena dari DNA hibrid 15N - 14N generasi-1 akan menyumbangkan satu
utasan 15N dan satu utasan 14N, selanjutnya utasan 15N pada medium isotop 14N akan
menghasilkan DNA hibrid 15N - 14N dan utasan 14N akan menghasilkan DNA 14N
(kedua utasan mengandung 14N). Pada generasi-3 akan diperoleh kembali dua jenis DNA
seperti pada generasi-2, tetapi dengan nisbah yang berbeda. Dari DNA hibrid pada generasi-2
akan dihasilkan DNA hibrid dan DNA 14N, sedangkan dari DNA 14N (generasi-2)
dihasilkan seluruhnya DNA 14N. Jadi dilihat dari segi kuantitas akan terjadi peningkatan (a)
Gambar 4.2. (a) Sentrifugasi dengan tabung penyangga berkepekatan
bertingkat berhasil memisahkan DNA berdasarkan beratnya, 15N (berat), 15N-
14
N,(hibrid), dan 14N.(ringan) , dan kemudian (b) dan menangkap signal dengan film dan memriksa kepekatan dengan densitometer
Bakteri kontrol ditumbuhkan pada medium ringan 14N
Bakteri generasi-0 ditumbuh-kan pada medium berat 15N
Bakteri generasi-1 ditumbuh-kan pada medium ringan 14N
Bakteri generasi-2 ditumbuh-kan pada medium ringan 14N
Pita DNA berat (15N-15N)
Pita DNA hibrid (15N-15N)
Pita DNA ringan (15N-15N)
DNA 14N dan penurunan DNA hibrid 15N - 14N. Pada generasi-3 ini pada pola
semikonservatif akan diperoleh nisbah 3 : 1 antara DNA 14N dengan DNA 15N - 14N.
Hasil percobaan Meselson dan Stahl telah membuktikan kebenaran semua hipotesis yang
telah dijelaskan pada dua alinea sebelumnya. Pada generasi-0 diperoleh DNA yang setara
dengan DNA 15N; pada generasi-1 diperoleh seluruhnya DNA hibrid 15N-14N; pada
generasi-2 terdapat DNA hibrid 15N-14N dan DNA 14N dengan perbandingan 1:1; dan pada generasi-3
diperoleh DNA 14N dan DNA hibrid 15N-14N dengan perbandingan 3:1 (Gambar 4.13). Jadi
melalui percobaan Meselson dan Stahl telah terbukti kebenaran pola replikasi
semikonservatif.
B. Sintesis dengan Arah Pertumbuhan 5-3
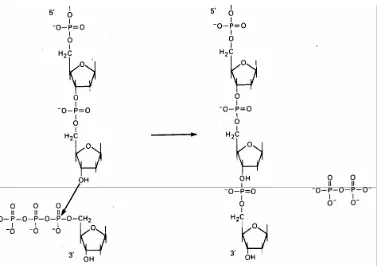
Dalam keadaan bebas, nukleotida akan berada dalam bentuk nukleotida trifosfat. Dalam
proses sintesis DNA, dua nukleotida digabungkan satu dengan yang lain dengan cara
menghubungkan karbon gula kelima (C5) yang mengandung fosfat dari satu nukleotida
kepada karbon gula ketiga (C3) yang mengandung OH dari nukleotida lain, membentuk
ikatan 5--3 fosfodiester (Gambar 4.14). Ada dua cara yang mungkin dilakukan dalam
menambahkan satu nukleotida ke dalam rantai polinukleotida yang sudah ada sebelumnya,
Gambar 4.3. Hasil percobaan Meselson & Stahl. Pemeriksaan densitometer terhadap
fotoradiografi DNA, menunjukkan bahwa kuantitas jenis DNA dari beberapa generasi berurutan mendukung pola replikasi semikonservatif.
Generasi-0 : 100 % DNA berat (15N-15N)
Generasi-1 : 100 % DNA hibrid (15N-14N)
Generasi-2 : 50 % DNA hibrid (15N-14 N) 50 % DNA ringan (14N-14N)
yaitu ditambahkan pada ujung 3'OH (pertumbuhan 5--3) atau ditambahkan pada ujung 5'P
(pertumbuhan 3--5). dan secara kimia, pertumbuhan 5-3 adalah yang paling efisien.
Pada situs awal replikasi polimerase DNA akan mengudar pilinan heliks ganda menjadi
dua utasan tunggal. Dalam proses pengudaran ini akan terbentuk percabangan replikasi
seperti huruf Y, dengan dua cabang utas tunggal dan batang utas ganda. Berdasarkan aturan
antiparalel dari utas-utas heliks ganda DNA, maka pada percabangan replikasi akan terdapat
dua cabang yang berbeda ujungnya yaitu ujung 3'OH dan ujung 5'P (Gambar 4.15). Akibat
dari arah pertumbuhan DNA dari ujung 5'P ke ujung 3'OH; maka dalam percabangan
replikasi akan terdapat dua pola sintesis DNA baru, yaitu pada cabang berujung 3'OH sintesis
akan berjalan dari bagian ujung ke arah pangkal percabangan, sedangkan pada cabang 5'P
sintesis akan dimulai dari pangkal percabangan dan bergerak ke arah ujung (Gambar 4.15).
Cabang yang berujung 3'OH disebut cabang "Leading" sedangkan yang berujung 5'P disebut
cabang "lagging". Pada utas "leading" karena arah sintesis berjalan dari ujung menuju
pangkal percabangan, maka sintesis dapat berjalan seara kontinu sejalan dengan proses
pengudaran pilinan heliks ganda. Pada utas "lagging" karena setiap tahap sintesis harus
dimulai pada pangkal percabangan, dan bergerak ke arah ujung cabang, maka setiap saat
percabangan yang diikuti oleh sintesis dengan arah ke bagian luar cabang. Jadi, pada utas
lagging, sintesis akan berjalan secara diskontinyu. Oleh karena itu akan ditemukan berbagai
fragmen DNA yang disebut fragmen Okazaki sesuai dengan nama penemunya Reiji Okazaki
(Okazaki et al, 1969).
Dalam replikasi DNA berlangsung tiga tahap atau proses penting, yaitu sebagai berikut:
(i) Pengenalan situs awal replikasi; (ii) Pengudaran (Pemisahan) pilinan heliks ganda; dan
(iii) Sintesis rantai polinukleotida baru. Kedalam tahapan tersebut dilibatkan sejumlah protein
dan enzim (Gambar 4.15).
A. Pengenalan Situs Awal Replikasi
Syarat pertama agar suatu molekul DNA dapat bereplikasi ialah bahwa pada molekul
tersebut terdapat situs awal replikasi. Hasil pengamatan terhadap kromosom E. coli
memperlihatkan bahwa proses replikasi selalu dimulai dari satu titik awal (Cairn, 1963).
Sekarang telah diketahui bahwa titik awal tersebut ternyata merupakan satu ruas yang
mempunyai runtunan basa tertentu. Situs awal replikasi dikenal juga dengan istilah titik ori
(kependekan dari origin of replication); sebagai contoh Ori C pada kromosom E. coli.
Pengenalan situs awal replikasi E. coli dilakukan oleh satu protein, yaitu protein DnaA.
yang dihasilkan oleh gen dnaA. DnaA dapat mengenali titik ori melalui interaksi khusus,
yaitu dengan mengenali runtunan basa ruas ori. Perubahan yang terjadi pada runtunan basa
ori atau konfigurasi DnaA dapat menyebabkan protein tersebut tidak dapat mengenali titik
ori, dan akibatnya DNA tidak mampu bereplikasi. Jadi kecocokan antara situs awal replikasi
dengan DnaA akan menentukan kemampuan suatu DNA untuk bereplikasi dalam suatu sel.
B. Pengudaran (pemisahan) Pilinan Heliks Ganda
Dalam struktur heliks ganda terlihat bahwa basa-basa berada di bagian dalam pilinan yang
terlindung dari kontak dengan luar. Dalam proses replikasi, basa-basa yang terdapat pada
rantai polinukleotida akan digandakan sebagai model dalam menyusun utasan nukleotida
baru, sehingga pilinan heliks ganda harus dibuka dan dipisahkan utasan-utasannya menjadi
utasan tunggal. Terdapat tiga protein dan enzim yang berperan dalam proses ini yaitu
Helikase, Girase, dan Protein Pelindung Utas Tunggal (PPUT).
Helikase adalah kelompok protein yang berfungsi mengudar (memisahkan) pilinan heliks
ganda dengan cara menghilangkan ikatan hidrogen, dan memisahkan utasan-utasannya
menjadi utas tunggal. Sebagai contoh cara kerja helikase, pada E. coli helikase menempel
pada wilayah salah satu utasan tunggal DNA dan kemudian bergerak dengan arah dari ujung
3 ke ujung 5, menuju bagian utas ganda dan membebaskan utasan-utasan dari pilinan heliks.
Selanjutnya utasan tunggal yang telah terbebaskan akan ditempeli PPUT.
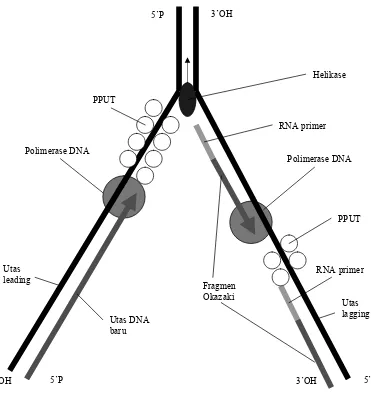
Gambar 4.5. Kegiatan yang berlangsung pada suatu percabangan replikasi; helikase dan girase mengudar pilinan heliks ganda membentuk utas leading dan utas lagging. Protein SSB akan menutupi utas tunggal yang terbentuk sebelum digunakan sebagai model catakan. Primer RNA akan disintesisi untuk menolong Polimerase DNA mengaitkan nukleotida DNA dalam rangka sintesis utasan baru. Sintesis berjalan dengan arah 5-3; pada utas leading berjalan dari ujung ke pangkal percabangan sedangkan pada utas lagging dari pangkal ke ujung cabang. Sintesis berjalan secara bertahap membentuk fragmen Okazaki.
5’P 3’OH
3’OH 5’P
3’OH 5’P
Helikase
Polimerase DNA RNA primer
PPUT
RNA primer
Utas lagging Utas
leading
Fragmen Okazaki
Utas DNA baru Polimerase DNA
Girase adalah enzim yang berfungsi untuk menghilangkan tegangan pada percabangan
replikasi. Di atas telah dijelaskan bahwa pilinan heliks ganda akan diuraikan oleh helikase.
Penguraian pilinan heliks oleh helikase dapat menyebabkan terjadi ketegangan pada bagian
pangkal percabangan replikasi. Akibat ketegangan tersebut akan terbentuk struktur
superheliks. Girase akan menghilangkan ketegangan tersebut dengan cara melakukan rotasi
pilinan ke arah yang berlawanan.
Penempelan PPUT pada utas tunggal berfungsi untuk melindungi utas tunggal DNA yang
telah diuraikan oleh helikase dari kemungkinan berpasangan kembali dengan utas
pasangannya membentuk heliks ganda. Protein ini akan menempel dan berasosiasi dengan
DNA utas tunggal begitu helikase selesai mengudar heliks ganda. Penempelan ini juga
melindungi utas tunggal dari kemungkinan kerusakan oleh enzim nuklease, dan kemungkinan
digunakan oleh transikriptase untuk melakukan transkripsi.
C. Sintesis Rantai DNA
Dalam proses sintesis fragmen Okazaki tersebut di atas akan digunakan utas DNA lama
sebagai model cetakan. Dalam proses sintesis ini akan dilibatkan sejumlah enzim. Sebagai
contoh pada E. coli, sintesis DNA dapat dibagi menjadi empat tahap atau langkah dengan
bantuan enzim yang berbeda-beda. Keempat langkah tersebut adalah (Gambar 4.16).
(1) Inisiasi sintesis fragmen Okazaki oleh Polimerase RNA,
(2) Sintesis perpanjangan DNA oleh Polimerase DNA III,
(3) Pengisian celah oleh Polimerase DNA I, dan
(4) Pematrian fragmen-fragemen Okazaki oleh ligase
C1. Inisiasi Sintesis Fragmen Okazaki oleh Polimerase RNA
Dalam proses replikasi, sintesis fragmen Okazaki diawali oleh sintesis rangkaian
beberapa basa RNA primer. Hal ini diperlukan karena enzim pengkatalisis sintesis DNA yaitu
polimerase DNA tidak mempunyai kemampuan mengawali sintesis, melainkan hanya
memperpanjang rantai yang sudah ada. Jadi untuk mengawali sintesis DNA perlu dibentuk
RNA primer yang terdiri dari beberapa basa yang akan menjadi tempat polimerase DNA
mengkaitkan nukleotida DNA pertama. Polimerase RNA akan meletakkan ribonukleotida
pada utas tunggal DNA hasil pengudaran (pemisahan) helikase leading atau lagging, dan
mensintesis rangkaian beberapa basa dengan arah 5-3.
C2: Sintesis Perpanjangan Rantai DNA oleh Polimerase DNA III
Enzim ini akan bekerja begitu RNA primer selesai dibentuk, dengan cara mengaitkan
dengan perpanjangan rantai DNA dengan pertumbuhan 5-3. Sintesis oleh Polimerase DNA
III akan berjalan sampai pertumbuhan 5-3 tersebut mencapai RNA primer dari fragmen
Okazaki yang terdapat di depannya. Polimerase DNA III akan berhenti melakukan sintesis
karena terhalang oleh adanya RNA primer tersebut. Untuk melakukan sintesis lanjutan
diperlukan adanya enzim lain yang mampu membuang basa-basa RNA, dan enzim tersebut
adalah Polimerase DNA I. Oleh karena itu untuk menjalankan tugas selanjutnya Polimerase
DIA III diganti oleh Polimerase DNA I.
C3: Pembuangan RNA Primer dan Pengisian Celah oleh Polimerase DNA I
Polimerase DNA I akan bekerja membuang RNA primer yang terdapat pada bagian depan
setiap fragmen okazaki, dan mengisi celah antara dua fragmen tersebut dengan nukleotida
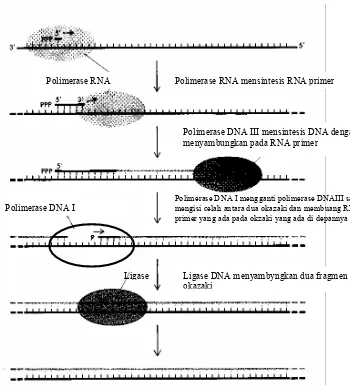
Gambar 4.6. Langkah sintesis utasan baru DNA melibatkan empat enzim, Polimerase
RNA mengawali sintesis, Polimerase DNA III memperpanjang rantai nukleotida, Polimerase DNA I membuang RNA primer dan mengisi celah dan Ligase menyambungkan dua fragmen Okazaki.
Polimerase RNA Polimerase RNA mensintesis RNA primer
Polimerase DNA III mensintesis DNA dengan menyambungkan pada RNA primer
Polimerase DNA I mengganti polimerase DNAIII saat mengisi celah antara dua okazaki dan membuang RNA primer yang ada pada okzaki yang ada di depannya
Polimerase DNA I
Ligase DNA menyambyngkan dua fragmen okazaki
DNA. Tugas Polimerase DNA I akan berakhir bila semua nukleotida RNA habis tergantikan
oleh nukleotida DNA. Pada saat itu rangkaian basa DNA yang disintesis telah mencapai
rangkaian DNA dari fragmen Okazaki yang ada di depannya.
C4. Penyatuan Fragmen-Fragmen DNA oleh Ligase.
Ligase adalah enzim yang berfungsi menyambungkan dua fragmen DNA. Dalam
replikasi, ligase berperanan menyambungkan dua fragmen Okazaki setelah RNA promer
dibuang oleh Polierase DNA I. Dengan disambungkannya berbagai fragmen Okazaki maka
diperolehlah satu utasan nukleotida sebagai utasan baru dari heliks ganda.
A. Replikasi Model
θ
pada Kromosom Bakteri
Visualisasi kromosom bakteri serta cara replikasinya pertama kali dilakukan oleh John
Cairns (1963), dengan bantuan teknik autoradiografi pada kromosom E. coli. Dari hasil
penelitiannya diperoleh pengetahuan pertama tentang bentuk kromosom sirkular, dan yang
kedua mekanisme replikasi dari kromosom tersebut. Pada kromosom bakteri, replikasi
dimulai pada satu titik awal, yaitu Ori-C, dan kemudian bergerak kedua arah atau dwiarah
(Gambar 4.17). Pada foto autoradiografi, utasan DNA utuh akan terlihat sebagai garis, dan
titik awal replikasi terlihat sebagai gelembung. Gelembung ini sesuai dengan periode
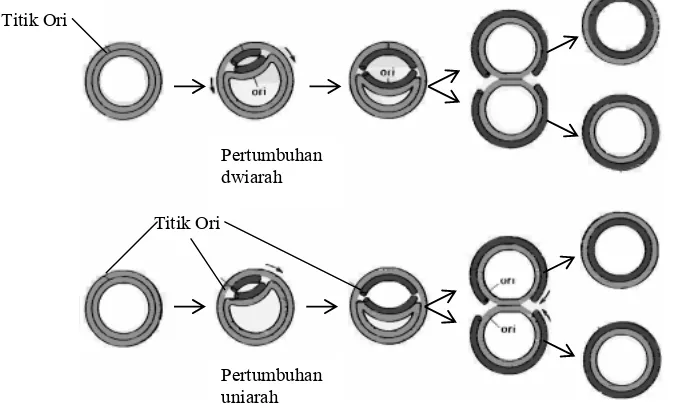
Gambar 4.7. Perbandingan replikasi model θ dwiarah dan uni arah pada kromosom bakteri. (a) replikasi dwiarah, dan (b) replikasi uniarah
Titik Ori Titik Ori
Pertumbuhan dwiarah
Pertumbuhan uniarah
pertumbuhan bakteri, akan membesar ke dua arah, dan pada satu saat akan terlihat sebagai
huruf Yunani teta (θ).
Bentuk gelembung ditafsirkan sebagai akibat terjadinya pengudaran heliks ganda menjadi
utas tunggal, dan masing-masing utas tunggal menjadi media untuk sitesis utas DNA baru.
Pada kedua ujung gelembung terbentuk percabangan replikasi; proses replikasi akan
berlangsung pada kedua ujung tersebut. Oleh karena itu replikasi akan berjalan ke dua arah,
atau dwiarah. Hasil akhir dari proses replikasi model θ adalah dua molekul DNA sirkular (Gambar 4.17). Selain berlangsung pada kromosom bakteri, replikasi model θ juga digunakan dalam replikasi vegetatif plasmid.
B. Replikasi Kromosom Eukariot Berjalan dari Banyak Titik Ori
Secara garis besar replikasi DNA kromosom eukariot sama dengan yang berlangsung
pada kromosom bakteri, tetapi terdapat beberapa perbedaan yang menarik. Enzim yang
mengkatalisis polimerisasi DNA eukariot berbeda dari yang digunakan dalam replikasi
prokariot. Perbedaan yang kedua ialah bahwa eukariot mempunyai banyak titik Ori (situs
awal replikasi). Hal ini diperlukan karena eukariot mempunyai ukuran kromosom yang
sangat besar. Adanya banyak titik, ori terlihat pada foto autoradiografi sebagai banyak
gelembung.
DNA kromosom eukariot merupakan molekul linear, pada setiap situs awal yang terdapat
sepanjang molekul tersebut akan terjadi pemisahan utas ganda dan terjadi replikasi dwiarah.
Dari setiap situs awal akan terbentuk gelembung yang akan membesar, dan berbagai
Gambar 4.8. Replikasi kromosom eukariot dimulai dari banyak titik Ori. Replikasi berjalan ke dua arah; dari banyak titik awal akan terbentuk gelembung yang membesar, kemudian
gelembung-gelembung tersebut menyatu dan akhirnya terbentuk dua kromosom
gelembung akan menyatu membentuk gelembung yang lebih besar, dan akhirnya terbentuk
dua molekul DNA linear atau kromosom (Gambar 4.18).
C. Model Replikasi Lingkaran Berputar
Cara ini digunakan untuk memperbanyak kromosom virus atau plasmid saat konjugasi.
Sistem kerja replikasi ini mirip dengan kerja mesin stensil, untuk memperbanyak tulisan
dengan cara memutar lembaran model pencetak. Dalam model lingkaran berputar, satu utas
DNA dipertahankan dalam bentuk sirkular dan satu dipotong linear. Utas sirkular akan
digunakan sebagai model cetakan dan sintesis utas baru akan menghasilkan utas DNA linear
sebagai hasil cetakannya.
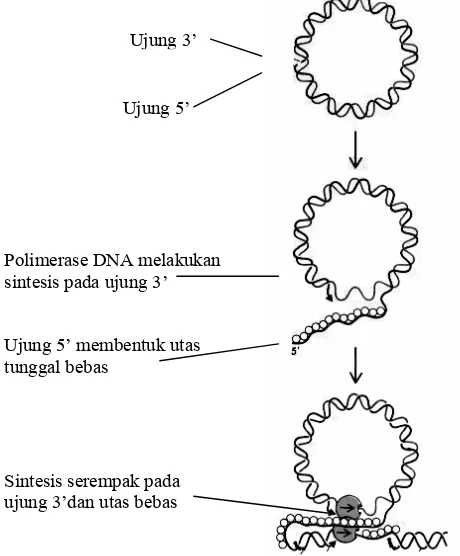
Untuk menjelaskan proses ini kita gunakan kromosom virus DNA utas ganda; kita akan
mendapatkan padanya utas(+) dan utas(-). Tahap awal dari replikasi ini ialah pemotongan
utas(-) tanpa memotong utas(+), (sering disebut dengan istilah nick) (Gambar 4.18). Dari
hasil pemotongan ini akan diperoleh ujung 5'P dan ujung 3'OH pada utas(-). Bersamaan
dengan perputaran utas(+) sirkular bagian ujung 5'P utas(-) akan terlepas dari pilinan heliks
ganda membentuk utas tunggal, sedangkan bagian ujung 3'OH masih tetap menempel sebagai
heliks ganda dengan utas(+). Bersamaan dengan gerakan berputar tersebut, Polimerase DNA
III akan mensintesis runtunan
nukleotida baru pada ujung 3'OH
dengan menggunakan utas(+)
sebagai modelnya. Bersamaan
dengan gerakan tersebut, utas
tunggal arah ujung 5'P yang terlepas
dari pilinan heliks ganda juga
bertambah panjang. Polimerase
DNA III juga mensintesis utas(+)
dengan menggunakan utas(-) yang
terlepas tersebut sebagai modelnya.
Jadi sejalan dengan perputaran
lingkaran utas(+) sirkular itu akan
diperoleh heliks ganda linear baru.
Satu putaran lengkap dari utas(+)
sirkular akan menghasilkan utasan
heliks ganda baru yang linear
Gambar 4.9. Model replikasi lingkaran berputar, digunakan pada replikasi virus
Ujung 3’
Ujung 5’
Polimerase DNA melakukan sintesis pada ujung 3’
Ujung 5’ membentuk utas tunggal bebas
berukuran sama dengan kromosom virus. Perputaran yang berlangsung berulang kali akan
menghasilkan satu molekul linear yang panjang, yang di dalamnya terkandung banyak
salinan dari kromosom virus. Molekul seperti itu disebut molekul konkatamer, dan pada
proses pengemasan atau pembentukan virus konkatamer ini akan dipenggal menjadi
kromosom virus tunggal.
D. DNA Mitokondria Memiliki Titik Ori Untuk Masing-Masing Utasan
Mitokondria adalah organel yang terdapat di dalam sitoplasma eukariot. Organel ini
mempunyai fungsi utama sebagai tempat sintesis ATP yang berfungsi dalam respirasi. Untuk
mendukung fungsinya DNA dilengkapi dengan bahan genetik sendiri yang bebas dari bahan
genetik yang terdapat pada inti.
Mitokondria mempunyai DNA sirkular berutas ganda. Replikasi DNA mitokondria
mempunyai ciri tersendiri yang berbeda dari DNA lain, yaitu terdapat dua titik Ori yang
berbeda untuk masing-masing utasan. Posisi titik Ori satu utasan berbeda dari titik Ori utasan
lain. Mula-mula replikasi akan berjalan pada satu utasan yang bergerak ke satu arah,
sedangkan pada utasan lain tidak terjadi kegiatan sintesis DNA. Setelah proses sintesis pada
utasan pertama berjalan dan mencapai posisi Ori utasan kedua, maka pada utasan kedua baru
berlangsung sintesis DNA dengan arah yang berlawanan dari arah pada utasan pertama.
Kedua proses sintesis tersebut berjalan secara kontinu.
DNA sebagai bahan genetik merupakan unsur yang sangat penting bagi organisme sebab
molekul itu akan menentukan pola kehidupan organisme tersebut. Karena fungsinya yang
sangat menentukan maka kestabilan DNA harus dijaga dengan baik. Kestabilan tersebut
meliputi dua hal, yaitu terpelihara dari kerusakan struktur molekul akibat pengaruh luar, dan
terpelihara dari kesalahan selama replikasi, yang dapat merubah struktur DNA. Struktur
heliks ganda dengan ikatan kovalen gula fosfat yang terletak di bagian luar menjamin
kestabilan DNA dari berbagai serangan enzim atau aksi fisik. Model replikasi
semikonservatif menjamin kesamaan struktur DNA baru dengan DNA tetuanya. Di samping
kedua hal tersebut, sistem kerja enzim Polimerase DNA juga menjamin kestabilan struktur
DNA.
Polimerase DNA mempunyai sistem pemeriksaan ketepatan pemasangan basa saat
replikasi. Enzim ini mempunyai aktivitas ganda, yaitu aktivitas sintesis DNA, dan sekaligus
aktivitas kontrol ketepatan sintesis tersebut. Enzim ini mempunyai kemampuan pembacaan
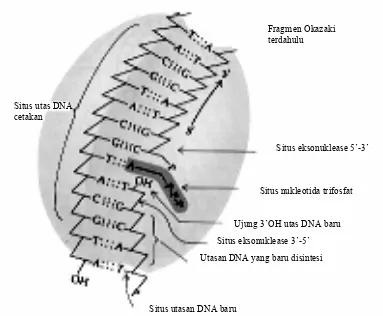
ulang terhadap hasil sintesis, berkat adanya situs eksonuklease 3--5. Pada Gambar 4.19
dilukiskan skema polimerase DNA I denan berbagai situs penting yang dikandungnya, yaitu
situs utas cetakan, situs utas hasil cetakan, situs nukleosida-trifosfat, situs eksonuklease 3--5,
dan situs eksonuklease 5-3. Polimerase DNA III mempunyai semua situs tersebut kecuali
situs eksonuklease 5-3, yang dipunyai oleh Polimerase DNA I untuk memotong RNA primer.
Polimerase DNA akan menempel pada utas tunggal DNA yang sedang bereplikasi, dan
menempatkannya pada situs utas cetakan. Mononukleosida-trifosfat bebas, yang akan
dirangkaikan menjadi rantai nukleotida akan masuk menempati situsnya pada Polimerase
DNA. Kemudian enzim tersebut akan memasangkan basa dari mononukleosida-trifosfat yang
terakhir masuk dengan basa pada utas cetakan. Pemeriksaan pertama untuk ketepatan
pemasangan basa dilakukan pada situs ini. Kecocokan diperiksa berdasarkan jumlah ikatan
hidrogen yang terbentuk, yaitu dua untuk A-T dan tiga untuk C=G. Pasangan basa yang
cocok akan dapat membentuk ikatan hidrogen.
Gambar 4.10. Skema polimerase DNA I. Situs eksonuklease 3-5 berfungsi dalam pembacaan ulang basa yang menjamin ketepatan replikasi
Situs utas DNA cetakan
Fragmen Okazaki terdahulu
Situs eksonuklease 5’-3’
Situs nukleotida trifosfat
Ujung 3’OH utas DNA baru Situs eksonuklease 3’-5’ Utasan DNA yang baru disintesi
Bila basa-basa yang diperiksa ternyata bukan pasangannya, maka mononukleosida
trifosfat akan dikeluarkan oleh polimerase DNA, dan selanjutnya akan dipilih
nukleosida-trifosfat yang lain. Bila nukleosida-nukleosida-trifosfat ternyata merupakan pasangan yang tepat dari
basa nukleotida pada utas cetakan, maka polimerase DNA akan merangkaikan nukleosida
tersebut dengan membentuk ikatan fosfodiester kepada nukleotida terakhir dari
Polinukleotida baru yang sedang disintesis. Selanjutnya polimerase DNA akan bergerak maju
membaca nukloetida berikutnya pada utas cetakan, dan nukleotida terakhir yang baru saja
dirangkaikan akan masuk ke dalam situs eksonuklease 3-5, yang berada di belakang situs
mononukleotida-trifosfat. Di dalam situs ini dilakukan pemeriksaan kedua terhadap
kecocokan pasangan basa antara nukleotida utas cetakan dengan basa yang terakhir
dirangkaikan. Seandainya masih terdapat pasangan basa yang tidak tepat dan lolos dari
pemeriksaan pertama, maka nukleotida tersebut akan dipotong dari rantai polinukleotida
dengan kegiatan eksonuklease 3-5; kemudian Polimerase DNA akan mundur satu langkah
dan mengulangi proses sintesis DNA. Adanya pemeriksaan ganda ini menjamin ketepatan
yang tinggi dari replikasi DNA dalam menyusun runtunan basa. Telah diketahui bahwa
frekuensi kesalahan dalam replikasi sangat kecil, yaitu antara 10-9, sampai 10-7.
Replikasi DNA mengikuti pola semikonservatif dimana sejumlah enzim dan protein dilibatkan di dalamnya. Heliks ganda akan diudar menjadi utas tunggal dengan bantuan helikase, girase, dan protein SSB. Utas tunggal yang terbentuk akan membentuk percabangan replikasi dan akan digunakan sebagai utas model cetakan. Karena pertumbuhan sintesis DNA berjalan dengan arah 5-3, maka pada utas leading (berujung 3'OH) sintesis akan bergerak dari ujung ke arah pangkal percabangan replikasi. Sebaliknya pada utas lagging (berujung 5'P), sintesis berjalan dari pangkal ke ujung percabangan . Sintesis ini berjalan secara bertahap dalam bentuk fragmen Okazaki.
Polimerase DNA mempunyai tingkat ketepatan yang tinggi karena dilengkapi dengan perangkat baca ulang. Dengan situs eksonuklease 3-5 nukleotida yang salah akan dibuang dan diganti dengan nukleotida yang seharusnya.
Dalam replikasi kromosomnya, bakteri menggunakan replikasi model q yang dimulai dari satu titik Ori yaitu Ori-C. Replikasi kromosom eukariot dimulai dari banyak titik Ori, dan berjalan dwiarah. Virus menggunakan cara replikasi lingkaran berputar dalam proses replikasinya.
Pilih jawaban yang benar
1) Pada kromosom E. coli terdapat satu titik Ori (Ori-C), replikasi dari titik Ori ini akan menghasilkan....
A. dua DNA sirkular
B. satu DNA sirkular dan satu DNA linear
Rangkuman
C. dua DNA linear D. satu DNA sirkular
2) Replikasi plasmid F. E. coli yang dimulai dari Ori T plasmid akan menghasilkan.... A. dua DNA sirkular
B. satu DNA sirkular dan satu DNA linear C. dua DNA linear
D. semuanya benar
3) Helikase mempunyai fungsi.... A. mengudar pilinan heliks ganda
B. menghilangkan tegangan yang muncul pada pangkal percabangan replikasi C. mencegah utas tunggal DNA berpasangan kembali membentuk heliks ganda D. semuanya benar
4) Girase mempunyai fungsi.... A. mengudar pilinan heliks ganda
B. menghilangkan tegangan yang muncul pada pangkal percabangan replikasi C. mencegah utas tunggal DNA berpasangan kembali membentuk heliks ganda D. semuanya benar
5) Akibat pertumbuhan 5-3 maka pada percabangan replikasi....
1. pada utas lagging sintesis DNA akan berjalan dari ujung menuju pangkal percabangan 2. pada utas leading proses sintesis akan berjalan secara kontinu
3. pada utas lagging akan terbentuk fragmen-fragmen Okazaki A, B, C, D
6) RNA primer dibentuk.... 1.oleh Polimerase RNA
2.di depan semua fragmen Okazaki
3.karena polimerase DNA tidak mampu meletakkan basa pertama atau mengawali sintesis DNA
A, B, C, D
7) Polimerase DNA III diganti oleh Polimerase DNA I karena.... 1. Polimerase DNA III tidak mampu mengawali proses replikasi
2. Polimerase DNA III tidak mampu membuang RNA primer yang ada di depannya 3. Polimerase DNA I mengandung situs eksonuklease 5-3
A, B, C, D
Adams RLP, Knowler JT, and Leader DP. 1986. The Biochemistry of Nucleic Acids. Tenth Edition. Chapman and Hall. London, New York.
Albert B, Bray D, Lewis J, Raff M, Roberts K, and Watson JD. 1994. Molecular Biology of The Cell. Third Edition. Garland Publishing Inc. New York, London.
Chargaff E, Visher E, Doninger R, Green C, and Missani F. 1949. The Composition of the Deoxyribonucleic Acid of Thymus and Spleen. J. Biol Chem. 177: 405-416
Lehninger, A.L. 1982. Principle of Biochemistry, Worth Publisher, New York
Levine, L. (ed) 1971. Papers of Genetics. A book of readings. Mosby International Edition. The C.V. Mosby Cmpany Saint Lovis.
Singer M and Berg P. 1991. Genes and Genom. University Science Books, Mill Valley California. Blackwell Scientific Publications. Oxford, London, Edinburgh, Melbourne, London, Berlin, Vienna
Stryer L. 1995. Biochemistry. WH Freeman and Company. New York
Watson J.D. and Crick FHC. 1953. The Structure of DNA. Cold Spring Harbour Symposia Quant Biol XVIII :123-131
Watson JD and Crick FHC. 1953. Genetical Implication of The Structure of Deoxyribo-nucleic Acid. Nature 171:738-740
Zubay G and Marmur J. (Eds). 1973. Papers in Biochemical Genetics. Second Edition. Holt, Rinehart and Winston, Inc. New York, Chicago, San Francisco, Atlanta, Dallas, Montreal, Toronto, London.